Clear Sky Science · pt
Perfilagem mecanística baseada em solubilidade de terapias medicamentosas combinadas
Por que combinar medicamentos pode importar
O tratamento oncológico moderno frequentemente depende de combinações de medicamentos, mas identificar quais fármacos funcionam melhor em conjunto ainda é, em grande parte, um processo de tentativa e erro. Este estudo foca na leucemia mieloide aguda, um câncer sanguíneo agressivo que frequentemente recidiva após o tratamento. Os pesquisadores apresentam uma nova forma de observar, em larga escala, como as proteínas celulares respondem quando dois medicamentos são administrados juntos. A abordagem ajuda a explicar por que certas combinações são ao mesmo tempo mais eficazes e menos tóxicas, e oferece um roteiro para projetar terapias combinadas mais inteligentes e precisas para cânceres de difícil tratamento.
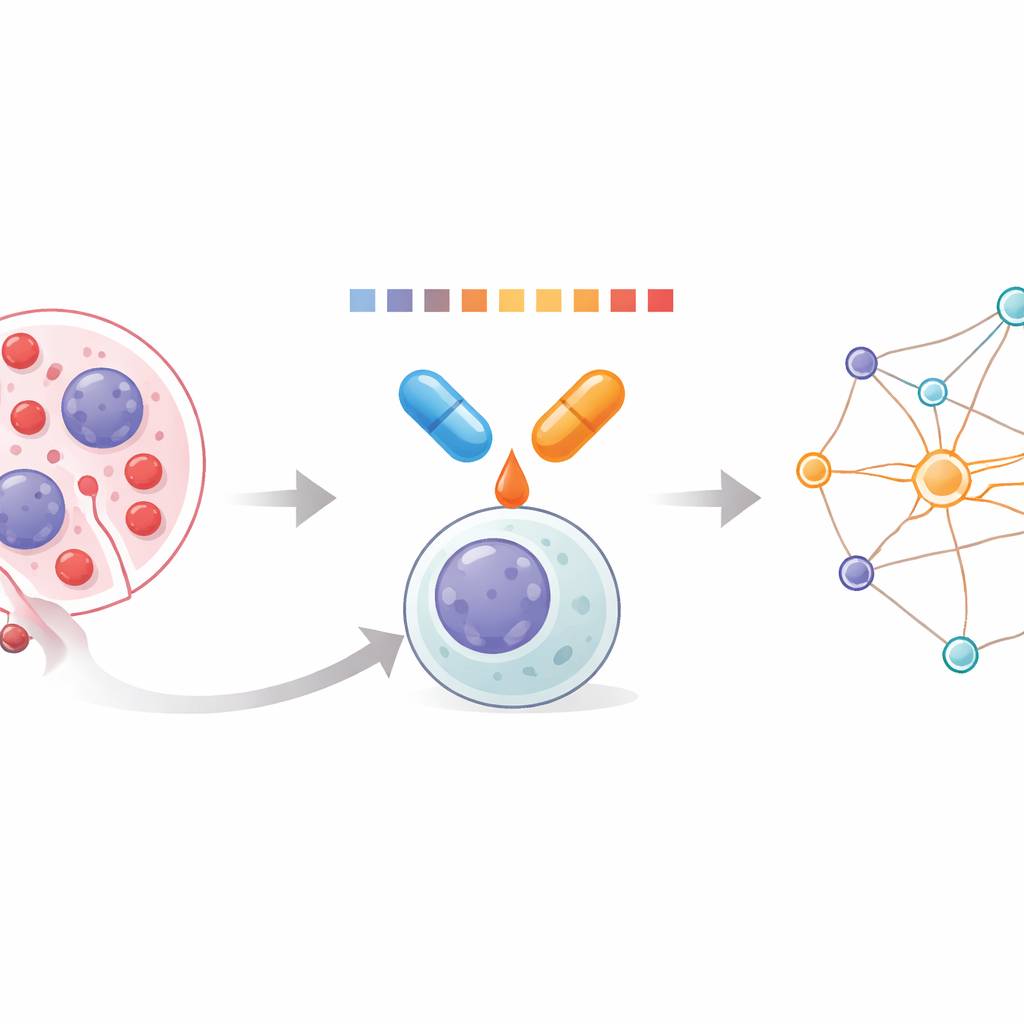
Observando dentro das células leucêmicas
A leucemia mieloide aguda (LMA) surge quando células brancas imaturas na medula óssea crescem descontroladamente e deslocam a formação de sangue saudável. Como a LMA é impulsionada por muitas alterações genéticas diferentes, fármacos únicos raramente funcionam por muito tempo. Combinações podem ser mais eficazes, mas os médicos têm ferramentas limitadas para ver como pares de medicamentos atuam juntos no nível de milhares de proteínas dentro da célula. A equipe por trás deste trabalho procurou medir esses efeitos combinados diretamente, usando um método que avalia quão facilmente as proteínas se dissolvem ou se agregam quando aquecidas. Mudanças na solubilidade revelam quais proteínas estão sendo estabilizadas ou desestabilizadas pelo tratamento, oferecendo uma janela para o verdadeiro impacto dos fármacos.
Uma nova maneira de perfilar pares de medicamentos
Os pesquisadores desenvolveram um fluxo de trabalho que chamam de Análise Combinatorial Proteome Integral Solubility/Stability Alteration, ou CoPISA. Células, ou seus extratos proteicos, são expostos ao medicamento A, ao medicamento B, à combinação de A e B, ou nenhum fármaco. Cada amostra é então brevemente aquecida em uma série de temperaturas, e as proteínas ainda dissolvidas são capturadas e quantificadas por espectrometria de massa. Em vez de ajustar curvas complexas proteína a proteína, o método usa a área total sob o perfil de fusão de cada proteína como uma medida compacta de seu comportamento. Comparar essas áreas entre tratamentos mostra quais proteínas se tornam mais ou menos solúveis sob cada condição, revelando padrões exclusivos de fármacos isolados versus combinações.
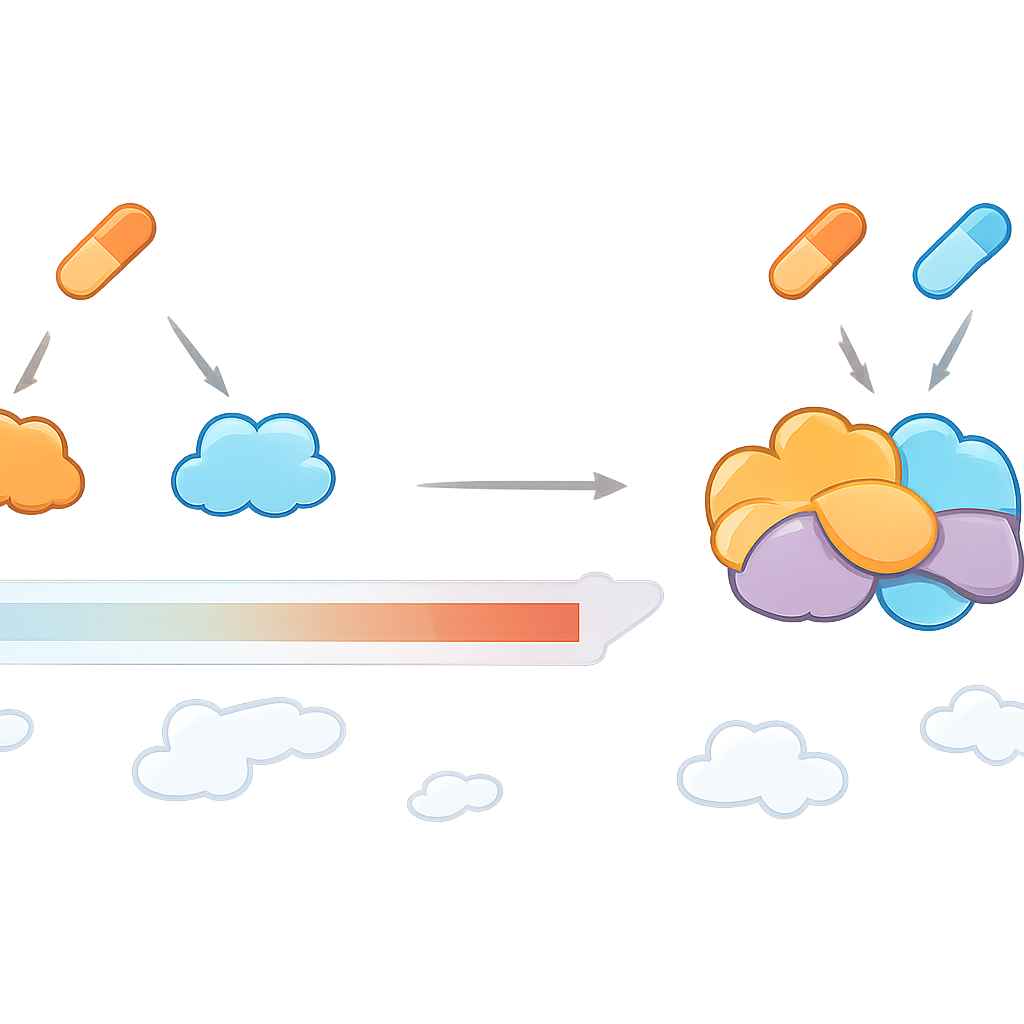
Encontrando alvos que só aparecem com ambos os fármacos
O CoPISA foi aplicado a dois pares de medicamentos escolhidos cuidadosamente para LMA: LY3009120 com sapanisertibe (chamado LS), e ruxolitinibe com ulixertinibe (RU). Esses pares já haviam mostrado forte atividade e toxicidade relativamente baixa em amostras de pacientes, linhas celulares e modelos em peixe-zebra. O CoPISA revelou não apenas proteínas afetadas por cada fármaco isoladamente, mas também um conjunto distinto de proteínas cuja solubilidade mudou apenas quando ambos os fármacos estavam presentes. Os autores descrevem isso como “direcionamento conjuntivo”, semelhante a uma porta lógica E: a proteína responde somente se ambas as entradas (fármacos) estiverem ativas. Para LS, esses efeitos exclusivos da combinação convergiram em processos como empacotamento do DNA, pequenas marcas proteicas chamadas SUMO que controlam a estabilidade do genoma, e em como as células leucêmicas se aderem ao tecido ao redor. Para RU, alvos únicos indicaram pontos de checagem de dano ao DNA enfraquecidos, produção de energia mitocondrial comprometida e processamento de RNA perturbado.
Mapeando os pontos fracos do câncer
Ao sobrepor seus dados de solubilidade a mapas amplos de genes e vias relacionados à LMA, os pesquisadores puderam ver como cada tratamento remodelava a fiação interna do câncer. Muitos genes conhecidos da LMA — como DNMT3A, NPM1 e TP53 — foram afetados de maneiras que apareceram apenas sob terapia combinada, reforçando a ideia de que fármacos emparelhados podem expor vulnerabilidades invisíveis a agentes isolados. A equipe também examinou decorações químicas em proteínas, como acetilação, metilação e fosforilação, que atuam como interruptores moleculares. Eles descobriram que certas formas modificadas de proteínas-chave, incluindo NPM1 e o fator de reparo de DNA BLM, foram afetadas especificamente pelas combinações, sugerindo que alterações na localização e no sinal das proteínas contribuem para o efeito ampliado.
O que isso significa para tratamentos futuros
No conjunto, o estudo mostra que combinações de medicamentos podem criar sua própria paisagem única de alvos proteicos, em vez de simplesmente somar os efeitos de cada fármaco. O CoPISA fornece uma maneira prática de mapear essa paisagem, destacando proteínas e vias que só se tornam vulneráveis quando dois medicamentos atuam em conjunto. Para pacientes, isso pode se traduzir em terapias combinadas escolhidas não apenas porque reduzem tumores em placa de cultura, mas porque atingem pontos fracos mais profundos do câncer enquanto limitam toxicidade desnecessária. Embora demonstrado aqui na LMA, a abordagem é amplamente aplicável e pode ajudar a orientar o desenho racional de tratamentos combinados em muitas doenças complexas.
Citação: Gholizadeh, E., Zangene, E., Vadadokhau, U. et al. Solubility based mechanistic profiling of combinatorial drug therapy. Nat Commun 17, 2744 (2026). https://doi.org/10.1038/s41467-026-70394-3
Palavras-chave: leucemia mieloide aguda, combinações de medicamentos, proteômica, solubilidade de proteínas, terapia direcionada