Clear Sky Science · pt
snoRNAs com terminação CPF‑CF atravessam o citoplasma via um mecanismo de vigilância mediado por uma proteína guarda do mRNA
Como guias de RNA minúsculos fazem um desvio inesperado
Dentro de cada célula, a síntese de proteínas depende de uma coreografia molecular precisa. Uma parte essencial dessa dança é controlada por pequenos RNAs nucleolares, ou snoRNAs, que ajudam a moldar os ribossomos da célula — as máquinas que constroem proteínas. Este estudo revela que alguns desses guias minúsculos deixam inesperadamente o núcleo, visitam brevemente o citoplasma e então retornam, tudo por causa de como sua produção é interrompida. Compreender essa rota oculta de tráfego esclarece como as células protegem a qualidade do RNA e preservam sua informação genética.
Um olhar mais atento aos ajudantes de RNA da célula
SnoRNAs são moléculas de RNA curtas que atuam como guias, direcionando modificações químicas em outros RNAs, especialmente aqueles que formam os ribossomos. Em células de levedura, a maioria dos snoRNAs é produzida no núcleo e se acreditava que permanecia ali por toda a vida, formando parcerias estáveis com proteínas específicas para criar os snoRNPs, os complexos ativos que modificam o RNA ribossômico. Ainda assim, trabalhos anteriores detectaram snoRNAs em contato com proteínas normalmente envolvidas no envio de RNAs mensageiros para fora do núcleo. Essa observação intrigante levantou uma questão: os snoRNAs às vezes viajam para o citoplasma e, em caso afirmativo, por quê?
Descobrindo snoRNAs em movimento
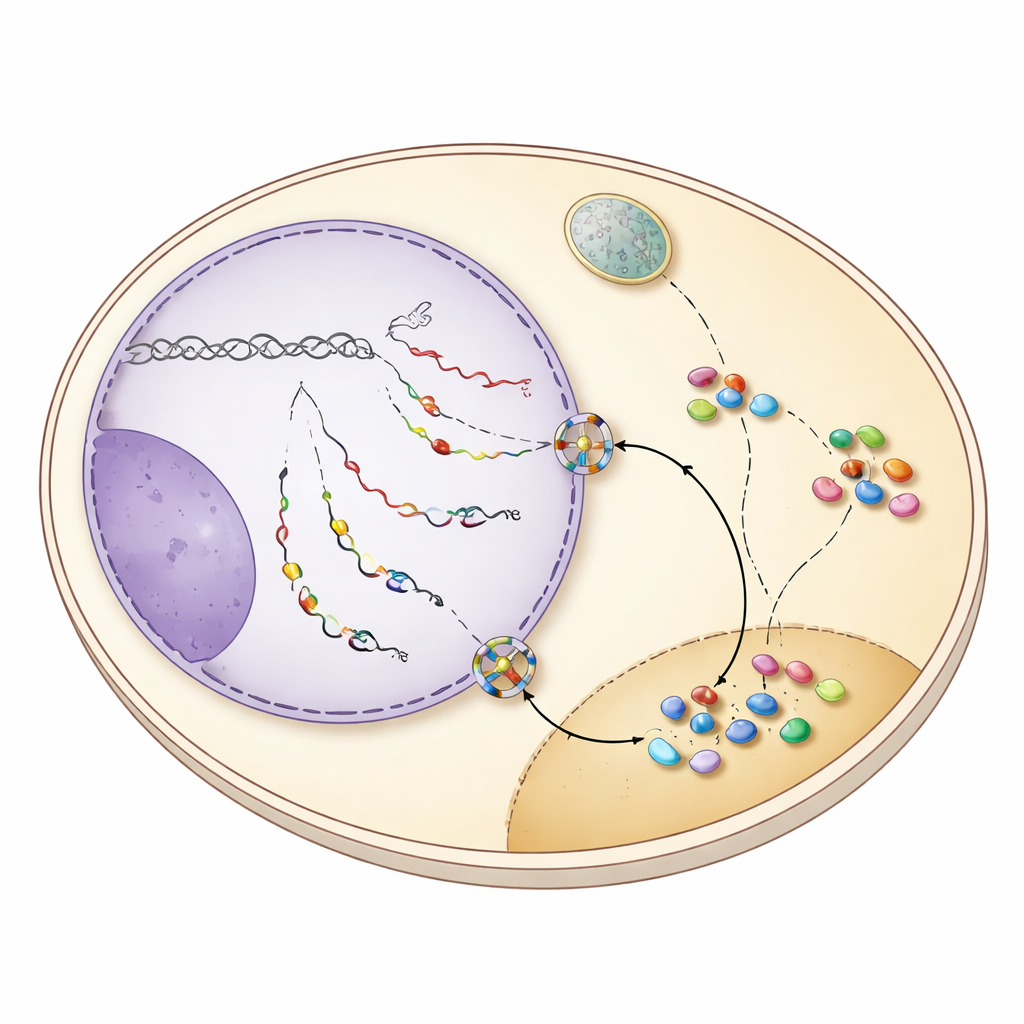
Ao reanalisar dados de sequenciamento de RNA de frações nucleares e citoplasmáticas cuidadosamente separadas, os autores encontraram que muitos snoRNAs estão de fato presentes no citoplasma de células de levedura normais, em níveis semelhantes aos de mRNAs típicos. Quando inativaram fatores-chave de exportação, Mex67 e Xpo1, o pool citoplasmático de snoRNAs diminuiu e precursores imaturos de snoRNA com extensões 3′ acumularam-se no núcleo. Microscopia com sondas fluorescentes confirmou essa mudança: sinais que normalmente apareciam tanto no nucleolo quanto de forma tênue no citoplasma tornaram-se fortemente nucleares quando a exportação foi bloqueada. Essas descobertas mostram que um subconjunto de snoRNAs, frequentemente ainda carregando sequência extra nas extremidades, é transportado ativamente para fora do núcleo e não está apenas vazando ou contaminando amostras.
A troca da proteína guarda que envia snoRNAs para fora
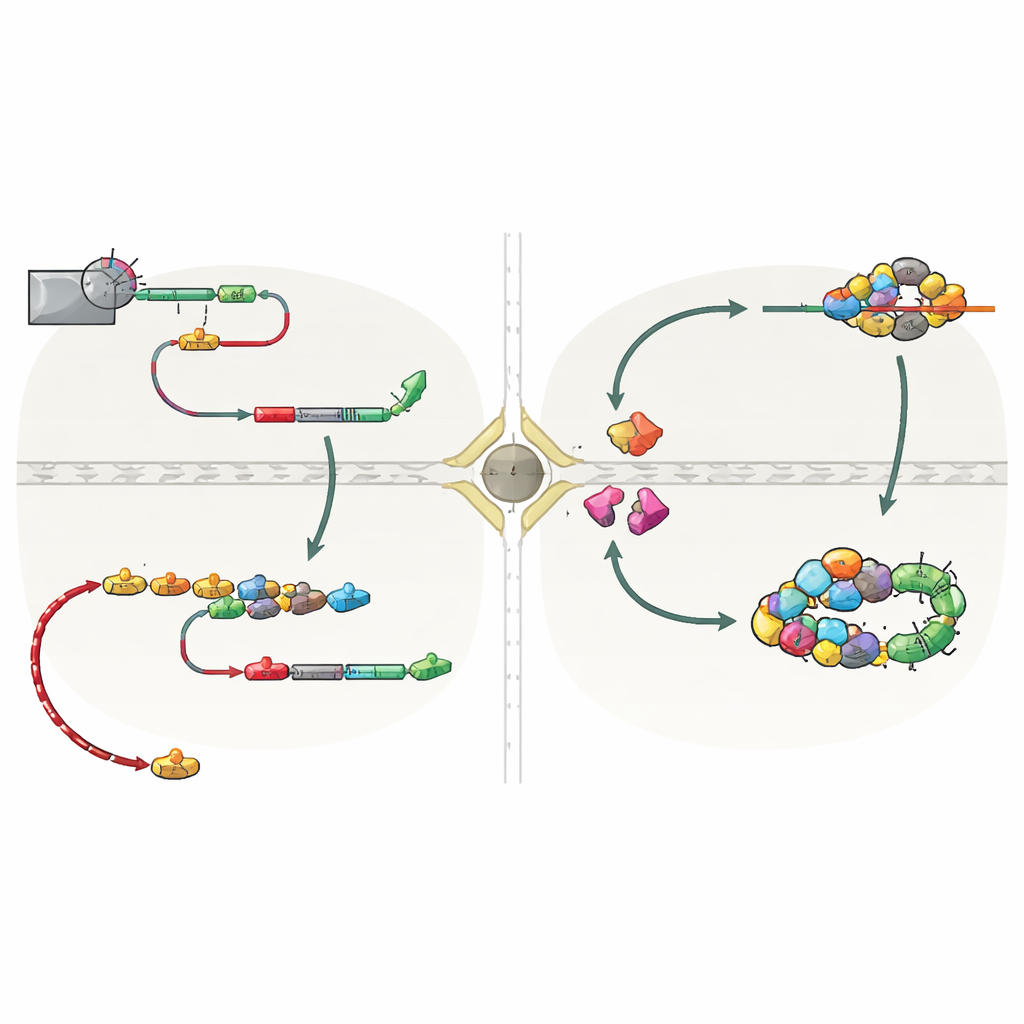
A chave desse comportamento de trânsito reside em como o término da transcrição dos snoRNAs é realizado. Em leveduras, a maioria dos snoRNAs normalmente é liberada da maquinaria de transcrição por um sistema chamado NNS, que lhes deixa uma cauda curta que é rapidamente aparada no núcleo. Muitos genes de snoRNA, no entanto, também abrigam sinais de parada de reserva reconhecidos por um segundo sistema, CPF‑CF, mais conhecido por finalizar mRNAs e adicionar longas caudas poli(A). Quando o término por NNS falha, os transcritos de snoRNA seguem até esses sítios CPF‑CF a jusante e recebem uma cauda mais longa. Esse final alterado recruta um conjunto de proteínas “guarda” — Hrp1 e Nab2 entre elas — que verificam o processamento correto e, simultaneamente, atraem o fator de exportação Mex67. O estudo mostra que quando os snoRNAs são finalizados pelo CPF‑CF, proteínas guarda e Mex67 trabalham em conjunto para enviar esses snoRNAs acaudalados através dos poros nucleares para o citoplasma.
Passagens de ida e volta e controle de qualidade
Uma vez no citoplasma, os snoRNAs não ficam desassistidos. Eles permanecem ligados por um anel protetor de proteínas Lsm e pelo fator Lhp1, que protegem a extremidade de RNA vulnerável. Essas características permitem que dois receptores de importação, Cse1 e Mtr10, reconheçam os snoRNAs em trânsito e os tragam de volta ao núcleo. Quando os autores desativaram esses fatores de importação ou o anel Lsm, snoRNAs imaturos acumularam-se no citoplasma, confirmando que essa maquinaria medeia seu retorno. De volta ao núcleo, as caudas longas são aparadas pelo exossomo nuclear, proteínas centrais dos snoRNPs são completamente montadas e os complexos maduros se realocam ao nucleolo. Importante: os snoRNAs que fizeram esse desvio permaneceram plenamente funcionais: um snoRNA modelo, snR13, ainda realizou suas modificações químicas específicas no RNA ribossômico após ser terminado pelo CPF‑CF e enviado pelo citoplasma.
Por que essa via oculta importa
Este trabalho revela que o trânsito de snoRNAs não é um caso excepcional, mas uma rota de reserva incorporada controlada pela maneira como a transcrição termina. Quando o sistema primário NNS é enfraquecido — por exemplo, em estágios particulares do ciclo celular — sinais CPF‑CF a jusante resgatam a produção de snoRNA. Isso evita o desperdício de RNA já sintetizado e impede transcrição descontrolada que poderia interferir com genes vizinhos e danificar o DNA. Os autores também encontram indícios de um resgate semelhante em células humanas, onde snoRNAs codificados individualmente podem adquirir caudas poli(A) em sítios relacionados. Em termos simples, o estudo mostra que o “sinal de parada” escolhido no final de um gene de snoRNA decide se aquele RNA amadurece silenciosamente no núcleo ou sai brevemente e retorna sob o olhar atento de proteínas guarda. Esse mecanismo de vigilância dirigido pelo término de transcrição ajuda a manter o repertório de RNA da célula ao mesmo tempo flexível e seguro.
Citação: Yu, F., Zaccagnini, G., Duan, Y. et al. CPF-CF-terminated snoRNAs shuttle through the cytoplasm via an mRNA guard protein-mediated surveillance mechanism. Nat Commun 17, 2328 (2026). https://doi.org/10.1038/s41467-026-70373-8
Palavras-chave: snoRNA, controle de qualidade de RNA, exportação nuclear, término de transcrição, genética de leveduras