Clear Sky Science · pt
Variação alélica de genes Avr em linhagens altamente virulentas explica graves epidemias de ferrugem-do-colmo do trigo
Por que a ferrugem do trigo importa para todos
A ferrugem-do-colmo do trigo é uma doença de culturas com séculos de história que pode despojar campos de grãos e ameaçar o abastecimento alimentar global. Nas últimas duas décadas, formas novas e altamente agressivas desse fungo causaram surtos danosos na África e na Europa, contornando variedades de trigo que haviam sido desenvolvidas para resisti-las. Este estudo faz uma pergunta simples, porém crucial: o que, exatamente, mudou nessas novas linhagens fúngicas que lhes permitiu romper as defesas do trigo e se espalhar tão amplamente?
Como plantas e fungos jogam esconde‑esconde molecular
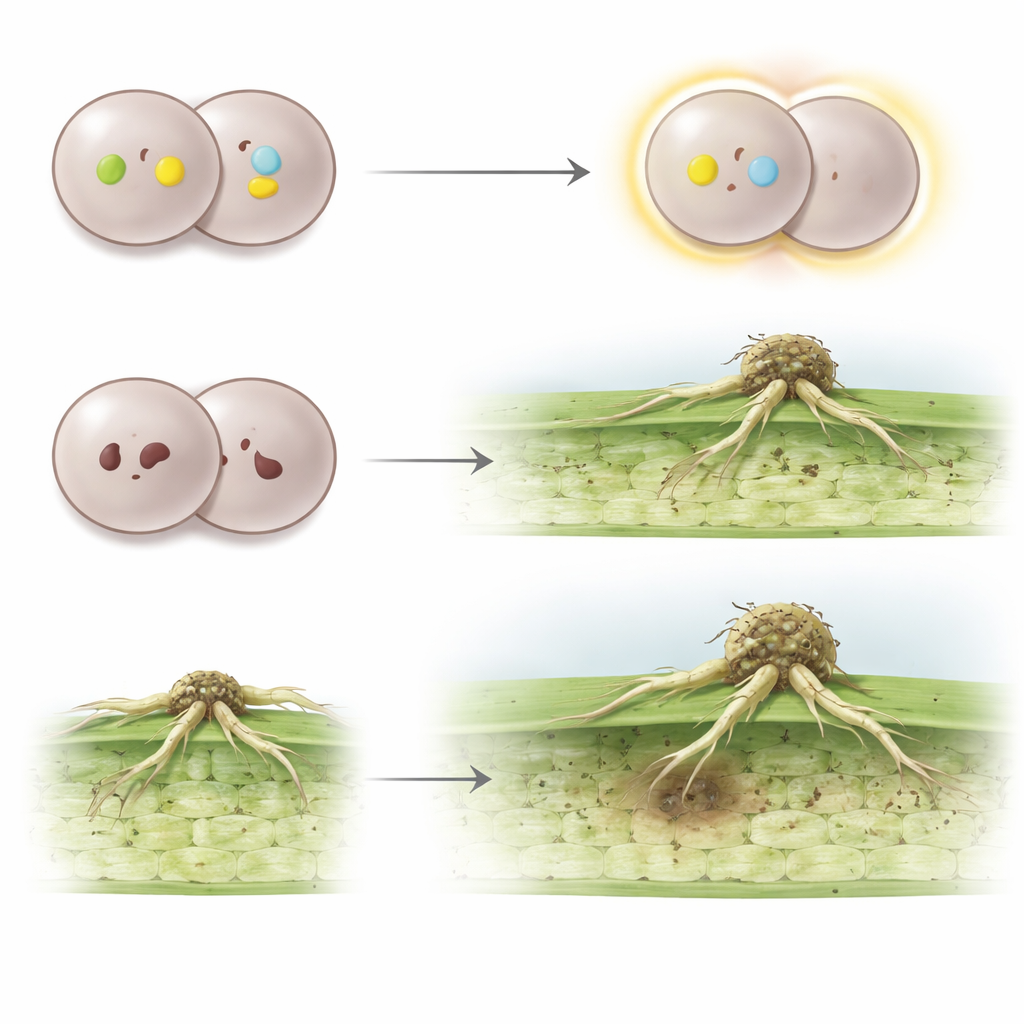
O trigo se defende usando genes de resistência que podem detectar moléculas específicas produzidas por fungos invasores. Quando um gene de resistência reconhece uma dessas moléculas fúngicas, ele desencadeia uma reação imunológica que impede a infecção. O fungo, por sua vez, carrega genes de "avirulência" correspondentes que codificam justamente as moléculas que a planta tenta identificar. Se a molécula fúngica está presente e intacta, uma variedade de trigo que carrega o gene de resistência correspondente pode bloquear a doença. Mas se o fungo deleta ou altera essa molécula, ele pode escapar ao sistema de vigilância da planta. O surgimento recorrente de novas raças de ferrugem-do-colmo reflete essa corrida armamentista genética entre genes de avirulência fúngicos e genes de resistência do trigo.
Lendo os genomas do fungo cromossomo a cromossomo
O fungo da ferrugem-do-colmo é incomum porque cada indivíduo carrega dois núcleos distintos, cada um com seu próprio genoma completo. Isso torna difícil identificar quais versões dos genes de avirulência estão presentes. Os autores usaram o sequenciamento de DNA de última geração com leituras longas e mapeamento cromossômico tridimensional para produzir mapas genômicos completos, núcleo por núcleo, de duas linhagens epidêmicas: ETH2013‑1, responsável por um grande surto na Etiópia em 2013, e ITA2018‑1, parte de uma linhagem que se espalhou pela Europa após eclodir pela primeira vez na Sicília em 2016. Eles demonstraram que os quatro núcleos desses dois isolados formam quatro "haplótipos" genômicos únicos que são distintos de cepas de referência estudadas anteriormente, fornecendo uma imagem muito mais clara da diversidade genética e da árvore genealógica do fungo.
Identificando as alterações gênicas por trás das epidemias recentes
Com esses genomas completos em mãos, a equipe examinou sistematicamente genes de avirulência conhecidos, associados a genes importantes de resistência do trigo. Catalogaram dezenas de variantes de sequência, incluindo alterações no número de cópias do gene, mutações sutis que alteram um único aminoácido e casos em que o gene foi completamente deletado. Usando uma combinação de ensaios em células vegetais, plantas-modelo e um sistema de entrega baseado em vírus, testaram se cada variante fúngica ainda é reconhecida pelo gene de resistência de trigo correspondente. No total, caracterizaram funcionalmente 22 novas variantes de avirulência. Isso lhes permitiu explicar, em nível molecular, por que algumas linhagens de ferrugem-do-colmo conseguem infectar determinadas variedades de trigo enquanto outras não.
Como um gene ausente ajudou uma linhagem a varrer a Europa
Uma descoberta marcante envolve a raça conhecida como TTRTF, que causou o mortal surto siciliano e mais tarde se tornou disseminada na Europa. Muitos cultivares de trigo durum nos campos afetados carregavam um gene de resistência chamado Sr13b, esperado para protegê‑los. Os pesquisadores descobriram que a linhagem epidêmica italiana possui uma deleção limpa do gene de avirulência correspondente, AvrSr13, em ambos os seus núcleos. Sem esse gene, o fungo não produz mais a molécula indicadora que as defesas baseadas em Sr13 foram projetadas para detectar, permitindo que TTRTF infecte trigo com Sr13b sem controle. A mesma linhagem também apresenta uma forma modificada de outro gene de avirulência, AvrSr35, o que explica sua capacidade de contornar um segundo gene de resistência do trigo, Sr35.
Construindo um atlas genético para ficar à frente da ferrugem
Além de explicar surtos recentes, o estudo estabelece um "atlas de genes Avr" para o fungo da ferrugem-do-colmo: um mapa de referência que vincula variantes específicas de genes de avirulência ao seu comportamento contra genes-chave de resistência do trigo. Esse atlas pode ser usado para interpretar sequências de DNA coletadas de esporos de ferrugem no campo e para prever, apenas a partir da sequência, quais variedades de trigo provavelmente estarão em risco. Para melhoristas de plantas e equipes de vigilância de doenças, isso significa que eles podem escolher genes de resistência que as populações dominantes de ferrugem ainda não conseguem evadir e detectar rapidamente quando surgem novas variantes mais perigosas.
O que isso significa para proteger colheitas futuras
Em termos práticos, este trabalho mostra exatamente como cepas recentes de ferrugem têm destrancado alguns dos melhores sistemas de segurança do trigo. Ao revelar quais chaves fúngicas mudaram e quais trancas vegetais ainda resistem, o estudo fornece um roteiro para projetar variedades de trigo com resistência de maior duração e para usar ferramentas portáteis baseadas em DNA para rastrear tipos perigosos de ferrugem enquanto se deslocam pelo mundo. Em última análise, entender esses detalhes moleculares é um passo prático para manter as colheitas de trigo seguras diante de um patógeno em evolução.
Citação: Spanner, R.E., Henningsen, E.C., Langlands-Perry, C. et al. Allelic variation of Avr genes in highly virulent strains explains severe wheat stem rust epidemics. Nat Commun 17, 2718 (2026). https://doi.org/10.1038/s41467-026-69508-8
Palavras-chave: ferrugem-do-colmo do trigo, imunidade vegetal, genes de avirulência, sequenciamento genômico, vigilância de doenças em culturas