Clear Sky Science · pt
Descoberta de peptídeos antimicrobianos que atacam Acinetobacter baumannii por meio de um pipeline baseado em few‑shot learning pré‑treinado e ajustado
Por que isso importa para a saúde cotidiana
Infecções resistentes a medicamentos estão aumentando tão rapidamente que, até meados do século, podem matar mais pessoas por ano do que o câncer. Um dos culpados mais preocupantes é Acinetobacter baumannii, um germe hospitalar resistente que ignora muitos antibióticos e frequentemente infecta pacientes em ventiladores. Este estudo mostra como cientistas combinaram inteligência artificial com experimentos de laboratório para descobrir rapidamente novos candidatos a fármacos pequenos que podem matar essa bactéria causando muito menos dano ao organismo do que o nosso atual medicamento de última linha.
Um superbactéria hospitalar difícil de matar
Acinetobacter baumannii é uma bactéria Gram‑negativa que prospera em unidades de terapia intensiva, particularmente em pacientes dependentes de ventiladores. Sua camada externa resistente e seu genoma de rápida evolução a tornam imune a muitos antibióticos padrão. Hoje, uma das poucas opções remanescentes é um fármaco chamado polimixina B, mas ele pode causar sérios danos aos rins e a bactéria ainda pode desenvolver resistência. Ao mesmo tempo, uma classe promissora de pequenos fragmentos proteicos, chamados peptídeos antimicrobianos, tem sido explorada contra outros microrganismos, mas muito poucos foram identificados que funcionem especificamente bem contra A. baumannii. A triagem tradicional por tentativa e erro é simplesmente lenta e cara demais para vasculhar o número astronomicamente grande de possíveis sequências curtas de peptídeos.
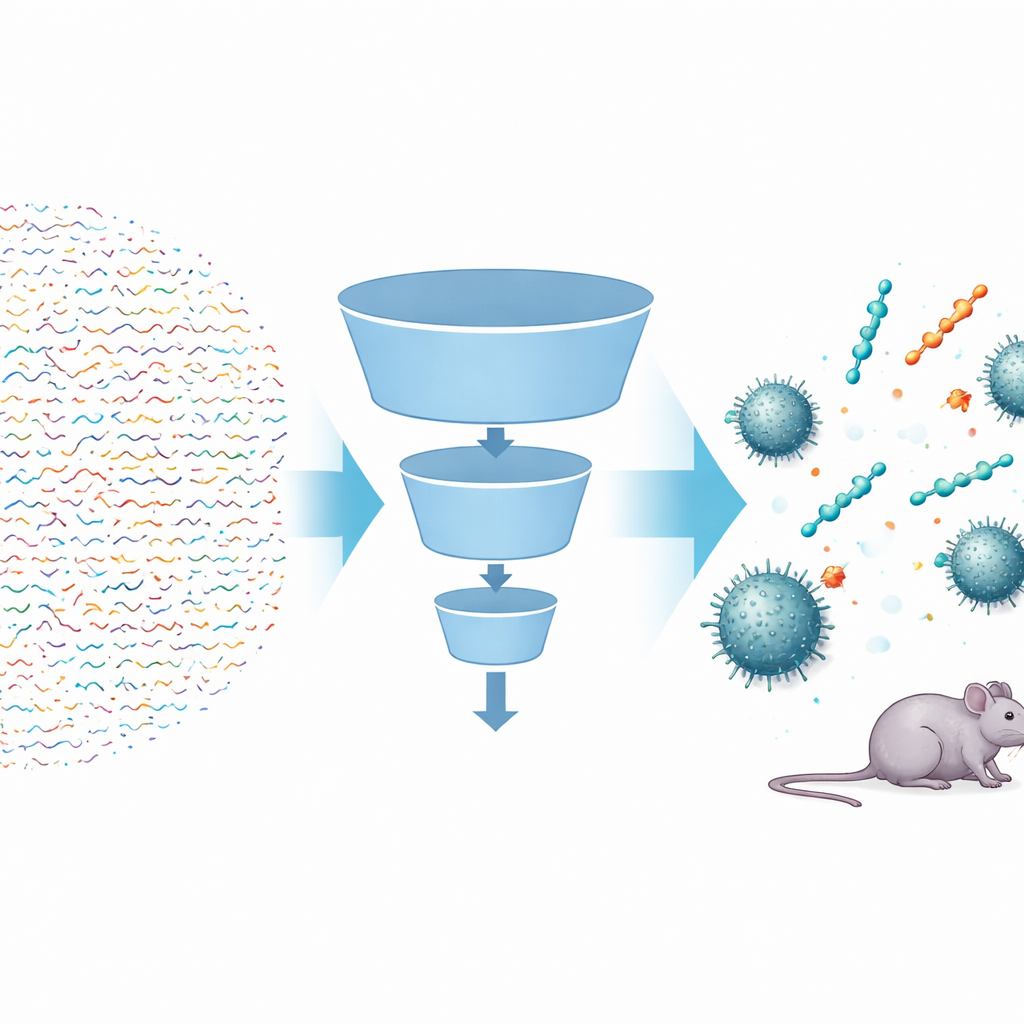
Usando algoritmos inteligentes para explorar um espaço enorme
Os pesquisadores construíram um pipeline de inteligência artificial em múltiplas etapas, chamado FSLSMEP, para varrer bibliotecas inteiras de peptídeos curtos — aqueles com seis, sete ou oito blocos de construção — totalizando dezenas de bilhões de candidatos. O desafio era que eles dispunham de apenas 148 peptídeos conhecidos ativos contra A. baumannii, número muito pequeno para métodos de aprendizado de máquina padrão. Para contornar isso, começaram com um modelo pré‑treinado poderoso que já havia “lido” centenas de milhões de sequências proteicas naturais e aprendido regras gerais sobre como essas moléculas se comportam. Em seguida, ajustaram finamente esse modelo em duas etapas: primeiro em um conjunto maior de peptídeos ativos contra uma bactéria relacionada, Pseudomonas aeruginosa, e finalmente nos escassos dados de A. baumannii. Ao longo do caminho, três módulos vinculados — um para separar peptídeos prováveis de improváveis, outro para ranqueá‑los e um terceiro para estimar quão potente cada um poderia ser — atuaram como filtros sucessivos em um funil.
De previsões computacionais a sucessos em tubo de ensaio
Depois de afastar primeiro os peptídeos menos promissores usando regras químicas simples, a equipe alimentou quase quatro milhões de candidatos em seu pipeline. O classificador eliminou a maioria das sequências que não pareciam antimicrobianas; o modelo de ranqueamento favoreceu aquelas cujas características sugeriam forte atividade; e o modelo de regressão previu a menor concentração do fármaco necessária para interromper o crescimento bacteriano. A partir de sessenta e quatro milhões de peptídeos de seis unidades, o sistema propôs apenas dez candidatos principais. Quando sintetizados e testados em laboratório, nove desses mostraram atividade antibacteriana real, uma taxa de acerto impressionante em descoberta de fármacos. Os mesmos modelos treinados foram então aplicados, sem novo treinamento, a espaços muito maiores de peptídeos de sete e oito unidades, dos quais os pesquisadores escolheram sequências adicionais melhor ranqueadas para teste. Novamente, a maioria mostrou ser ativa, incluindo heptapeptídeos tão potentes quanto a polimixina B contra algumas linhagens.
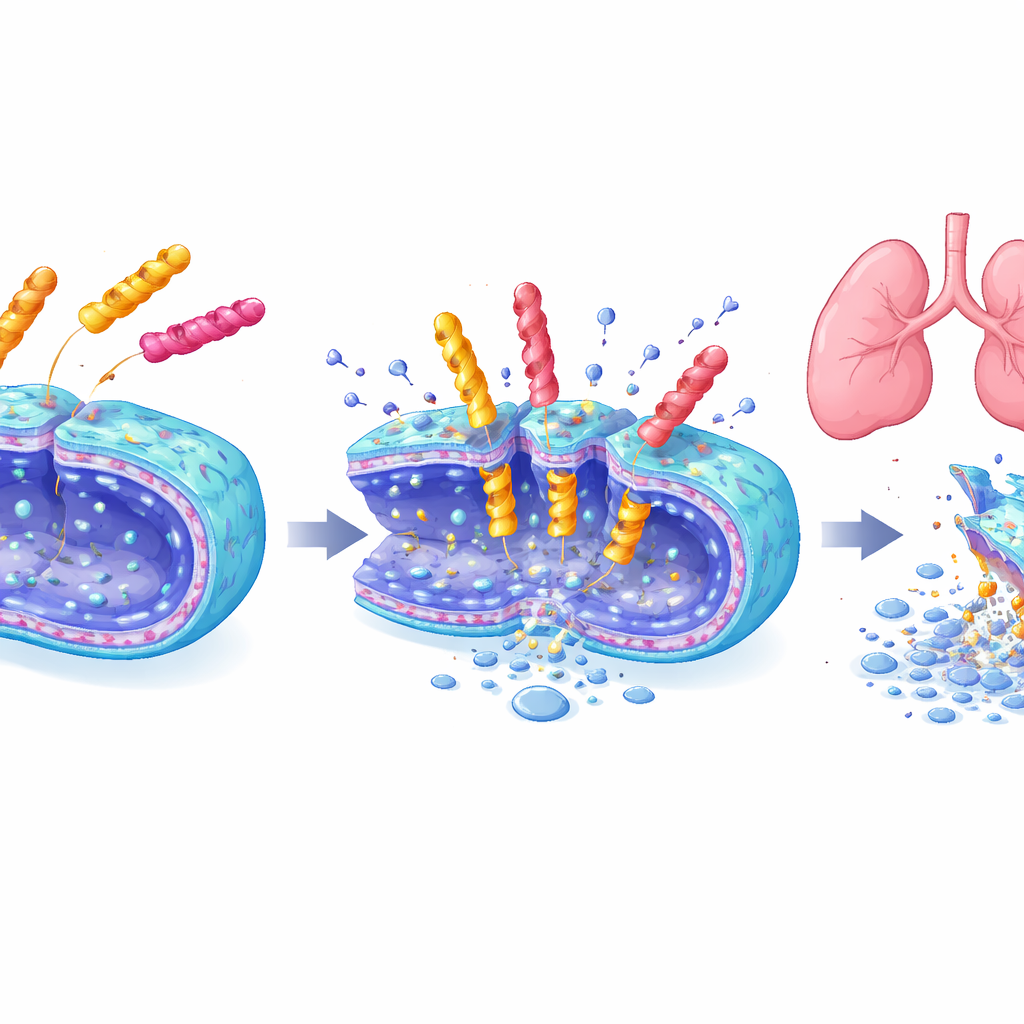
Potentes matadores com toque mais suave
Três peptídeos líderes — um de cada uma das bibliotecas de seis, sete e oito unidades — foram examinados em detalhe. Eles eliminaram rapidamente populações de A. baumannii em minutos a horas, danificaram membranas bacterianas conforme observado em microscópios eletrônicos e também atuaram contra vários outros micróbios perigosos. Ao mesmo tempo, causaram pouco dano a células de mamíferos em cultura ou a glóbulos vermelhos, em contraste com alguns peptídeos antimicrobianos existentes. Em testes de exposição a longo prazo, as bactérias não desenvolveram resistência facilmente a essas novas moléculas, enquanto a resistência à polimixina B aumentou rapidamente. O mais marcante: em um modelo murino de pneumonia, uma dose inalada do heptapeptídeo EME7(7) eliminou infecções pulmonares tão efetivamente quanto a polimixina B, mas não lesionou os rins, ao passo que a polimixina B causou danos renais claros e aumentos em marcadores sanguíneos de estresse renal.
O que isso significa para futuros medicamentos
Este trabalho demonstra que um pipeline de IA cuidadosamente projetado pode transformar um conjunto de dados pequeno e incompleto em um motor poderoso para descobrir novos peptídeos antimicrobianos. Ao combinar pré‑treinamento amplo, ajuste fino em etapas e múltiplas camadas de filtragem, os pesquisadores exploraram de forma eficiente bibliotecas inteiras de peptídeos curtos e encontraram candidatos que tanto combatem um perigoso supergermes hospitalar quanto aparentam ser mais seguros para órgãos vitais. A mesma estratégia também obteve sucesso em encontrar peptídeos ativos contra o patógeno fúngico Candida albicans, sugerindo que ela pode ser reutilizada para buscar muitos outros tipos de peptídeos terapêuticos. Para os pacientes, essa abordagem poderia eventualmente se traduzir em novos medicamentos que tratem infecções persistentes sem os fortes efeitos colaterais e a resistência rápida que afligem os antibióticos de última linha atuais.
Citação: Huang, J., Zhang, W., Wang, A. et al. Discovery of antimicrobial peptides targeting Acinetobacter baumannii via a pre-trained and fine-tuned few-shot learning-based pipeline. Nat Commun 17, 2475 (2026). https://doi.org/10.1038/s41467-026-69306-2
Palavras-chave: peptídeos antimicrobianos, resistência a antibióticos, Acinetobacter baumannii, descoberta de fármacos por aprendizado de máquina, few‑shot learning