Clear Sky Science · pt
Utilizando a cinética previsível de ligação do DNA-PAINT para remover ruído de imagens de super-resolução
Visões mais nítidas do mundo minúsculo
Microscópios modernos agora conseguem “ver” moléculas individuais dentro de células, mas essas imagens frequentemente aparecem salpicadas por pontos de fundo enganosos. Este estudo apresenta uma forma de limpar essas imagens aproveitando como fragmentos de DNA naturalmente se ligam e se desligam ao longo do tempo. O resultado são imagens mais nítidas da maquinaria molecular dentro das células, o que importa para tudo, desde biologia básica até descoberta de fármacos.
Como um truque de piscar revela detalhes ocultos
Um método de imagem poderoso, chamado DNA-PAINT, transforma o agarre aleatório de pequenas fitas de DNA em um microscópio de super-resolução. Uma fita de DNA é ligada à proteína que o cientista quer ver; uma fita complementar carregando um corante fluorescente flutua na solução. Quando a fita flutuante se liga brevemente à sua parceira, ela produz um pequeno flash de luz. Registrando muitos desses piscos e determinando com precisão suas posições, os pesquisadores podem reconstruir as localizações de proteínas com precisão nanométrica — muito mais nítido que microscópios ópticos convencionais.
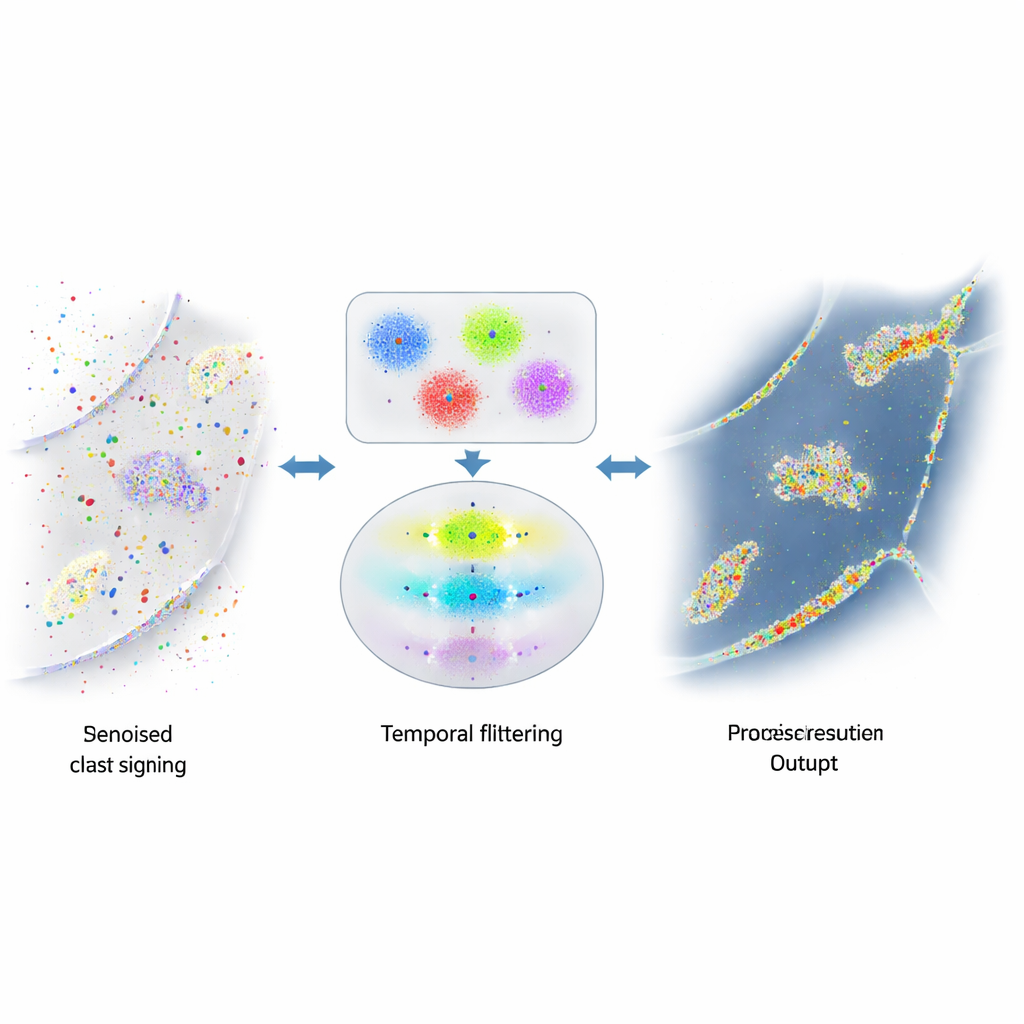
Quando sinais úteis estão enterrados no ruído
A força do DNA-PAINT — muitas fitas fluorescentes em movimento livre — também cria um problema. Essas fitas ocasionalmente aderem onde não deveriam, por exemplo a superfícies celulares aleatórias ou ao abundante DNA dentro do núcleo. Esses flashes acidentais são indistinguíveis em aparência dos reais e poluem a imagem final com pontos e aglomerados falsos. Tentativas anteriores de reduzir esse ruído se concentraram em alterar a química para tornar a ligação indesejada mais rara, ou em regras grosseiras para detectar outliers óbvios. Ainda assim, uma quantidade substancial de sinal enganoso permanecia, limitando o quão confiavelmente os cientistas podiam medir o número de proteínas ou relações espaciais.
Usando o tempo para separar verdade de truque
Os autores perceberam que os pares reais de DNA no DNA-PAINT obedecem a uma regra temporal simples: as pausas entre eventos genuínos de ligação seguem um padrão exponencial previsível. Em contraste, eventos de ligação aleatória não seguem esse padrão. Eles criaram um algoritmo em vários passos que primeiro agrupa piscadas próximas em pequenos aglomerados com base em onde ocorrem, usando uma combinação de agrupamento baseado em densidade e k-means para dividir formas complexas em unidades do tamanho de uma localização. Para cada aglomerado, então constroem uma “trilha temporal” dos eventos de ligação, fundindo cuidadosamente piscadas rápidas de on‑off provenientes da mesma ligação em eventos únicos. Finalmente, aplicam um teste estatístico para verificar se as lacunas entre eventos em cada aglomerado correspondem ao comportamento exponencial esperado. Aglomerados que passam no teste são tratados como reais; os que falham são descartados como ruído.
Testando o método em células reais
Para testar a abordagem, a equipe imageou a proteína de adesão celular E-cadherina em câmaras de ovo de mosca-da-fruta, onde algumas células produziam a proteína marcada e células vizinhas não. Isso criou áreas lado a lado ricas em sinal genuíno e áreas que deveriam conter apenas fundo. Ajustando quantos eventos de ligação um aglomerado deve exibir antes de ser testado, eles encontraram configurações que removeram mais de 90% dos aglomerados espúrios enquanto preservavam mais de 98% dos verdadeiros nas bordas celulares. Em imagens denoised, estruturas finas como tubos delgados e vesículas ficaram muito mais claras. A mesma estratégia funcionou em outros sistemas, incluindo mitocôndrias e microtúbulos, e mesmo em proteínas com distribuições mais difusas e amorfas, onde padrões espaciais sozinhos não dão pista sobre o que é real.
Mapas moleculares mais claros para estudos futuros
Ao ouvir o “ritmo” da ligação de DNA em vez de apenas olhar onde os piscos ocorrem, esse método remove de forma confiável o fundo enganoso dos dados de DNA-PAINT. Para não especialistas, o resultado central é simples: mapas moleculares mais nítidos e mais confiáveis dentro das células. Isso torna mais seguro contar quantas moléculas de proteína estão presentes, avaliar quão próximos diferentes proteínas estão umas das outras e construir imagens mais precisas da vida interna das células. À medida que a imagem baseada em DNA continua a crescer, esse tipo de denoising inteligente será essencial para transformar imagens puntilhadas brutas em conhecimento biológico sólido.
Citação: Sirinakis, G., Allgeyer, E.S., Richens, J.H. et al. Utilizing the predictable binding kinetics of DNA-PAINT to denoise super-resolution images. Nat Commun 17, 2397 (2026). https://doi.org/10.1038/s41467-026-69304-4
Palavras-chave: DNA-PAINT, microscopia de super-resolução, redução de ruído em imagens, imagem de molécula única, mapeamento de proteínas