Clear Sky Science · pt
Propriedades eletrostáticas de regiões desordenadas controlam a busca de fatores de transcrição e atividade pioneira
Como as “pontas” das proteínas ajudam genes a ligar
Cada célula do seu corpo precisa decidir rapidamente quais genes ativar, apesar de seu DNA estar compactado em cromatina. Este artigo explora como extensões flexíveis e eletricamente carregadas de proteínas-chave de controle gênico agem como auxiliares de busca integrados, permitindo que algumas proteínas localizem interruptores de DNA enterrados e abram o material ao redor, enquanto outras têm dificuldade em fazê‑lo. Compreender essa camada oculta de controle esclarece como células-tronco mantêm a flexibilidade e como células mudam de identidade.
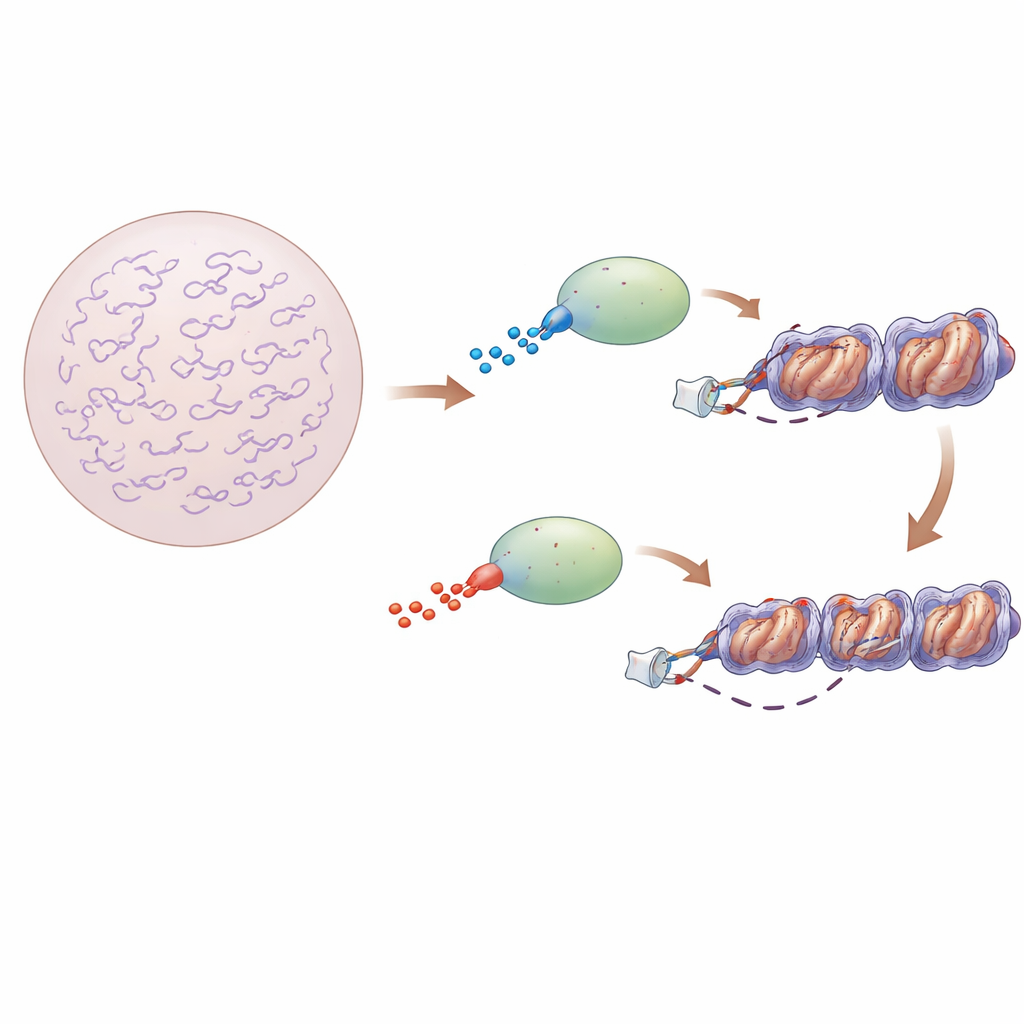
Interruptores gênicos em um cenário de DNA lotado
Fatores de transcrição são proteínas que localizam sequências curtas de DNA e ativam genes próximos. Em bactérias, o DNA está relativamente exposto, e modelos clássicos descrevem essas proteínas como saltando repetidamente para a solução e então deslizando ao longo do DNA nu até encontrarem seus alvos. Em células animais, porém, o DNA está enrolado em proteínas semelhantes a carretéis para formar nucleossomos e ainda dobrado em cromatina compacta. Essa lotação torna incerto como fatores de transcrição ainda conseguem encontrar os pontos corretos rápido o suficiente para controlar milhares de genes.
Regiões proteicas flexíveis com influência oculta
Muitos fatores de transcrição contêm núcleos estruturados que prendem o DNA, ladeados por longos trechos desordenados de aminoácidos. Essas regiões flexíveis não se dobram em formas fixas, mas carregam cargas elétricas. Os autores focaram em dois fatores intimamente relacionados, Sox2 e Sox17, que compartilham um núcleo de reconhecimento de DNA quase idêntico, mas se comportam de maneira muito diferente nas células. Sox2 é um clássico fator “pioneiro” que pode se ligar ao DNA escondido na cromatina compacta e é essencial para manter células‑tronco em um estado flexível e pluripotente. Sox17, em contraste, atua normalmente mais tarde no desenvolvimento e tem muito menos capacidade de se ligar ao DNA densamente empacotado. A diferença chave: a região logo após o núcleo de ligação ao DNA de Sox2 é mais carregada positivamente, enquanto a região equivalente em Sox17 é mais carregada negativamente.
Observando moléculas individuais buscar o DNA
Para ver como essas diferenças de carga afetam o processo de busca, os pesquisadores usaram microscopia de molécula única tanto em células‑tronco de camundongo vivas quanto com componentes purificados sobre superfícies de vidro. Eles projetaram versões de Sox2 e Sox17 que trocam essas “pontas” carregadas, e também versões contendo apenas o núcleo de reconhecimento do DNA. Em células, rastrearam proteínas marcadas fluorescentemente uma a uma, medindo quão rápido elas difundem, quanto tempo permanecem ligadas e com que frequência pousam no DNA. Proteínas com a ponta positivamente carregada de Sox2 ligaram-se à cromatina com mais frequência e passaram mais tempo em interações de longa duração do que aquelas com a ponta de Sox17, mesmo que todas as versões reconhecessem essencialmente as mesmas letras do DNA.
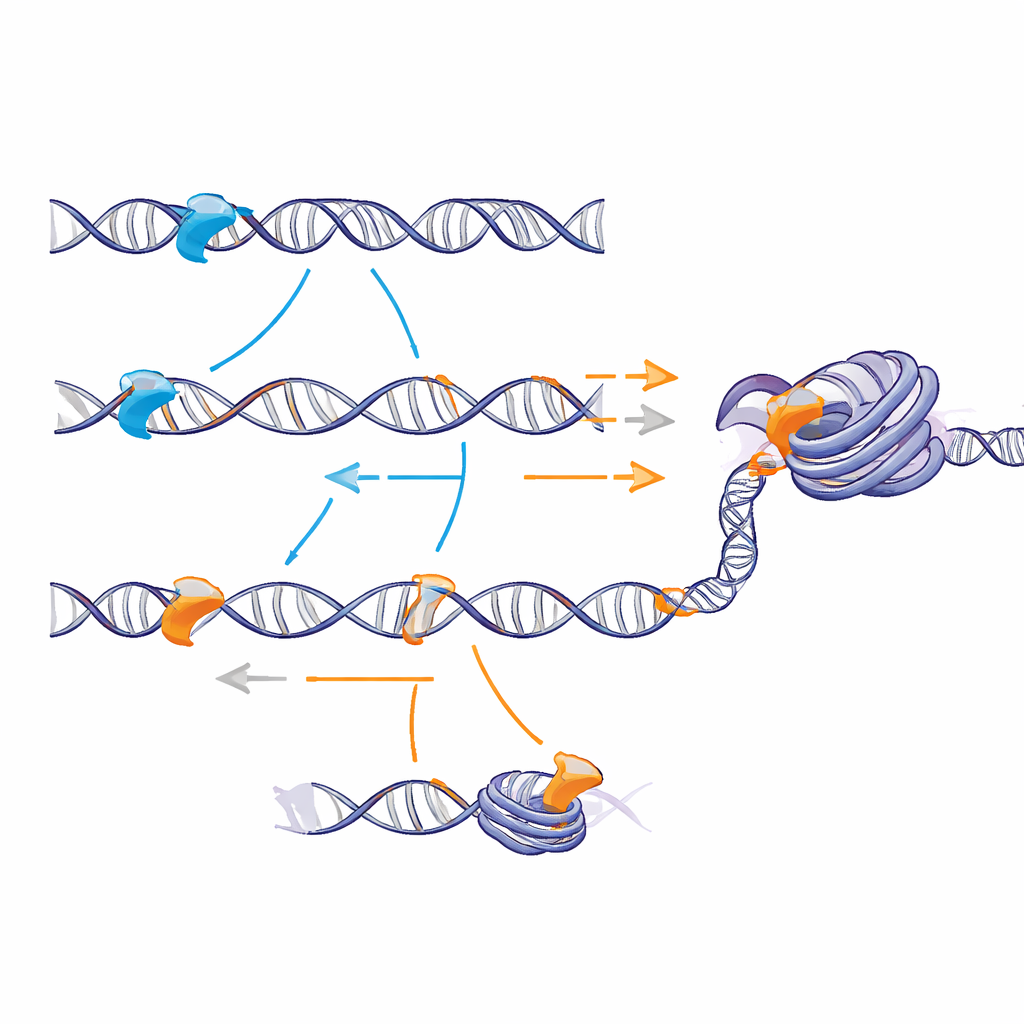
Deslizamento lento, mas melhor reconhecimento
Em experimentos cuidadosamente controlados em tubo de ensaio com fragmentos de DNA nu, as pontas carregadas não alteraram com que frequência as proteínas colidiam inicialmente com o DNA a partir da solução. Em vez disso, elas mudaram o que acontecia depois que uma proteína havia pousado. Combinando experimentos e modelagem matemática, os autores mostraram que a ponta de Sox2 faz a proteína deslizar mais devagar ao longo do DNA, mas aumenta a probabilidade de “notar” seu alvo específico quando o atravessa. A ponta de Sox17 permite movimento mais rápido, mas aumenta a chance de simplesmente passar pelo sítio correto sem se fixar. Isso revela um trade‑off entre velocidade e reconhecimento: uma ponta mais aderente e carregada positivamente torna o ambiente energético mais áspero, elevando as chances de captura bem‑sucedida do alvo.
Invadindo e abrindo cromatina compacta
Quando a equipe reconstruiu nucleossomos e fibras curtas de cromatina in vitro, o contraste ficou mais nítido. A ponta de Sox2 promoveu contatos frequentes e de curta duração tanto com o DNA enrolado quanto com os carretéis de histonas, que ocasionalmente se convertiam em ligações específicas mais longas em sítios enterrados. Em fibras cromatínicas modelo, isso levou a uma ligação mais estável e maior acesso a sítios internos do que observado com a ponta de Sox17. Em células‑tronco, a expressão artificial de Sox2 aumentou a ligação em regiões de cromatina naturalmente fechadas e tornou essas regiões mais acessíveis, medida por um ensaio que detecta com que facilidade enzimas podem cortar o DNA. A versão de Sox2 carregando a ponta de Sox17 ligou‑se menos e abriu a cromatina com menos eficiência, embora ainda reconhecesse os mesmos motivos de DNA.
O que isso significa para a identidade celular
No conjunto, o estudo mostra que a carga elétrica de “pontas” desordenadas de proteínas pode ajustar como fatores de transcrição buscam o DNA e com que eficácia conseguem invadir e afrouxar a cromatina compacta. Uma ponta mais carregada positivamente, como em Sox2, promove contatos não específicos frequentes e afina o reconhecimento do alvo, sustentando forte atividade pioneira e ajudando a manter o panorama de cromatina aberto em células‑tronco. Esses princípios provavelmente se estendem a muitas outras proteínas de controle gênico, adicionando uma nova regra de projeto sobre como as células programam e reprogramam sua atividade genética.
Citação: Sakong, S., Fierz, B. & Suter, D.M. Electrostatic properties of disordered regions control transcription factor search and pioneer activity. Nat Commun 17, 2512 (2026). https://doi.org/10.1038/s41467-026-69284-5
Palavras-chave: fatores de transcrição, cromatina, Sox2, regiões intrinsecamente desordenadas, atividade pioneira