Clear Sky Science · pt
Multicópia heterogênea de variantes blaCTX-M no mesmo plasmídeo aumenta a adaptabilidade evolutiva em Klebsiella pneumoniae clínica
Por que isso importa para a medicina moderna
Infecções resistentes a antibióticos representam uma ameaça crescente em hospitais ao redor do mundo, e os médicos dependem cada vez mais de fármacos de último recurso para salvar pacientes. Este estudo explica como uma bactéria hospitalar comum, Klebsiella pneumoniae, pode usar um truque genético sutil para resistir a combinações poderosas de antibióticos que foram projetadas para contornar a resistência. Ao revelar essa estratégia, a pesquisa ajuda a entender por que algumas infecções retornam apesar de tratamentos agressivos — e oferece pistas sobre como os médicos podem se manter um passo à frente.
Um germe hospitalar sob pressão
A história começa em uma unidade de terapia intensiva, onde dois pacientes foram infectados por linhagens quase idênticas de K. pneumoniae. Uma linhagem foi facilmente tratada com o par moderno de drogas ceftazidima/avibactam, enquanto a outra mostrou forte resistência. Comparações genéticas mostraram que ambas as linhagens carregavam a mesma família ampla de enzimas de resistência, chamadas β-lactamases, em um plasmídeo compartilhado — um pequeno círculo de DNA móvel dentro da bactéria. Mas na linhagem resistente, uma dessas enzimas havia mudado sutilmente, e essa variante, denominada CTX-M-249, permitiu que a bactéria resistisse à combinação de fármacos que deveria tê-la eliminado.
Uma pequena mudança com grandes consequências
Testes bioquímicos mais detalhados revelaram que CTX-M-249 troca um tipo de proteção por outro. A versão habitual, CTX-M-65, é excelente em degradar certos antibióticos como cefotaxima, mas permanece vulnerável ao inibidor avibactam. CTX-M-249, alterada em apenas duas posições na proteína, torna-se eficaz contra ceftazidima mais avibactam, mas perde grande parte de sua força contra cefotaxima. No papel, isso parece um clássico trade-off evolutivo: ganhar uma defesa enquanto enfraquece outra. Ainda assim, a linhagem clínica evitou essa desvantagem por carregar várias cópias intimamente relacionadas do gene ao mesmo tempo, de modo que diferentes versões da enzima puderam coexistir na mesma linhagem bacteriana.
Muitas cópias, muitas opções
Usando sequenciamento de DNA de leituras longas e métodos precisos de quantificação, os pesquisadores descobriram que o plasmídeo na linhagem resistente carregava dois sítios blaCTX-M separados, e um deles podia existir em múltiplas versões ligeiramente diferentes. Na ausência de pressão medicamentosa, cerca de metade da população carregava a versão mais antiga CTX-M-65 e quase metade carregava CTX-M-249, com uma pequena fração apresentando formas intermediárias. Quando as bactérias foram expostas a doses crescentes de ceftazidima/avibactam, tanto o número de cópias do gene quanto a proporção de CTX-M-249 aumentaram rapidamente. Às vezes isso ocorreu pelo aumento do número de plasmídeos por célula; em níveis mais altos do fármaco, o próprio plasmídeo desenvolveu repetições em tandem curtas do gene de resistência. Em efeito, as bactérias usaram a duplicação de DNA como um botão de ajuste que podiam girar para cima ou para baixo para se adequar aos antibióticos do ambiente.
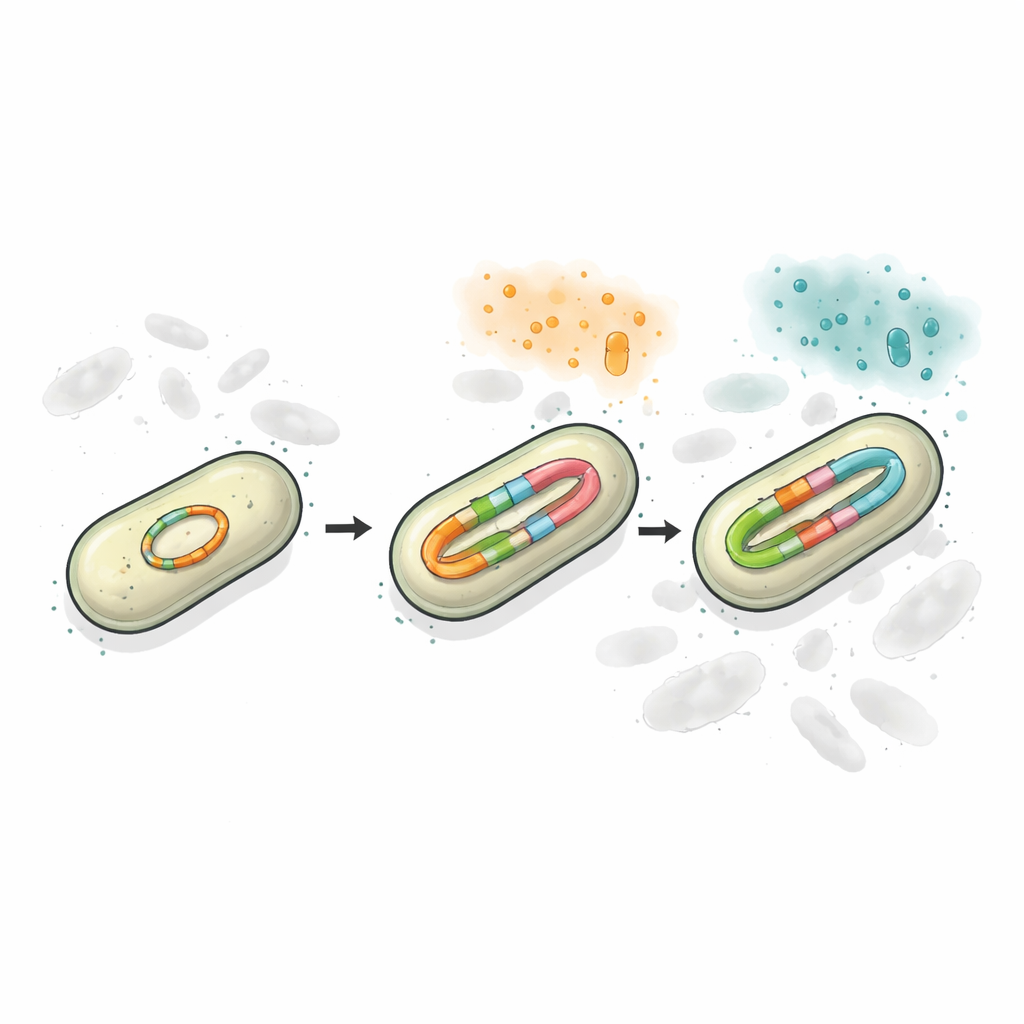
Manter diversidade em um único círculo de DNA
Para testar como esse arranjo molda a sobrevivência, a equipe construiu modelos laboratoriais simplificados nos quais as bactérias carregavam ou uma versão de resistência, duas versões em plasmídeos separados, ou ambas as versões codificadas juntas em um único plasmídeo. Quando desafiados com dois antibióticos diferentes do grupo das cefalosporinas, os sistemas mistos superaram as linhagens de gene único, porque ao menos uma versão da enzima podia lidar com cada fármaco. No entanto, a configuração em que ambas as variantes do gene ficavam no mesmo plasmídeo mostrou-se a mais estável. Quando os antibióticos eram aplicados por vários dias ou alternados de um fármaco para outro, células com dois plasmídeos separados frequentemente perdiam um deles, sacrificando parte de sua proteção. Em contraste, o plasmídeo “dois-em-um” era herdado como um pacote, preservando ambas as opções de resistência mesmo quando impunha um custo de crescimento a curto prazo.
Um padrão mais amplo em bactérias perigosas
Modelos matemáticos reproduziram esses experimentos, mostrando que, acima de certos níveis de antibiótico, bactérias com um único plasmídeo carregando múltiplas variantes de resistência acabam dominando populações mistas. Os pesquisadores então pesquisaram milhares de genomas de K. pneumoniae de hospitais, fazendas, alimentos e do ambiente. Eles frequentemente encontraram múltiplas cópias ligeiramente diferentes de genes-chave de resistência — especialmente em isolados clínicos humanos que enfrentam forte exposição a fármacos. Isso sugere que construir “heterogeneidade multicópia” em plasmídeos não é uma raridade excêntrica, mas uma tática disseminada que as bactérias usam para proteger suas apostas contra tratamentos variáveis.
O que isso significa para pacientes e tratamentos
Para um não-especialista, a mensagem central é que algumas bactérias não carregam simplesmente um único gene de resistência; elas carregam famílias de versões relacionadas agrupadas no mesmo elemento móvel de DNA, dando-lhes um conjunto de ferramentas flexível contra diferentes fármacos. Esse arranjo lhes permite manter a resistência por longos períodos, mesmo quando os médicos mudam as terapias, e ajuda a explicar por que certas infecções são tão difíceis de erradicar. Ao mesmo tempo, o estudo mostra que combinações de fármacos escolhidas com cuidado — como emparelhar ceftazidima/avibactam com cefotaxima — podem explorar fragilidades nesse sistema e suprimir até mesmo essas linhagens bem armadas. Entender como as bactérias constroem e usam esses plasmídeos multicópia é, portanto, crucial para desenhar estratégias antimicrobianas mais inteligentes e retardar a marcha da resistência.
Citação: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Palavras-chave: resistência a antibióticos, Klebsiella pneumoniae, plasmídeos, beta-lactamases, terapia multimecanismo