Clear Sky Science · pt
TANGO: Análise e seleção de partículas em criotomografia eletrônica
Ver células em 3D e depois interpretar a multidão
A criotomografia eletrônica permite que cientistas congelem células vivas em ação e as capturem em três dimensões, quase como pausar um filme em detalhe atômico. Mas, uma vez que milhares de pequenos “pontos” moleculares foram mapeados dentro de uma célula, surge um novo problema: como entender quem está ao lado de quem, quem forma equipes e onde os padrões importantes estão escondidos nessa cidade molecular superpovoada? Este estudo apresenta o TANGO, um conjunto de software que transforma mapas 3D brutos de partículas em histórias legíveis sobre como as moléculas estão organizadas e funcionam em conjunto.
De pontos no gelo a um mapa de vizinhança molecular
A criotomografia eletrônica começa inclinando uma amostra congelada no microscópio para registrar muitas imagens 2D. Essas imagens são combinadas em um volume 3D, chamado tomograma, onde complexos moleculares individuais aparecem como manchas desfocadas. Métodos existentes já usam esses dados para aprimorar as formas das moléculas por meio de média de muitas cópias, mas em grande parte ignoram um tesouro igualmente rico: as posições e orientações exatas de cada partícula. O TANGO foi desenvolvido para explorar essa informação negligenciada. Ele trata todas essas partículas como pontos no espaço, cada um com uma direção, e analisa como elas estão posicionadas e orientadas em relação umas às outras. Fazendo isso, vai além de simplesmente perguntar “como esta molécula se parece?” para questionar “como essas moléculas estão organizadas juntas na célula?” 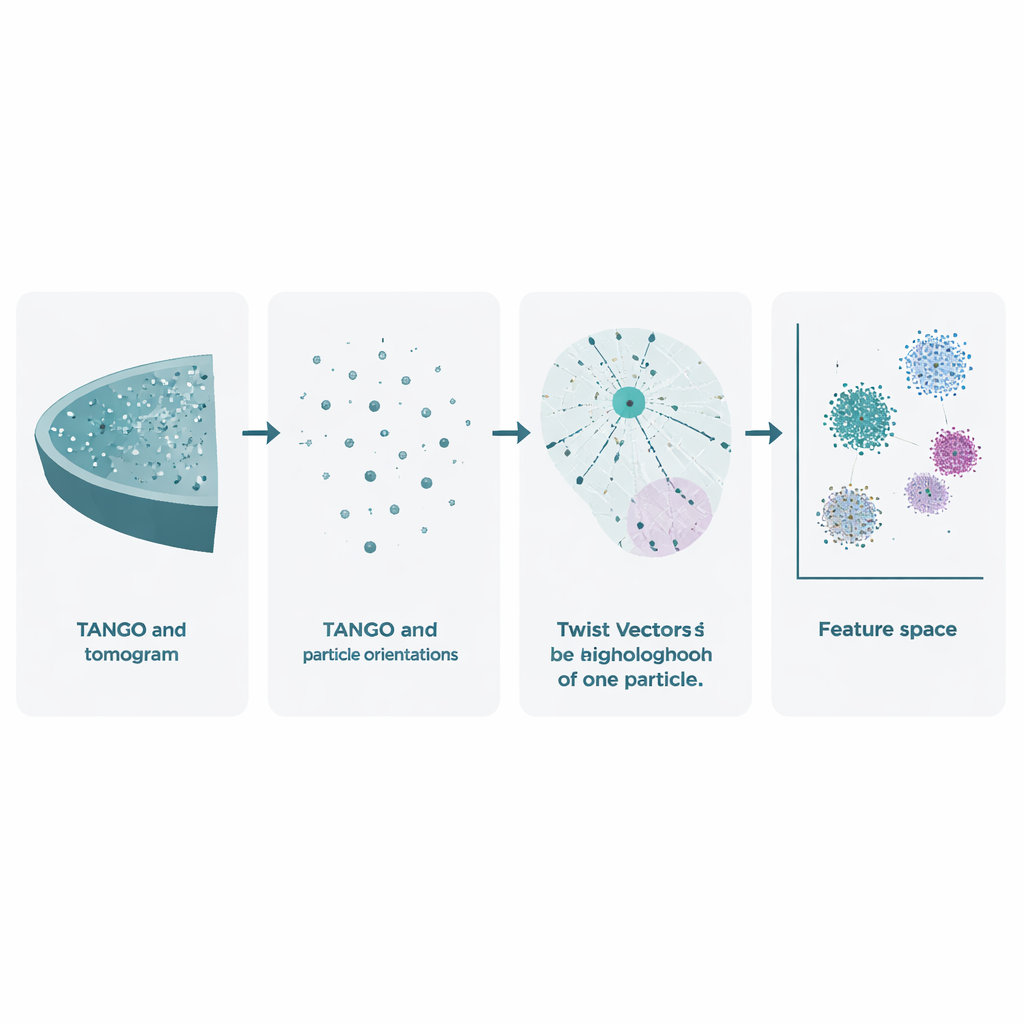
Capturando torções e voltas com um novo descritor
No coração do TANGO está a ideia de “vetores de torção”. Para uma dada partícula, o software observa todos os seus vizinhos dentro de um raio escolhido e registra duas coisas: onde cada vizinho se encontra no espaço 3D e como ele está rotacionado em relação à partícula central. Essas relações combinadas de posição e ângulo são codificadas como descrições numéricas concisas conhecidas como descritores de torção. Como o TANGO sempre reorienta as vizinhanças para um quadro de referência comum, esses descritores são insensíveis à forma como a amostra inteira está rotacionada no microscópio. Isso torna possível comparar vizinhanças locais entre diferentes tomogramas e experimentos de maneira consistente.
Purificando dados ruidosos e reconstruindo montagens moleculares
Dados experimentais reais são bagunçados: métodos automáticos de detecção podem incluir muitas partículas falsas e perder a noção de quais pequenos pedaços pertencem a quais estruturas maiores. O TANGO aborda isso transformando a rede de relações de torção em um grafo, onde partículas são nós e ligações de vizinhança são arestas. Analisando como os nós se conectam, o TANGO consegue agrupar partículas de volta em suas montagens parentais corretas e descartar outliers que não se encaixam na geometria esperada. Os autores mostram que essa abordagem recupera com precisão a arquitetura em anel dos poros nucleares na membrana nuclear, o arranjo tubular dos microtúbulos e as cascas aproximadamente esféricas de partículas semelhantes a vírus imaturos do HIV. Em cada caso, o TANGO tanto limpa as listas de partículas quanto restaura quais peças pertencem juntas, muitas vezes igualando ou melhorando a curadoria manual cuidadosa.
Detectando defeitos sutis e padrões em ladrilhos
Muitos vírus e estruturas celulares formam grades repetitivas, como ladrilhamento molecular em superfícies curvas. O TANGO usa seus descritores de torção para medir o quão regulares esses padrões são e para detectar locais onde eles se dobram ou se rompem. Um ingrediente-chave é uma “pontuação angular” que compara orientações respeitando simetrias internas, como a simetria de seis vezes de hexâmeros. Aplicado a capsídeos maduros do HIV, o TANGO detecta pentâmeros — unidades de cinco partes necessárias para fechar a casca cônica — escondidos em grandes campos de hexâmeros. Em grades imaturas do HIV, separa regiões bem ordenadas de regiões distorcidas e correlaciona baixas pontuações angulares com áreas irregulares e quebradas da casca. Análises semelhantes em dados de cromatina sintética e ribossomos revelam nucleossomos empilhados, arranjos helicoidais de DNA–proteína e pares recorrentes de ribossomos que se assemelham a estados de tradução descritos anteriormente. 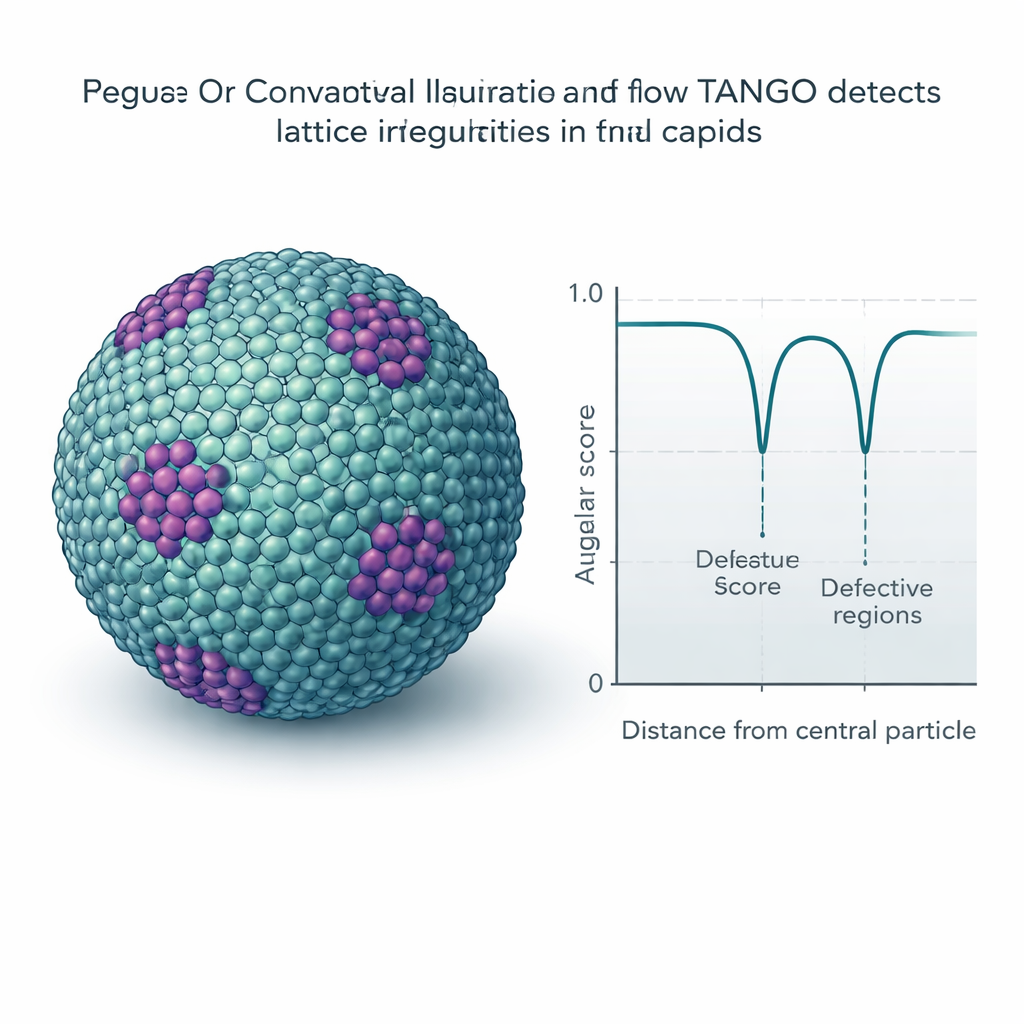
Uma caixa de ferramentas flexível para explorar a arquitetura celular
O TANGO é implementado como software Python de código aberto e vem com uma interface gráfica para que usuários possam testar diferentes formatos de vizinhança, filtros e características sem programação intensa. Por ser modular, pesquisadores podem inserir suas próprias medidas geométricas ou descritores de padrão e usá-los imediatamente dentro do mesmo fluxo de trabalho. Para novatos, isso reduz a barreira para explorar a organização espacial; para especialistas, fornece um arcabouço que pode crescer com novas ideias e conjuntos de dados.
Por que isso importa para entender células vivas
Em termos simples, este trabalho dá aos biólogos uma maneira de ir de imagens estáticas de moléculas individuais para mapas dinâmicos de como essas moléculas estão organizadas e cooperam dentro das células. Ao codificar as relações de “quem está perto de quem” e “como estão orientados” em características numéricas robustas, o TANGO transforma dados ruidosos de microscopia 3D em padrões que podem ser agrupados, comparados e testados estatisticamente. Isso pode revelar montagens ocultas, localizar defeitos em cascas virais e descobrir arranjos moleculares raros ligados a doenças ou à ação de fármacos. À medida que a criotomografia eletrônica se torna mais amplamente usada, ferramentas como o TANGO ajudarão a transformar nuvens densas de partículas em percepções claras sobre a coreografia interna da vida.
Citação: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Palavras-chave: criotomografia eletrônica, organização espacial, ladrilhos moleculares, capsídeos virais, ribossomos