Clear Sky Science · pt
PRICE: detecção direta e robusta de microRNAs com resolução de único nucleotídeo
Por que pequenas mensagens genéticas importam
Dentro de cada célula existe um enxame de pequenas moléculas de RNA chamadas microRNAs que ajudam a ajustar finamente quais genes são ativados ou desligados. Uma alteração de apenas uma “letra” nessas moléculas curtas pode desequilibrar o organismo em direção à saúde ou à doença, incluindo cânceres. Médicos e pesquisadores gostariam de ler essas pequenas diferenças diretamente no sangue ou em tecidos, mas os métodos atuais costumam ser lentos, caros e pouco precisos para identificar de forma confiável uma mudança de uma única letra. Este artigo apresenta uma nova técnica de laboratório, chamada PRICE, que promete ler esses erros microscópicos em microRNAs de forma mais simples e precisa, abrindo portas para detecção precoce do câncer e melhor acompanhamento do comportamento dos tumores.
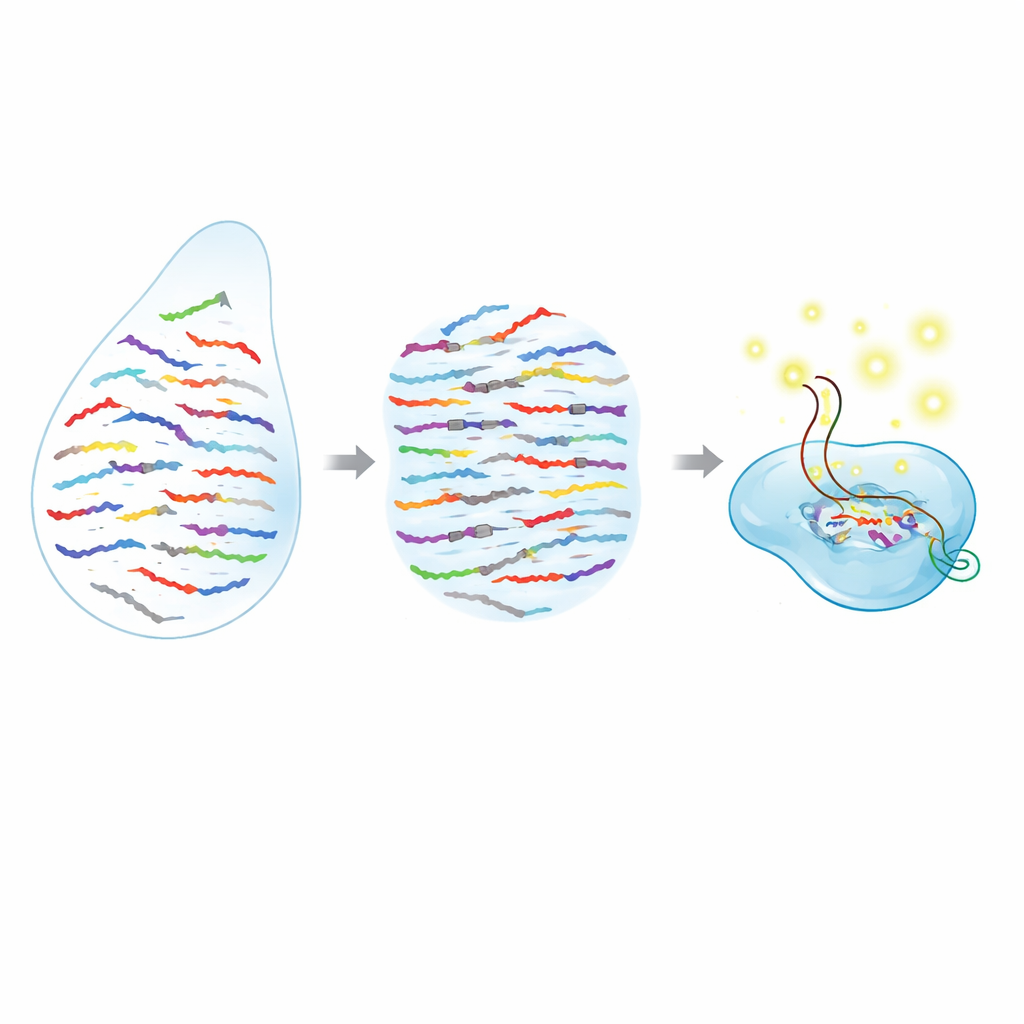
Uma nova forma de separar moléculas quase idênticas
MicroRNAs são extremamente curtos, o que os torna difíceis de distinguir quando suas sequências diferem por apenas um componente. Muitas ferramentas atuais, como PCR e sequenciamento de RNA, fazem um bom trabalho ao quantificar microRNAs em geral, mas têm dificuldade quando duas versões são quase idênticas, ou exigem preparo de amostra complexo e instrumentos caros. Os autores combinam duas ideias poderosas para superar isso: uma “tesoura” molecular programável da família CRISPR e peças sintéticas semelhantes ao DNA chamadas ácidos nucleicos peptídicos (PNAs). A enzima CRISPR Cas13a pode ser programada para reconhecer um RNA específico e, ao encontrar seu alvo, começa a cortar moléculas repórter próximas, produzindo um sinal fluorescente intenso. Os PNAs, por sua vez, são fitas curtas que se ligam de forma especialmente forte a sequências de RNA correspondentes, mas perdem essa afinidade de forma abrupta se mesmo uma única letra estiver errada.
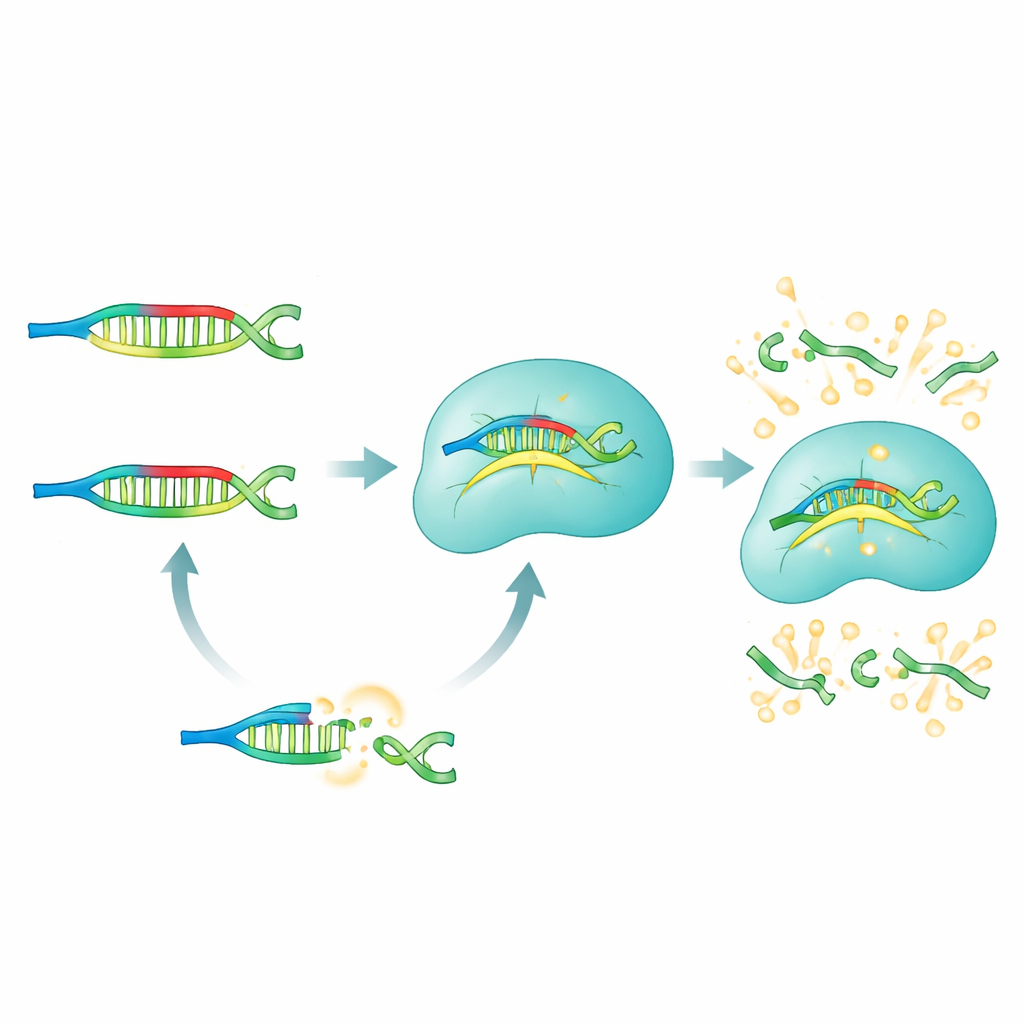
Como o método PRICE funciona
No sistema PRICE, os PNAs atuam como bloqueadores seletivos que silenciam tudo o que os pesquisadores não querem detectar. Para um microRNA de interesse, a equipe projeta um painel de bloqueadores PNA que casam perfeitamente com todas as versões “erradas”—aquelas com mudanças indesejadas de uma única letra—enquanto deliberadamente fazem um desacordo com o alvo escolhido. Quando uma amostra biológica (soro, células ou tecido) é misturada com esses PNAs, os microRNAs não alvo ficam fortemente ligados e efetivamente mascarados. O verdadeiro alvo permanece não ligado e livre para interagir com o complexo Cas13a, que foi pré‑programado com um RNA guia que reconhece esse microRNA. Somente esse alvo desbloqueado pode ativar a Cas13a em seu modo cortador, que por sua vez fragmenta moléculas repórter fluorescentes e gera um brilho forte e facilmente mensurável.
Ajustando com precisão de uma única letra
Os autores exploraram sistematicamente como projetar bloqueadores PNA que sejam fortes o suficiente para capturar o microRNA errado, mas fracos o bastante para ignorar o desejado que difere por apenas uma letra. Eles descobriram que duas regras de projeto análogas à temperatura são cruciais: o PNA deve formar um par estável com o mutante indesejado em ou acima da temperatura corporal, mas formar um par muito mais fraco com o alvo que se desfaça bem abaixo dessa temperatura. Usando essas regras, apoiadas por um modelo preditivo simples, construíram PNAs que reduziram sinais falsos de microRNAs mutantes em mais de 70% enquanto deixavam o sinal verdadeiro praticamente intacto. Importante, os PNAs adicionados não reduziram a sensibilidade geral: o PRICE ainda conseguiu detectar microRNAs em concentrações de apenas algumas dezenas de femtomolares, comparável aos melhores testes baseados em amplificação, porém sem as etapas extras de cópia.
Aplicando o teste em amostras de câncer
Para mostrar que o PRICE é mais do que um dispositivo teórico, a equipe focou na família let‑7 de microRNAs, que está fortemente envolvida na biologia do câncer. Eles demonstraram que o PRICE pode identificar microRNAs alvo em misturas contendo muitos membros da família quase idênticos e pode até detectar variantes raras que representam apenas 5% de uma amostra. Os pesquisadores então testaram material clínico real: linhagens celulares de câncer de fígado, biópsias de tecido e soro de pacientes. Tanto em tecido tumoral quanto no sangue, o PRICE detectou consistentemente níveis mais baixos de microRNAs let‑7 específicos em pacientes comparados a controles sem câncer, em acordo com estudos anteriores. Quando comparado diretamente ao RT‑qPCR padrão, o PRICE mostrou desempenho pelo menos similar e muitas vezes melhor na distinção entre casos com e sem câncer, especialmente em amostras de soro de baixa abundância onde os resultados de PCR ficavam ruidosos.
Por que isso importa para diagnósticos futuros
No essencial, este trabalho mostra que é possível ler diretamente diferenças de uma única letra em pequenos RNAs regulatórios de maneira prática e escalável. Ao permitir que PNAs prendam sequências parecidas indesejadas e entregar a leitura final a uma enzima CRISPR, o PRICE oferece uma caixa de ferramentas flexível para projetar testes que podem ser redirecionados simplesmente trocando o painel de bloqueadores e o RNA guia. Além do câncer de fígado e da família let‑7, a mesma estratégia pode ser estendida a muitas outras doenças nas quais pequenas mudanças em RNAs importam, e até a variantes de DNA quando combinada com enzimas CRISPR relacionadas. Os autores também demonstram um leitor compacto e multicanal que pode executar ensaios PRICE fora de grandes laboratórios centrais, sugerindo testes futuros no ponto de atendimento. Se desenvolvido além, o PRICE pode se tornar uma forma prática de monitorar alterações genéticas sutis que sinalizam câncer e outras doenças muito antes do aparecimento de sintomas.
Citação: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Palavras-chave: diagnóstico por microRNA, CRISPR Cas13a, ácido nucleico peptídico, variante de nucleotídeo único, biomarcadores de câncer de fígado