Clear Sky Science · pt
Um modelo polimérico informado por experimentos revela organização de alta resolução de lócus genômicos
Como o dobramento do DNA molda a identidade celular
Cada célula do seu corpo carrega essencialmente o mesmo DNA, ainda que neurônios, células da pele e células-tronco se comportem de maneiras muito diferentes. Uma razão central é como esse DNA é dobrado e compactado dentro do núcleo. Este estudo apresenta uma nova forma de “ver” esse dobramento em detalhes notáveis, conectando o arranjo físico do DNA ao fato de genes importantes estarem ativados ou silenciados. Ao combinar experimentos com simulações computacionais baseadas em física, os autores revelam aglomerados ocultos de material genético que parecem atuar como blocos construtivos fundamentais da organização do genoma.
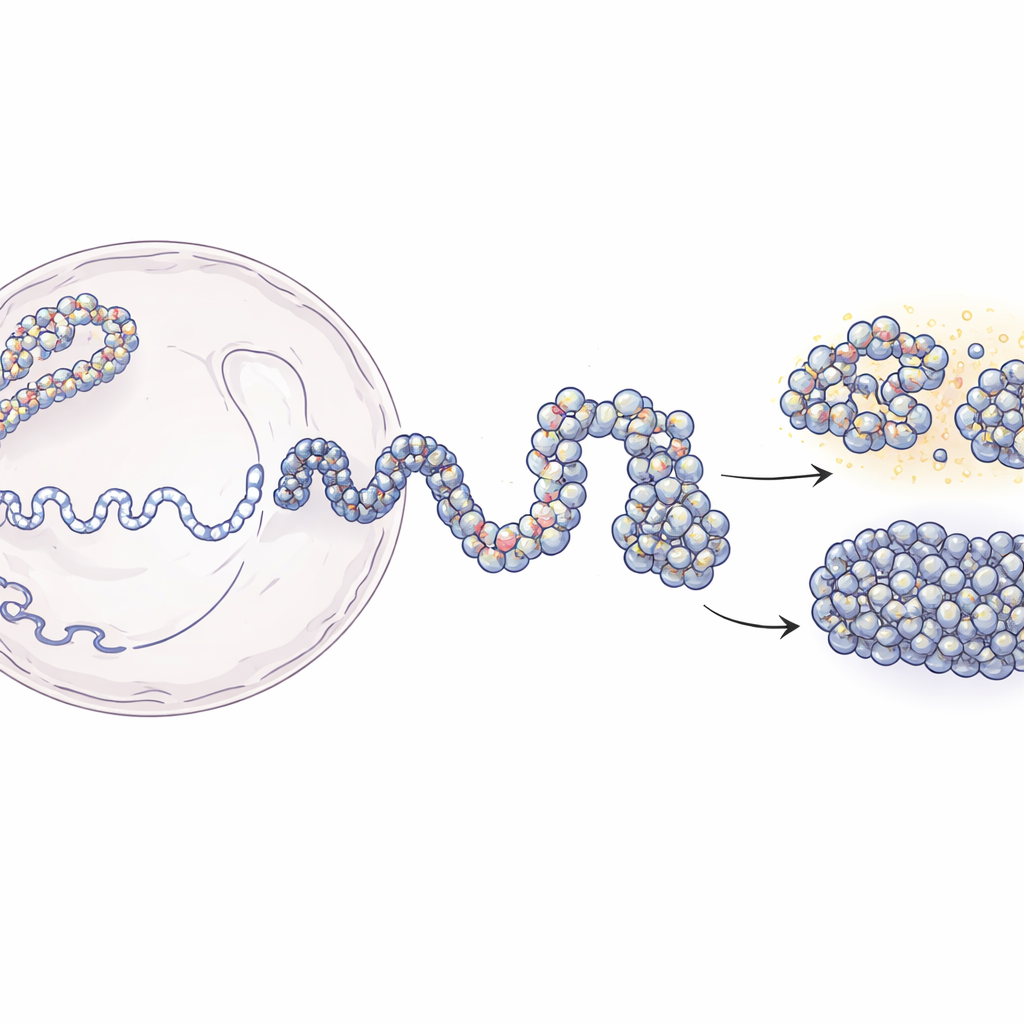
De filamentos longos de DNA a mapas 3D do genoma
No interior do núcleo, o DNA se enrola em torno de carretéis proteicos chamados nucleossomos, formando uma estrutura de contas em um fio conhecida como cromatina. Técnicas modernas como Hi-C e Micro-C informam quais pedaços de DNA estão próximos no espaço 3D, mas normalmente oferecem instantâneos borrados que representam médias de populações celulares. Por outro lado, experimentos que localizam nucleossomos individuais fornecem detalhes locais nítidos, mas pouca noção da estrutura maior. Este trabalho preenche essa lacuna. Os autores partem de mapas de contato de baixa resolução que relatam com que frequência segmentos distantes do DNA se tocam e os combinam com mapas experimentais de posições de nucleossomos. Usando princípios da física de polímeros, eles constroem conjuntos 3D simulados de cromatina que se ajustam aos dados experimentais e, ao mesmo tempo, resolvem estruturas até algumas dezenas de bases de DNA.
Uma estratégia em duas etapas para reconstruir a cromatina
A abordagem de modelagem se desdobra em duas etapas principais. Primeiro, a equipe usa dados de Hi-C para gerar muitas possíveis formas em grande escala de um trecho de DNA de 200.000 bases, tratando a cromatina como uma cadeia flexível em que segmentos de 5.000 bases são orientados suavemente para fazer ou evitar contatos conforme observado nos experimentos. Essas estruturas grosseiras capturam o padrão de dobramento global que proteínas na célula ajudam a criar. Na segunda etapa, cada grande “conta” é substituída por uma cadeia muito mais refinada composta por nucleossomos individuais e pelos curtos conectores de DNA entre eles. As posições desses nucleossomos vêm de um método de mapeamento baseado em enzima (MNase-seq) que revela onde eles tipicamente se posicionam ao longo do genoma. As cadeias refinadas são então permitidas dobrar mantendo, porém, a arquitetura mais ampla. Quando os pesquisadores “borram” seus modelos de alta resolução de volta às resoluções experimentais, eles reproduzem mapas de contato de Hi-C e Micro-C com alta precisão.
Descobrindo ‘blobs’ de nucleossomos como unidades estruturais
Ao ampliar suas estruturas simuladas, emergiu um padrão marcante: os nucleossomos não estavam distribuídos de forma homogênea, mas sim agrupados em aglomerados irregulares, que os autores chamam de blobs de nucleossomos. Esses blobs lembram as estruturas granuladas observadas anteriormente em imagens de microscopia de super-resolução de células reais. Ao analisar milhares de instantâneos simulados, a equipe mostrou que esses blobs são alongados, não esféricos, e tipicamente contêm vários nucleossomos compactados juntos. Crucialmente, os contatos dentro desses blobs correspondem de forma estreita aos blocos de interação em domínio vistos nos dados experimentais, indicando que os blobs não são acidentes aleatórios, mas unidades 3D fundamentais da organização da cromatina. As simulações até predizem limites de domínio sutis adicionais que são difíceis de detectar experimentalmente, sugerindo que esse modelo físico pode revelar características em escala fina ocultas em dados ruidosos.
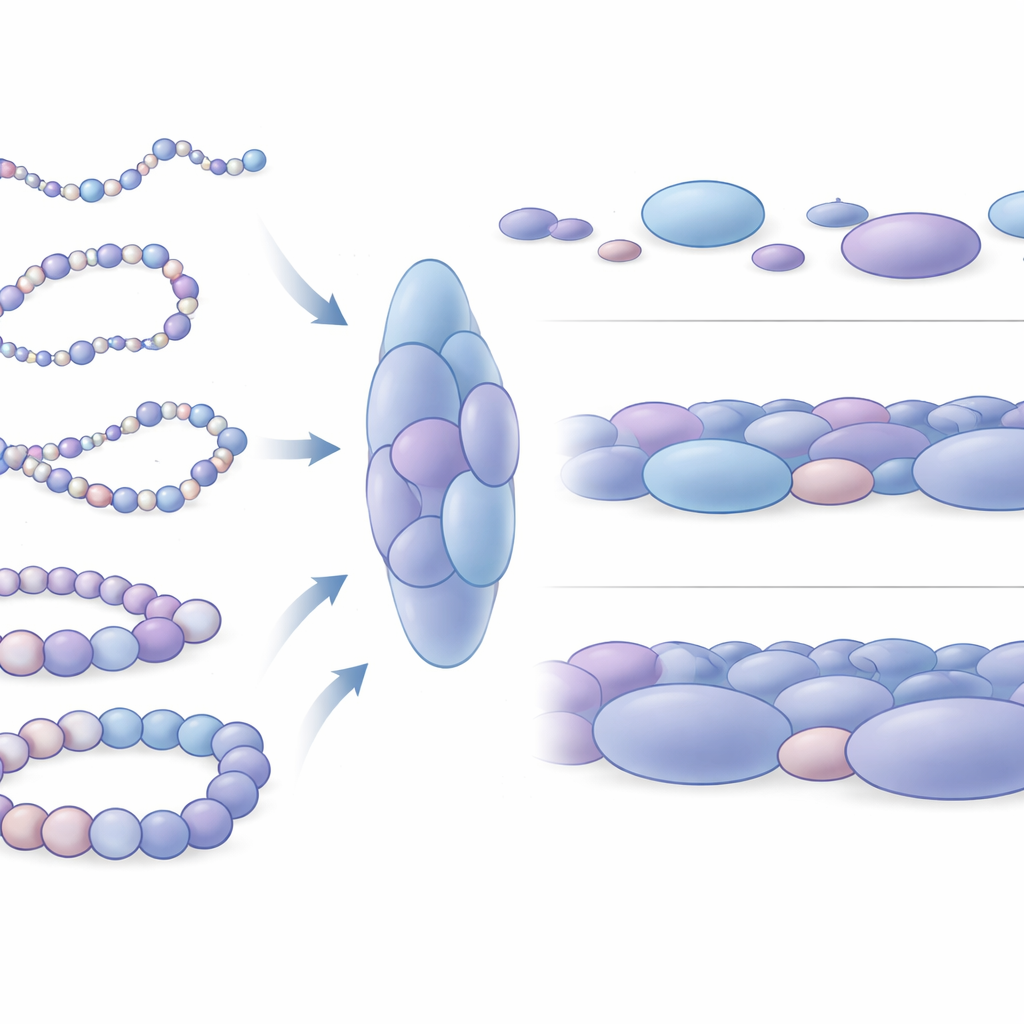
Como diferenças de empacotamento refletem a atividade gênica
Os pesquisadores então investigaram como esses blobs diferem em torno de genes ativos versus genes silenciosos. Eles se concentraram em quatro trechos bem estudados do DNA humano, incluindo dois genes que ajudam a manter células-tronco em um estado flexível e indiferenciado (Nanog e Lin28A) e dois genes de controle do desenvolvimento (HoxB4 e HoxA13) que estão desligados nas mesmas células. Em torno dos genes inativos, os blobs eram, em média, maiores e mais densamente empacotados, com nucleossomos formando arranjos locais mais fechados. Em contraste, os blobs próximos a genes ativos eram menores, um pouco mais frouxos e mais diversos. Em escala mais ampla, o DNA ao redor de genes ativos explorava muitas mais formas distintas e era mecanicamente mais flexível, enquanto as regiões ao redor de genes silenciosos comportavam-se como segmentos de cromatina mais rígidos. Essa diferença mecânica provavelmente afeta com que facilidade elementos regulatórios distantes podem se encontrar e cooperar com os interruptores gênicos.
Por que isso importa para entender o controle gênico
Em conjunto, os achados desenham um quadro em que o genoma é construído a partir de aglomerados dinâmicos de nucleossomos cuja dimensão, forma e espaçamento ajudam a determinar se genes próximos estão acessíveis ou trancados. O novo modelo conecta dados experimentais de contato, mapas de nucleossomos e princípios físicos em uma única estrutura que explica como genes de células-tronco podem permanecer flexíveis e interativos enquanto genes de desenvolvimento ficam sequestrados em vizinhanças mais rígidas e compactas. Para não especialistas, a ideia central é que a atividade gênica não é governada apenas pela sequência de DNA; ela também depende de como esse DNA é dobrado em estruturas tridimensionais. Ao revelar os blobs de nucleossomos como blocos básicos desse dobramento, este trabalho oferece uma rota poderosa para vincular a arquitetura microscópica do genoma a processos em larga escala como desenvolvimento, identidade celular e doença.
Citação: Mittal, R., Heermann, D.W. & Bhattacherjee, A. An experimentally-informed polymer model reveals high resolution organization of genomic loci. Nat Commun 17, 2338 (2026). https://doi.org/10.1038/s41467-026-68928-w
Palavras-chave: Dobramento da cromatina, aglomerados de nucleossomos, organização 3D do genoma, regulação gênica, modelagem polimérica