Clear Sky Science · pt
Um atlas de quantificação absoluta de pequenos RNAs não codificadores em diversos tecidos e linhagens celulares de mamíferos
Por que moléculas de RNA minúsculas importam
Dentro de cada célula, frotas de pequenas moléculas de RNA ajudam a decidir quais genes são ativados ou silenciados. Esses pequenos RNAs não codificadores funcionam como reguladores graduais dos nossos programas genéticos, moldando o desenvolvimento, a função de órgãos e doenças. Ainda assim, apesar das poderosas tecnologias de sequenciamento, os cientistas têm encontrado dificuldades para medir exatamente quantas dessas moléculas estão presentes em diferentes células e tecidos. Este estudo apresenta uma forma mais precisa de contá‑las e constrói um atlas detalhado que mostra sua verdadeira abundância em muitos tecidos de mamíferos e em linhagens celulares comuns de laboratório.
Uma maneira mais clara de contar pequenos RNAs
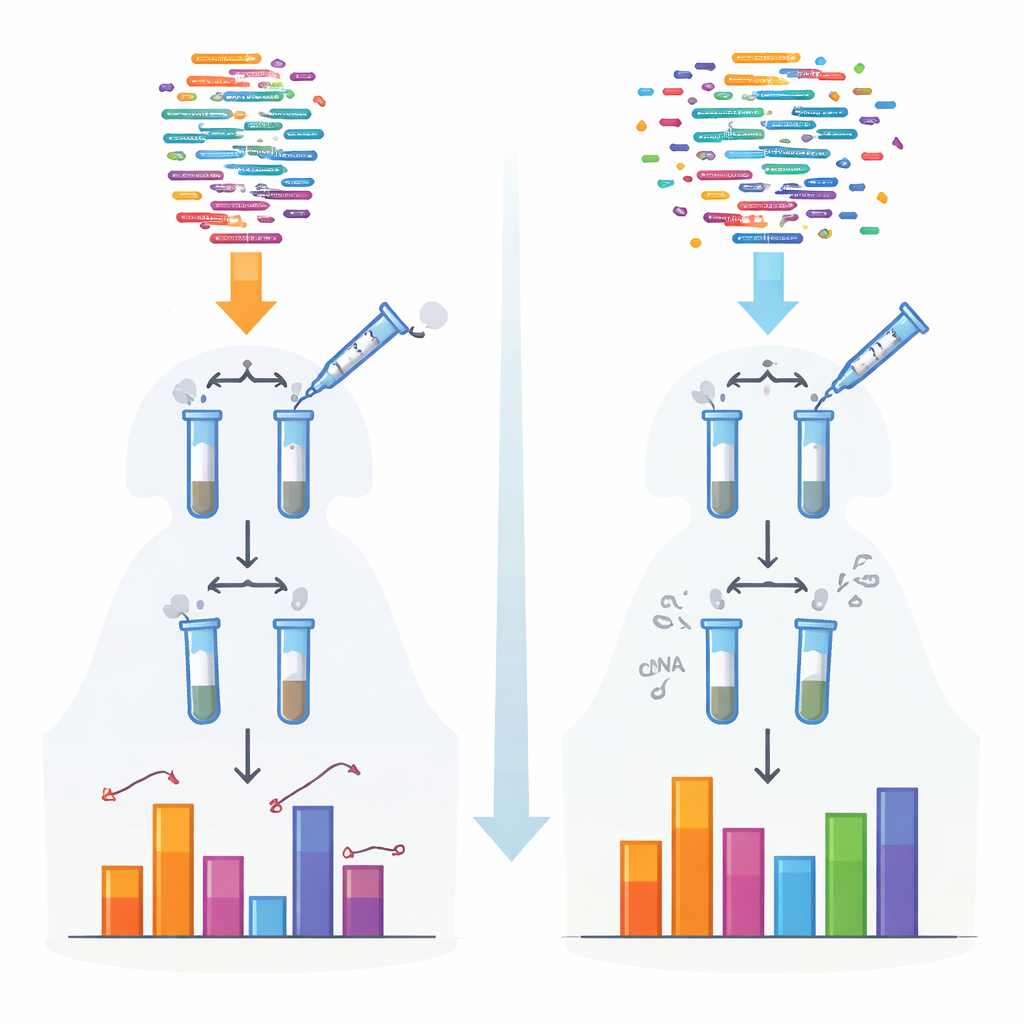
Os métodos tradicionais de sequenciamento de pequenos RNAs dependem de enzimas que ligam adaptadores às moléculas antes da leitura. Essas enzimas preferem certas conformações e terminações químicas, de modo que alguns RNAs são capturados com eficiência enquanto outros são perdidos ou subcontados. Esse viés é particularmente severo para classes específicas, como piRNAs e pequenos RNAs de plantas, que carregam capas químicas protetoras nas extremidades. Os autores criaram um novo protocolo, chamado 4NBoost, que redesenha os adaptadores e as condições da reação para equilibrar essas preferências e acrescenta códigos de barras moleculares integrados para distinguir moléculas verdadeiras de cópias geradas durante a amplificação.
Transformando um protocolo em uma ferramenta de medição
Para transformar o 4NBoost de uma leitura relativa em uma ferramenta de medição real, a equipe adicionou RNAs sintéticos “spike‑in” cuidadosamente projetados em concentrações conhecidas que cobriam uma faixa muito ampla. Ao comparar quantas vezes cada spike‑in foi lido pelo sequenciador com a quantidade originalmente adicionada, construíram curvas padrão que convertem contagens de leitura em números absolutos de moléculas. Testes com diferentes misturas de spike‑ins e RNAs de controle adicionados mostraram que o 4NBoost consegue acompanhar a abundância com precisão ao longo de várias ordens de magnitude, incluindo RNAs com modificações químicas problemáticas. Mesmo partindo de tão pouco quanto um nanograma de RNA total, o método ainda capturou fielmente o panorama dos pequenos RNAs.
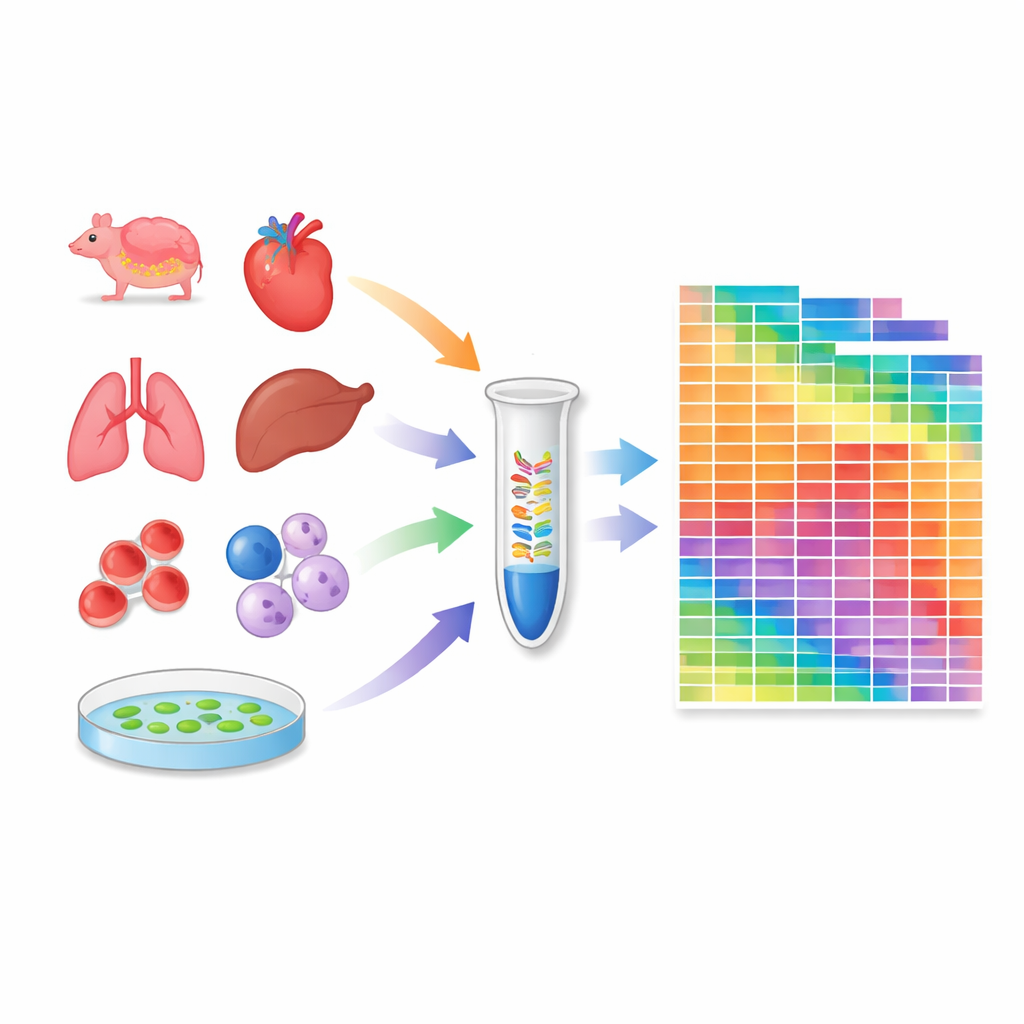
Construindo um atlas entre tecidos e linhagens celulares
Munidos desse protocolo calibrado, os pesquisadores perfilaram 259 amostras: 20 tecidos de camundongos, 18 de macacos‑crab‑eating (macaco‑de‑cauda‑crava), 24 linhagens celulares amplamente usadas de humanos e camundongos, e vários tecidos da planta modelo Arabidopsis. Para cada amostra, estimaram o número absoluto de moléculas para milhares de microRNAs e piRNAs. Isso revelou quantas espécies diferentes de microRNA estão presentes em cada contexto e como suas quantidades totais variam entre tecidos e espécies. Algumas linhagens celulares e órgãos apresentam repertórios particularmente ricos em microRNAs, enquanto outros, como células sanguíneas, são dominados por algumas espécies altamente abundantes. O atlas também expôs diferenças substanciais entre tecidos de camundongo e macaco, ressaltando que a regulação por pequenos RNAs pode ser específica por espécie.
Corrigindo dados antigos e revisando suposições comuns
Quando o novo atlas foi comparado com bancos de dados populares de pequenos RNAs construídos com métodos convencionais, surgiram discrepâncias marcantes. Várias famílias importantes de microRNAs — como miR‑19 e miR‑29 — mostraram ser muito mais abundantes do que se pensava, enquanto outras — como as amplamente estudadas famílias let‑7 e miR‑10 — frequentemente foram superestimadas. O estudo também reexaminou qual “braço” de cada pré‑hairpin é realmente usado nas células, revelando casos em que as anotações atuais listam a cadeia principal errada. Para resgatar a riqueza de conjuntos de dados existentes e enviesados, os autores treinaram um modelo de aprendizado de máquina que aprende como as medições convencionais se desviam do 4NBoost e, em seguida, corrige matematicamente esses valores para refletir melhor as abundâncias reais.
Um recurso público para explorar pequenos RNAs
Todas as medições do 4NBoost e o modelo de correção estão disponibilizados gratuitamente por meio de uma plataforma online chamada SmRNAQuant. Pesquisadores podem navegar ou baixar níveis absolutos de pequenos RNAs para tecidos, linhagens celulares ou microRNAs específicos, e podem enviar seus próprios dados preparados com kits comuns para obter valores corrigidos contra vieses. Para não especialistas, a mensagem principal é que a contagem importa: pequenas diferenças no número de cópias de um pequeno RNA podem significar a diferença entre regulação gênica ativa e nenhuma efeito. Ao oferecer números mais confiáveis e uma maneira de corrigir dados antigos, este trabalho estabelece uma base quantitativa mais sólida para entender como pequenos RNAs moldam a biologia normal e as doenças.
Citação: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
Palavras-chave: quantificação de microRNA, pequeno RNA não codificante, viés em sequenciamento de RNA, atlas de expressão tecidual, correção por aprendizado de máquina