Clear Sky Science · pt
Grafos de pangenoma impulsionados por montagem em fases para genotipagem de variantes estruturais e mapeamento de traços complexos em bovinos leiteiros
Por que a genética da vaca importa para o seu copo de leite
Vacas leiteiras são os motores invisíveis por trás do leite, do queijo e do iogurte. Ainda assim, mesmo dentro de uma única raça como as Holsteins, nenhum animal compartilha exatamente o mesmo DNA. Grande parte dessa variação oculta não vem de pequenas trocas de letras no genoma, mas de adições, deleções e rearranjos maiores de DNA. Este estudo mostra como um novo tipo de genoma de referência para bovinos, chamado grafo de pangenoma, pode capturar essa grande diversidade estrutural do DNA e conectá-la a traços importantes, como produção de leite, tamanho corporal, fertilidade e resistência a doenças.
Olhando além de um genoma “padrão” de vaca
Por anos, estudos genéticos em humanos e em animais de criação se apoiaram em um único genoma de referência como mapa. Essa abordagem funciona razoavelmente bem para mudanças de uma única letra no DNA, mas deixa de detectar muitas variantes estruturais maiores, que podem se estender por dezenas a milhões de bases. Essas alterações maiores são especialmente comuns em regiões difíceis de sequenciar, como trechos repetitivos próximos às extremidades dos cromossomos. Em bovinos, já se sabe que variantes estruturais afetam produção de leite, crescimento, reprodução e saúde, mas o sequenciamento tradicional por leituras curtas e mapas baseados em uma única referência deixam grande parte dessa variação invisível.
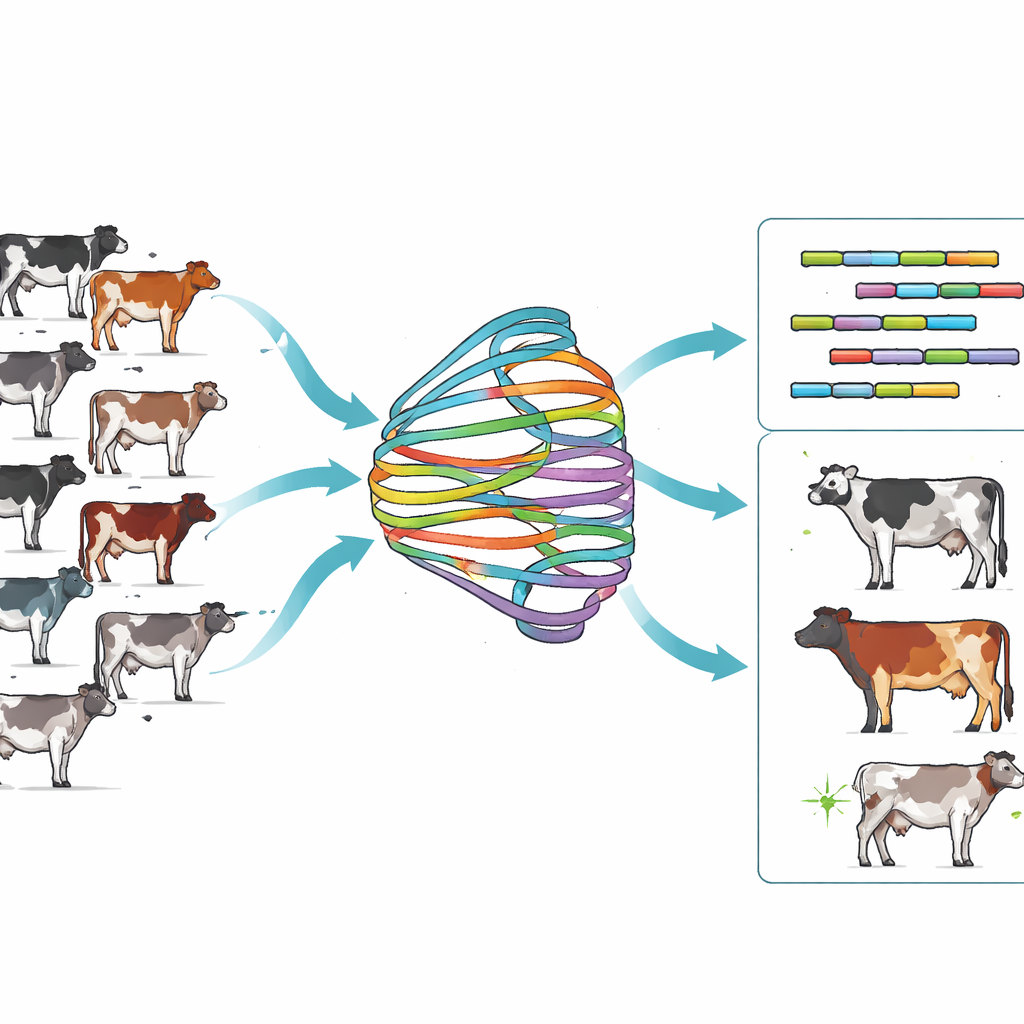
Construindo um mapa de DNA mais rico para bovinos Holstein
Os pesquisadores propuseram-se a construir um mapa genético muito mais completo para Holsteins, a raça leiteira dominante no mundo. Eles usaram sequenciamento por leituras longas para gerar 40 montagens de genomas haploides a partir de 20 vacas Holstein e então as combinaram com um método chamado Minigraph-Cactus para construir um grafo de pangenoma específico da raça, batizado de H20D. Em vez de uma sequência linear única de DNA, esse grafo contém um “núcleo” compartilhado pela maioria das vacas e várias ramificações alternativas que capturam inserções, deleções e rearranjos complexos. Cerca de 95% da sequência foi compartilhada entre todos os animais, mas os 5% restantes continham segmentos variáveis e até únicos que seriam ignorados em uma referência única. Ao comparar o H20D com um grafo de bovinos entre raças construído a partir de 13 raças, a equipe constatou que o grafo focado em Holstein era menos emaranhado, mas ainda rico em variação relevante para a raça, especialmente diferenças estruturais maiores e mais complexas.
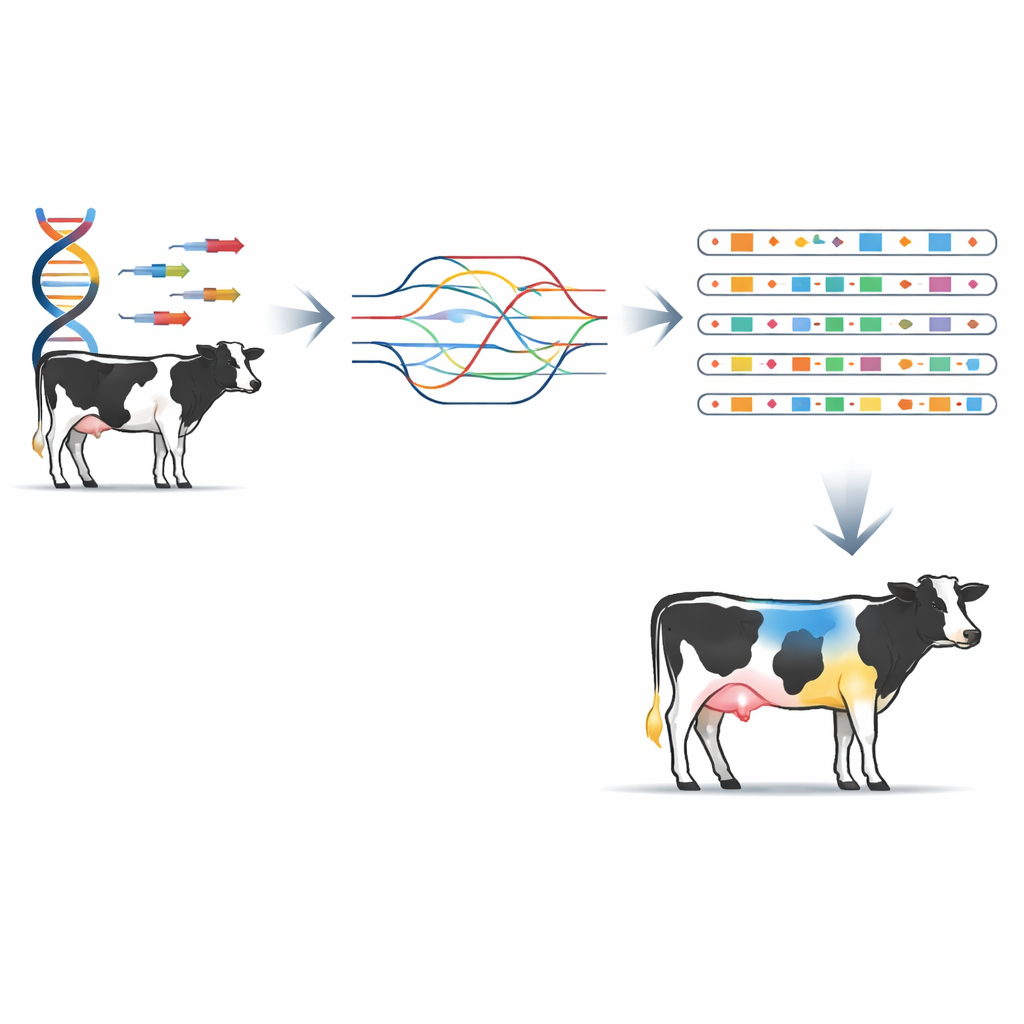
Encontrando variantes mais significativas, com mais precisão
Para testar se esse novo mapa realmente melhora a análise genética, os autores compararam chamadas de variantes estruturais baseadas no H20D com um conjunto de ferramentas populares que trabalham ou a partir de genomas montados ou diretamente de alinhamentos de leituras. Usando o pangenoma como referência, o grafo totalmente faseado e dentro da raça superou consistentemente tanto métodos de leituras longas quanto de leituras curtas isoladamente, identificando cerca de dez mil variantes estruturais adicionais por animal. Grafos diplóides (duas cópias) construídos a partir de montagens faseadas capturaram muito mais variantes e produziram genótipos mais precisos do que grafos construídos a partir de montagens únicas não faseadas. As vantagens foram mais fortes em regiões problemáticas ricas em repetições, onde outros métodos frequentemente discordavam ou falhavam. De forma crucial, quando a equipe usou o grafo H20D como referência para uma ferramenta de genotipagem por leituras curtas chamada PanGenie, foi possível recuperar uma grande fração das descobertas feitas com leituras longas — muito mais do que com chamadores tradicionais de variantes estruturais por leituras curtas.
Das estruturas de DNA aos traços reais no ambiente da produção leiteira
Com esse mapa estrutural detalhado, os pesquisadores então voltaram-se para animais reais e para traços produtivos. Eles genotiparam variantes estruturais em 173 bovinos Holstein com registros de desempenho extensos e conduziram estudos de associação em todo o genoma para 46 traços abrangendo produção de leite, conformação corporal, fertilidade, saúde e longevidade. Descobriram 196 associações significativas, envolvendo 135 variantes estruturais ligadas a 42 traços. Em muitas regiões genômicas, variantes estruturais concordaram com sinais conhecidos de uma única letra, mas exibiram suporte estatístico mais forte, sugerindo que podem estar mais próximas das causas biológicas reais. Por exemplo, uma deleção considerável que sobrepõe o gene MATN3 foi associada à estatura e pode alterar o desenvolvimento ósseo, enquanto uma inserção próxima ao gene EPPK1 em tecidos adiposo e cerebral foi associada à porcentagem de gordura do leite, indicando possíveis efeitos no metabolismo ou na secreção de gordura.
O que isso significa para rebanhos futuros
Este trabalho demonstra que grafos de pangenoma construídos a partir de montagens faseadas dentro de uma única raça podem ampliar muito nossa visão da genética bovina. Ao capturar variantes estruturais que referências padrão perdem e ligá-las diretamente a traços de importância econômica, esses mapas prometem decisões de melhor precisão na seleção genética. Na prática, isso pode significar selecionar touros e fêmeas não apenas com base em milhares de marcadores de uma letra, mas também considerando segmentos maiores de DNA que influenciam produção de leite, eficiência, saúde e resistência. À medida que o sequenciamento por leituras longas e as ferramentas de pangenoma se tornam mais acessíveis, abordagens semelhantes podem acelerar a melhoria genética em muitas espécies de produção, moldando rebanhos mais saudáveis e uma produção de laticínios mais sustentável.
Citação: Yang, L., Gao, Y., Kuhn, K.L. et al. Phased-assembly-driven pangenome graphs for structural variant genotyping and complex trait mapping in dairy cattle. Nat Commun 17, 2186 (2026). https://doi.org/10.1038/s41467-026-68807-4
Palavras-chave: pangenoma de bovinos, variantes estruturais, Holstein leiteiro, associação em todo o genoma, seleção de precisão