Clear Sky Science · pt
Mapeamento automatizado da progressão da forquilha de replicação do DNA em células humanas com ForkML
Por que acompanhar a velocidade de cópia do DNA importa
Cada vez que uma célula humana se divide, ela precisa copiar mais de três bilhões de letras de DNA de forma rápida e precisa. Se esse processo de cópia desacelera ou trava, pode haver danos ao genoma e contribuir para cânceres e distúrbios do desenvolvimento. Ainda assim, até agora os cientistas não dispunham de um método simples para observar exatamente quão rápido as “máquinas de copiar” individuais do DNA percorrem trechos específicos do genoma humano. Este artigo apresenta o ForkML, uma técnica nova que usa sequenciamento por nanopore e aprendizado de máquina para automatizar essa tarefa em escala sem precedentes.
Observando as máquinas de cópia da célula indiretamente
O DNA é duplicado por pequenas máquinas moleculares chamadas forquilhas de replicação, que se movem ao longo da dupla hélice formando novas fitas. O ForkML permite aos pesquisadores observar essas forquilhas indiretamente ao adicionar uma etiqueta química inócua, BrdU, no DNA recém-sintetizado em dois pulsos muito curtos separados por um intervalo de tempo fixo. Como o BrdU pode ser detectado em moléculas únicas por sequenciadores nanopore, os cientistas veem duas “faixas” marcadas em cada fita de DNA onde a forquilha passou durante os dois pulsos. Medindo a distância entre as faixas e dividindo pelo intervalo de tempo conhecido, eles podem calcular quão rápido cada forquilha se moveu naquela região do genoma. 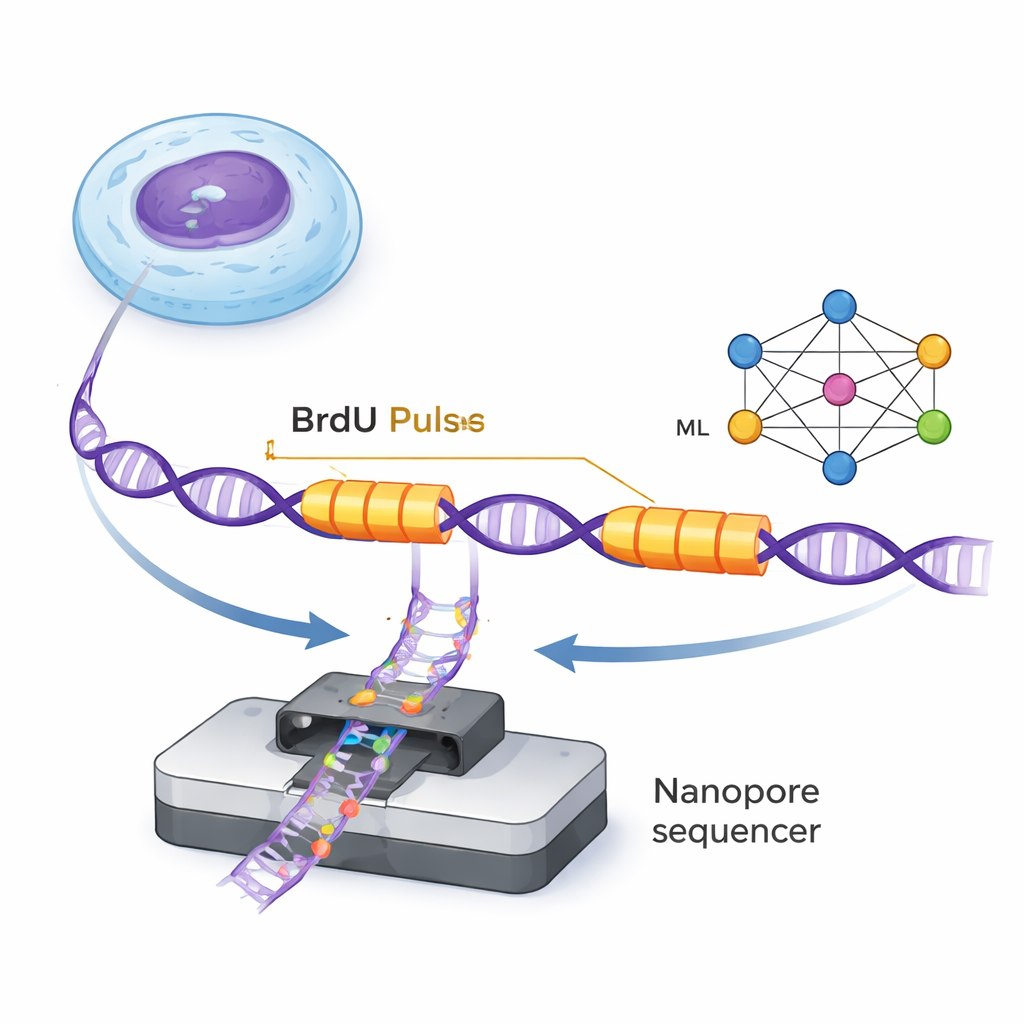
Ensinando um computador a ler as trilhas químicas
Em trabalhos anteriores com levedura, os autores conseguiam identificar essas trilhas de BrdU usando regras simples, mas em células humanas os sinais são mais fracos e complexos. Especialistas humanos ainda conseguem reconhecer o padrão característico—um aumento acentuado de BrdU quando o pulso começa, seguido por um declínio suave quando ele é lavado—mas fazer isso manualmente para milhões de fragmentos de DNA é impossível. O ForkML resolve esse problema treinando uma rede neural, uma forma de aprendizado de máquina, em milhares de exemplos anotados manualmente. O modelo aprende a classificar cada trecho de DNA como fundo ou como uma forquilha movendo-se para a direita ou para a esquerda, e a localizar com alta precisão o início de cada pulso de BrdU. Isso permite o mapeamento totalmente automatizado de milhares de velocidades individuais de forquilhas a partir de uma única corrida de sequenciamento.
Medindo estresse e diferenças ao longo do genoma
Ao aplicar o ForkML em uma linhagem celular de câncer colorretal humano, a equipe obteve mais de 2.000 medidas de velocidade de forquilhas por experimento e descobriu que a forquilha típica se move a cerca de 1,2 kilobases por minuto, consistente com métodos anteriores de menor rendimento. Quando trataram as células com fármacos conhecidos por retardar a replicação do DNA, o ForkML detectou claramente a desaceleração, comprovando que pode mensurar sensivelmente o estresse de replicação. Como cada forquilha é mapeada de volta à sua posição no genoma de referência, os autores puderam relacionar a velocidade a outras características, como o momento em que uma região normalmente replica durante o ciclo celular, quão compactado está seu DNA e quão ativamente ele é transcrito em RNA. 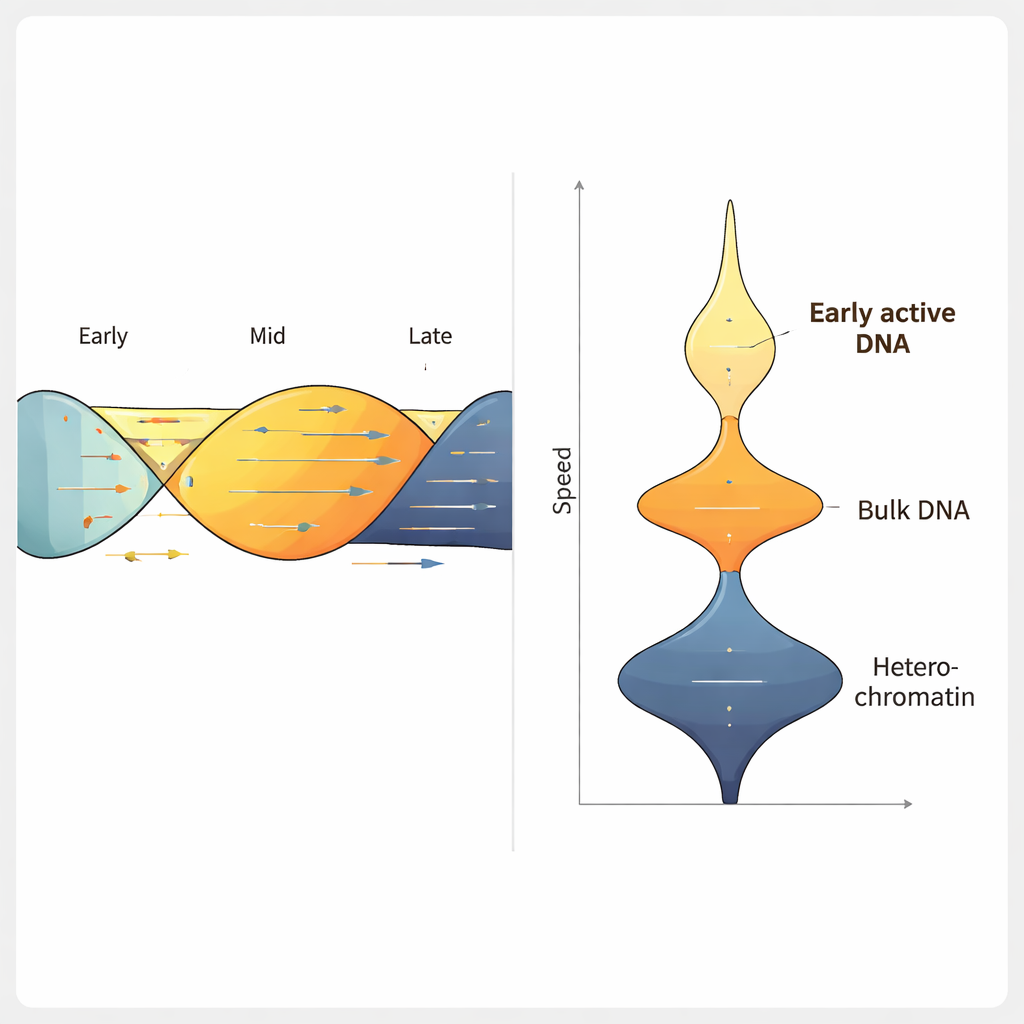
Revelando onde a cópia do DNA começa e como as fitas diferem
Além da velocidade, o ForkML também identifica onde a replicação do DNA começa e termina, ao detectar pontos em que forquilhas divergem ou convergem ao longo da mesma molécula. Mapeando mais de 20.000 desses locais de início, os autores confirmam que células humanas usam uma estratégia mista: algumas cópias começam em zonas de iniciação bem definidas, mas a maioria dos inícios está espalhada pelo genoma. Ao combinar a direção da forquilha com qual fita de DNA foi lida pelo sequenciador, o ForkML também pode distinguir as taxas de síntese da fita líder e da fita retardatária, algo que ensaios tradicionais baseados em fibras não conseguem fazer. Testes em seis diferentes linhagens celulares humanas—tanto normais quanto cancerosas—mostram que as mesmas condições simples de marcação com BrdU funcionam amplamente e fornecem estimativas robustas de velocidade em cada caso.
Uma atualização digital de uma técnica clássica
Para não especialistas, o ForkML pode ser visto como uma versão moderna e digital do clássico ensaio de fibras de DNA: usa um esquema de marcação semelhante, mas substitui a microscopia manual por sequenciamento de leitura longa e aprendizado de máquina. Isso traz um rendimento muito maior, a colocação direta de cada medida no genoma e informações mais detalhadas sobre onde e quão rapidamente o DNA é copiado. Como o protocolo é simples, compatível com o hardware nanopore atual e adaptável a outros organismos, o ForkML está pronto para se tornar uma ferramenta padrão no estudo da replicação do DNA. Em termos práticos, oferece aos pesquisadores uma maneira poderosa de vincular a velocidade local de cópia do DNA—normal ou sob estresse—a atividade gênica, ao estado da cromatina e a alterações relacionadas a doenças no genoma.
Citação: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
Palavras-chave: Replicação do DNA, velocidade da forquilha de replicação, sequenciamento por nanopore, marcação com BrdU, aprendizado de máquina em genômica