Clear Sky Science · pt
Análise genômica multipaís destaca a propagação regional da cólera na África
Por que rastrear germes além das fronteiras importa
A cólera ainda adoece e mata dezenas de milhares de pessoas por ano na África, mas perguntas básicas permanecem sobre como os surtos começam, se deslocam entre países e reaparecem. Este estudo reúne cientistas e equipes de saúde pública de sete nações africanas para rastrear a bactéria responsável pela cólera por meio da leitura de seu código genético. Ao comparar centenas de genomas bacterianos, os pesquisadores mostram como as ondas recentes de cólera cruzaram fronteiras, que tipos de cepas circulam em cada região e como esse conhecimento pode aprimorar os esforços para impedir futuras epidemias.
Uma visão continental da cólera
Para ir além de relatos de casos isolados, os Centros Africanos para Controle e Prevenção de Doenças lançaram uma colaboração chamada Consórcio de Genômica da Cólera na África (CholGEN). Laboratórios em Camarões, República Democrática do Congo, Malawi, Moçambique, Nigéria, Uganda e Zâmbia sequenciaram 763 genomas de alta qualidade do Vibrio cholerae O1, em sua maioria entre 2019 e 2024. Isso representa o maior conjunto de genomas de cólera já gerado dentro da própria África. Ao posicionar esses novos genomas ao lado de quase 1.800 amostras previamente sequenciadas da África e da Ásia, a equipe pôde reconstruir como os surtos africanos recentes se encaixam na longa pandemia global de cólera.
Cepas antigas, novas rotas
A análise mostrou que as cepas de cólera responsáveis pelos surtos atuais na África não representam uma ameaça inteiramente nova. Em vez disso, todas as bactérias recém-sequenciadas descendem de introduções já conhecidas da linhagem da sétima pandemia da cólera, que chegou à África vindas da Ásia em 1970. Países da África Ocidental e Central, como Nigéria, Camarões e República Democrática do Congo, tendem a ser dominados por uma ou duas linhagens de longa duração que persistem por décadas. Países do Leste e do Sul da África, por outro lado, abrigam uma mistura de várias linhagens ao mesmo tempo. Uma linhagem em particular, denominada AFR15, espalhou-se rapidamente nos últimos anos e está ligada a surtos incomumente grandes no Malawi, Zâmbia e países vizinhos, além de epidemias em partes do Oriente Médio e do Sul da Ásia.
Quando o tamanho dos surtos não está nos genes
Poder-se-ia supor que a propagação explosiva da AFR15 se deva a mudanças genéticas importantes que a tornam mais perigosa ou mais capaz de escapar ao tratamento. No entanto, quando os pesquisadores compararam a taxa e o padrão de mutações entre várias linhagens ativas, não encontraram diferenças marcantes. As bactérias evoluíam em velocidades semelhantes, e os tipos de mutações e os genes afetados eram muito parecidos de uma linhagem para outra. Os perfis gerais de genes de resistência a antibióticos também permaneceram em grande parte estáveis ao longo do tempo e entre países. A exceção principal foi em Uganda, onde bactérias adquiriram um grande elemento de DNA móvel chamado plasmídeo, que carrega múltiplos genes de resistência, provavelmente importado junto com cepas ligadas a surtos no Iêmen e no Líbano. Ainda assim, o estudo não identificou novos genes que, por si só, expliquem a gravidade dos surtos africanos recentes.
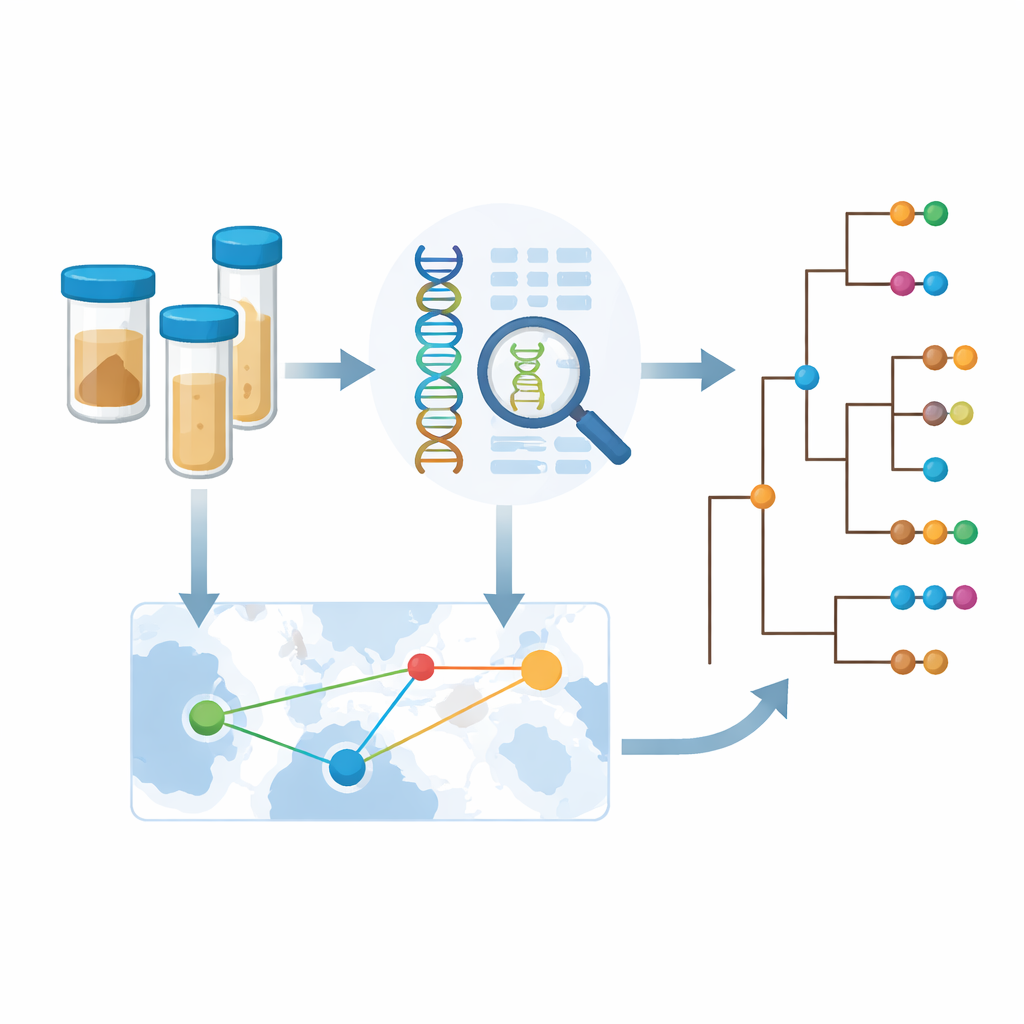
Jornadas ocultas reveladas por amostragem melhor
Como os genomas bacterianos carregam um registro de onde cepas estreitamente relacionadas foram encontradas, a equipe pôde inferir com que frequência a cólera cruza fronteiras. Eles detectaram muitos exemplos de disseminação internacional entre países vizinhos, incluindo trocas repetidas entre Zâmbia e República Democrática do Congo. No entanto, ao olhar mais de perto, viram que os sinais estatísticos de saltos transfronteiriços eram mais fortes em anos e locais com amostragem intensiva. Isso sugere que os movimentos reais da cólera são mais frequentes do que os dados atuais revelam; muitos eventos de transmissão provavelmente passam despercebidos simplesmente porque ninguém está sequenciando bactérias nesses locais ou períodos. Para enfrentar isso, os autores desenvolveram uma estrutura para estimar quanto de informação nova um país ganha ao sequenciar amostras adicionais, equilibrando diversidade genética, número de introduções e dados existentes.
Usando a genômica para orientar esforços de controle mais inteligentes
O estudo conclui que, para a cólera na África hoje, como e onde a doença se espalha importa mais do que qualquer mudança dramática na própria bactéria. As descobertas defendem a vigilância genômica rotineira e coordenada regionalmente, para que países vizinhos possam detectar surtos compartilhados cedo, rastrear suas fontes e direcionar intervenções como campanhas de vacinação, melhorias em água e saneamento e respostas em áreas de fronteira com mais eficiência. Ao construir capacidade de sequenciamento em laboratórios de saúde pública africanos e compartilhar dados entre países, iniciativas como o CholGEN oferecem um roteiro prático para usar a genética moderna na aproximação da meta ambiciosa de eliminar a cólera como ameaça à saúde pública até 2030.
Citação: Mboowa, G., Matteson, N.L., Tanui, C.K. et al. Multicountry genomic analysis underscores regional cholera spread in Africa. Nat Commun 17, 2539 (2026). https://doi.org/10.1038/s41467-026-68642-7
Palavras-chave: cólera, vigilância genômica, África, transmissão transfronteiriça, resistência antimicrobiana