Clear Sky Science · pt
Um decodificador de bases consciente do contexto duplo para sequenciamento direto de RNA por nanopore
Por que decodificar as letras do RNA importa
Cada célula do seu corpo está constantemente lendo e reescrevendo mensagens escritas em RNA, a cópia de trabalho dos nossos genes. Novas máquinas “nanopore” podem ler moléculas individuais de RNA diretamente, prometendo revelar como genes são ativados, como os RNAs são emendados e como marcas químicas no RNA influenciam saúde e doença. Mas há um problema: esses dispositivos medem correntes elétricas muito pequenas, que precisam ser traduzidas — “basecalled” — nas familiares letras A, C, G e U. Se essa tradução estiver errada, a história biológica que inferimos pode ficar seriamente distorcida. Este artigo apresenta o Coral, um novo sistema de inteligência artificial que torna essa tradução muito mais precisa.
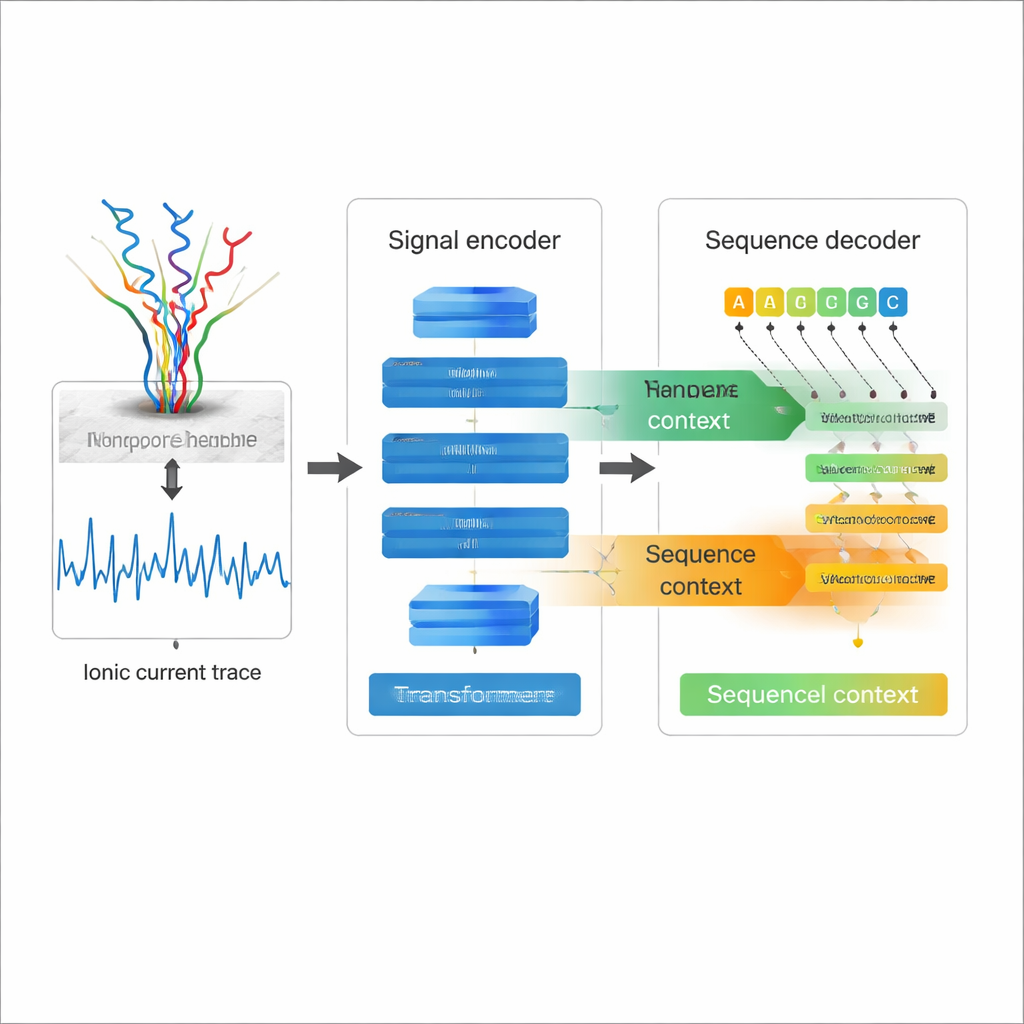
Lendo eletricidade em vez de letras
O sequenciamento direto de RNA por nanopore funciona passando uma única fita de RNA por um buraco molecular — um nanopore — enquanto se mede como a corrente elétrica muda à medida que cada nucleotídeo passa. Esses traçados de corrente ondulados contêm a informação sobre a sequência de RNA e suas modificações químicas. O sequenciamento tradicional de RNA converte o RNA em DNA e o amplifica, etapas que podem introduzir viés e apagar muitas marcas químicas naturais. O sequenciamento direto de RNA evita esses problemas, mas o preço tem sido uma taxa de erro relativamente alta ao transformar traçados de corrente em sequências, especialmente para recursos desafiadores como bases repetidas e estruturas complexas de RNA. Um basecalling melhor é essencial se os cientistas quiserem confiar nos detalhes finos dessas longas leituras de RNA.
Um tradutor mais inteligente que usa dois tipos de contexto
A maioria dos basecallers de nanopore existentes trata o sinal elétrico como a principal fonte de informação e decodifica cada posição quase de forma independente, o que limita o quanto podem aproveitar a estrutura da própria sequência de RNA. O Coral segue uma abordagem diferente. Ele usa uma arquitetura codificador–decodificador baseada em Transformer, similar em espírito aos modelos de linguagem modernos. Primeiro, uma rede codificadora construída com convoluções e camadas de self‑attention processa o sinal de corrente bruto em uma descrição compacta de como o sinal varia ao longo do tempo. Em seguida, um decodificador prevê cada nova base de RNA um passo por vez, olhando simultaneamente para trás, nas bases que já escreveu, e lateralmente, para o sinal codificado. Dois tipos de atenção — dentro da sequência de RNA em crescimento e entre sequência e sinal — permitem que o Coral pese tanto o contexto elétrico quanto o contexto da sequência ao decidir qual letra vem a seguir.
Sequências mais nítidas e menos moléculas perdidas
Os autores testaram o Coral contra vários basecallers de ponta, incluindo ferramentas comerciais da Oxford Nanopore, em RNA de humanos e outros organismos e em múltiplas químicas de nanopore. Ao longo de seis espécies e kits de sequenciamento de RNA mais antigos, o Coral obteve uma precisão mediana típica de leitura em torno de 97%, claramente superior aos métodos concorrentes. Com o kit de RNA mais recente, sua precisão ultrapassou 99%. O Coral produziu menos discordâncias, inserções e deleções, e gerou leituras mais longas e melhor alinhadas, com menos sequências que não puderam ser mapeadas. Foi especialmente eficaz no tratamento de curtas séries de bases repetidas — muito comuns em dados reais — que são uma fonte frequente de erros para outras ferramentas. Ao capturar de forma mais confiável trechos mais longos de sequência correta, o Coral também se destacou na predição de padrões de sequência curtos (k‑mers) e permaneceu robusto mesmo quando etapas anteriores de decodificação continham pequenos erros.
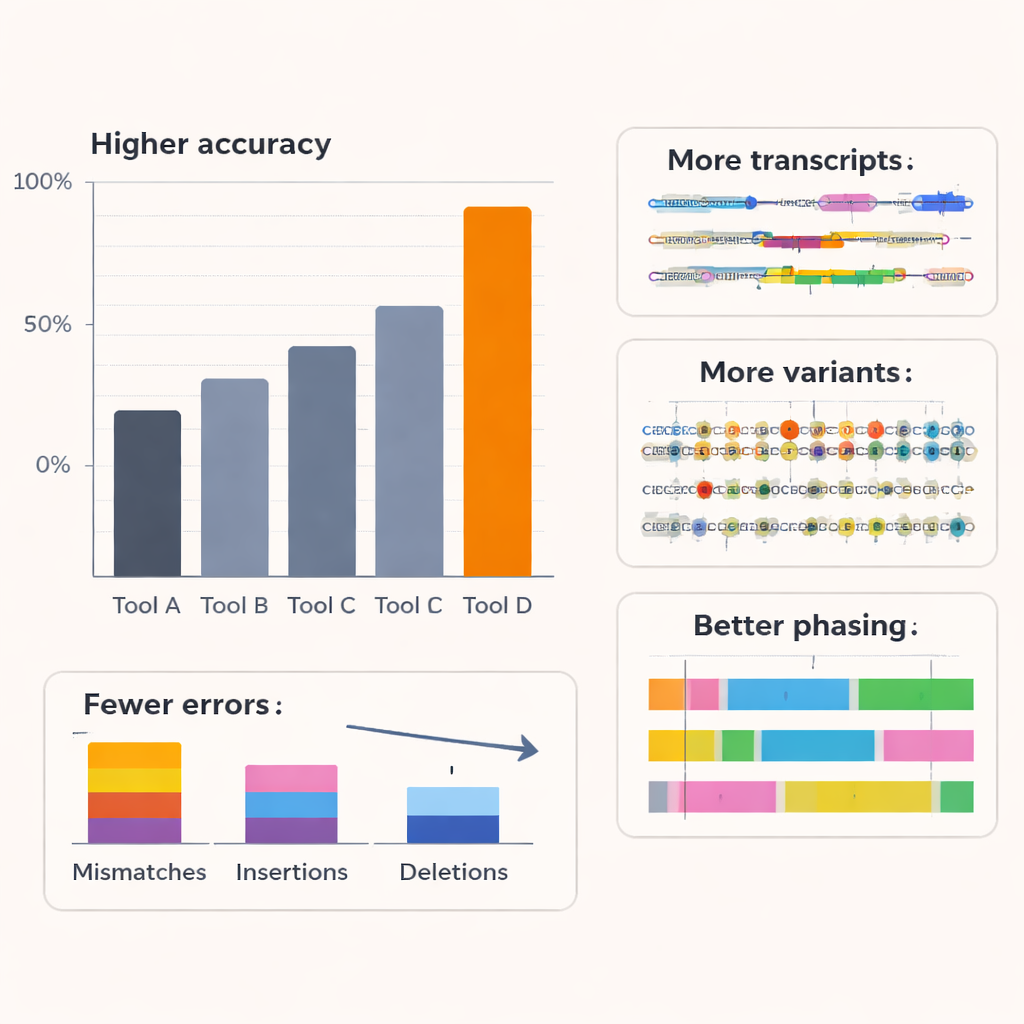
Vendo mais detalhes ocultos do transcriptoma
Melhorar o basecalling só é valioso se levar a biologia melhor. Para testar isso, a equipe examinou como a saída do Coral afetou análises a jusante em linhagens celulares humanas. Usando uma ferramenta especializada para reconstruir isoformas completas de RNA — as diferentes versões emendadas de cada gene — eles descobriram que as leituras do Coral expuseram mais estruturas de transcritos conhecidas e muitas isoformas adicionais de baixa abundância que outros basecallers perderam. Muitos transcritos específicos do Coral foram suportados por dados independentes de leituras curtas, indicando que são reais em vez de artefatos. O Coral também detectou mais transcritos de referência artificiais com concentrações conhecidas em um experimento spike‑in e estimou sua abundância com mais precisão. Além da descoberta de transcritos, o Coral melhorou a detecção de eventos de fusão gênica em uma linha celular de câncer de mama e aumentou o número e a confiabilidade de genes mostrando expressão alelo‑específica, onde uma cópia parental do gene é mais ativa que a outra.
Variantes genéticas mais claras e linhagens familiares
Porque leituras longas de RNA podem cobrir variantes genéticas distantes, elas são ferramentas poderosas para determinar quais variantes viajam juntas na mesma cópia do cromossomo — um processo chamado faseamento de haplótipos. Usando uma amostra humana bem estudada com um mapa de variantes padrão‑ouro, os autores mostraram que as leituras de maior qualidade do Coral levaram a uma detecção mais precisa de mudanças de nucleotídeo único e a muito menos erros de faseamento: erros de troca e taxas gerais de discordância dentro de blocos faseados caíram em até cerca de três quartos em comparação com outros métodos, enquanto substancialmente mais variantes puderam ser faseadas. Estudos de simulação variando a precisão das leituras confirmaram que, uma vez que o basecalling se aproxima de cerca de 95% de precisão, o desempenho na descoberta de transcritos, expressão alelo‑específica e faseamento melhora acentuadamente e depois se estabiliza. O Coral está nessa zona de alto benefício, sugerindo que captura a maior parte da informação biologicamente relevante presente nos sinais ruidosos de nanopore.
O que isso significa para pesquisas futuras em RNA
Para não‑especialistas, a mensagem principal é que o Coral age como um tradutor muito mais confiável entre a linguagem elétrica dos sequenciadores de nanopore e a linguagem genética do RNA. Ao usar melhor o contexto tanto no sinal quanto na sequência em crescimento, ele produz leituras mais limpas que revelam mais variantes de transcritos, detectam genes de fusão raros e acompanham com mais confiança quais variantes vêm de qual progenitor. O software é de código aberto, de modo que pesquisadores podem adaptá‑lo a novos organismos, químicas ou mesmo para estudar marcas químicas no próprio RNA. À medida que a tecnologia de nanopore continua a melhorar, ferramentas como o Coral ajudarão a transformar traçados de corrente bruta em mapas confiáveis e detalhados do mundo do RNA dentro das células.
Citação: Xie, S., Ding, L., Yu, Y. et al. A dual context-aware basecaller for nanopore direct RNA sequencing. Nat Commun 17, 1851 (2026). https://doi.org/10.1038/s41467-026-68566-2
Palavras-chave: sequenciamento de RNA por nanopore, basecalling, modelo Transformer, isoformas de transcritos, faseamento de haplótipos