Clear Sky Science · pt
Descoberta em todo o genoma e fenotipagem de transcritos não codificantes em A. fumigatus revela lncRNAs com papel na sensibilidade a antifúngicos
Por que um bolor em nossas casas importa
A maioria de nós pensa em bolor como um incômodo no pão ou em cantos úmidos, mas um bolor comum, Aspergillus fumigatus, é responsável por mais de dois milhões de mortes a cada ano — mais do que malária e HIV juntos. Os médicos contam com um arsenal estreito de antifúngicos para controlar esse patógeno, e a resistência a esses medicamentos está aumentando rapidamente. Este estudo explora uma camada oculta do genoma do fungo — os RNAs longos não codificantes, ou lncRNAs — que não produzem proteínas, mas ainda podem influenciar como o fungo responde ao tratamento. Compreender esses elementos genéticos “silenciosos” pode abrir novas formas de prever, rastrear e, eventualmente, combater a resistência aos antifúngicos.
Mensagens escondidas no DNA fúngico
Classicamente, os genes eram vistos como trechos de DNA que codificam proteínas, as máquinas da célula. Na última década, os cientistas descobriram que vastas regiões do genoma são transcritas em moléculas de RNA que nunca viram proteínas. Esses RNAs longos não codificantes ainda podem afetar o comportamento das células, inclusive sua resposta a fármacos. Embora lncRNAs tenham sido mapeados em humanos e em leveduras, eles eram em grande parte inexplorados em bolores causadores de doença, como A. fumigatus. Os autores decidiram mudar isso construindo um catálogo em todo o genoma desses transcritos misteriosos e investigando se algum deles inclina a balança entre sensibilidade e resistência a medicamentos.
Ouvindo o fungo sob ataque de fármacos
Para descobrir lncRNAs, a equipe expôs A. fumigatus a seis compostos antifúngicos diferentes, incluindo azóis amplamente usados que miram a membrana celular fúngica, e então sequenciou todos os RNAs produzidos. Usando um pipeline bioinformático personalizado, montaram dezenas de milhares de transcritos e eliminaram sistematicamente qualquer coisa correspondente a genes codificadores de proteínas conhecidos ou a pequenos RNAs de manutenção. Após múltiplas rodadas de filtragem e curadoria manual, chegaram a um conjunto de alta confiança de 1.089 novos RNAs longos não codificantes espalhados pelo genoma. A maioria situava‑se entre genes conhecidos ou os sobrepunha na direção oposta, e juntos eles ampliaram a fração do genoma fúngico conhecida por ser ativamente transcrita de cerca de dois terços para mais de quatro quintos.
Respostas coordenadas e pontos quentes conservados
Quando os pesquisadores compararam como esses lncRNAs mudavam sob diferentes doses de fármacos, descobriram que o fungo não os emprega aleatoriamente. Em vez disso, os lncRNAs se agruparam em cerca de 15 padrões de resposta distintos, alguns compartilhados entre vários medicamentos e outros únicos para tratamentos específicos. Por exemplo, fármacos que atingem vias bioquímicas semelhantes tendiam a desencadear assinaturas de lncRNA sobrepostas, enquanto um inibidor da síntese proteica produziu muitas respostas únicas. Muitos lncRNAs ficavam muito próximos de genes já conhecidos por influenciar a sensibilidade a azóis, como aqueles envolvidos na captação de ferro ou na biossíntese de ergosterol, um componente-chave das membranas fúngicas. Em vários casos, um lncRNA próximo e um gene de resposta a fármacos eram regulados para cima ou para baixo em conjunto, sugerindo que esses elementos não codificantes podem ajudar a coordenar programas cruciais de sobrevivência.
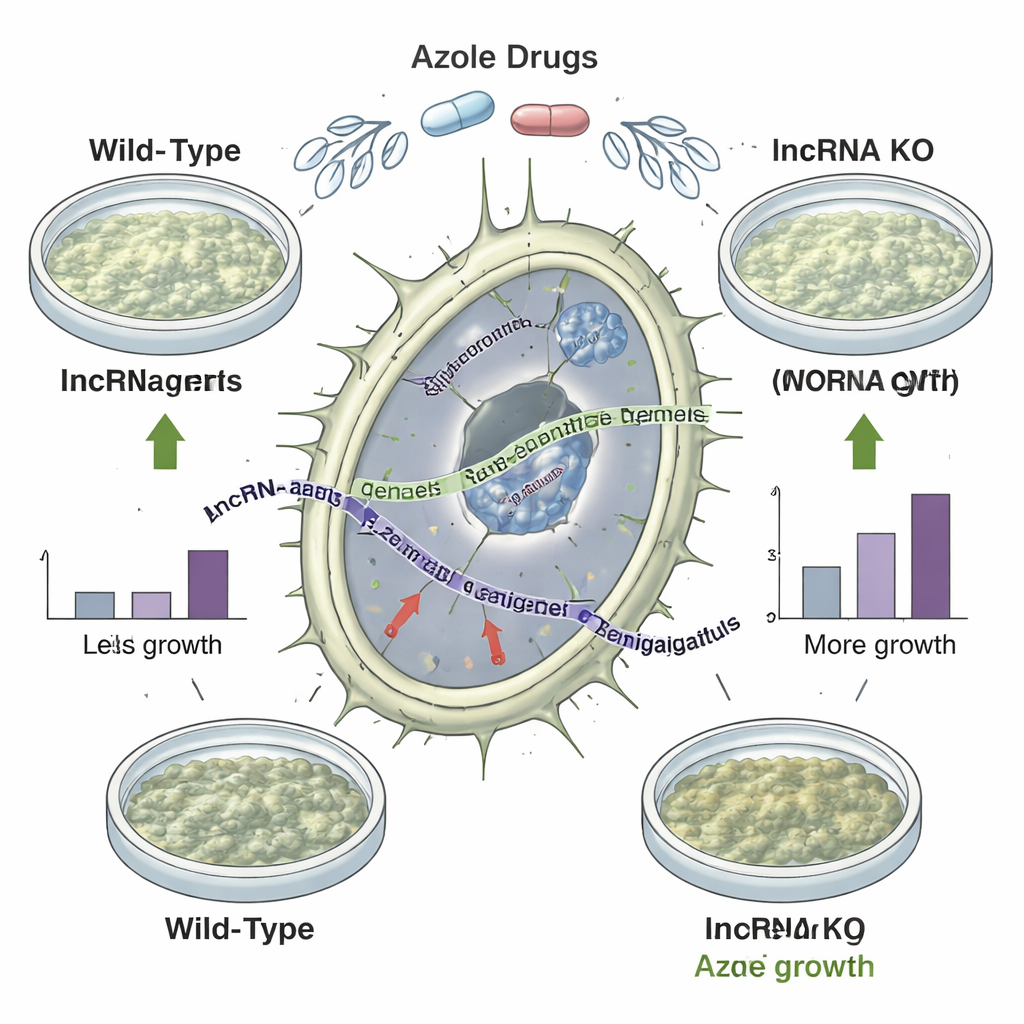
Eliminar “genes silenciosos” altera a sensibilidade a fármacos
Catalogar lncRNAs é uma coisa; provar que eles importam é outra. A equipe deletou 92 regiões lncRNA selecionadas do genoma do fungo e comparou como os mutantes cresciam sob uma variedade de estresses, incluindo alta temperatura, baixo ferro e exposição a três azóis diferentes. Sessenta mutantes mostraram mudanças de aptidão específicas por condição, e 35 cresceram na verdade melhor do que a cepa original quando desafiadas com azóis. Uma linhagem de deleção de destaque exibiu crescimento aprimorado em todos os azóis testados sem simplesmente aumentar genes codificadores de proteínas próximos, sugerindo fortemente que o lncRNA ausente em si restringia a tolerância ao fármaco. Ao examinar muitas amostras clínicas e ambientais com perfis de suscetibilidade a drogas conhecidos, os autores também verificaram que a presença ou ausência de certos genes lncRNA acompanhava a facilidade com que cada linhagem era inibida por azóis.
O que isso significa para combater infecções fúngicas letais
Para não especialistas, a mensagem principal é que partes do genoma fúngico antes descartadas como “lixo” estão ativamente moldando o quão perigoso A. fumigatus pode ser e quão bem nossos medicamentos funcionam contra ele. Ao construir o primeiro mapa abrangente de RNAs longos não codificantes neste importante patógeno e vincular dezenas deles a mudanças mensuráveis na resposta a fármacos, este trabalho abre uma nova classe de marcadores genéticos e potenciais alvos. A longo prazo, lncRNAs podem ajudar a explicar por que algumas linhagens são naturalmente mais difíceis de tratar, orientar o desenvolvimento de diagnósticos mais eficazes e inspirar terapias que desarmem a resistência não matando o fungo diretamente, mas silenciando os reguladores silenciosos que o ajudam a sobreviver.
Citação: Weaver, D., Qi, T., Chown, H. et al. Genome-wide discovery and phenotyping of non-coding transcripts in A. fumigatus reveals lncRNAs with a role in antifungal drug sensitivity. Nat Commun 17, 1832 (2026). https://doi.org/10.1038/s41467-026-68543-9
Palavras-chave: Aspergillus fumigatus, resistência a antifúngicos, RNA longo não codificante, fármacos azóis, genômica fúngica