Clear Sky Science · pt
Identificação de peptídeos antimicrobianos a partir de microbiomas intestinais antigos
Escavando pistas antigas para combater germes modernos
À medida que a resistência a antibióticos aumenta no mundo todo, os médicos estão ficando sem opções para tratar infecções perigosas. Este estudo adota uma abordagem incomum para o problema: ele não recorre a laboratórios de química high-tech, mas às amostras fossilizadas de fezes humanas — "cápsulas do tempo" intestinais antigas — para descobrir moléculas naturais que combatem germes e que podem ainda ser eficazes contra as bactérias de hoje.
Micróbios antigos como armários de remédios ocultos
Muito antes da medicina moderna, o intestino humano já era um campo de batalha onde micróbios benéficos e germes invasores competiam por espaço e alimento. Muitas bactérias intestinais amigas produzem peptídeos antimicrobianos — fragmentos curtos de proteína que perfuram células bacterianas ou as desabilitam de outras maneiras. A pesquisa moderna tem buscado principalmente esses peptídeos em microbiomas contemporâneos. Mas nossas comunidades intestinais atuais evoluíram junto com o uso de antibióticos e estilos de vida modernos, dando às bactérias nocivas muitas oportunidades de desenvolver resistência. Em contraste, comunidades intestinais antigas, preservadas em fezes secas chamadas coprólitos, formaram-se em um mundo sem antibióticos prescritos. Isso as torna uma fonte promissora de defesas "esquecidas" que os patógenos modernos talvez ainda não tenham aprendido a evitar.
Uma ferramenta de IA leve para ler DNA fossilizado
Para explorar essa farmácia antiga, os pesquisadores construíram uma nova ferramenta computacional chamada AMPLiT (AMP Lightweight Identification Tool). Em vez de depender de supercomputadores, o AMPLiT roda de forma eficiente em um laptop comum mantendo alta precisão. Ele varre enormes conjuntos de dados de DNA de amostras de microbioma e sinaliza sequências curtas que provavelmente codificam peptídeos antimicrobianos. A equipe afinou o projeto do AMPLiT para que ele pudesse processar milhões de fragmentos de DNA danificado, com séculos de idade, em questão de horas, reduzindo o tempo de treinamento em cerca de 80% em comparação com métodos anteriores, sem perder desempenho próximo ao estado da arte na identificação de candidatos prováveis a matar germes.
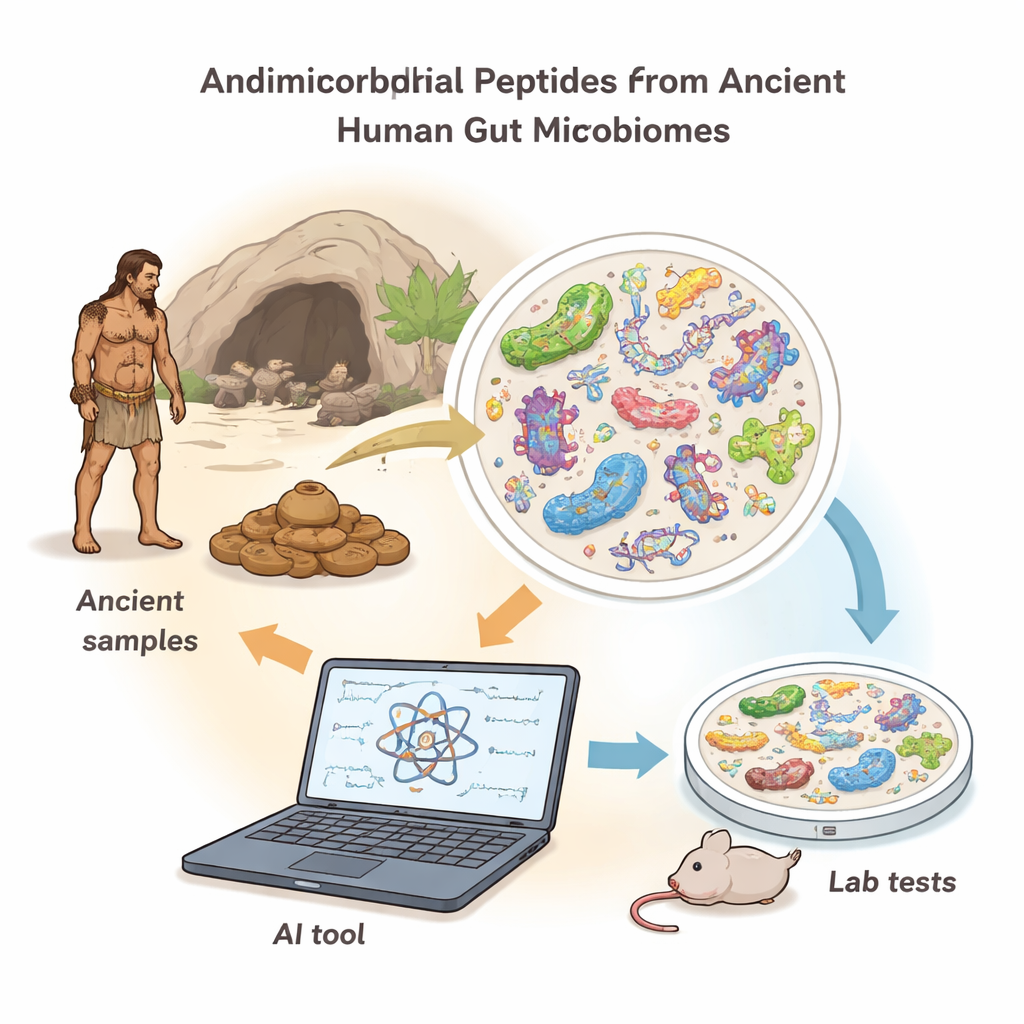
Ressuscitando matadores de germes de um habitante intestinal antigo
Usando o AMPLiT, os cientistas examinaram DNA intestinal de sete humanos antigos que viveram há 1.000–2.000 anos na América do Norte. Após remover contaminações ambientais e focar em comprimentos curtos e práticos de peptídeos, a ferramenta previu centenas de milhares de possíveis sequências antimicrobianas. Uma série mais rigorosa de filtros — presença em múltiplos indivíduos, propriedades químicas e baixa toxicidade prevista — reduziu isso a 41 candidatos de alta confiança, dos quais 40 puderam ser sintetizados quimicamente em laboratório. Quando testados contra bactérias "Gram-positivas" e "Gram-negativas" (dois grandes grupos que incluem muitos patógenos comuns), 36 dos 40 peptídeos retardaram ou interromperam o crescimento bacteriano em doses relativamente baixas, uma taxa de sucesso incomumente alta para esse tipo de descoberta.
A estrela surpreendente: um aliado intestinal em extinção
Cerca de dois terços dos peptídeos mais ativos provinham de uma única bactéria intestinal: Segatella copri, um parente próximo de um micro-organismo anteriormente classificado como Prevotella copri. Essa espécie era abundante em intestinos antigos e ainda é comum em pessoas com dietas mais tradicionais e menos industrializadas, mas agora é rara em muitas populações urbanas ocidentais. Ao traçar onde os genes dos peptídeos ficam no genoma de Segatella, a equipe descobriu que a maioria são na verdade fragmentos de genes maiores, do tipo "housekeeping", que o micróbio aparentemente reutilizou como armas — um truque evolutivo eficiente. Muitos desses peptídeos antigos parecem bem diferentes dos presentes em bancos de dados modernos, sugerindo que representam projetos químicos genuinamente novos, e não apenas variações menores de antibióticos conhecidos.
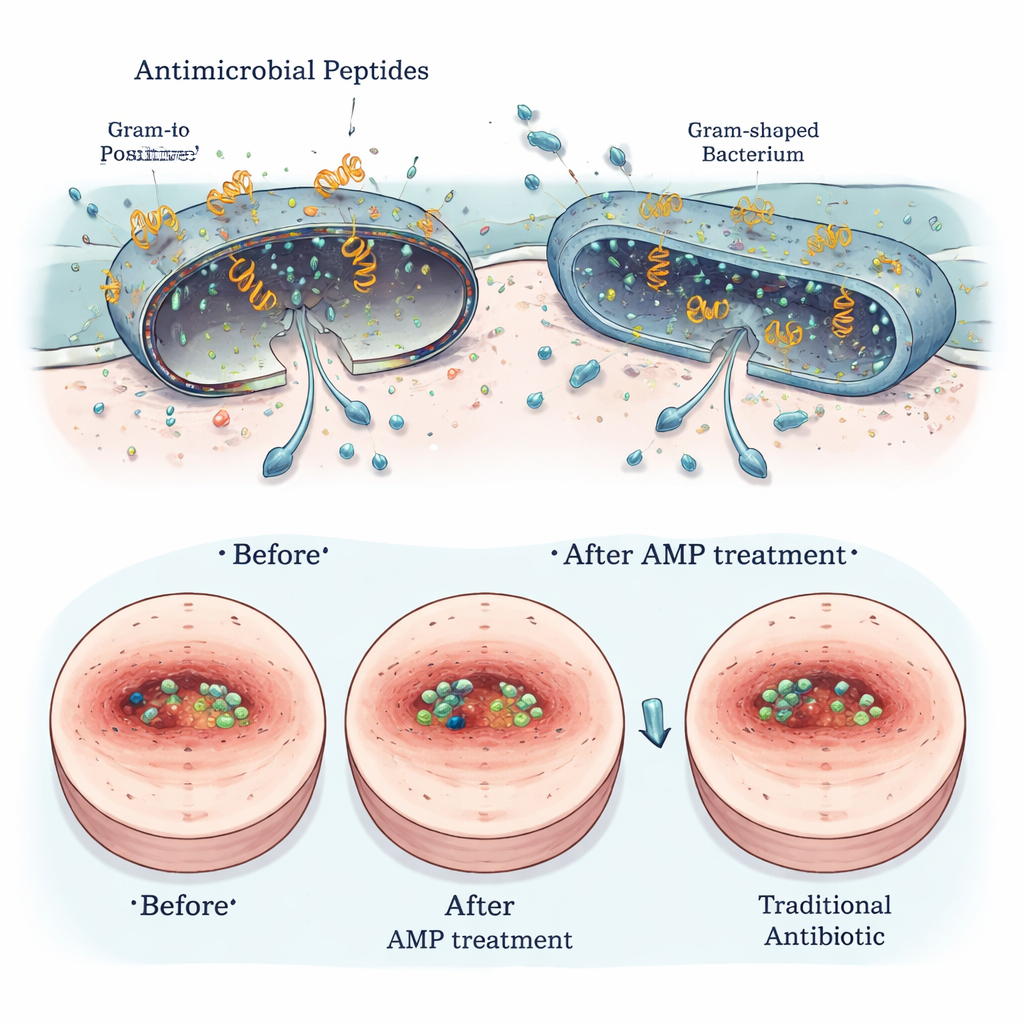
Seguros para hospedeiros, duros com germes — e promissores em feridas
Vários dos peptídeos de Segatella mais promissores foram testados quanto à segurança e utilidade no mundo real. Em placas de laboratório, eles causaram pouco ou nenhum dano às hemácias e apenas efeitos leves, se houver, em células semelhantes às intestinais humanas. Microscopia de alta resolução mostrou que os peptídeos desestruturaram fisicamente as membranas externas das bactérias nocivas, poupando células de mamíferos. Em modelos de feridas infectadas em roedores, peptídeos selecionados aplicados na pele reduziram a carga bacteriana, aceleraram o fechamento da ferida e reduziram sinais de inflamação, com desempenho comparável a antibióticos estabelecidos como vancomicina e polimixina B, especialmente contra bactérias Gram-positivas como Staphylococcus aureus.
O que isso significa para futuros medicamentos
Para um não-especialista, a mensagem é direta: os micróbios intestinais de nossos antepassados podem conter projetos para novos antibióticos que ainda funcionam contra infecções difíceis de tratar hoje. Este estudo mostra que, com ferramentas de IA inteligentes e eficientes como o AMPLiT, os cientistas podem minerar DNA antigo em busca de peptídeos antimicrobianos que sejam potentes e relativamente suaves para células humanas. Embora muitos passos ainda sejam necessários antes que qualquer uma dessas moléculas vire medicamento, o trabalho sugere que reviver parceiros microbianos "perdidos" como Segatella copri — ou pelo menos emprestar suas armas moleculares — pode ajudar a reabastecer nosso arsenal em encolhimento contra bactérias resistentes.
Citação: Chen, S., Yuan, Y., Wang, Y. et al. Identification of antimicrobial peptides from ancient gut microbiomes. Nat Commun 17, 1788 (2026). https://doi.org/10.1038/s41467-026-68495-0
Palavras-chave: peptídeos antimicrobianos, microbioma antigo, Segatella copri, resistência a antibióticos, mineração metagenômica