Clear Sky Science · pt
Modificação de DNA por fosforotioato por sistemas BREX tipo 4 no microbioma intestinal humano
Ajustes Químicos Ocultos nas Nossas Bactérias Intestinais
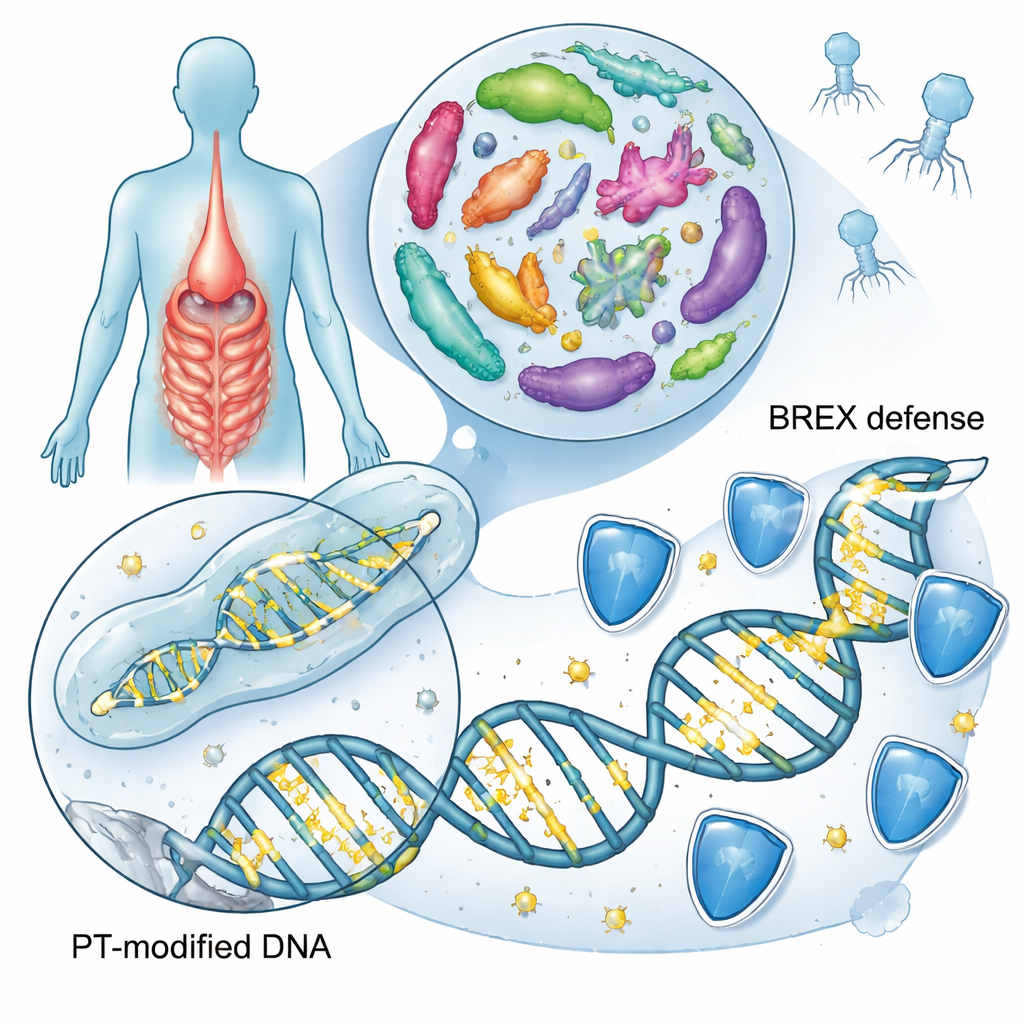
No interior do intestino humano, trilhões de bactérias estão constantemente trocando genes, combatendo vírus e reagindo à química do que comemos. Este estudo revela que muitas desses micróbios silenciosamente reescrevem a espinha dorsal de seu próprio DNA ao substituir átomos de oxigênio por enxofre, criando uma marca especial chamada fosforotioato. O trabalho desvenda uma nova versão desse sistema, ligada a um conjunto de defesa bacteriana chamado BREX tipo 4, e explora quão difundidas essas marcas de enxofre são em bactérias intestinais que podem influenciar a saúde e a doença.
Um Tipo Diferente de Marca no DNA
A maioria das pessoas já ouviu falar das letras do DNA—A, T, C e G—sendo modificadas por pequenas etiquetas químicas como grupos metil, parte central da epigenética. Aqui, o foco é algo muito mais radical: algumas bactérias substituem um dos átomos de oxigênio na própria espinha dorsal do DNA por enxofre. Essa edição da espinha dorsal, conhecida como fosforotioação, altera o comportamento do DNA sem modificar o código genético. Estudos anteriores haviam mostrado duas principais famílias de genes, chamadas dnd e ssp, que instalam essas marcas de enxofre em cerca de uma em cada dez espécies bacterianas e arqueanas. Essas marcas ajudam as bactérias a reconhecer seu próprio DNA, repelir vírus invasores chamados fagos e potencialmente responder ao estresse oxidativo e à inflamação.
Buscando em Milhares de Genomas Intestinais
Para saber quão comum é o DNA marcado com enxofre em nossos intestinos, os pesquisadores vasculharam 13.663 genomas bacterianos provenientes de três grandes coleções de micróbios humanos intestinais. Eles caçaram assinaturas genéticas chave suficientes para construir marcas de enxofre: conjuntos de genes dnd, ssp ou um novo conjunto candidato chamado brx, que faz parte do BREX, um sistema anti-fago conhecido. Cerca de 6,3% dos genomas intestinais carregavam pelo menos um desses sistemas, principalmente nos grupos comuns do intestino Bacteroidota, Bacillota e Pseudomonadota. Em comparação com um catálogo mais amplo de bactérias de muitos ambientes, o intestino mostrou um enriquecimento claro da versão BREX tipo 4, sugerindo que essa defesa baseada em enxofre é especialmente favorecida no ecossistema intestinal.
Um Novo Sistema de Defesa Baseado em Enxofre
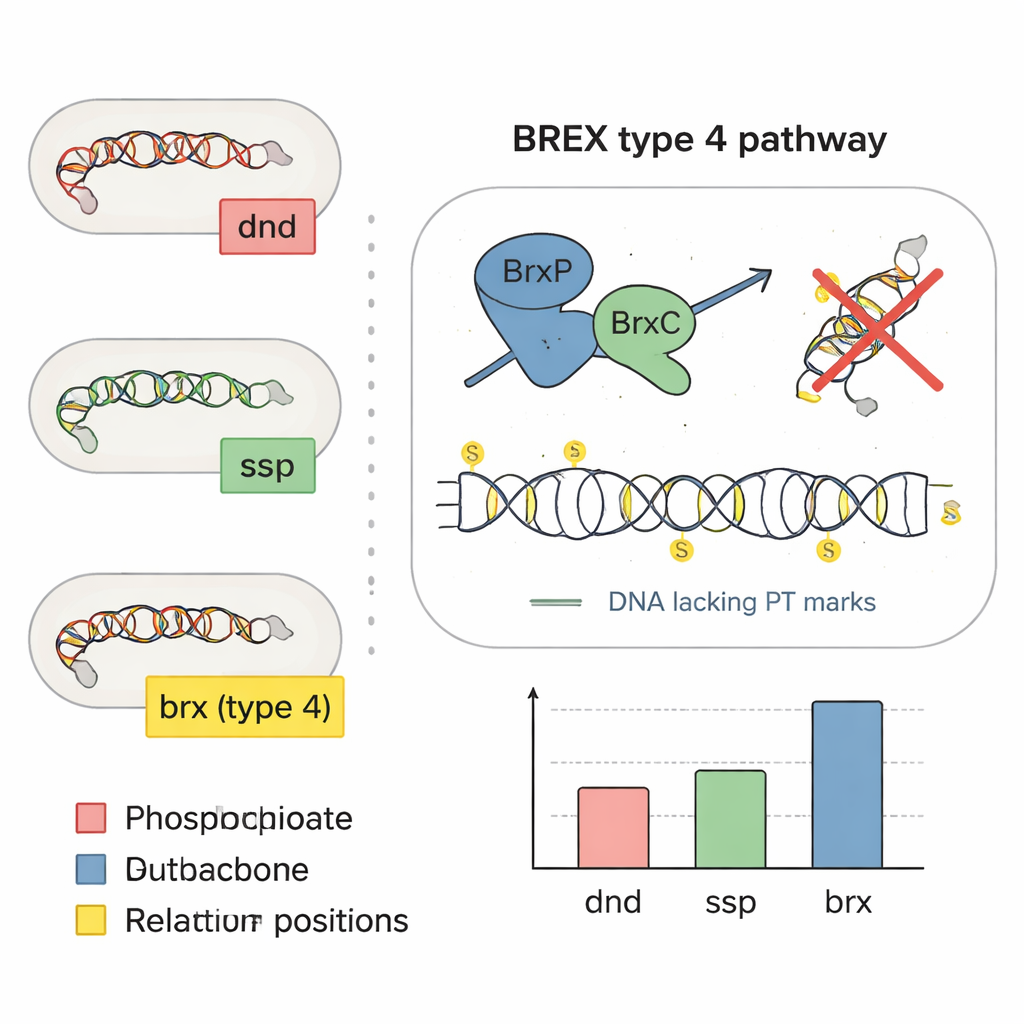
Ao examinar como os genes se organizam ao longo dos cromossomos bacterianos, a equipe notou genes semelhantes a dnd aninhados entre genes de defesa BREX, sugerindo que alguns sistemas BREX podem instalar diretamente marcas de enxofre. Eles se concentraram em um conjunto de quatro genes centrais, brxP, brxC, brxZ e brxL, e usaram análise de sequência para mostrar que BrxP e BrxC se assemelham às proteínas manuseadoras de enxofre dos sistemas ssp. Experimentos na bactéria intestinal humana Bacteroides salyersiae confirmaram a suspeita: quando os pesquisadores deletaram o gene brxC, o DNA modificado por enxofre desapareceu; quando restauraram brxC em um plasmídeo, as marcas de enxofre reapareceram. Eles também transferiram genes BREX-chave para outra bactéria intestinal que normalmente não possui esses sistemas e mostraram que ela começou a produzir o mesmo padrão de DNA com enxofre, demonstrando que a maquinaria BREX tipo 4 pode, por si só, criar marcas de fosforotioato.
Mapeando Onde o Enxofre Cai no Genoma
Encontrar as marcas de enxofre é apenas metade da história; saber exatamente onde elas aparecem ao longo do DNA é crucial para entender sua função. Os pesquisadores combinaram espectrometria de massa sensível com um método de sequenciamento personalizado chamado PT-seq, que corta seletivamente o DNA em sítios modificados por enxofre e então lê a sequência ao redor. Entre 226 isolados bacterianos intestinais, identificaram oito dinucleotídeos distintos contendo enxofre como “blocos de construção” e, a partir de estirpes representativas, determinaram motivos de sequência curtos completos onde o enxofre tende a se instalar. Curiosamente, bactérias com sistemas dnd, ssp ou BREX produziram conjuntos diferentes de padrões de enxofre, como diferentes dialetos da mesma linguagem química. As marcas não estavam espalhadas aleatoriamente: foram enriquecidas em genes de RNA ribossômico e, em geral, evitavam o início e o fim de genes codificadores de proteínas, sugerindo que as bactérias podem estar direcionando o enxofre para longe de regiões sensíveis ao controle.
O Que Isso Significa para Nossa Saúde
Para um público não especialista, essas descobertas mostram que as bactérias intestinais fazem mais do que apenas se alimentar do que ingerimos—elas reescrevem ativamente a química de seu próprio DNA de maneiras que moldam como combatem vírus e respondem às condições oxidantes severas que frequentemente acompanham a inflamação. Ao identificar o BREX tipo 4 como um novo sistema de marcação por enxofre e ao mostrar que cerca de uma em cada treze microrganismos intestinais carrega alguma forma de maquinário de fosforotioato, este trabalho lança as bases para explorar como essas marcas de DNA incomuns influenciam a estabilidade do microbioma, a resistência a infecções e possivelmente o curso de doenças como a doença inflamatória intestinal. A longo prazo, entender e talvez manipular esses sistemas epigenéticos baseados em enxofre pode oferecer novas estratégias para ajustar o microbioma intestinal e apoiar a saúde humana.
Citação: Yuan, Y., DeMott, M.S., Byrne, S.R. et al. Phosphorothioate DNA modification by BREX type 4 systems in the human gut microbiome. Nat Commun 17, 1717 (2026). https://doi.org/10.1038/s41467-026-68412-5
Palavras-chave: microbioma intestinal, epigenética bacteriana, fosforotioação do DNA, sistema de defesa BREX, bacteriófagos