Clear Sky Science · pt
Atlas multiómico integrado revela a hierarquia das redes regulatórias espaciotemporais da gastrulação em camundongo
Como um embrião constrói seu plano corporal
Todo mamífero, incluindo os humanos, começa a vida como uma pequena bola de células que precisa se organizar rapidamente em um corpo complexo com cabeça, cauda, dorso, ventre e órgãos internos. Essa remodelação dramática ocorre durante uma janela curta chamada gastrulação. O artigo resumido aqui constrói um mapa detalhado e multilayer desse processo em embriões de camundongo, mostrando como genes, interruptores do DNA e sinais químicos atuam juntos no espaço e no tempo para guiar as células rumo aos seus destinos futuros.
Observando milhares de células fazerem suas escolhas
Para acompanhar a gastrulação em ação, os pesquisadores analisaram mais de 35.000 células individuais de embriões de camundongo em cinco estágios próximos entre si, do início ao final da gastrulação. Para cada célula, mediram não apenas quais genes estavam ativados, mas também quais trechos de DNA estavam abertos e acessíveis, um indicativo de que podem atuar como interruptores regulatórios. Com esses dados, identificaram 31 tipos celulares distintos e traçaram como células iniciais e flexíveis se ramificam progressivamente nas três camadas germinativas principais — ectoderma, mesoderma e endoderma — que eventualmente formam todos os tecidos e órgãos. Desenvolveram também um novo método computacional, BioCRE, para conectar com mais precisão genes com seus elementos regulatórios do DNA, revelando que muitos interruptores importantes estão localizados longe dos genes que regulam.
Construindo um atlas molecular 3D no espaço real do embrião
A maioria dos métodos de célula única perde a posição original de cada célula no embrião, mas a localização é crítica para entender o padrãoamento. A equipe superou isso alinhando seus dados de célula única a um mapa tridimensional existente da atividade gênica em embriões de camundongo. O resultado é o ST-MAGIC, um “embrião digital” no qual cada pequena localização é anotada com os tipos celulares prováveis, os genes que expressam e a acessibilidade do DNA ao redor. Esse atlas mostra, por exemplo, como diferentes subtipos de mesoderma — futuros coração, músculo e tecidos de suporte — surgem em regiões distintas e como genes amplamente expressos como Otx2 usam elementos regulatórios diferentes na superfície externa (epiblasto) e interna (endoderma visceral) do embrião.
Quando a simetria se rompe e o lado esquerdo difere do direito
Uma característica marcante dos planos corporais é que lados esquerdo e direito não são idênticos — pense no coração levemente deslocado para a esquerda. Os autores usaram seu atlas espacial para focar no mesoderma lateral, onde as diferenças esquerda–direita surgem primeiro. Eles encontraram assimetrias sutis mas consistentes em quais tipos celulares se enriquecem em cada lado e em quais regiões do DNA ficam mais abertas. No direito, regiões ligadas a uma via de sinalização de crescimento chamada BMP estavam mais acessíveis; no esquerdo, predominaram regiões associadas a genes necessários para formar segmentos e estruturas cardíacas. Alguns desses elementos do DNA, incluindo novos elementos que controlam o gene Lefty2, tornam-se acessíveis antes das diferenças visíveis na expressão gênica, sugerindo que um “preparação” precoce do paisagem de cromatina prepara cada lado do embrião para interpretar os sinais de maneira diferente.
Um revezamento de fatores guia a linha média do corpo
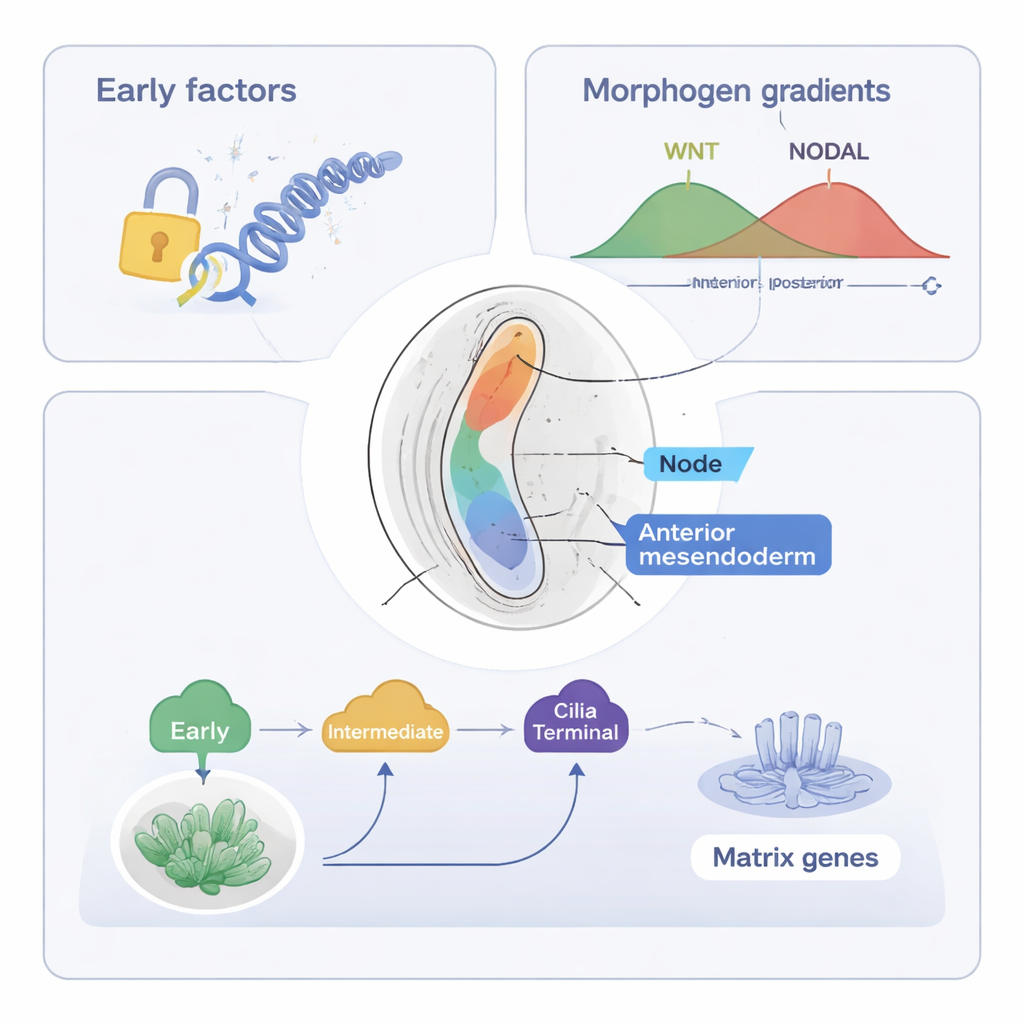
O estudo então foca no mesendoderma axial, uma população de células que formará a notocorda — uma estrutura em forma de haste ao longo da linha média que ajuda a organizar a coluna e o sistema nervoso. Usando suas ferramentas combinadas (ST-MAGIC e uma versão estendida chamada ST-MAGIC (+)), os autores acompanharam como essas células surgem da faixa primitiva anterior e se dividem em dois ramos: células do nodo, que constroem uma estrutura ciliada importante para a detecção esquerda–direita, e mesendoderma anterior, que contribui para tecidos da linha média. Eles revelaram um revezamento hierárquico de fatores de transcrição — proteínas que controlam a atividade gênica. Fatores iniciais, como EOMES, e fatores intermediários, incluindo FOXA2 e LHX1, primeiro abrem regiões-chave do DNA e estabelecem responsividade a sinais principais como WNT e NODAL. Mais tarde, fatores “terminais” como NOTO, SOX9 e um fator recém-implicado POU6F1 ativam programas gênicos especializados, por exemplo os necessários para cílios ou matriz extracelular.
Sinais, cromatina e especialistas de ação tardia
Ao integrar conjuntos de dados públicos sobre onde efetores das vias WNT e NODAL se ligam ao DNA, os autores mostraram que a responsividade do embrião a esses sinais muda no espaço antes mesmo das fontes dos sinais se moverem. Na região preparada para se tornar mesendoderma axial, sítios de DNA responsivos a NODAL e WNT abrem-se cedo, e muitos contêm motivos para FOXA2, Zfp281 e outros reguladores, sugerindo controle cooperativo. A deleção experimental de fatores de ação tardia NOTO e POU6F1 em camundongos perturbou a expressão de genes específicos do nodo e relacionados a cílios e encurtou cílios do nodo, porém a paisagem de DNA aberta subjacente permaneceu em grande parte intacta. Isso indica que fatores anteriores estabelecem os alicerces epigenéticos, enquanto fatores tardios refinam principalmente a expressão gênica sem remodelar a cromatina.
Por que isso importa para entender o desenvolvimento
Para um não especialista, este trabalho pode ser visto como a construção de um “diagrama de fiação” em alta resolução de como um embrião define seu plano corporal. Os autores mostram que as decisões de destino celular durante a gastrulação são governadas não apenas por quais sinais estão presentes, mas também por quando e onde os interruptores do DNA são abertos e quais fatores de transcrição atuam em sequência. Seus atlas ST-MAGIC e ST-MAGIC (+) fornecem um recurso para explorar essas relações ao longo do espaço e do tempo, oferecendo um arcabouço que pode informar estudos sobre defeitos congênitos, modelos embrionários baseados em células-tronco e, eventualmente, aspectos do desenvolvimento humano.
Citação: Yang, X., Xie, B., Shen, P. et al. Integrated multi-omic atlas reveals the hierarchy of spatiotemporal regulatory networks of mouse gastrulation. Nat Commun 17, 1572 (2026). https://doi.org/10.1038/s41467-026-68291-w
Palavras-chave: gastrulação, redes regulatórias de genes, multiômica de célula única, padrionização embrionária, desenvolvimento em camundongo