Clear Sky Science · pt
Autoinibição inter-monômero de HEXIM1 governa a especificidade de ligação ao RNA 7SK e a inativação de P-TEFb
Por que esse pequeno RNA é importante para o controle gênico
Cada célula precisa decidir quando ativar e desativar genes, e faz isso controlando cuidadosamente uma enzima que impulsiona a produção de RNA. Este artigo revela como uma pequena proteína chamada HEXIM1, trabalhando em conjunto com um RNA não codificante chamado 7SK, age como um trava de segurança nessa enzima. Entender esse sistema molecular de segurança ajuda a explicar como nossas células evitam uma ativação gênica descontrolada e também esclarece como vírus como o HIV sequestram a mesma maquinaria.
Um freio molecular na expressão gênica
Em células humanas, um passo-chave da expressão gênica é controlado por um fator chamado P-TEFb, que ajuda a RNA polimerase II a sair de um estado de pausa e entrar em transcrição em alta velocidade. As proteínas HEXIM, especialmente a HEXIM1, são centrais para manter o P-TEFb sob controle. Elas fazem isso dentro de um grande complexo chamado RNP 7SK, organizado em torno do RNA 7SK. Quando HEXIM1 e 7SK se associam, eles aprisionam o P-TEFb para que ele não possa impulsionar a transcrição. Até agora, a peça faltante era como a própria HEXIM1 evita se ligar ao P-TEFb cedo demais e como o RNA 7SK transforma a HEXIM1 de um estado inativo para um inibidor ativo no momento certo.
Uma proteína que se “abraça” e é mantida sob controle
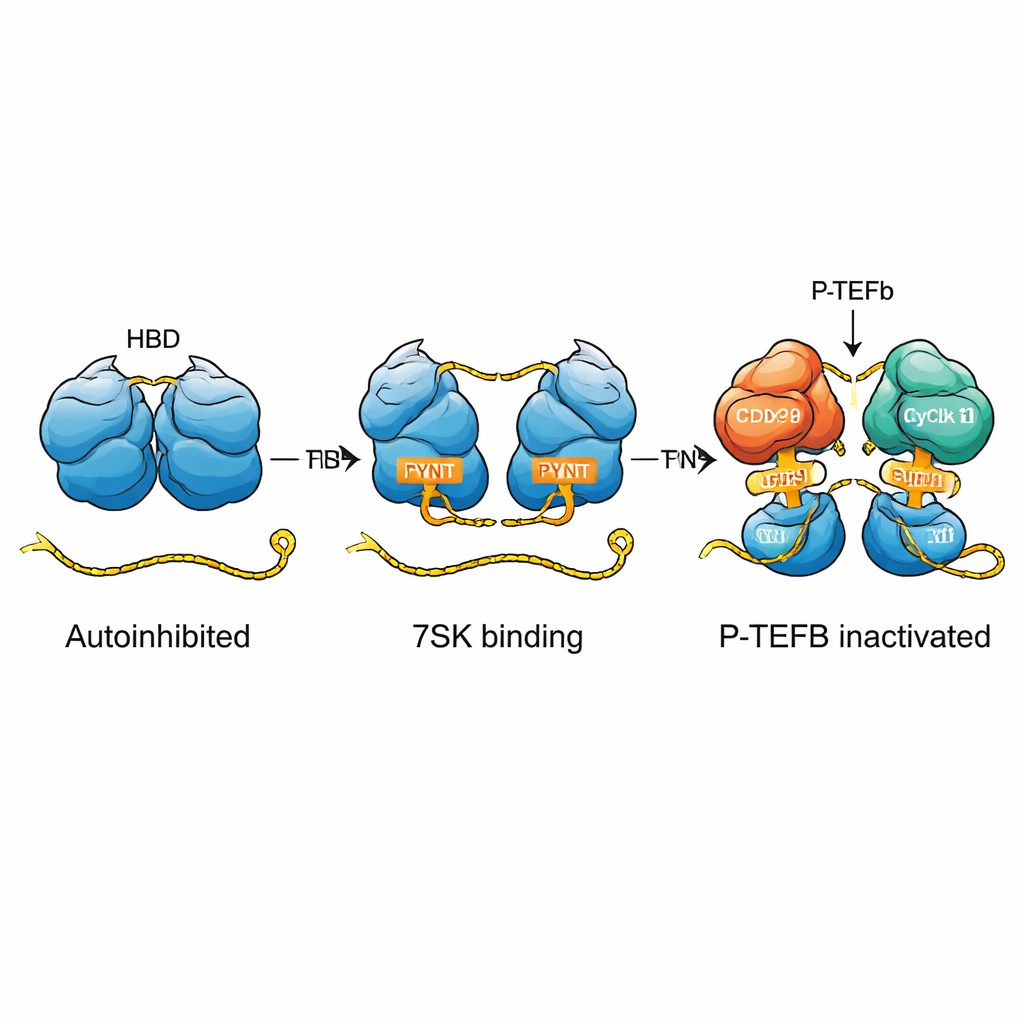
Os autores mostram que a HEXIM1 forma naturalmente um dímero — duas cadeias proteicas idênticas emparelhadas — e que as partes centrais flexíveis de cada cadeia se envolvem uma à outra num arranjo de “autoabraço”. Nesse estado, um segmento curto crucial chamado motivo PYNT, que normalmente se liga e desativa a quinase P-TEFb, fica escondido na interface entre as duas cadeias. Usando métodos sensíveis de RMN e técnicas biofísicas, a equipe mapeou como regiões básicas (carga positiva) e ácidas (carga negativa) dos dois monômeros interagem para criar esse dímero autoinibido. Essa restrição incorporada impede que a HEXIM1 se prenda aleatoriamente ao P-TEFb quando o RNA 7SK não está presente.
Como o RNA 7SK desbloqueia a HEXIM1
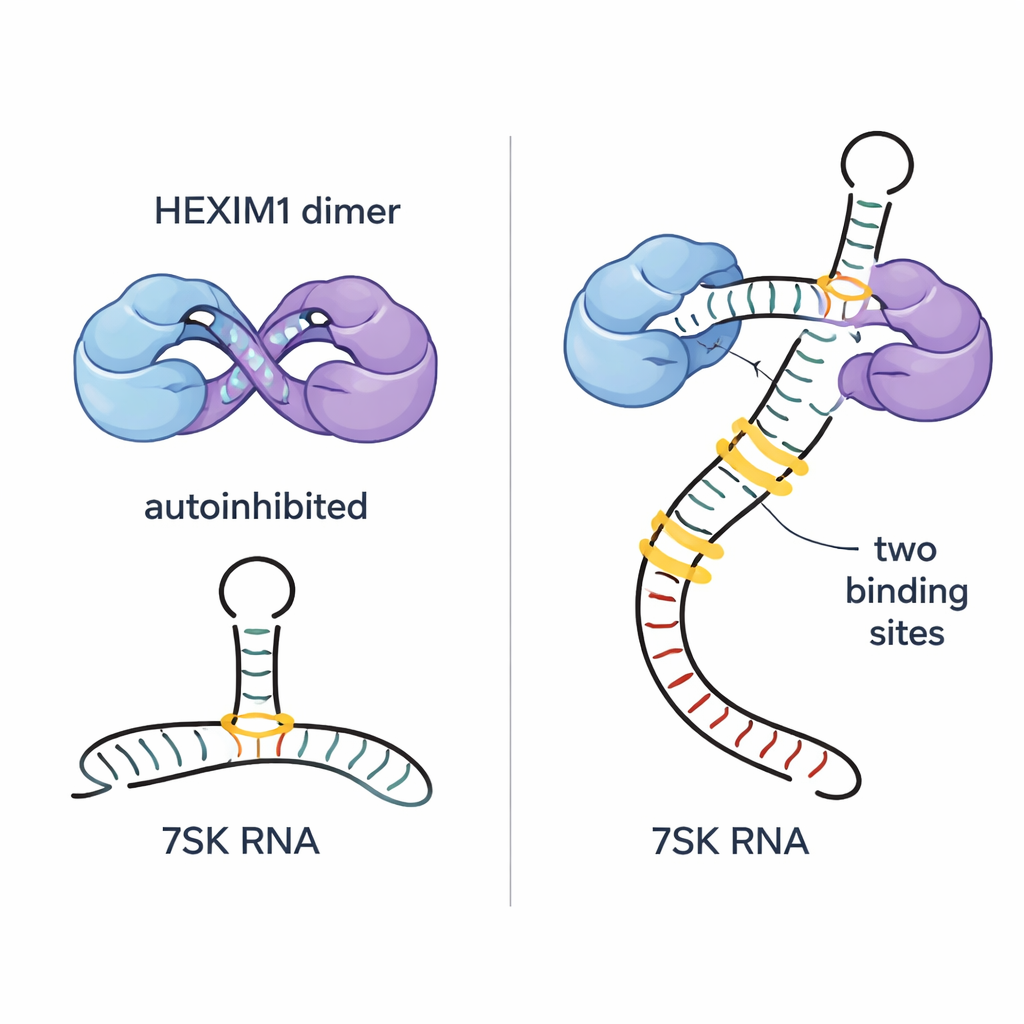
O RNA 7SK contém várias características estruturais, incluindo uma longa região haste-alça chamada SL1. Ao dissecar esse RNA em fragmentos menores e acompanhar mudanças sutis nos sinais de RMN, os pesquisadores identificaram cinco possíveis sítios de ligação da HEXIM1 ao longo do SL1. Dois desses sítios se destacam como pontos de ancoragem de alta afinidade; ambos compartilham uma seção de dupla-hélice rica em A–U e uma saliência rica em U nas proximidades que pode formar interações especiais de três bases. A equipe descobriu que cada metade do dímero HEXIM1 se liga a um desses dois sítios fortes no RNA 7SK linear. Quando ambos os sítios estão ocupados, a região central da HEXIM1 se rearranja, rompendo os contatos do autoabraço e expondo os motivos PYNT ocultos, preparando efetivamente a proteína para capturar o P-TEFb.
Escolhendo a forma correta do RNA — e evitando as erradas
O RNA 7SK não existe em apenas uma conformação; ele pode alternar entre uma forma linear, que apresenta ambos os sítios de alta afinidade, e uma forma mais circular com apenas um sítio adequado. Os autores mostram que a autoinibição da HEXIM1 a torna surpreendentemente exigente: o dímero liga-se fracamente a sítios únicos isolados, mas muito mais fortemente e de forma cooperativa ao segmento SL1 linear completo que oferece ambos os sítios fortes. Essa exigência de dois sítios evita que a HEXIM1 fique presa em RNAs aleatórios no resto da célula e torna sua ligação altamente específica para a conformação linear do 7SK que monta o complexo repressivo ativo. Eles também demonstram que adicionar cargas negativas extras perto da região de ligação ao RNA (imitando fosforilação em uma serina chave) enfraquece a ligação ao RNA sem romper totalmente a autoinibição, um possível mecanismo para as células liberarem o P-TEFb quando necessário.
Do interruptor molecular ao impacto celular
No geral, o estudo revela a HEXIM1 como um interruptor molecular finamente sintonizado. Em seu estado de repouso, de autoabraço, ela mantém seus segmentos PYNT bloqueadores de P-TEFb ocultos. Somente quando encontra o RNA 7SK linear com dois sítios de ligação adequadamente dispostos é que a proteína muda para um estado “ligado”, expondo esses segmentos para que possa capturar e inativar o P-TEFb — frequentemente duas cópias ao mesmo tempo. Esse mecanismo explica como as células usam um pequeno RNA e uma proteína flexível para impor um controle preciso sobre a transcrição e fornece um quadro mais claro para entender como sinais celulares, modificações químicas ou proteínas virais como a Tat do HIV podem inclinar o equilíbrio entre a expressão gênica em pausa e ativa.
Citação: Yang, Y., Murrali, M.G., Galvan, S. et al. HEXIM1 inter-monomer autoinhibition governs 7SK RNA binding specificity and P-TEFb inactivation. Nat Commun 17, 1570 (2026). https://doi.org/10.1038/s41467-026-68285-8
Palavras-chave: regulação da transcrição, RNA 7SK, HEXIM1, P-TEFb, HIV Tat