Clear Sky Science · pt
Um longo caminho até genomas de plantas medicinais confiáveis e completos
Por que mapas do DNA de plantas importam para a saúde humana
Muitos dos medicamentos mais potentes de hoje — desde fármacos contra o câncer como o paclitaxel até analgésicos como a morfina e o antimalárico artemisinina — vêm de plantas. No entanto, para a maioria das plantas medicinais, os cientistas ainda não dispõem de um “manual de instruções” completo do seu DNA. Esta revisão explica como novas tecnologias genômicas estão transformando nossa capacidade de ler esses manuais, por que os genomas vegetais atuais ainda são frequentemente incompletos ou defeituosos, e como genomas realmente precisos poderiam desbloquear melhores medicamentos, produção mais sustentável e conservação aprimorada de espécies valiosas.
A promessa de ler os roteiros das plantas medicinais
Por milênios, as pessoas dependeram de remédios herbais, e a farmacologia moderna continua a se basear fortemente em produtos naturais vegetais. Essas moléculas especializadas — alcaloides, terpenoides, compostos fenólicos e muitos outros — são produzidas por vias metabólicas complexas codificadas no DNA das plantas. Até recentemente, os cientistas precisavam montar essas vias com ferramentas lentas e trabalhosas, como rastreamento isotópico e clonagem gene a gene. A chegada do sequenciamento de DNA de alto rendimento e acessível mudou o cenário. Em fevereiro de 2025, genomas de 431 plantas medicinais (correspondendo a 203 espécies) haviam sido sequenciados, dando aos pesquisadores um modo sistemático de caçar genes de vias metabólicas, entender como compostos valiosos são regulados e explorar como essas químicas evoluíram.
Um boom no sequenciamento, mas muitos genomas imperfeitos
Tecnologias de sequenciamento de leituras longas da PacBio e da Oxford Nanopore, combinadas com dados de leituras curtas da Illumina e métodos de mapeamento ao nível de cromossomo como Hi‑C, melhoraram dramaticamente a qualidade dos genomas vegetais. Quase metade de todos os conjuntos genômicos de plantas medicinais foi liberada apenas nos últimos três anos, e a maioria dos genomas recentes agora é construída em escala cromossômica. No entanto, a revisão mostra que a quantidade superou a qualidade. Mais da metade dos genomas existem apenas numa versão inicial, muitos permanecem em nível de rascunho, e apenas 11 plantas medicinais têm montagens sem lacunas “telômero‑a‑telômero” (T2T) que capturam completamente centrômeros e outras regiões repetitivas. Métricas padrão como N50 (uma medida de contiguidade) e escores BUSCO (uma medida de genes conservados) parecem encorajadoras no geral, mas podem mascarar lacunas críticas exatamente onde residem genes biossintéticos chave.
Lacunas ocultas onde deveriam estar os genes medicinais
Para testar quão úteis os genomas atuais realmente são, os autores examinaram genes de vias conhecidos e validados experimentalmente em nove plantas medicinais bem estudadas. Mesmo em algumas montagens ao nível de cromossomo, enzimas importantes para compostos como ginsenosídeos em ginseng ou artemisinina em Artemisia annua estavam ou completamente ausentes ou apenas parcialmente representadas. Em outros casos, os genes estavam presentes na sequência genômica bruta, mas ausentes ou truncados nas anotações gênicas oficiais, tornando‑os difíceis de encontrar. Um exemplo marcante vem da erva produtora de cumarina Peucedanum praeruptorum: um genoma cromossômico mais antigo quebrou um gene chave e deixou de identificar outros dois; uma montagem T2T mais nova não só restaurou esses genes como revelou que vários deles se agrupam em um cluster gênico biossintético compactado. Esse tipo de mapa de cluster é exatamente o que os pesquisadores precisam para projetar plantas ou micróbios que produzam medicamentos com mais eficiência.
Por que é tão difícil montar genomas de plantas
Plantas medicinais apresentam desafios especiais que vão além daqueles de muitas espécies cultivadas. Seus genomas frequentemente exibem altos níveis de heterozigosidade (muitas diferenças de DNA entre as duas cópias de cada cromossomo), poliploidia frequente (múltiplos conjuntos cromossômicos) e grandes frações de DNA repetitivo — características que confundem algoritmos de montagem e levam a quebras ou junções incorretas. Cerca de um terço das plantas medicinais sequenciadas têm genomas com mais de 70% de conteúdo repetitivo, e mais de um quarto mostra heterozigosidade muito alta. Criar linhagens altamente endogâmicas ou isolar tecido haplóide pode ajudar, mas isso é lento, caro ou biologicamente difícil para muitas espécies. Novas estratégias que montam cada haplótipo parental separadamente e algoritmos mais poderosos ajustados para genomas ricos em repetições e poliploides estão começando a aliviar esses obstáculos, mas ainda não são rotineiros.
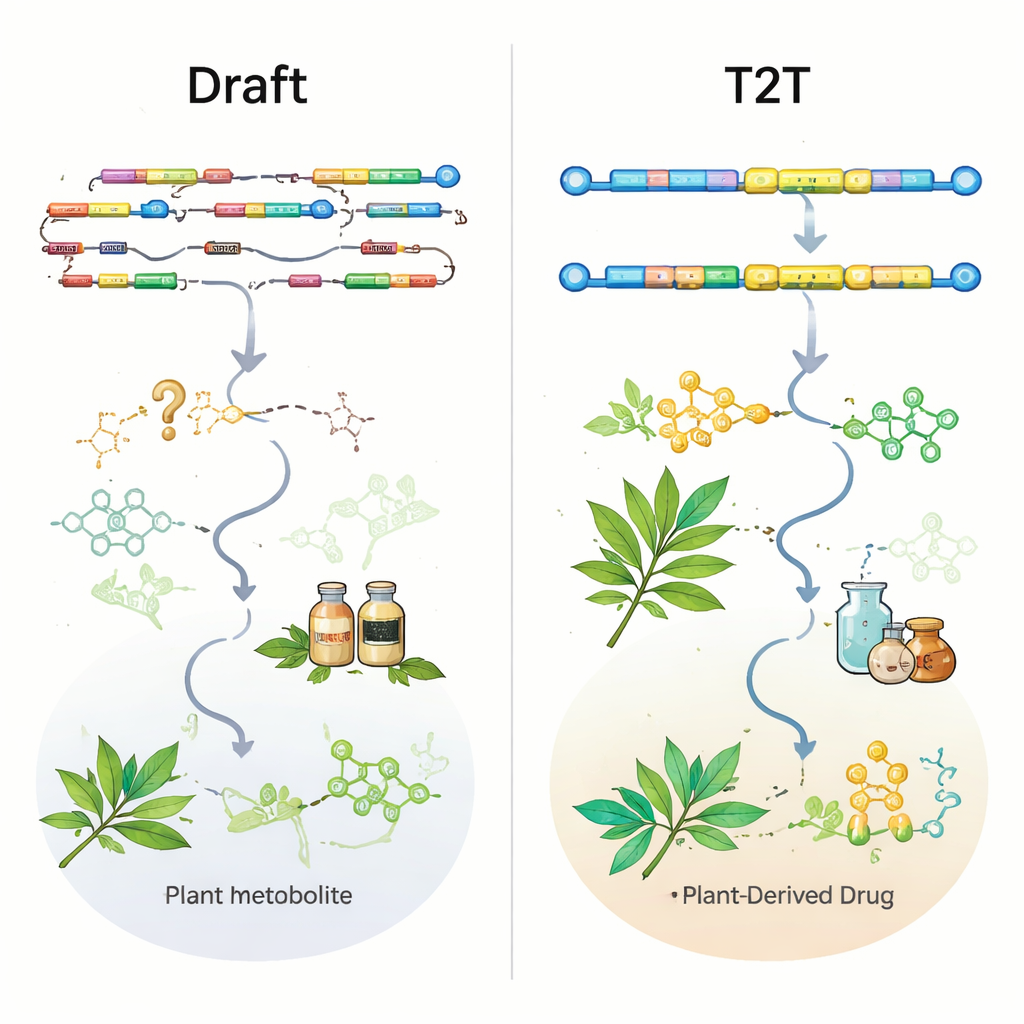
De genomas a novos medicamentos e direções futuras
Quando os genomas são bons o suficiente, tornam‑se motores poderosos de descoberta. Pesquisadores podem combinar dados de genoma completo com transcriptômica, metabolômica e biologia sintética para localizar enzimas, genes regulatórios e clusters gênicos biossintéticos que controlam a produção de compostos de alto valor. Esses conhecimentos já permitiram a reconstrução de vias vegetais complexas — como as do vinblastina, paclitaxel e muitos outros fármacos — em leveduras ou plantas modelo, abrindo um caminho para a bioprodução estável e em larga escala. Olhando adiante, os autores defendem uma mudança de “um genoma rascunho por espécie” para múltiplas montagens de alta qualidade, T2T e resolvidas por haplótipo que capturem a diversidade intraespecífica, de modo semelhante aos pan‑genomas na pesquisa de culturas. Acoplar esses genomas de referência com reseqüenciamento em larga escala, fenotipagem avançada e emergentes transcriptômicas espaciais e de célula única deve iluminar como ambiente, tipo celular e redes gênicas interagem para moldar a química medicinal.
O que isso significa para pacientes e para o planeta
A mensagem central da revisão é que genomas completos e confiáveis de plantas medicinais não são um luxo; são a base para transformar séculos de conhecimento herbal em terapias modernas e precisas. Genomas melhores ajudarão os cientistas a encontrar etapas ausentes em vias de drogas, a projetar suprimentos mais seguros e abundantes de medicamentos críticos e a identificar espécies alternativas capazes de produzir os mesmos compostos. Também orientarão a conservação e o uso sustentável de plantas medicinais ameaçadas, a maioria das quais ainda carece de qualquer recurso genômico. Em resumo, concluir o mapeamento preciso desses genomas pode acelerar a descoberta de fármacos, estabilizar cadeias de suprimento e preservar a diversidade botânica — tudo em benefício final da saúde humana.
Citação: Cheng, LT., Wang, ZL., Zhu, QH. et al. A long road ahead to reliable and complete medicinal plant genomes. Nat Commun 16, 2150 (2025). https://doi.org/10.1038/s41467-025-57448-8
Palavras-chave: genômica de plantas medicinais, clusters gênicos biossintéticos, genomas telômero-a-telômero, biossíntese de produtos naturais, biologia sintética