Clear Sky Science · pt
Categorização de 34 métodos computacionais para detectar genes espacialmente variáveis a partir de dados de transcriptômica espacialmente resolvida
Por que a localização importa para nossos genes
Nossos corpos são formados por células que não só diferem no que fazem, mas também em onde se situam dentro dos tecidos e órgãos. Novas tecnologias de “transcriptômica espacial” agora conseguem identificar quais genes estão ativos mantendo o registro do endereço de cada célula em um mapa do tecido. Este artigo de revisão explica como os cientistas detectam genes cuja atividade varia de um lugar para outro — os chamados genes espacialmente variáveis — e por que chegar a um consenso sobre como encontrá‑los é vital para entender câncer, função cerebral e muitas outras doenças.
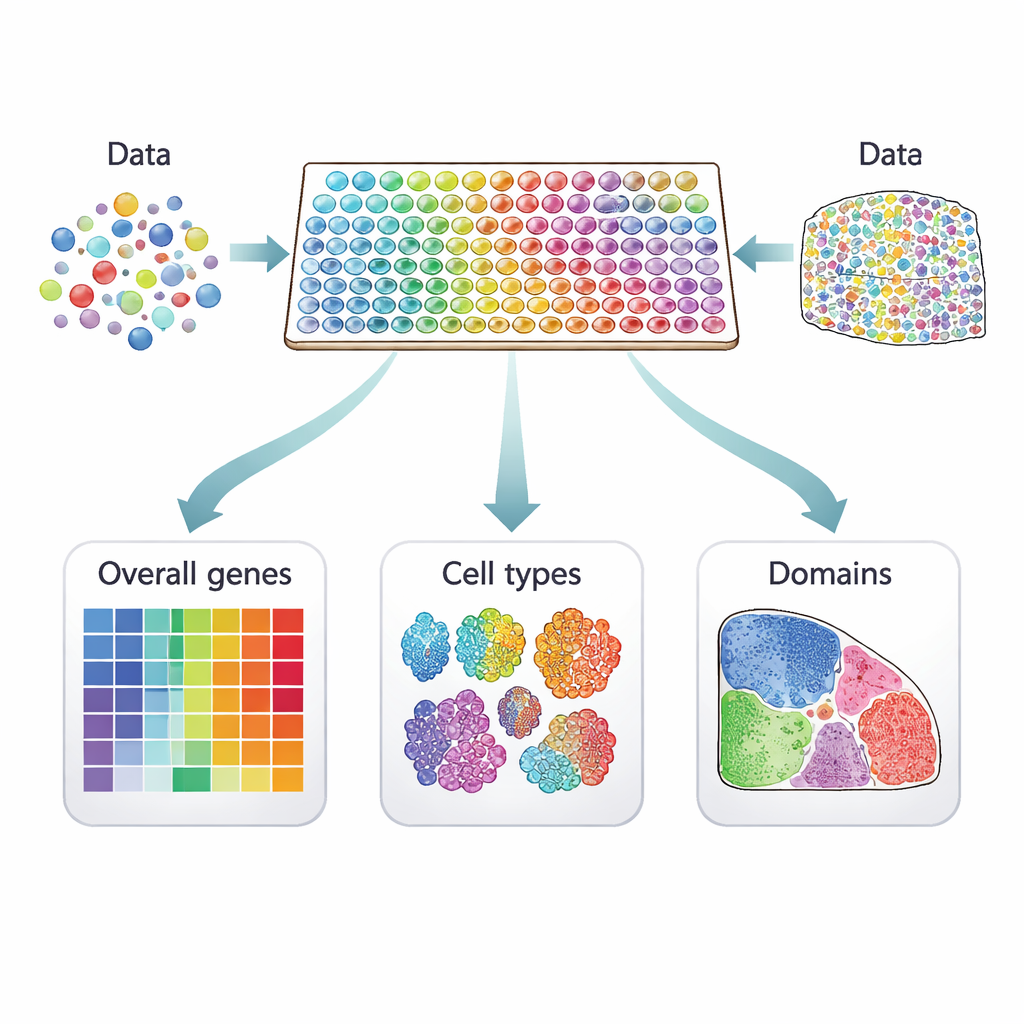
De células dispersas a mapas vivos
Estudos tradicionais de célula única medem a atividade gênica em milhares de células individuais, mas perdem a informação sobre de onde essas células vieram. A transcriptômica espacial preenche essa lacuna ao medir a atividade gênica diretamente em lâminas de tecido. Cada medição está ligada a um “ponto” na lâmina, que pode conter uma célula ou várias, dependendo da tecnologia. Métodos baseados em imagem localizam algumas centenas de genes selecionados com altíssima resolução espacial, enquanto plataformas baseadas em sequenciamento capturam quase todos os genes com resolução mais baixa. Juntas, essas abordagens transformam uma seção tecidual em um mapa colorido de atividade gênica que pode revelar estruturas ocultas, como camadas no cérebro ou regiões dentro de um tumor.
Três tipos de genes sensíveis à localização
Muitos métodos computacionais foram propostos para identificar genes que exibem padrões significativos nesses mapas teciduais, mas nem todos procuram a mesma coisa. Os autores classificam 34 métodos atuais em três categorias claras. O primeiro grupo busca genes espacialmente variáveis “gerais”, cuja atividade muda pelo tecido de qualquer forma não aleatória — talvez formando listras, aglomerados ou gradientes. O segundo grupo foca em genes espaciais “específicos de tipo celular” que variam dentro de um único tipo de célula, ajudando a distinguir, por exemplo, subtipos de neurônios ou estados diferentes de células imunes. O terceiro grupo procura genes “marcadores de domínios” que são fortemente ativados em regiões ou camadas particulares, tornando‑os rótulos úteis para essas zonas teciduais.
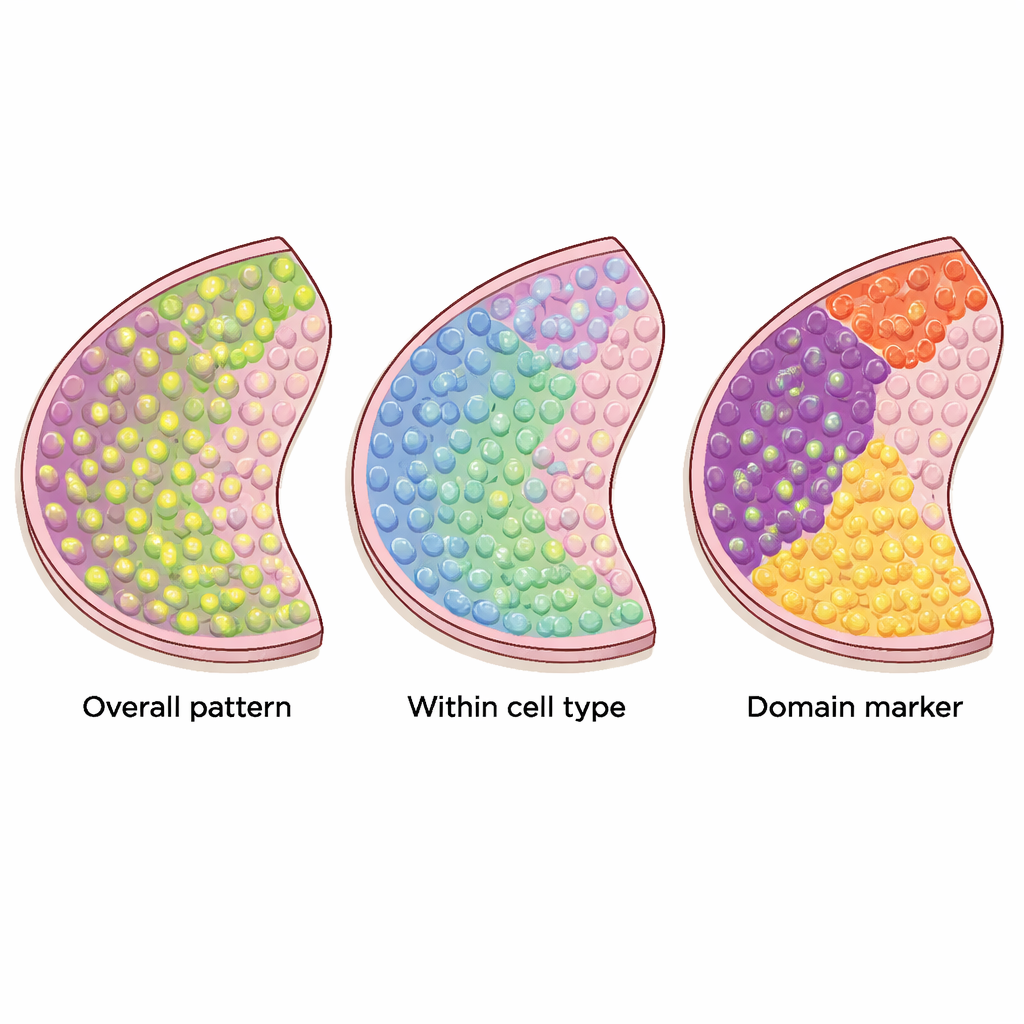
Diferentes ferramentas para diferentes padrões
A revisão explica como esses métodos funcionam por baixo do capô. Alguns tratam a lâmina tecidual como pontos em um espaço bidimensional regular e usam “núcleos” matemáticos para procurar padrões como pontos ou ondas. Outros primeiro conectam locais próximos em uma rede, ou grafo, e então verificam se alta expressão tende a se agrupar ao longo das ligações desse grafo. Certas ferramentas dependem de testes estatísticos formais com taxas de erro bem definidas, enquanto outras classificam genes principalmente pela intensidade com que seus padrões se destacam. Métodos que miram padrões muito específicos podem ser poderosos quando os dados correspondem às suas expectativas, mas podem perder formas mais irregulares ou complexas, como as observadas em muitos cânceres. Também há um trade‑off entre flexibilidade e velocidade: algumas abordagens escalam para centenas de milhares de pontos, enquanto outras têm dificuldade com conjuntos de dados muito grandes.
O que esses genes podem revelar
Uma vez identificados, os genes espacialmente variáveis tornam‑se matéria‑prima para descobertas biológicas mais profundas. Genes espaciais gerais são frequentemente usados como filtro inicial para reduzir o número de genes antes de agrupar pontos em “domínios espaciais” — regiões cujas células compartilham perfis de expressão semelhantes. Esses domínios podem coincidir com estruturas teciduais conhecidas, sugerir sub‑regiões novas ou destacar vizinhanças celulares distintas, como frentes invasivas em tumores. Genes marcadores de domínios ajudam então a explicar o que torna cada região única e podem ser reutilizados para rotular estruturas semelhantes em outras amostras. Enquanto isso, genes espaciais específicos de tipo celular prometem uma visão mais refinada de como tipos celulares particulares mudam ao longo de um tecido, o que pode elucidar interações tumor‑imunes ou circuitos especializados no cérebro.
Desafios e o caminho adiante
Os autores enfatizam que nenhum método único é o melhor para todas as tarefas, e que comparar ferramentas de forma justa exige reflexão cuidadosa sobre que tipo de gene espacial cada método foi realmente projetado para encontrar. Eles pedem por melhores benchmarks usando conjuntos de dados realistas, padrões estatísticos mais claros para evitar descobertas falsas e novas abordagens que respeitem as diferenças entre tecnologias e tipos de tecido. Para não especialistas, a mensagem central é que genes espacialmente variáveis transformam listas planas de genes em mapas vivos, ligando a atividade molecular à estrutura tecidual. Métodos robustos para detectar e interpretar esses genes serão centrais para transformar a transcriptômica espacial em insights práticos sobre desenvolvimento, função cerebral e doenças.
Citação: Yan, G., Hua, S.H. & Li, J.J. Categorization of 34 computational methods to detect spatially variable genes from spatially resolved transcriptomics data. Nat Commun 16, 1141 (2025). https://doi.org/10.1038/s41467-025-56080-w
Palavras-chave: transcriptômica espacial, genes espacialmente variáveis, padrões de expressão gênica, microambientes teciduais, genômica computacional