Clear Sky Science · pt
Assinaturas funcionais da deficiência de recombinação homóloga no câncer de próstata reveladas pela fragmentação de ctDNA e acessibilidade de fatores de transcrição
Por que isso importa para pacientes com câncer
Muitos homens com câncer de próstata avançado poderiam se beneficiar de medicamentos que exploram fraquezas nos mecanismos de reparo do DNA dos tumores. Ainda assim, hoje os médicos frequentemente deixam de identificar quem responderá, porque os testes costumam exigir biópsias difíceis de tecido e focam em apenas um conjunto restrito de genes. Este estudo mostra como uma simples coleta de sangue pode ser transformada em uma leitura rica e multissensorial dessas vulnerabilidades no reparo do DNA, potencialmente orientando escolhas de tratamento mais precisas e menos agressivas.
Uma nova forma de ler sinais do câncer no sangue
Os pesquisadores concentraram-se em um problema de reparo específico chamado deficiência de recombinação homóloga, ou HRD, que torna tumores especialmente vulneráveis a medicamentos como inibidores de PARP e a certas quimioterapias. Em vez de depender de amostras tumorais retiradas de osso ou tecido prostático, analisaram fragmentos de DNA tumoral que circulam na corrente sanguínea, conhecidos como DNA tumoral circulante. De 375 homens com câncer de próstata metastático, selecionaram 106 cujos exames de sangue continham DNA tumoral suficiente para estudo aprofundado e então aplicaram vários testes complementares às mesmas amostras de plasma.
Indo além de mutações em genes isolados
Primeiro, sequenciaram um painel de genes-chave de reparo de DNA, incluindo nomes conhecidos como BRCA2, BRCA1 e PALB2, além de outros genes que influenciam a agressividade dos tumores de próstata. O BRCA2 emergiu como o gene de reparo mais comumente alterado e frequentemente aparecia junto com perdas de outras salvaguardas importantes como PTEN e RB1. Mas a equipe também examinou mudanças em grande escala na estrutura cromossômica em todo o genoma, usando sequenciamento do genoma inteiro em baixa profundidade para calcular uma pontuação de instabilidade genômica. Tumores com genes BRCA danificados, ou com pontuações altas, apresentavam genomas fortemente reordenados e se associavam a pior sobrevida global, ressaltando que grandes mudanças estruturais podem ser tão informativas quanto mutações específicas.
Rastros da falha de reparo nos padrões de mutação
Em um subconjunto de pacientes, os cientistas aprofundaram-se ao sequenciar todas as regiões codificadoras de proteínas para ler o padrão detalhado de mutações acumuladas ao longo do tempo. Certas combinações de trocas de bases e pequenas inserções/deleções atuam como impressões digitais dos processos que as geraram. Eles encontraram assinaturas clássicas associadas à HRD, como uma chamada SBS3 e outro padrão de indel conhecido como ID6, enriquecidas em tumores com defeitos nos genes de reparo e alta instabilidade genômica. Outras assinaturas indicaram problemas distintos, como falha no reparo de incompatibilidades (mismatch repair) ou um subtipo próprio dirigido por CDK12, mostrando que diferentes colapsos do reparo do DNA deixam cicatrizes reconhecíveis no genoma.
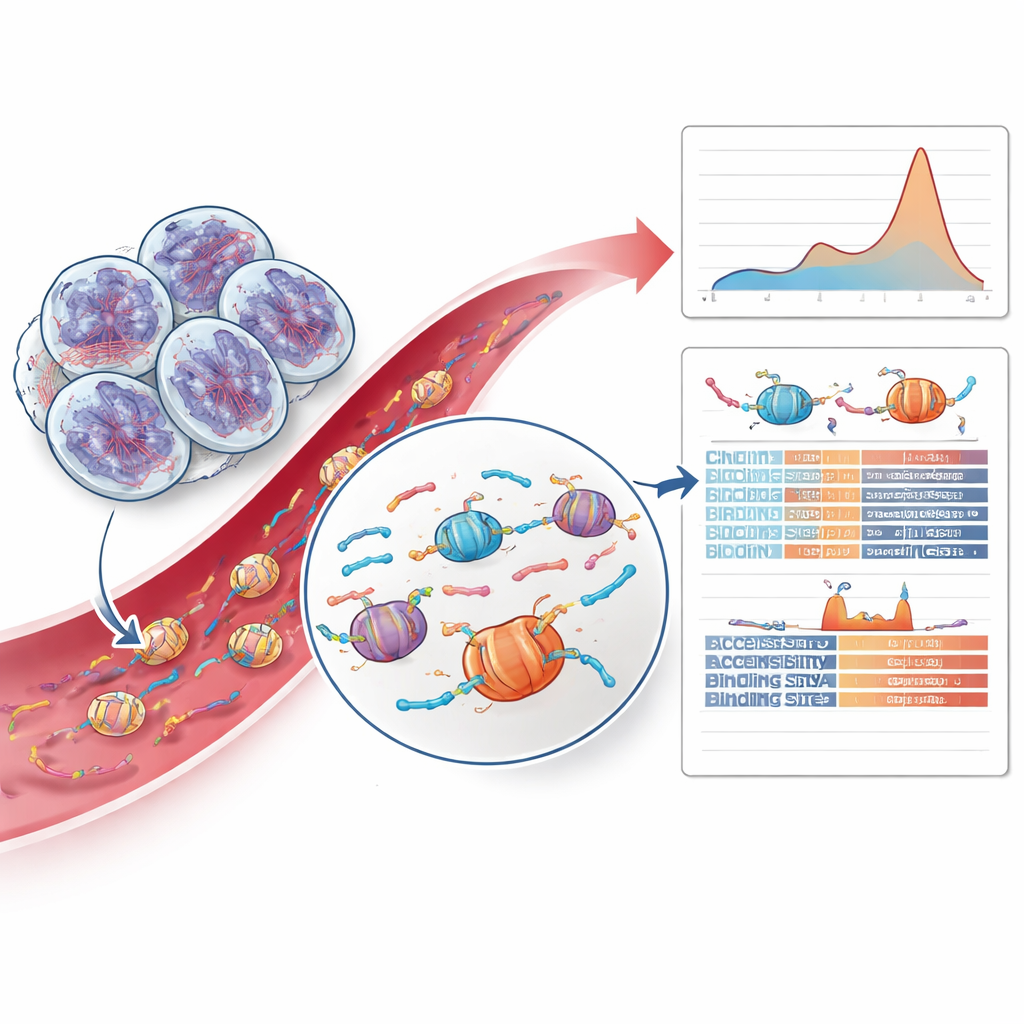
Decodificando padrões de fragmentos de DNA e pistas cromatínicas
A parte mais inovadora do trabalho foi além das mutações e examinou como os fragmentos de DNA tumoral eram cortados. Quando as células morrem, seu DNA é cortado ao redor de pacotes proteicos chamados nucleossomos, criando fragmentos com comprimentos e padrões de extremidade característicos. A equipe descobriu que tumores com HRD mostravam um excesso relativo de fragmentos ligeiramente mais longos correspondentes a dois nucleossomos, um deslocamento não observado em outros cânceres de próstata ou em controles saudáveis. Ao treinar um modelo de aprendizado de máquina cauteloso com comprimentos de fragmentos e características das extremidades, eles conseguiram identificar casos positivos para HRD apenas a partir do sangue com precisão encorajadora. Também investigaram quão acessíveis eram diferentes regiões do genoma em torno de sítios de ligação para fatores de transcrição — proteínas que controlam a atividade gênica — e descobriram que certos sítios de ligação de dedos de zinco estavam menos acessíveis em tumores com HRD, sugerindo mudanças mais profundas relacionadas ao reparo na organização da cromatina.
O que isso pode significar para os pacientes
Juntas, essas camadas de informação — desde mutações genéticas específicas e grandes reordenamentos cromossômicos até mudanças sutis no tamanho dos fragmentos de DNA e na acessibilidade da cromatina — formam um quadro mais completo da fraqueza no reparo do DNA no câncer de próstata. Para um leigo, a mensagem central é que uma amostra de sangue cuidadosamente analisada pode revelar não apenas se um gene conhecido como BRCA2 está mutado, mas se um tumor se comporta como aquele com um defeito sério de reparo, mesmo quando os testes usuais parecem normais. Se validada em grupos maiores e mais diversos de pacientes, essa abordagem multimodal baseada em sangue poderia ajudar os médicos a identificar com mais confiabilidade quem provavelmente se beneficiará de inibidores de PARP ou de drogas à base de platina, monitorar alterações ao longo do tempo e, em última instância, personalizar a terapia usando um exame simples e repetível.
Citação: Vlachos, G., Moser, T., Lazzeri, I. et al. Functional footprints of homologous recombination deficiency in prostate cancer revealed by ctDNA fragmentation and transcription factor accessibility. Br J Cancer 134, 949–960 (2026). https://doi.org/10.1038/s41416-025-03301-0
Palavras-chave: câncer de próstata, biópsia líquida, reparo de DNA, DNA tumoral circulante, inibidores de PARP