Clear Sky Science · pl
Bardzo szybka i specyficzna ilościowa analiza miRNA za pomocą kinetyki wygaszania fluorescencji pojedynczych cząsteczek
Dlaczego szybkie testy chorób mają znaczenie
Rozpoznawanie chorób takich jak nowotwory czy infekcje wirusowe często sprowadza się do wykrycia śladowych ilości materiału genetycznego we krwi lub innych płynach ustrojowych. Dzisiejsze testy referencyjne mogą być bardzo dokładne, ale bywają powolne, kosztowne lub mają trudności z wykryciem bardzo rzadkich sygnałów. W badaniu przedstawiono nową metodę mikroskopową, nazwaną Q‑FISH, która potrafi odczytywać te genetyczne wskazówki w mniej niż sekundę. Jeśli zostanie przeniesiona do narzędzi klinicznych, taka szybkość i precyzja mogą ułatwić wcześniejsze wykrywanie chorób, monitorowanie skuteczności terapii i dopasowywanie opieki do potrzeb pacjenta.
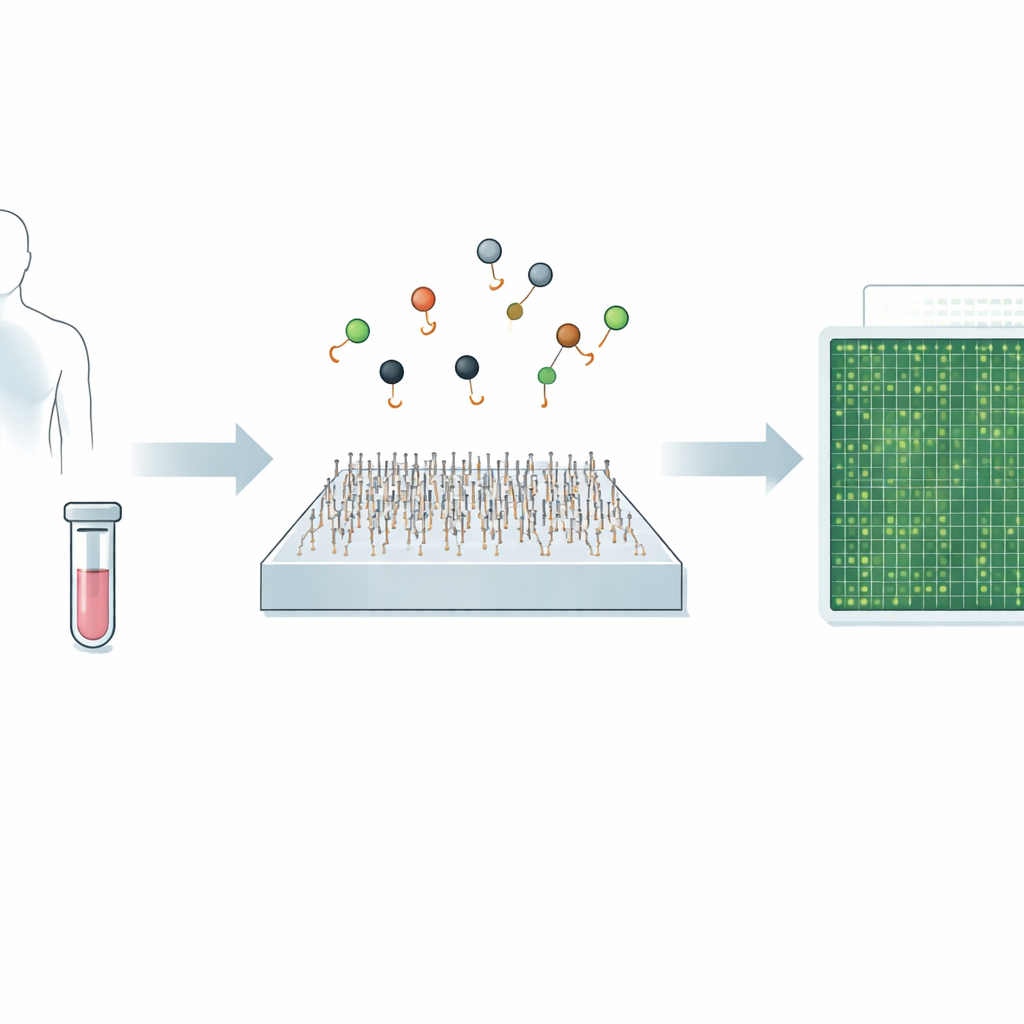
Nowy sposób dostrzegania drobnych komunikatów genetycznych
Praca koncentruje się na microRNA — krótkich fragmentach RNA, które regulują wykorzystanie genów i są silnie powiązane z wieloma nowotworami, chorobami serca, infekcjami i zaburzeniami neurologicznymi. Ponieważ microRNA są bardzo krótkie i często różnią się tylko jednym lub dwoma nukleotydami, standardowe metody, takie jak PCR czy sekwencjonowanie nowej generacji, mają trudności z rozróżnieniem blisko spokrewnionych typów, zwłaszcza gdy występują na bardzo niskim poziomie. Ostatnie podejścia obrazowania pojedynczych cząsteczek poprawiły specyficzność, śledząc wiązanie i odłączanie pojedynczych sond, lecz nadal były stosunkowo wolne — analiza pojedynczego celu zajmowała około dziesięciu minut.
Obserwowanie migotania światła, by znaleźć właściwy cel
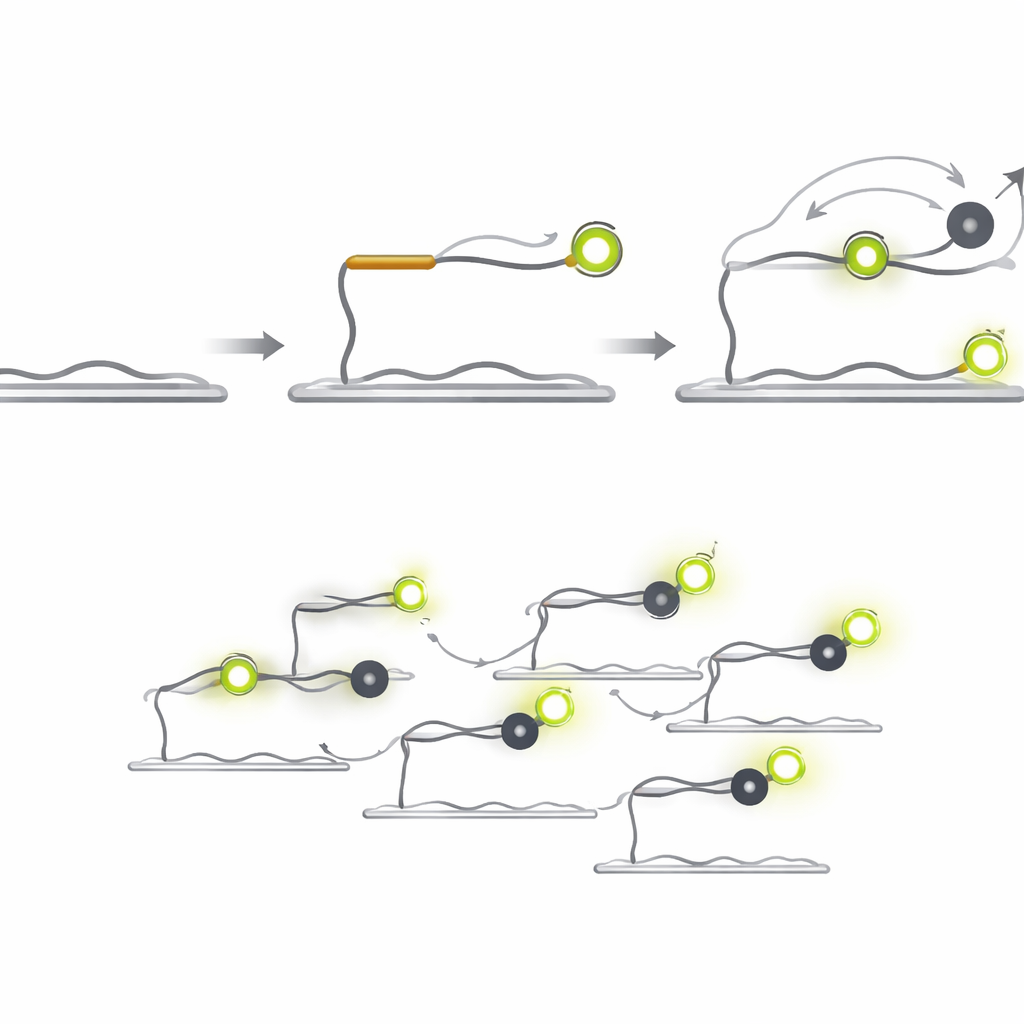
Q‑FISH odwraca problem, wykorzystując krótkotrwałe migotania światła pojedynczych cząsteczek. Metoda używa dwóch krótkich sond DNA, które rozpoznają sąsiadujące miejsca na docelowym microRNA. Jedna sonda niesie barwnik fluorescencyjny świecący pod laserem, druga ma „wygaszacz”, który pochłania światło, gdy znajdzie się blisko. Sonda fluorescencyjna przyłącza się do celu i utrzymuje się wystarczająco długo, by ją zobaczyć, podczas gdy sonda z wygaszaczem została zaprojektowana tak, by wiązać się i odłączać bardzo szybko. Za każdym razem, gdy wygaszacz ląduje obok barwnika, intensywność światła nagle spada; gdy odchodzi — skacze z powrotem. Rejestrując te szybkie przełączania stanu pojedynczych cząsteczek i analizując długości jasnych i przyciemnień okresów, system może stwierdzić, czy obecny jest prawdziwy cel.
Z minut do milisekund
Ponieważ sonda z wygaszaczem sama nie emituje światła, można jej używać w znacznie wyższych stężeniach niż sond fluorescencyjnych bez tworzenia tła świetlnego. Skrócenie sondy z wygaszaczem zwiększa tempo jej odłączania, a zwiększenie jej stężenia zwiększa częstotliwość przystanków przy barwniku. Te decyzje projektowe prowadzą łącznie do dramatycznego wzrostu szybkości. W testach z microRNA związanym z rakiem, zwanym let‑7a, Q‑FISH osiągnął ponad 70% maksymalnej wydajności detekcji w zaledwie jedną sekundę obserwacji. Porównywalne metody obrazowania pojedynczych cząsteczek potrzebowały dziesiątek do setek sekund, by osiągnąć podobną wydajność, co w praktyce czyni Q‑FISH ponad 600 razy szybszym.
Rozróżnianie niemal identycznych sygnałów i pomiar próbek biologicznych
Naukowcy pokazali także, że Q‑FISH potrafi odróżnić kilka członków rodziny microRNA let‑7, które mają niemal identyczną sekwencję, a pełnią różne role w regulacji genów związanych z rakiem. Zastosowali dwie strategie multiplexowania. W jednej wprowadzano różne sondy z wygaszaczami kolejno, każdą dostrojona do nieco innego microRNA; w drugiej sondy były oznaczone różnymi kolorami i obrazowane jednocześnie. W obu przypadkach odczytanie wzorców migotania pozwoliło poprawnie zidentyfikować, które microRNA to które, w około jedną sekundę. Na koniec zastosowali metodę do całkowitego RNA wyizolowanego z ludzkiej wątroby i płuc. Dodając znane ilości syntetycznych microRNA i zliczając powstałe plamki, zbudowali krzywe kalibracyjne, a potem odczytali naturalne poziomy obecne w tkankach, ujawniając wyraźne różnice między organami.
Co to może znaczyć dla przyszłych testów
Podsumowując, badanie pokazuje, że Q‑FISH potrafi wyodrębnić specyficzne microRNA z bardzo wysoką dokładnością, nawet gdy są one niemal identyczne, i robi to z prędkościami znacznie przewyższającymi wcześniejsze metody pojedynczych cząsteczek. Chociaż eksperymenty przeprowadzono na przygotowanych próbkach za pomocą specjalistycznego mikroskopu, zasadniczy pomysł — wykorzystanie szybkich zdarzeń wygaszania światła zamiast wyłącznie powolnego wiązania — można dostosować do wielu typów markerów genetycznych, w tym fragmentów DNA nowotworu we krwi. Przy dalszym opracowaniu i uproszczeniu przygotowania próbek podejście to może przyczynić się do wprowadzenia szybkiej, silnie multiplexowanej i wyjątkowo czułej diagnostyki molekularnej do codziennego użytku klinicznego.
Cytowanie: Kim, J., Hohng, S. Ultrafast and specific miRNA quantification via single-molecule fluorescence quenching kinetics. Commun Biol 9, 432 (2026). https://doi.org/10.1038/s42003-026-09714-8
Słowa kluczowe: wykrywanie microRNA, obrazowanie pojedynczych cząsteczek, diagnostyka molekularna, wygaszanie fluorescencji, biopsja płynna