Clear Sky Science · pl
DANST umożliwia dekonwolucję typów komórek w transkryptomice przestrzennej za pomocą głębokich, adwersarialnych sieci neuronowych
Widzenie komórek w ich sąsiedztwie
Ludzkie tkanki to zatłoczone miasta z wieloma różnymi typami komórek, z których każda pełni określoną rolę. Nowe technologie „transkryptomiki przestrzennej” potrafią mierzyć, które geny są aktywne w przekroju tkanki, ale każde takie pomiar często miesza sygnały pochodzące od kilku sąsiednich komórek. W artykule przedstawiono DANST — inteligentną metodę obliczeniową, która rozdziela te mieszanki. Informując, jakie typy komórek występują i gdzie w organach oraz guzach, pomaga naukowcom lepiej zrozumieć, jak zbudowane są tkanki, jak choroby się rozprzestrzeniają i gdzie leczenie może być najskuteczniejsze. 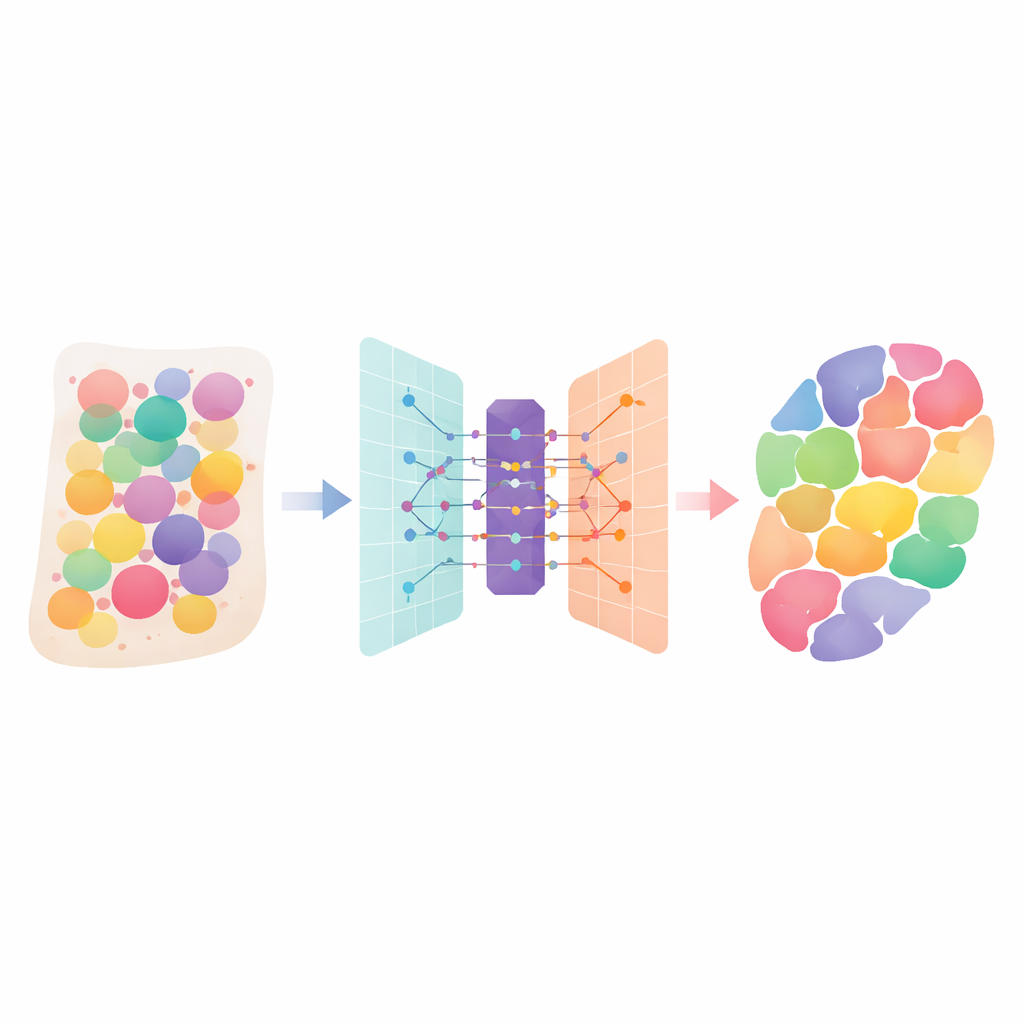
Wyzwanie rozplątywania tłumu komórek
Nowoczesne narzędzia odczytu genów mogą albo badać bardzo precyzyjnie pojedyncze komórki, albo odwzorowywać całą strukturę tkanki, ale rzadko robią obie rzeczy naraz. Popularne technologie przestrzenne rejestrują aktywność genów w stosunkowo dużych „punktach” (spotach), które mogą obejmować kilka komórek. Efekt przypomina słyszenie chóru bez możliwości rozpoznania, kto śpiewa które nuty. Aby to uporządkować, badacze potrzebują metod „dekonwolucji”, które oszacują, jak duży wkład każdego typu komórki przypada na dany punkt. Wiele istniejących podejść korzysta z danych pojedynczych komórek jako odniesienia, ale napotyka trudności, ponieważ oba typy danych pochodzą z różnych eksperymentów i nie pasują do siebie idealnie pod względem jakości, poziomu szumu czy rozdzielczości.
Budowanie mostu między światami danych
DANST rozwiązuje tę niezgodność, tworząc most między danymi z pojedynczych komórek a danymi przestrzennymi. Najpierw wykorzystuje szczegółowe profile pojedynczych komórek do symulowania wielu sztucznych, mieszanych punktów o znanych proporcjach typów komórek. Równocześnie grupuje rzeczywiste przestrzenne spoty według ich położenia w tkance i wzorców genowych, i używa odległości do tych grup, aby przypisać każdemu symulowanemu spotowi „pseudo” pozycję. Ten krok tworzy powiątaną mapę, gdzie sztuczne i rzeczywiste spoty dzielą wspólną ramę przestrzenną, co pozwala metodzie nauczyć się, jak mieszane sygnały powinny wyglądać w konkretnych sąsiedztwach tkanki. 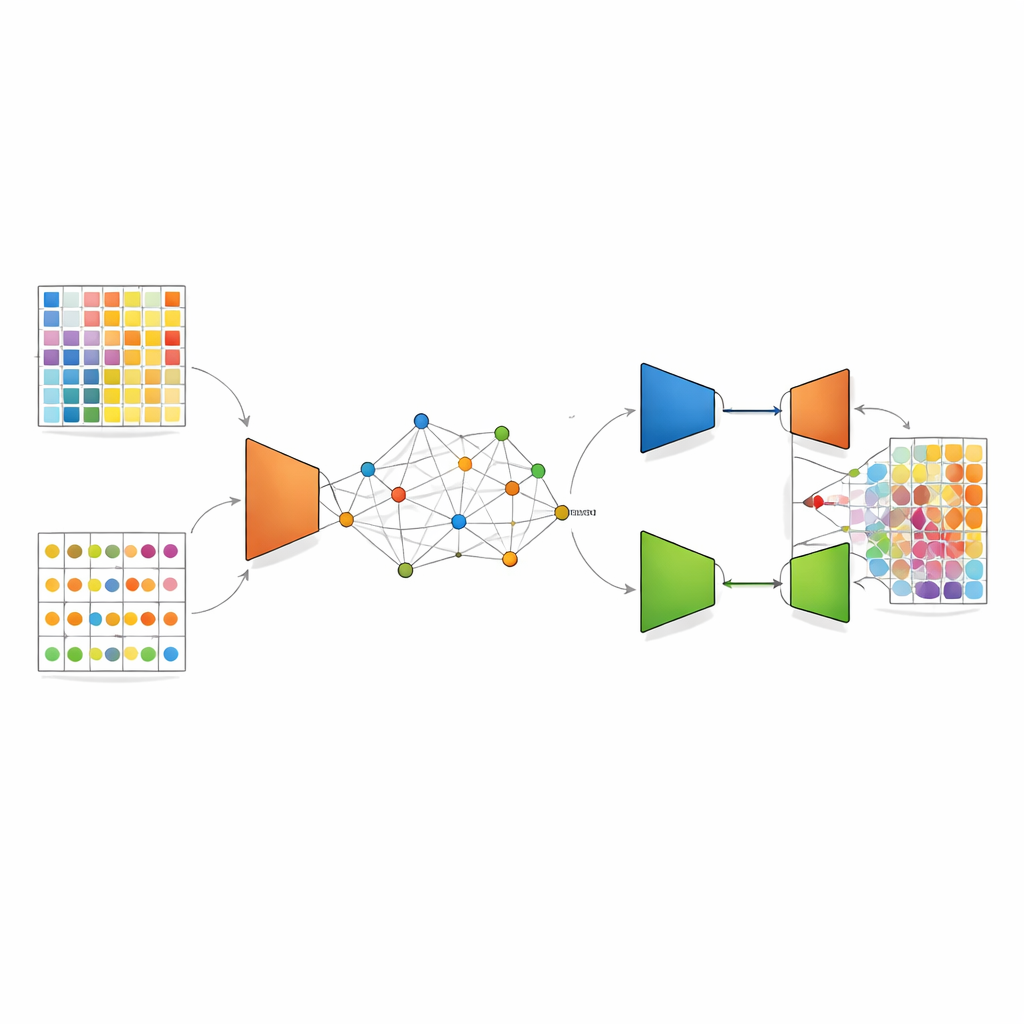
Oczyszczanie sygnałów i wyrównywanie domen
Gdy wspólna mapa jest gotowa, DANST stosuje rodzaj uczenia głębokiego zwanego wariacyjnym autoenkoderem. Sieć ta kompresuje wzorce genowe zarówno z rzeczywistych, jak i symulowanych spotów do udoskonalonej wewnętrznej reprezentacji, a następnie próbuje je odtworzyć, skutecznie odszumiając dane i eksponując istotne cechy. Ponadto autorzy dodają komponent adwersarialny: druga sieć próbuje rozróżnić, czy dana udoskonalona reprezentacja pochodzi z rzeczywistych danych przestrzennych, czy ze danych symulowanych, podczas gdy ekstraktor cech uczy się ją oszukiwać. Ten „pojedynek” popycha model w stronę cech, które działają dobrze dla obu źródeł danych, tak aby wiedza zdobyta na symulowanych spotach o znanych frakcjach typów komórek mogła być wiarygodnie przeniesiona na rzeczywiste spoty tkanki o nieznanym składzie.
Testy na sercach, mózgach i guzach
Zespół testował DANST zarówno na sztucznych benchmarkach, jak i na rzeczywistych próbkach biologicznych pochodzących od myszy i ludzi. W porównaniu z kilkoma wiodącymi metodami, DANST dokładniej odtwarzał proporcje typów komórek w zestawach syntetycznych i utrzymywał przewagę w bardzo różnych tkankach i na różnych platformach. W zestawie danych z mózgu myszy wyraźnie odtworzył warstwową organizację kory i pokrył się z regionami anatomicznymi zdefiniowanymi przez ekspertów. W odrębnym przekroju mózgu myszy uchwycił drobne wzorce w obszarach takich jak hipokamp. Co najważniejsze, w ludzkiej tkance raka piersi DANST odwzorował, jak różne komórki odpornościowe, komórki wspierające i hormonozależne komórki luminalne są rozmieszczone wewnątrz i wokół obszarów nowotworowych. Te mapy zgadzały się z znaną biologią i sugerowały cechy istotne klinicznie, takie jak zależność od hormonów i potencjalnie gorsze rokowanie tam, gdzie pewne komórki odpornościowe były rzadkie.
Co to oznacza dla biologii i medycyny
Dla osoby niezwiązanej ze specjalistyczną dziedziną, DANST można uznać za potężnego tłumacza, który zamienia rozmyte, nakładające się sygnały w wyraźny obraz tego, które komórki znajdują się gdzie w tkance. Poprzez niezawodne rozdzielenie typów komórek w przestrzeni daje badaczom ostrzejszy obraz tego, jak zorganizowane są zdrowe organy i jak choroba przebudowuje tę organizację. W onkologii może to ujawnić, jak komórki nowotworowe i komórki odpornościowe oddziałują w określonych regionach, co może ukierunkować terapie i pomóc przewidywać wyniki leczenia pacjentów. W miarę jak pojawiać się będzie coraz więcej zestawów danych przestrzennych i pojedynczych komórek, narzędzia takie jak DANST mają szansę stać się niezbędne do odczytywania komórkowych sąsiedztw leżących u podstaw zdrowia i choroby.
Cytowanie: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Słowa kluczowe: transkryptomika przestrzenna, dekonwolucja typów komórek, uczenie głębokie, mikrośrodowisko guza, sekwencjonowanie RNA pojedynczych komórek