Clear Sky Science · pl
Ocena jakości modeli struktury 3D RNA z użyciem głębokiego uczenia i pośrednich map 2D
Dlaczego ocena kształtów RNA ma znaczenie
W każdej komórce cząsteczki RNA skręcają się i składają w złożone, trójwymiarowe kształty, które pomagają kontrolować, które geny są aktywne, kierować reakcjami chemicznymi, a nawet zwalczać wirusy. Dziś potężne programy komputerowe potrafią przewidzieć wiele z tych kształtów, ale naukowcy wciąż stoją przed podstawowym problemem: gdy komputer generuje dziesiątki lub setki kandydatów dla tego samego RNA, który z nich jest rzeczywiście bliski rzeczywistości? W artykule przedstawiono RNArank — narzędzie sztucznej inteligencji zaprojektowane do rozwiązania tego problemu poprzez ocenę modeli 3D RNA, działając niczym inspektor jakości struktur, aby badacze mogli skupić się na najbardziej wiarygodnych przewidywaniach.
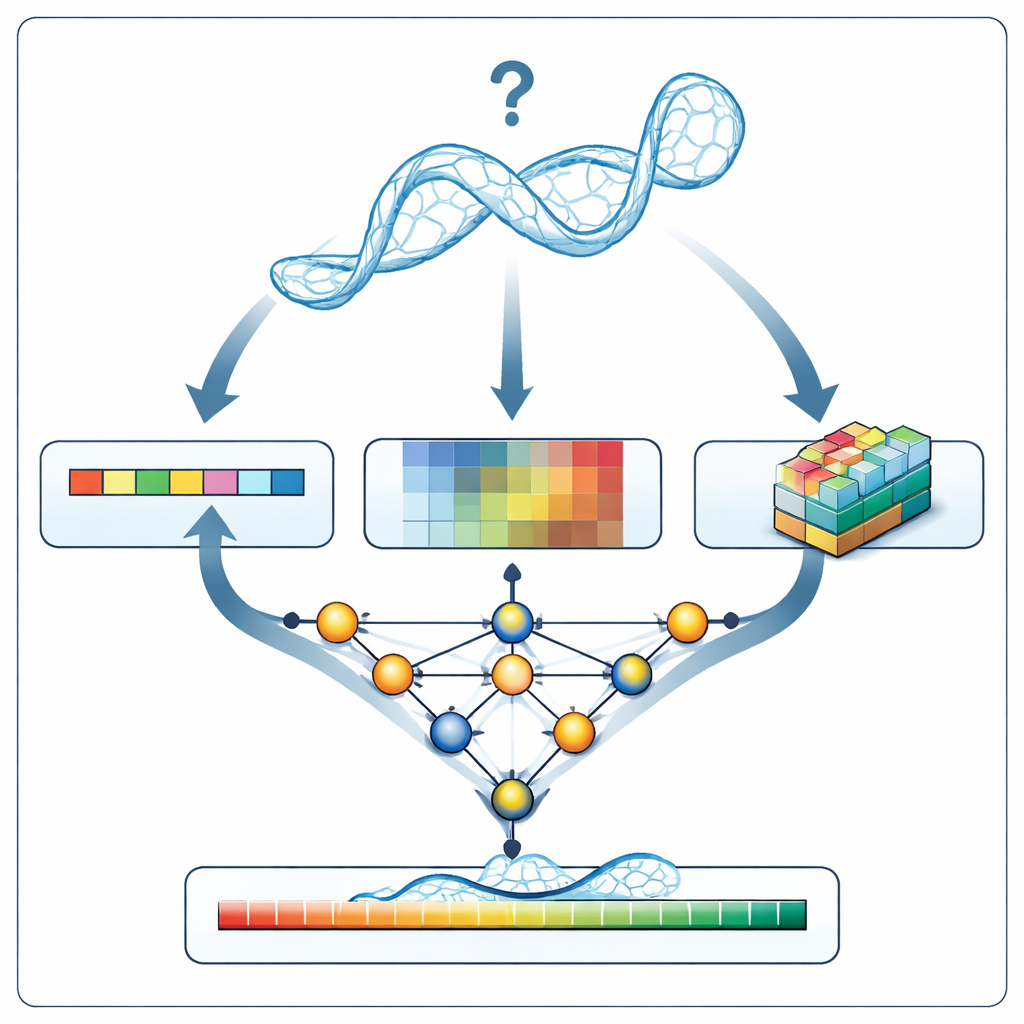
Nowy inspektor modeli RNA
RNArank został zbudowany, by oceniać jakość proponowanego kształtu RNA bez potrzeby wiedzy o tym, jak ten kształt powstał. Niezależnie od tego, czy model pochodzi z systemu opartego na głębokim uczeniu, z symulacji fizycznych, czy od eksperta, RNArank analizuje wyłącznie końcowe współrzędne 3D. Pyta w istocie: „Czy ta struktura wygląda jak realistyczne RNA?” Tego rodzaju niezależna ocena jakości jest kluczowa, ponieważ w przeciwieństwie do świata białek, gdzie narzędzia takie jak AlphaFold często dostarczają bardzo wiarygodnych wyników od razu, przewidywania RNA wciąż korzystają z łączenia wielu metod i ludzkiej wiedzy — oraz z inteligentnego sposobu porządkowania otrzymanych modeli.
Nauczanie SI, jak wygląda dobre RNA
Aby wytrenować RNArank, autorzy zebrali około 200 000 struktur RNA, obejmujących szerokie spektrum — od ewidentnie błędnych po niemal perfekcyjne. Modele te powstały na podstawie znanych struktur eksperymentalnych przy użyciu różnych podejść, w tym współczesnych predyktorów opartych na głębokim uczeniu, symulacji dynamiki molekularnej odtwarzającej ruchy atomów oraz celowych zniekształceń dokładnych struktur w celu stworzenia „decyoy”. Dla każdego modelu zespół obliczył, jak bardzo zgadza się on z rzeczywistą, doświadczalnie określoną strukturą RNA, używając udoskonalonej miary dokładności dostosowanej do RNA, zwanej lDDT_RNA. Ten wskaźnik koncentruje się na tym, jak dobrze odtwarzane są odstępy między parami nukleotydów, uwzględniając zarówno ogólny fałd, jak i lokalne detale, bez nadmiernej wrażliwości na długość cząsteczki.
Jak RNArank odczytuje i ocenia RNA
Gdy RNArank analizuje nowy model RNA, najpierw przekształca strukturę w trzy rodzaje informacji: 1D opis sekwencji i geometrii łańcucha, 2D opisy relacji między każdą parą nukleotydów (ich odległości, szacowane energie interakcji i możliwe kolizje atomowe) oraz 3D „woksele” — małe siatki uchwycąjące lokalną chmurę atomów wokół każdego nukleotydu. Wieloczęściowa sieć neuronowa splata te wskazówki w jedną spójną reprezentację, a następnie przewiduje dwie pośrednie mapy 2D: które nukleotydy prawdopodobnie wchodzą w kontakt oraz o ile każdy modelowany dystans może odbiegać od nieznanej prawdziwej struktury. Na podstawie tych map RNArank rekonstruuje zarówno ocenę zaufania per nukleotyd, jak i ogólną ocenę całego modelu RNA.
Sprawdzanie metody w praktyce
Zespół przetestował RNArank na trzech wymagających zbiorach danych: zestawie 24 świeżo rozwiązanych RNA z Protein Data Bank oraz celach RNA z dwóch międzynarodowych konkursów predykcji blind, CASP15 i CASP16, gdzie wiele grup przesyła modele nie znając wcześniej odpowiedzi. Wśród tysięcy kandydatów oceny RNArank korelowały z rzeczywistą jakością modelu ściślej niż kilka uznanych metod opartych na energii oraz inne podejścia oparte na głębokim uczeniu. Szczególnie dobrze radził sobie z wybieraniem najlepszego lub bliskiego najlepszemu modelu z puli oraz z identyfikacją fragmentów struktury, które prawdopodobnie są nierzetelne. Autorzy pokazali również, że RNArank utrzymuje swoją wydajność nawet dla RNA, których sekwencje wyraźnie różniły się od tych użytych w treningu, co świadczy o prawdziwej uogólnialności, a nie o zapamiętywaniu.
Dzisiejsze ograniczenia i perspektywy na przyszłość
RNArank nie jest doskonały: wciąż ma problem z wyjątkowo elastycznymi RNA, które przyjmują wiele kształtów, oraz z RNA zmieniającymi formę pod wpływem białek w dużych maszynach molekularnych. Jednak jest na tyle szybki, że może przetworzyć wiele modeli RNA o długości kilkuset nukleotydów w ciągu kilku sekund i już pomaga serwerom automatycznym wybierać modele wyższej jakości w testach społecznościowych. Dostarczając niezależnego od metody, analizującego wyłącznie strukturę sędziego modeli RNA, RNArank daje biologom ostrzejszy filtr do przekształcania surowych wyników komputerowych w wiarygodne hipotezy strukturalne, przybliżając dziedzinę do rutynowego, godnego zaufania przewidywania kształtów RNA i — w konsekwencji — do głębszego zrozumienia funkcjonowania tych wszechstronnych cząsteczek.
Cytowanie: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Słowa kluczowe: struktura 3D RNA, głębokie uczenie, ocena jakości modelu, bioinformatyka strukturalna, RNArank