Clear Sky Science · pl
PlantCLR: kontrastowe samouczenie wstępne dla uogólnialnej detekcji chorób roślin
Dlaczego dokładniejsze wykrywanie chorób roślin ma znaczenie
Choroby roślin po cichu odbierają żywność z globalnego stołu, zmniejszając plony i obniżając dochody rolników. W wielu regionach dostępnych jest tylko kilku wyszkolonych specjalistów zdolnych zdiagnozować problemy w terenie, a uzyskanie ich pomocy bywa powolne lub niemożliwe. W badaniu przedstawiono PlantCLR — system komputerowy, który uczy się rozpoznawać choroby na zdjęciach liści przy użyciu znacznie mniejszej liczby etykietowanych przykładów niż zwykle. Poprawiając dokładność, niezawodność i łatwość wdrożenia automatycznej diagnozy na skromnym sprzęcie, praca wskazuje drogę ku narzędziom na smartfony lub tanie kamery, które mogłyby pomóc rolnikom wcześnie wykrywać problemy i chronić plony.
Od zdjęć liści do wczesnych alarmów
Dziś wiele chorób roślin diagnozuje się tradycyjnie: osoba ogląda liść i ocenia, czy plamy, żółknięcie czy skręcanie świadczą o infekcji. Taka ocena może być różna w zależności od eksperta i łatwo zaburzana przez cienie, zagracone tło czy różne fazy wzrostu. Systemy widzenia komputerowego oparte na głębokim uczeniu zaczęły pomagać, ale zwykle wymagają tysięcy starannie oznakowanych zdjęć. W rolnictwie takie etykietowane obrazy są rzadkie i kosztowne w pozyskaniu, podczas gdy ogromne zbiory nieoznakowanych zdjęć z telefonów i kamer polowych często pozostają niewykorzystane. PlantCLR zaprojektowano tak, aby wykorzystać te nieoznaczone dane, ucząc się, jak wyglądają zdrowe i chore liście, zanim zobaczy jakiekolwiek etykiety.
Nauczanie modelu przez porównanie
PlantCLR opiera się na nowoczesnym podejściu zwanym kontrastowym uczeniem samonadzorowanym, w którym model uczy się przez porównywanie obrazów zamiast przez odczytywanie etykiet. Najpierw system bierze nieoznakowane zdjęcie liścia i tworzy dwie nieznacznie różne wersje poprzez losowe przycięcia, obroty, przesunięcia kolorów lub rozmycie. Obie wersje powinny wyraźnie przedstawiać ten sam liść, więc model trenuje się tak, aby traktował je jako dopasowaną parę i nadawał im podobne wewnętrzne reprezentacje, jednocześnie odpychając reprezentacje różnych liści w tej samej partii treningowej. Etap wstępnego uczenia wykorzystuje zwarty, ale nowoczesny rdzeń przetwarzania obrazu o nazwie ConvNeXt-Tiny, połączony z niewielkim dodatkowym modułem używanym tylko podczas tego kroku uczenia przez porównanie. 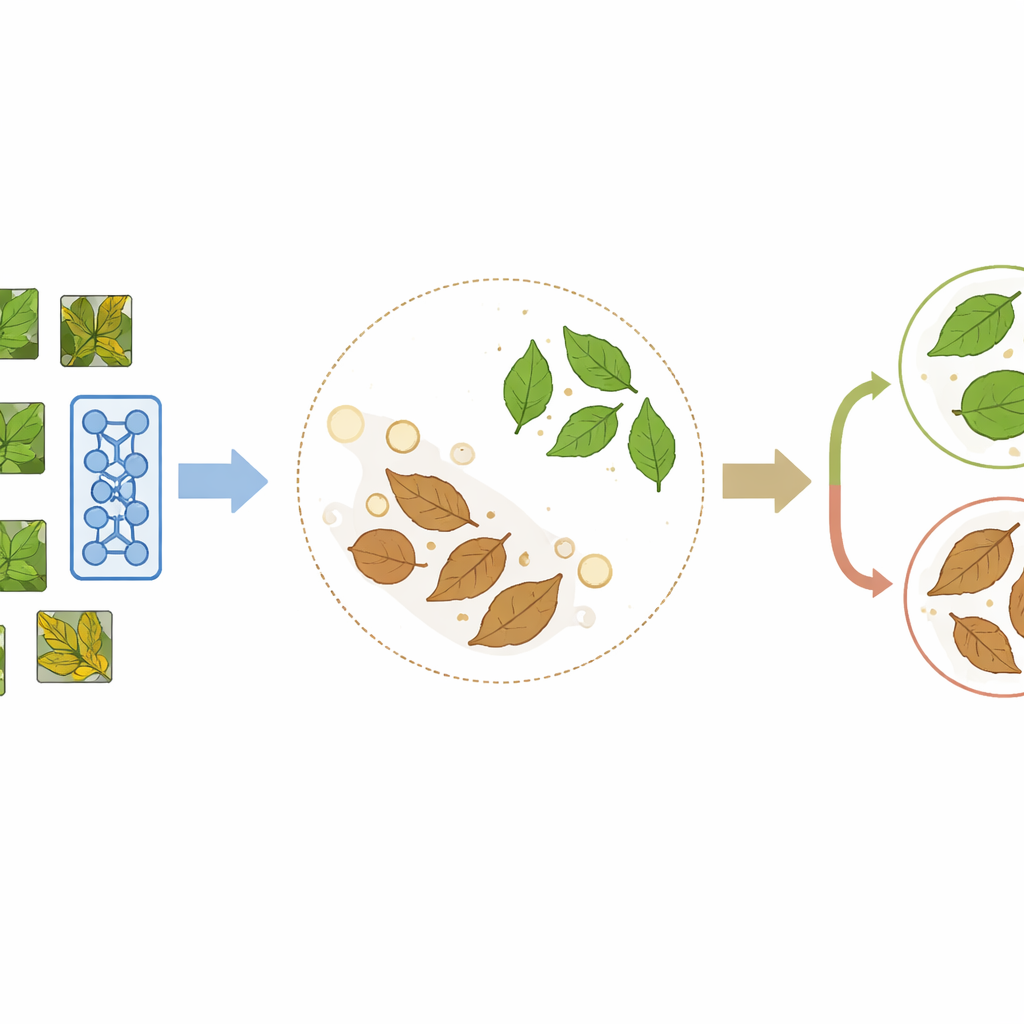
Testowanie systemu
Aby sprawdzić, jak dobrze ta strategia działa w praktyce, autorzy sięgnęli po dwa popularne zbiory zdjęć liści odzwierciedlające bardzo różne warunki terenowe. Zbiór PlantVillage zawiera ponad 54 000 zdjęć liści wykonanych w uporządkowanych, kontrolowanych warunkach, zazwyczaj na czystym tle i z wyraźnymi objawami obejmującymi 38 kategorii chorób i upraw. Dla porównania, zbiór Cassava Leaf Disease zawiera około 21 000 zdjęć liści manioku wykonanych bezpośrednio w polu, z chaotycznym tłem, nierównym oświetleniem i liśćmi zachodzącymi na siebie lub skręconymi pod różnymi kątami, obejmując pięć klas, w tym kilka poważnych infekcji wirusowych i bakteryjnych. W badaniu PlantVillage wykorzystano głównie jako bogate źródło nieoznakowanych obrazów do wstępnego treningu, a następnie oceniono działanie zarówno na tym zbiorze, jak i — co ważniejsze — na trudniejszych, polowych zdjęciach manioku.
Solidna wydajność w zmieniających się warunkach
PlantCLR osiągnął 99,10% dokładności na zestawie testowym PlantVillage oraz 96,83% dokładności na zestawie testowym Cassava, z podobnie wysokimi wynikami F1, które pokazują, że model radzi sobie dobrze nawet z rzadszymi chorobami. Te wyniki przewyższyły szereg znanych sieci głębokich, w tym DenseNet, ResNet, VGG oraz model typu vision transformer, wszystkie trenowane w czysto nadzorowany sposób w dopasowanych warunkach. 
Dlaczego to podejście to krok naprzód
Dla osób nie będących specjalistami kluczowy przekaz jest taki, że PlantCLR pokazuje, jak maszyna może stać się skutecznym „lekarzem roślin”, ucząc się najpierw z dużych zbiorów nieoznakowanych zdjęć, a następnie doszkalając swoje umiejętności na mniejszym, oznakowanym zestawie. Ta strategia nie tylko osiąga bardzo wysoką dokładność, ale też dobrze radzi sobie, gdy kamera przenosi się z laboratorium do pola, gdzie warunki są znacznie mniej uporządkowane. Ponieważ oparty model jest stosunkowo lekki, w przyszłości mógłby zostać wdrożony na niedrogim sprzęcie, czyniąc zaawansowane wykrywanie chorób bardziej dostępnym dla rolników i doradców na całym świecie. Krótko mówiąc, badanie demonstruje praktyczną ścieżkę do skalowalnych, odpornych i efektywnych pod względem etykiet narzędzi monitorowania zdrowia roślin, które mogą pomóc chronić zasoby żywnościowe.
Cytowanie: Shah, S.S.A., Saeed, F., Raza, M.U. et al. PlantCLR: contrastive self-supervised pretraining for generalizable plant disease detection. Sci Rep 16, 10550 (2026). https://doi.org/10.1038/s41598-026-45684-x
Słowa kluczowe: wykrywanie chorób roślin, uczenie samonadzorowane, uczenie kontrastowe, sztuczna inteligencja w rolnictwie, monitorowanie zdrowia upraw