Clear Sky Science · pl
Badanie interakcji białka odpornościowego kolicyny E9 Escherichia coli z gyrazą DNA Pseudomonas aeruginosa: zaawansowane podejście obliczeniowe do opracowywania nowych strategii przeciwbakteryjnych
Przekształcanie bakteryjnych „broni” w nowe leki
W miarę rozprzestrzeniania się oporności na antybiotyki lekarzom ubywa sposobów na powstrzymanie groźnych zakażeń. Niektóre z najbardziej uporczywych bakterii, jak Pseudomonas aeruginosa, są odporne na wiele leków. W tym badaniu szukano inspiracji bezpośrednio w świecie bakterii, analizując, czy wbudowane w nie białko ochronne można wykorzystać do unieruchomienia kluczowego enzymu innego drobnoustroju. Dzięki zaawansowanym symulacjom komputerowym autorzy pokazują, jak małe białko „odpornościowe” może ściśle przylegać do ważnego enzymu bakteryjnego, co wskazuje na potencjalną nową ścieżkę dla przyszłych środków przeciwdrobnoustrojowych.
Mała tarcza przeciw zabójczemu toksynowi
Niektóre szczepy Escherichia coli wytwarzają silne białkowe toksyny zwane kolicynami, które potrafią zabić sąsiednie bakterie. Aby nie zatruć samych siebie, te bakterie produkują też dopasowane białka odpornościowe. Jedno z tych ochronnych białek, znane jako białko odpornościowe kolicyny E9 (często określane jako Im9), wiąże się z domeną tnącą toksyny i zapobiega uszkodzeniu DNA gospodarza. Ponieważ to partnerstwo jest tak specyficzne i silne, naukowcy od dawna podejrzewali, że jego szczegółowe poznanie może ujawnić nowe sposoby kontroli szkodliwych bakterii. W tej pracy autorzy zastanawiają się, czy Im9 mógłby także przyczepić się do gyrazy DNA, niezbędnego enzymu Pseudomonas aeruginosa, który zarządza skręceniem i kopiowaniem jego DNA.
Atak na wrażliwy enzym w trudnym do leczenia drobnoustroju
Pseudomonas aeruginosa to ważny patogen szpitalny, zdolny przetrwać w trudnych warunkach i oporny na wiele leków. Gyraza DNA jest jednym z jego kluczowych enzymów, odpowiedzialnym za utrzymanie długich nici DNA bakterii we właściwym skręcie, co umożliwia ich replikację. Ponieważ zahamowanie tego enzymu może zatrzymać wzrost bakterii, jest on już sprawdzonym celem niektórych antybiotyków. Autorzy wykorzystali narzędzie oparte na głębokim uczeniu do przeszukania trójwymiarowej struktury gyrazy Pseudomonasa i oznaczenia prawdopodobnych „punktów gorących” — skupisk aminokwasów na jej powierzchni, które są najważniejsze dla wiązania partnerów. Regiony te tworzą aktywne kieszenie enzymu, gdzie zachodzi normalne przetwarzanie DNA i gdzie potencjalny inhibitor mógłby się przyczepić.
Symulowanie molekularnego uścisku dłoni
Aby sprawdzić, czy Im9 mógłby złapać te punkty gorące, badacze sięgnęli po programy do dokowania molekularnego, które wirtualnie „dopasowują” białka jak trójwymiarowe puzzle. Najpierw oczyścili i uzupełnili dostępne struktury zarówno Im9, jak i gyrazy DNA, naprawiając brakującą pętlę w enzymie i przeprowadzając krótkie symulacje w celu rozluźnienia naprężonych fragmentów. Następnie użyli dwóch komplementarnych narzędzi dokujących, ClusPro i LightDock, aby wygenerować wiele kandydackich kompleksów. Z tych modeli wybrali najbardziej obiecujące układy i poddali je długim symulacjom dynamiki molekularnej trwającym setki nanosekund. Te czasowo rozstrzelone „filmy” pozwoliły im obserwować, jak oba białka dopasowują się, odkształcają i osadzają w stabilniejszych kształtach po związaniu.
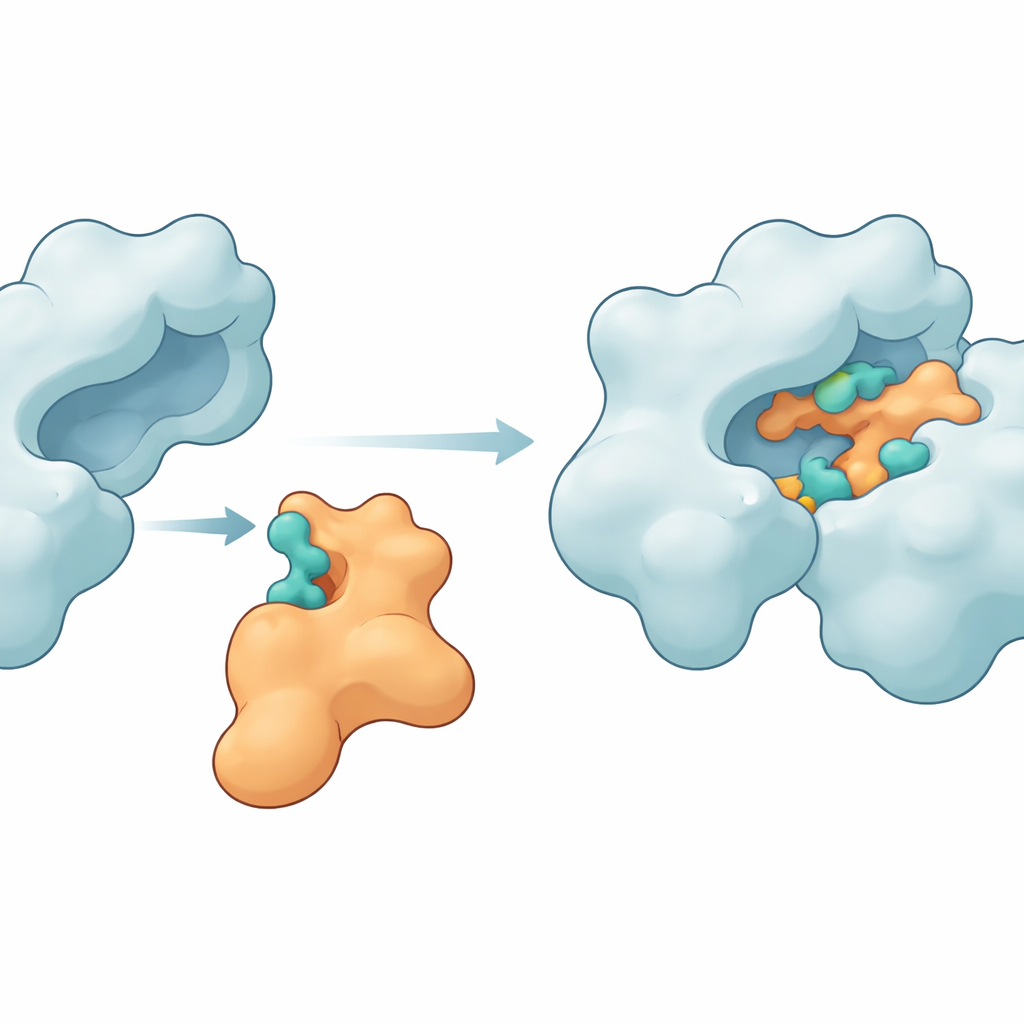
Kluczowe punkty kontaktowe łączące białka
Symulacje wykazały, że Im9 rzeczywiście może utworzyć ciasny i trwały kompleks z gyrazą DNA. Kilka aminokwasów w enzymie — takich jak MET27, ASP47, LYS105, LEU198, ASN199, ARG191 i GLU194 — wielokrotnie tworzyło wiązania wodorowe i inne siły przyciągające z odpowiadającymi miejscami na Im9. W jednym z wiodących modeli obaj partnerzy utrzymywali między sześcioma a dziesięcioma wiązaniami wodorowymi przez większość symulacji, co wskazuje na silny i dobrze zorganizowany interfejs. Inne miary strukturalne, w tym stopień zwartości białek i zakres ich fluktuacji kształtu, pokazały, że enzym pozostał nienaruszony, podczas gdy białko odpornościowe ugięło się na tyle, by dopasować się do powierzchni gyrazy. Obliczenia energii metodą MM-GBSA dodatkowo wspierały tezę, że te kontakty tworzą korzystną, choć umiarkowaną zmianę energii wiązania, zdominowaną przez wkład elektrostatyczny i oddziaływania van der Waalsa.
Od modeli komputerowych do przyszłych środków przeciwdrobnoustrojowych
Łącznie wyniki sugerują, że białko odpornościowe kolicyny E9 może stabilnie wiązać się z miejscem aktywnym gyrazy DNA Pseudomonasa, tworząc długotrwały kompleks, który w zasadzie mógłby blokować normalną rolę enzymu w obróbce DNA. Chociaż ustalenia te opierają się wyłącznie na modelach komputerowych i wciąż wymagają potwierdzenia eksperymentalnego, dostarczają szczegółowego planu, gdzie i jak białkowy inhibitor mógłby się przyczepić. Dla osób nietechnicznych kluczowe przesłanie jest takie, że naturalne bakteryjne „broń” i „tarcze” mogą inspirować nowe strategie przeciw trudnym do leczenia zakażeniom. Dzięki poznaniu tego mikroskopijnego uścisku dłoni w skali atomowej naukowcy przybliżają się do projektowania nowych antybiotyków, które wyłączają kluczowe enzymy bakteryjne, nie szkodząc komórkom ludzkim.
Cytowanie: Alfaraj, R., Alkathiri, F. & Chikhale, R. Investigating Escherichia coli Colicin E9 immunity protein interactions with DNA gyrase of Pseudomonas aeruginosa: advanced computational approach for developing novel antimicrobial strategies. Sci Rep 16, 10786 (2026). https://doi.org/10.1038/s41598-026-44427-2
Słowa kluczowe: oporność na antybiotyki, gyraza DNA, interakcje białko–białko, obliczeniowe projektowanie leków, Pseudomonas aeruginosa