Clear Sky Science · pl
Porównawcza genomika plastydów Hippophae ujawnia powiązania filogenetyczne i dostarcza kandydatów na markery DNA do identyfikacji taksonomicznej
Dlaczego ten wytrzymały krzew ma znaczenie
Rokitnik to wytrzymały krzew, który radzi sobie tam, gdzie wiele innych roślin zawodzi: na zimnych, suchych, wietrznych stokach Wyżyny Qinghai–Tybet i poza nią. Jego jaskrawo pomarańczowe jagody promowane są na całym świecie jako „superowoce”, a roślina jest powszechnie wykorzystywana do stabilizowania gruntów i rekultywacji zdegradowanych obszarów. Nawet eksperci mają jednak trudności z odróżnieniem blisko spokrewnionych gatunków i podgatunków tylko na podstawie wyglądu. W tym badaniu zadano proste, ale istotne pytanie: czy możemy odczytać wewnętrzny instruktaż rośliny — jej DNA — aby rozróżnić poszczególne taksony, i w ten sposób dać hodowcom oraz ochroniarzom przyrody potężne nowe narzędzie do zarządzania tym cennym zasobem?
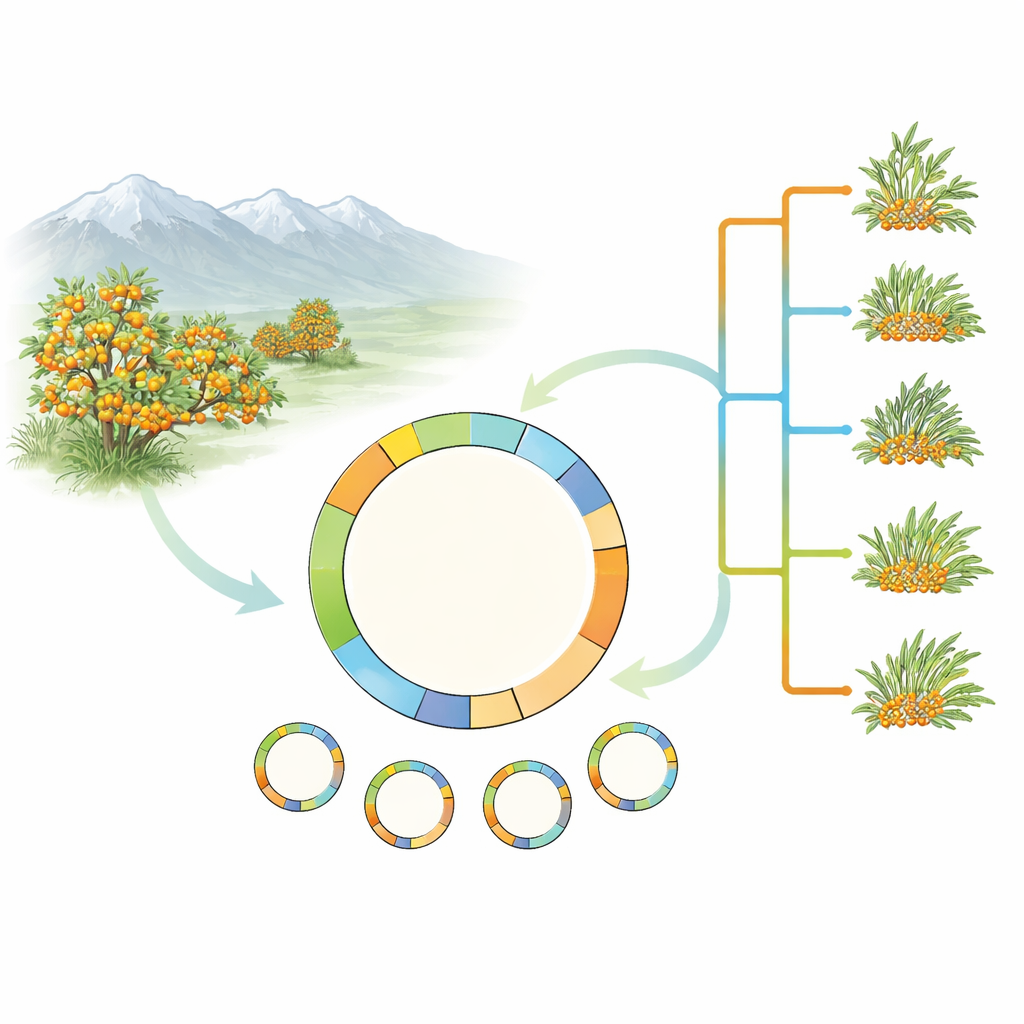
Zajrzeć do zielonych silników rośliny
Zamiast mierzyć się z pełną złożonością genomu rokitnika, badacze skupili się na plastydach — drobnych zielonych organellach w komórkach odpowiedzialnych za fotosyntezę. Plastydy posiadają własną małą, kolistą cząsteczkę DNA, dziedziczoną głównie po matce, która okazała się wyjątkowo przydatna do odtwarzania drzew rodowych roślin. Zespół zebrał i zsekwencjonował kompletne genomy plastydowe z 17 próbek obejmujących pięć gatunków rokitnika oraz kilka form rozpowszechnionego Hippophae rhamnoides. Dodano także nowo złożony genom plastydowy ważnego typu uprawnego, H. rhamnoides subsp. mongolica cv. Prevoskhodnaya, i starannie sprawdzono wcześniejsze wpisy w bazach danych pod kątem błędów.
Wspólny plan z wymownymi różnicami
Na pierwszy rzut oka DNA plastydowe wszystkich próbek rokitnika wyglądało zaskakująco podobnie. Każdy genom miał około 155 000 do 156 000 „liter” i wykazywał ten sam czteroczęściowy układ spotykany u wielu roślin kwitnących: dwie jednonikładowe (single-copy) rejony oddzielone parą zdublowanych segmentów. Ten sam zestaw genów był obecny i ułożony w tej samej kolejności, a nawet ogólny stosunek czterech zasad prawie się nie różnił. Taka stabilność strukturalna sugeruje, że na przestrzeni ewolucji plan plastydowy w Hippophae był zachowany. Gdy jednak badacze przyjrzeli się drobniejszym szczegółom — np. częstotliwości użycia określonych kodonów do zapisu tego samego aminokwasu — odkryli subtelne, specyficzne dla linii wzory, wskazujące na powolne, długoterminowe kształtowanie „kodowania” w różnych gałęziach rodzaju.
Rozplątywanie drzewa rodowego
Wykorzystując 78 genów kodujących białka z DNA plastydowego, zespół zbudował drzewa ewolucyjne umieszczające rokitnika w szerszej rodzinie różowatych, a następnie przyglądające się relacjom wewnątrz Hippophae. Analizy potwierdziły, że rokitnik jako grupa tworzy jedną naturalną linię, a H. rhamnoides wraz z jego podgatunkami również są ściśle powiązane. Intrygująco, jeden gatunek, H. tibetana, konsekwentnie pojawia się wewnątrz grupy H. rhamnoides w drzewie plastydowym, choć wcześniejsze prace z wykorzystaniem DNA jądrowego lokowały go bliżej podstawy rodzaju. Ta niezgodność między historiami jądrowymi a plastydowymi sugeruje przeszłe hybrydyzacje lub inne złożone zdarzenia ewolucyjne i wskazuje na potrzebę przyszłych badań łączących kompletne zbiory danych jądrowych i plastydowych.
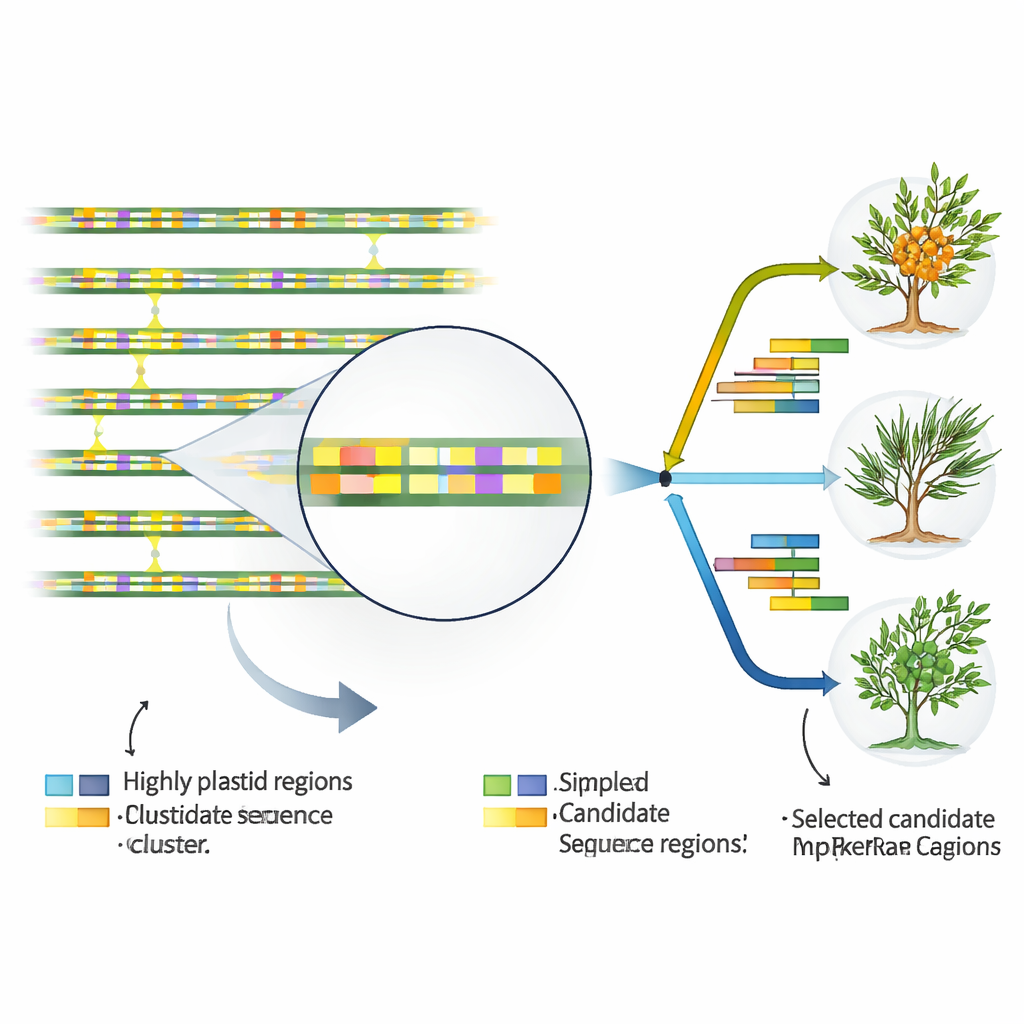
Odnajdywanie genomowych „hotspotów”, które oznaczają tożsamość
Aby przekształcić DNA plastydów w praktyczne narzędzia dla taksonomów i hodowców, autorzy poszukiwali fragmentów sekwencji zmieniających się szybciej niż reszta. Porównując wszystkie 17 genomów plastydowych, wyodrębnili 46 wyjątkowo zmiennych regionów, z których niemal wszystkie leżały między genami lub w niekodujących intronach, a nie w samych eksonach genów. Zmapowali także dziesiątki małych powtarzających się motywów znanych jako proste powtórzenia sekwencji (SSR), które są szczególnie bogate w litery A i T i skupiają się w obszarach niekodujących. Niektóre z tych powtórzeń i zmiennych segmentów wykazywały wyraźne różnice między gatunkami, a nawet między podgatunkami H. rhamnoides. Kilka regionów wyróżniało się jako „hotspoty” zarówno w porównaniach międzygatunkowych, jak i międzypodgatunkowych, co czyni je obiecującymi kandydatami na praktyczne markery DNA, które można badać prostymi testami laboratoryjnymi.
Od wzorców DNA do zastosowań w praktyce
Mapując zarówno stabilne ramy, jak i małe, lecz informatywne różnice w plastydowych genomach rokitnika, to badanie dostarcza zestawu narzędzi do wiarygodnej identyfikacji opartej na DNA. Proponowane regiony-markery mogą pomóc odróżniać podobne do siebie gatunki, weryfikować pochodzenie produktów jagodowych w handlu, chronić dziką różnorodność genetyczną oraz wspierać dobór rodziców w programach hodowlanych skierowanych na wartości odżywcze, zastosowania medyczne i rekultywację gruntów. Mówiąc wprost, autorzy pokazują, że uważnie odczytany chloroplastowy „instruktaż” może ujawnić, kto jest kim w rozszerzonej rodzinie tego odpornego krzewu, torując drogę do mądrzejszej ochrony i bardziej ukierunkowanego wykorzystania jednego z najtwardszych uprawnych owoców na świecie.
Cytowanie: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Słowa kluczowe: rokitnik, genom plastydowy, markery DNA, taksonomia roślin, różnorodność genetyczna