Clear Sky Science · pl
Zautomatyzowany pipeline analizy obrazów do szerokopolowego optycznego obrazowania redoksowego organoidów nowotworowych pochodzenia pacjenta
Dlaczego to badanie obrazowania nowotworów ma znaczenie
Znalezienie odpowiedniego leku dla nowotworu każdej osoby wciąż jest powolnym procesem metodą prób i błędów. To badanie adresuje ten problem, łącząc małe, w laboratorium hodowane guzy pochodzące od pacjentów — zwane organoidami — z szybką, kamerową metodą obserwacji zmian zużycia energii po dodaniu leków. Autorzy pokazują, jak nowy zautomatyzowany pipeline komputerowy potrafi przesiać duże stosy zdjęć mikroskopowych, śledzić setki organoidów przez kilka dni i ujawnić, które terapie działają — znacznie szybciej i bardziej niezawodnie niż człowiek robiący to ręcznie.
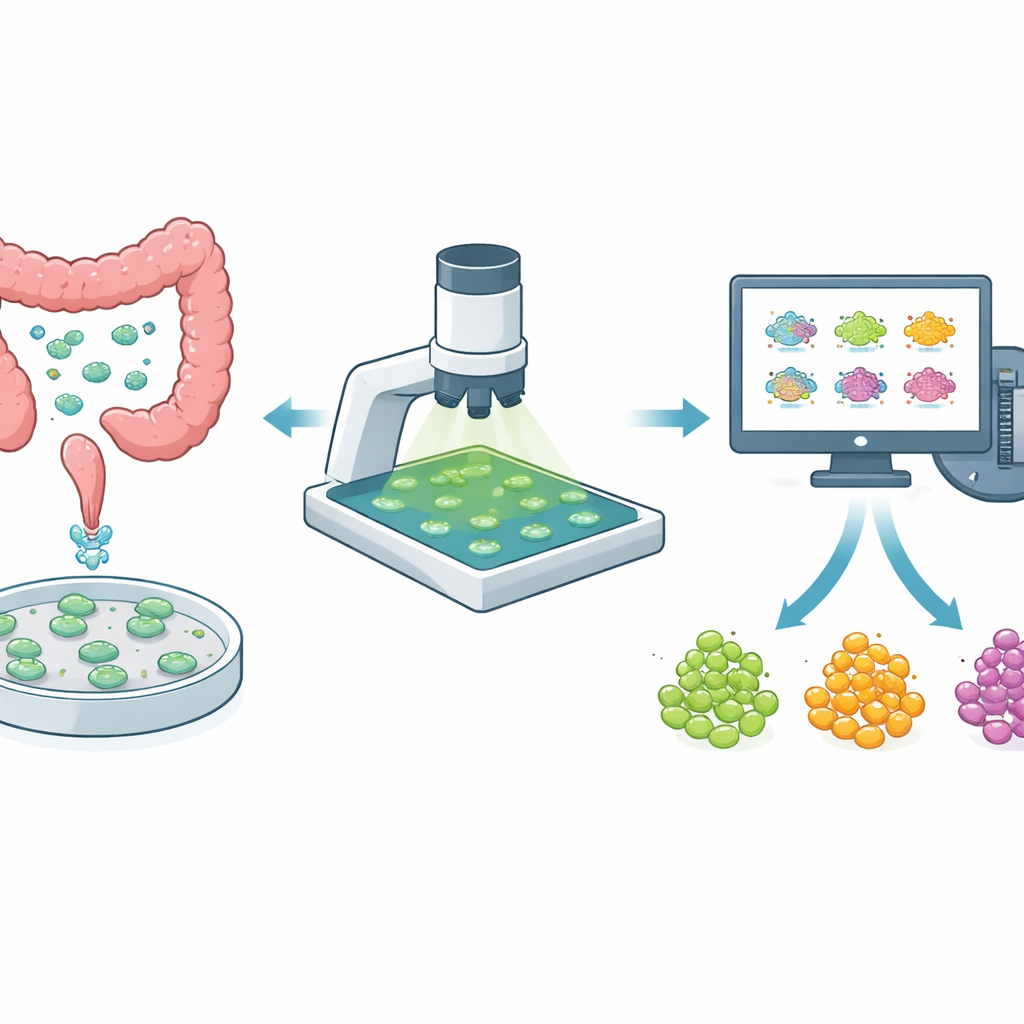
Mini-guzy w naczyniu jako pola testowe
Zamiast polegać wyłącznie na komórkach nowotworowych hodowanych w płaskich warstwach, badacze coraz częściej wykorzystują trójwymiarowe organoidy tworzone bezpośrednio z guza pacjenta. Te mini-guzy lepiej zachowują mieszankę typów komórek i ukryte skupiska komórek opornych na leki, jakie występują w organizmie. W raku jelita grubego, gdzie guzy różnią się znacznie między pacjentami, a nawet w obrębie jednego pacjenta, organoidy stanowią potężne narzędzie do testowania, jak działają nowe i istniejące leki. Aby jednak były użyteczne do kierowania terapią, testy na organoidach muszą być zarówno delikatne — tak by można było obserwować ten sam organoid w czasie — jak i wystarczająco szybkie, by przesiewać wiele leków i dawek.
Obserwacja „zużycia paliwa” guza za pomocą światła
Zespół używa techniki zwanej optycznym obrazowaniem redoksowym, która opiera się na słabym, naturalnym świeceniu się cząsteczek w komórkach zaangażowanych w produkcję energii. Poprzez oświetlenie określonymi kolorami i zbieranie emitowanego fluorescencyjnego sygnału, prosty mikroskop szerokopolowy może uchwycić mapę tego, jak „utleniony” lub „zredukowany” jest dany organoid — migawkę jego stanu metabolicznego. W przeciwieństwie do bardziej skomplikowanych mikroskopów wysokiej klasy, to ustawienie wykorzystuje standardowe komponenty, które wiele laboratoriów już posiada, co ułatwia jego wdrożenie. Zmiany w sygnale redoks często pojawiają się wcześniej niż zmiany wielkości organoidu czy śmierć komórek, co czyni je wczesnym sygnałem ostrzegawczym, czy lek działa czy nie.
Przekształcanie surowych obrazów w wiarygodne liczby
Do tej pory analiza tych obrazów wymagała ręcznego rysowania obrysów każdego organoidu, wybierania obszarów tła wzrokiem, a następnie próby śledzenia, który organoid jest który na przestrzeni kilku dni. Ten powolny, podatny na błędy sposób nie nadaje się do dużych przesiewów leków. Autorzy stworzyli kompleksowy, zautomatyzowany pipeline, który wykonuje trzy trudne zadania: precyzyjne oddzielenie każdego organoidu od otoczenia, przypisanie każdemu stałej tożsamości w kolejnych dniach oraz oszacowanie sygnału tła tak, by uniknąć uprzedzeń ludzkich. Dopracowali istniejące narzędzie sztucznej inteligencji (Cellpose), aby rozpoznawało organoidy nawet gdy różnią się kształtem, rozmiarem i ostrością, a następnie zbudowali algorytm śledzący, który wyrównuje obrazy zrobione w różnych dniach i dopasowuje organoidy na podstawie nakładania się ich kształtów i pozycji.
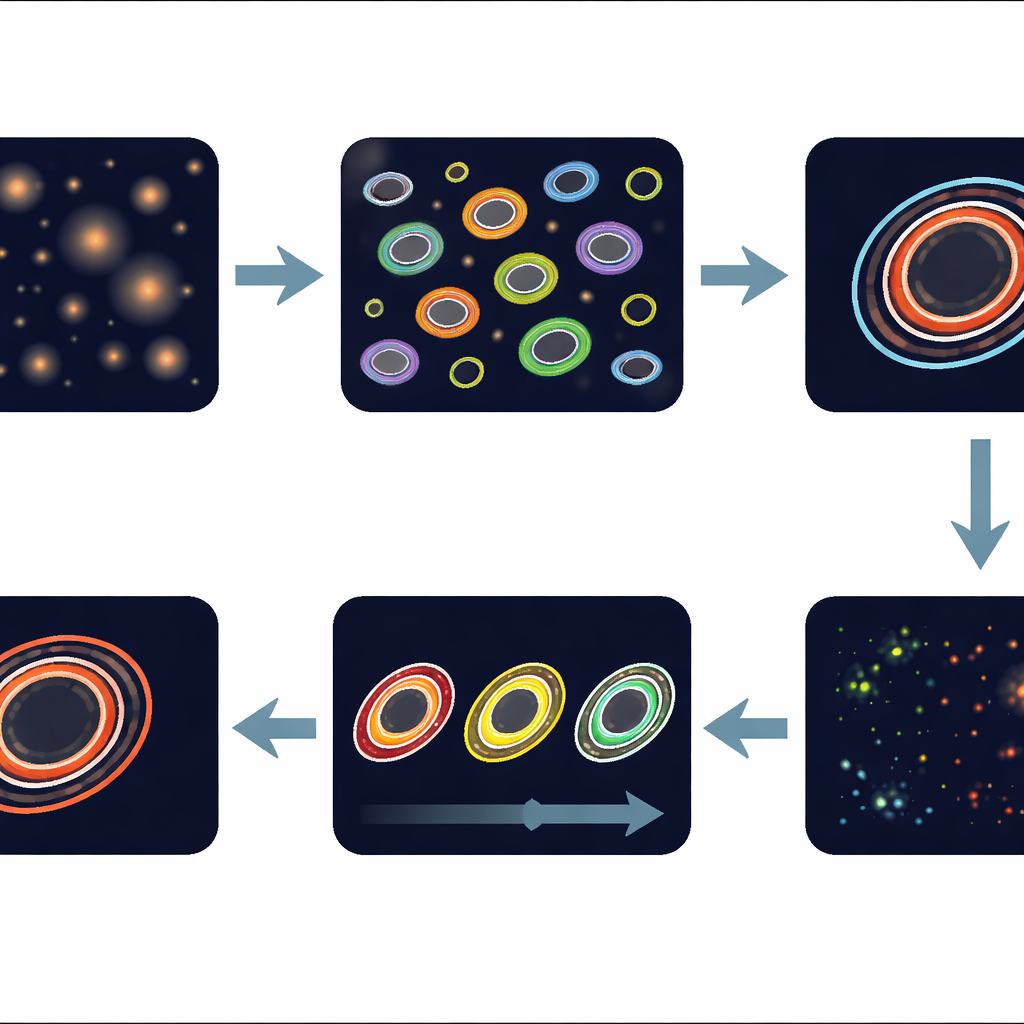
Zbliżenie na najbardziej aktywny brzeg
Organoidy mają wyraźne strefy: martwe lub umierające jądro, spokojny obszar środkowy i żywy zewnętrzny brzeg, gdzie komórki aktywnie rosną i często są najbardziej wrażliwe na leczenie. Pipeline automatycznie wycina ten cienki zewnętrzny pierścień — zwany krawędzią wiodącą — dla każdego organoidu i oblicza jego wartość redoks. Śledząc krawędź wiodącą tego samego organoidu przez trzy dni leczenia różnymi dawkami romidepsyny, oprogramowanie wykrywa subtelne przesunięcia w metabolizmie. Autorzy pokazują, że śledzenie organoid po organoidzie zmniejsza zmienność w porównaniu ze zliczaniem wszystkich organoidów razem, zwiększając moc statystyczną do wykrywania efektów leków nawet gdy odpowiedzi różnią się między mini‑guzami.
Szybsze, bardziej odporne wglądy w odpowiedź na leki
Naukowcy przetestowali swój pipeline na obrazach z dwóch różnych systemów mikroskopowych i stwierdzili, że zautomatyzowane obrysy bardzo dobrze odpowiadały obrysom rysowanym przez ekspertów, a śledzenie zgadzało się z ręcznym śledzeniem ponad 94 procent czasu. Porównując ogólne miary odpowiedzi na lek, metoda zautomatyzowana dorównywała czułości podejścia ręcznego, skracając czas analizy ponad stukrotnie — z wielu godzin pracy człowieka do zaledwie kilku minut przetwarzania komputerowego. Dla laboratoriów pracujących z organoidami pochodzenia pacjenta oznacza to realistyczną możliwość analizowania dużych zbiorów obrazów i odkrywania, jak każdy mini‑guź reaguje na leczenie. W dłuższej perspektywie taka zautomatyzowana analiza może przyspieszyć wprowadzenie testowania leków na organoidach do praktyki klinicznej, wspierając bardziej spersonalizowaną i skuteczną opiekę onkologiczną.
Cytowanie: Hsu, A., Samimi, K., Gillette, A.A. et al. An automated image analysis pipeline for wide-field optical redox imaging of patient-derived cancer organoids. Sci Rep 16, 9757 (2026). https://doi.org/10.1038/s41598-026-40249-4
Słowa kluczowe: rak jelita grubego, organoidy pochodzenia pacjenta, optyczne obrazowanie redoksowe, zautomatyzowana analiza obrazów, odpowiedź na leki