Clear Sky Science · pl
Klinicznie interpretowalny model genów pęcherzyków zewnątrzkomórkowych do nieinwazyjnej diagnostyki raka wątroby
Dlaczego test krwi na raka wątroby ma znaczenie
Rak wątroby jest jednym z najgroźniejszych nowotworów na świecie, w dużej mierze dlatego, że często wykrywany jest zbyt późno, by zastosować leczenie radykalne. Obecne narzędzia do wczesnego wykrywania — badania obrazowe i biopsje wątroby — są kosztowne, czasem ryzykowne i nie zawsze dokładne. W tej pracy badacze rozważają inną koncepcję: czy proste badanie krwi, analizowane przez zaawansowane modele komputerowe, może ujawnić wczesne oznaki raka wątroby poprzez odczytanie drobnych wiadomości genetycznych, które chore komórki wysyłają do krwiobiegu.
Maleńcy posłańcy krążący we krwi
Wszystkie komórki naszego organizmu regularnie uwalniają mikroskopijne pęcherzyki, zwane pęcherzykami zewnątrzkomórkowymi, do krwi i innych płynów ustrojowych. Pęcherzyki te niosą białka, lipidy i fragmenty materiału genetycznego, które odzwierciedlają stan komórek, z których pochodzą. Komórki nowotworowe również uwalniają takie pęcherzyki, ale ich zawartość różni się od tej w komórkach zdrowych. Ponieważ pęcherzyki krążą w krwiobiegu, można je pobrać z prostego pobrania krwi zamiast wkłuwania igły w wątrobę. Autorzy wykorzystali dużą publiczną bazę danych, exoRBase 3.0, która zawiera szczegółowe pomiary materiału genetycznego znalezionego w pęcherzykach od setek osób z rakiem wątroby i bez niego.
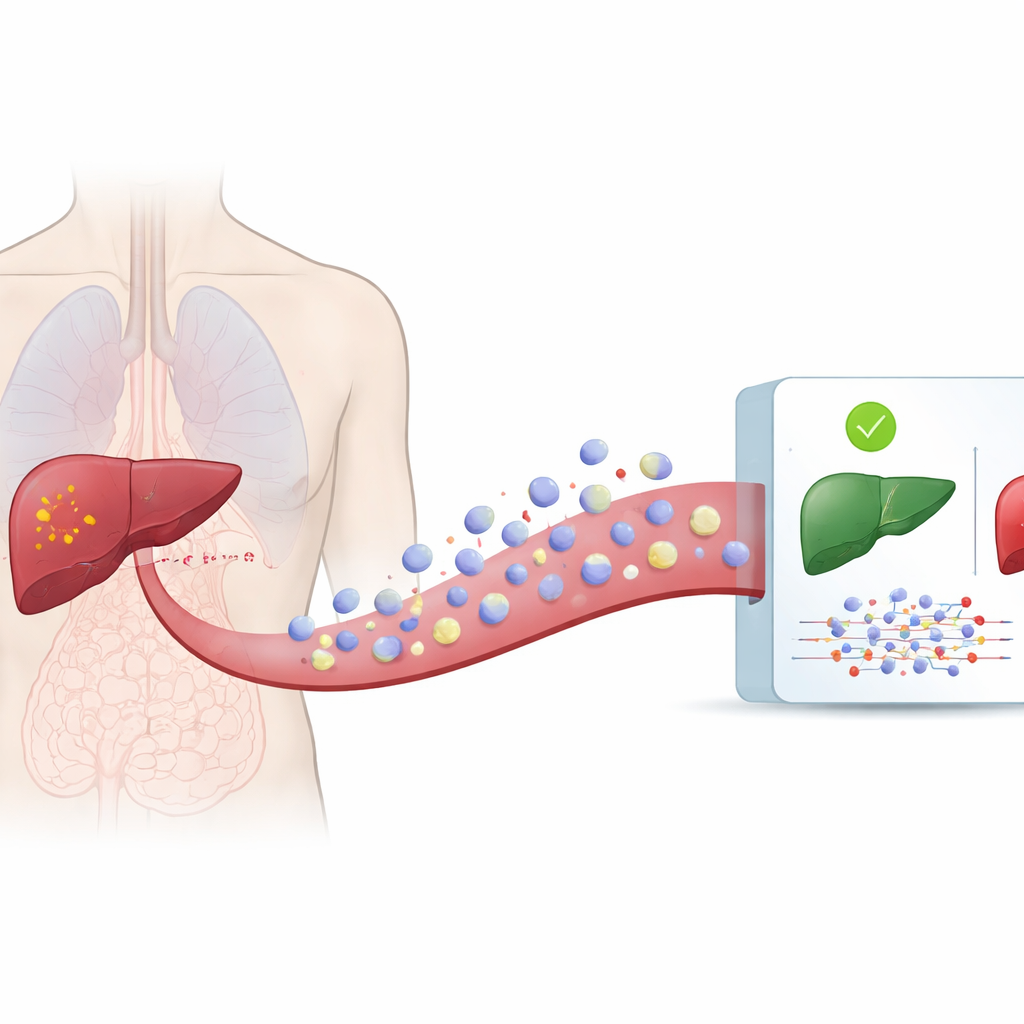
Nauczanie komputerów rozpoznawania sygnałów z pęcherzyków
Z tej bazy zespół zebrał informacje o dwóch typach cząsteczek RNA — mRNA, który niesie instrukcje do wytwarzania białek, oraz długich niekodujących RNA, które pomagają regulować zachowanie komórek. Przeanalizowali próbki od 112 pacjentów z rakiem wątroby i 118 osób zdrowych. Po oczyszczeniu i ustandaryzowaniu danych wytrenowali sześć różnych modeli komputerowych, aby rozróżniały próbki nowotworowe od nienowotworowych na podstawie wzorców w RNA pęcherzyków. Metody te obejmowały narzędzia statystyczne oraz bardziej elastyczne sieci neuronowe głębokiego uczenia, zdolne odkrywać złożone wzorce.
Wyszukanie niewielkiego, ale silnego panelu genów
Sieć neuronowa głębokiego uczenia osiągnęła najlepsze wyniki w tym zbiorze danych, często poprawnie rozdzielając próbki z rakiem od próbek zdrowych. Jednak model oparty na tysiącach pomiarów jest trudny do zrozumienia i niepraktyczny do rutynowych badań. Aby temu zaradzić, badacze zastosowali metodę zwaną SHAP, która pomaga określić, które wejścia mają największe znaczenie dla decyzji modelu. Pozwoliło to zawęzić sygnaturę do zaledwie dziesięciu konkretnych mRNA przenoszonych przez pęcherzyki. Jednym z nich, MTRNR2L8, wyróżniała się jako najsilniejszy wkład w przewidywania modelu, a inne, takie jak HBB, PF4, FTL i S100A9, również odgrywały kluczowe role. Nawet przy użyciu tylko tych dziesięciu RNA model nadal dobrze działał, co sugeruje, że stosunkowo mały, ukierunkowany panel mógłby wystarczyć do testu opartego na krwi.
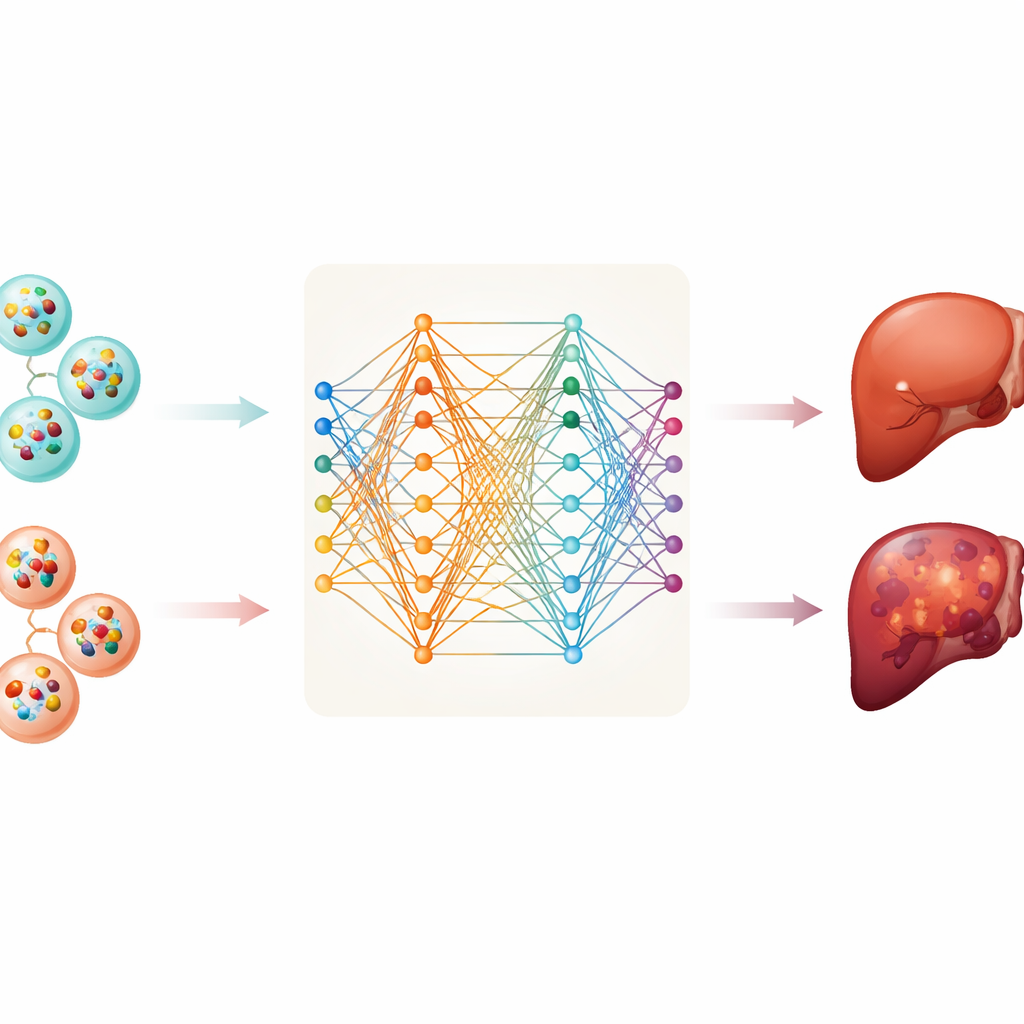
Otwieranie „czarnej skrzynki” sztucznej inteligencji
Lekarze często podchodzą z rezerwą do modeli komputerowych, które dają odpowiedzi bez jasnego uzasadnienia. Aby budować zaufanie, zespół podkreślił przejrzystość. SHAP wykorzystano nie tylko do uszeregowania ważności poszczególnych genów ogólnie, ale także do pokazania, jak dla konkretnego pacjenta każdy gen przesuwał przewidywanie w kierunku „rak” lub „zdrowy”. Naukowcy wypróbowali także nowszy typ sieci — Sieć Kolmogorowa–Arnolda, która reprezentuje zależności między wejściami a wyjściami przy pomocy jawnych krzywych matematycznych. Podejście to potwierdziło, że te same dziesięć genów niesie silne sygnały i zilustrowało, jak ich skumulowane zachowanie kształtuje ostateczną decyzję, oferując bardziej interpretowalny wgląd w to, czego model się nauczył.
Od koncepcji laboratoryjnej do potencjalnego narzędzia klinicznego
Jako dowód koncepcji autorzy przygotowali internetową platformę demonstracyjną, gdzie użytkownicy mogą wprowadzać pomiary genów z pęcherzyków i zobaczyć przewidywane prawdopodobieństwo raka wątroby oraz wizualne rozbicie, które geny wpłynęły na wynik. Zaznaczają jednak, że prace mają charakter eksperymentalny. Model był jak dotąd testowany jedynie na danych z tej samej publicznej bazy, podczas gdy pacjenci w rzeczywistym świecie często mają współistniejące choroby wątroby, różne terapie i techniczne różnice w sposobie pobierania próbek. Zanim taki test będzie mógł być stosowany w szpitalach lub programach przesiewowych, konieczne będą większe, starannie zaprojektowane badania na niezależnych grupach pacjentów — z użyciem ustandaryzowanych metod.
Co to oznacza dla pacjentów
Badanie pokazuje, że niewielki zestaw markerów genetycznych przenoszonych przez drobne cząstki we krwi mógłby w zasadzie pomóc wykryć raka wątroby bez inwazyjnych procedur. Łącząc te markery z modelami komputerowymi, które lekarze mogą rozumieć i weryfikować, praca wskazuje drogę do przyszłych testów krwi, które byłyby zarówno dokładne, jak i godne zaufania. Choć przed zastosowaniem klinicznym pozostaje jeszcze wiele przeszkód, takich jak potwierdzenie wyników w różnych populacjach oraz zapewnienie, że test będzie praktyczny i przystępny cenowo, badania te dają wyobrażenie, jak biopsje płynne i interpretowalna sztuczna inteligencja mogą pewnego dnia umożliwić wcześniejszą i bezpieczniejszą diagnostykę raka wątroby.
Cytowanie: Zhang, Y., Mo, Z., Zhang, L. et al. Clinically interpretable extracellular vesicle gene model for Non-Invasive liver cancer diagnosis. Sci Rep 16, 9054 (2026). https://doi.org/10.1038/s41598-026-40020-9
Słowa kluczowe: rak wątroby, biopsja płynna, pęcherzyki zewnątrzkomórkowe, uczenie maszynowe, wcześniejsza diagnoza