Clear Sky Science · pl
Wzmacniana dekonwolucja sterowana uwagą umożliwia bezodwoławczą estymację typów komórek w transkryptomice przestrzennej
Widzieć komórki na miejscu
Nowoczesna biologia potrafi odczytywać aktywność tysięcy genów jednocześnie — nie tylko w izolowanych komórkach, lecz bezpośrednio w cienkich przekrojach tkanki. Ten „pogląd transkryptomiczny przestrzenny” ujawnia, gdzie różne komórki występują i wchodzą w interakcje, ale każde pomiar często miesza sygnały wielu sąsiednich komórek. W badaniu wprowadzono nową metodę obliczeniową, nazwaną AGED, która potrafi rozplątać te mieszaniny i oszacować, jakie typy komórek występują w danym miejscu — bez potrzeby korzystania z oddzielnego, dokładnie dopasowanego zestawu referencyjnego z pojedynczych komórek. 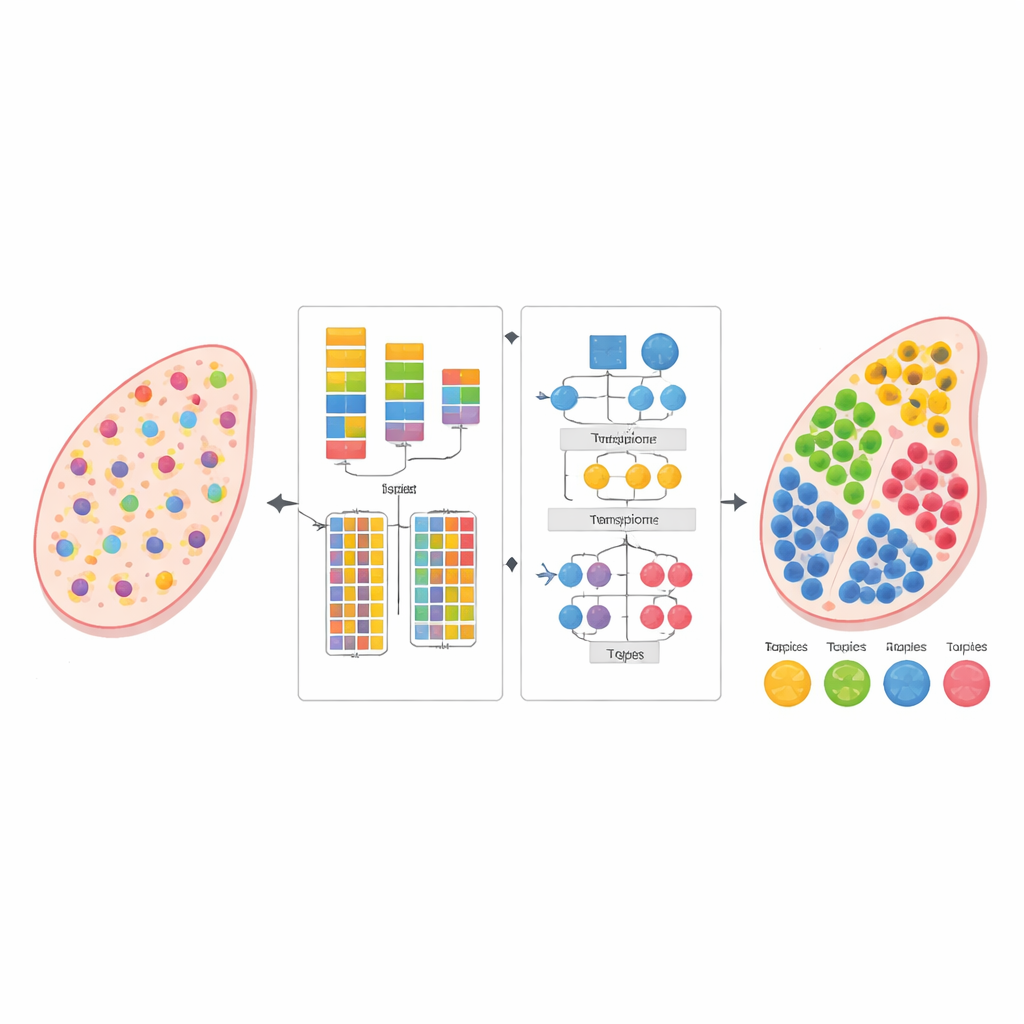
Dlaczego mapowanie komórek w tkankach jest trudne
Platformy transkryptomiki przestrzennej mierzą aktywność genów na siatce punktów umieszczonej na przekroju tkanki. Ponieważ większość punktów rejestruje kilka komórek jednocześnie, badacze muszą matematycznie rozłożyć zmieszane sygnały, aby odtworzyć bazowe typy komórek i ich proporcje. Istniejące narzędzia często opierają się na zewnętrznych atlasach pojedynczych komórek dla tej samej tkanki. Takie atlasy mogą nie istnieć dla rzadkich tkanek, specyficznych stanów chorobowych lub nietypowych warunków eksperymentalnych, a nawet gdy są dostępne, nie zawsze idealnie pasują, wprowadzając uprzedzenia. Metody bezodwoławcze unikają tej zależności, ale obecne podejścia mają trudności z złożonymi wzorcami przestrzennymi, subtelnymi relacjami między genami oraz wyzwaniem polegającym na określeniu, ile odrębnych typów komórek w ogóle szukać.
Dwustopniowa strategia rozplątywania mieszanin
Autorzy zaprojektowali AGED jako ramę dwuetapową, łączącą pomysły ze statystyki i nowoczesnego uczenia głębokiego. W pierwszym etapie metoda testuje zakres możliwości dotyczących liczby typów komórek, które mogą występować w tkance. Wykorzystuje szybką sieć neuronową opartą na mechanizmie uwagi, znaną jako Performer, do uczenia kandydatów rozkładów, a następnie ocenia je przy użyciu kilku kryteriów: jak dobrze model rekonstruuje obserwowane liczby genów, jak wyraźnie rozdzielają się wniosowane grupy komórek oraz jak zróżnicowane są te grupy. Procedura dopasowania krzywej znajduje punkt „kolana”, w którym dodanie kolejnych typów komórek przynosi niewielkie korzyści, pozwalając metodzie automatycznie wybrać odpowiednią liczbę zamiast polegać na zgadywaniu użytkownika.
Sterowana uwaga dla uchwycenia biologii
Gdy liczba typów komórek zostanie ustalona, drugi etap AGED dopracowuje rozwiązanie z użyciem bogatszej architektury opartej na uwadze. Rozpoczyna się od statystycznego modelu tematycznego, który traktuje każdy punkt tkanki jako mieszankę ukrytych „tematów” — tutaj zastępujących typy komórek — a każdy typ komórki jako charakterystyczny wzór genowy. Te początkowe tematy dostarczają struktury globalnej. Następnie model nakłada kilka mechanizmów uwagi: jeden łączy tematy statystyczne z siecią neuronową, drugi agreguje informacje z sąsiednich punktów w przestrzeni fizycznej, a trzeci wiąże tematy bezpośrednio z genami. System bramek pozwala modelowi zdecydować, w każdym przypadku, ile ufać wcześniejszym statystycznym wzorcom w porównaniu z lokalnymi danymi. Dodatkowe ograniczenia zachęcają do rozwiązań rzadkich, odzwierciedlając biologiczną rzeczywistość, że większość lokalizacji tkanki jest zdominowana przez tylko kilka głównych typów komórek. 
Próba w warunkach rzeczywistych
Badacze ocenili AGED na kilku typach danych. W symulowanej tkance opuszki węchowej myszy metoda odtworzyła cztery znane warstwy anatomiczne i lepiej dopasowała rzeczywiste składniki komórkowe niż powszechnie używane narzędzia oparte na referencjach i bez referencji, osiągając zarówno wysoką korelację z prawdą ziemi, jak i niski błąd rekonstruowania. W ludzkim gruczolakoraku przewodów trzustkowych AGED automatycznie wybrał rozwiązanie z dwudziestoma typami komórek, które zgadzało się z regionami adnotowanymi przez patologów, takimi jak guz, przewód i normalna trzustka, przewyższając inne metody w miarę podobieństwa strukturalnego porównującego wniosowane mapy z widoczną strukturą tkanki. W tkance grasicy człowieka AGED dokładnie rozdzielił kluczowe populacje komórek i uchwycił biologicznie oczekiwaną negatywną relację między dwoma wyspecjalizowanymi typami komórek nabłonkowych — wzorzec, którego konkurencyjne podejścia nie potrafiły odtworzyć. Dodatkowe analizy na innych zestawach danych i w rozdzielczości zbliżonej do pojedynczych komórek dodatkowo potwierdziły odporność metody.
Co to oznacza w przyszłości
Dla osoby niebędącej specjalistą AGED można widzieć jako inteligentny silnik rozdzielający mieszaniny w złożonych tkankach: uczy się, ile odrębnych społeczności komórkowych występuje, gdzie się znajdują i które geny je definiują — wszystko na podstawie samych danych przestrzennych. Poprzez splecenie interpretowalnych modeli statystycznych z elastycznymi sieciami neuronowymi opartymi na uwadze, ramy te oferują zarówno dokładność, jak i wgląd, nawet gdy nie istnieje odpowiedni atlas referencyjny. Czyni to narzędzie praktycznym do badania organizacji tkanek w zdrowiu i chorobie — od warstw mózgu po guzy i narządy odpornościowe — i wskazuje szerszą strategię używania wiedzy uprzedniej do kierowania potężnymi, ale nieprzezroczystymi modelami uczenia maszynowego w biologii.
Cytowanie: Yang, X., Wang, Y. & Chen, X. Attention-guided enhanced deconvolution enables reference-free cell type estimation in spatial transcriptomics. Sci Rep 16, 8097 (2026). https://doi.org/10.1038/s41598-026-39703-0
Słowa kluczowe: transkryptomika przestrzenna, dekonwolucja typów komórek, uczenie głębokie, architektura tkanki, analiza bez odwołań