Clear Sky Science · pl
Nowe markery genetyczne do jednoczesnego wykrywania Salmonella, EHEC O157:H7 i Cronobacter
Dlaczego to ma znaczenie dla codziennego bezpieczeństwa żywności
Od sałat po burgery i mleko modyfikowane — produkty, którym ufamy, czasami mogą zawierać niebezpieczne drobnoustroje. Trzy z najbardziej niepokojących sprawców — niektóre szczepy E. coli, Salmonella oraz mniej znana bakteria Cronobacter — mogą wywoływać ciężkie choroby, szczególnie u małych dzieci i osób wrażliwych. Badanie to pokazuje, jak naukowcy wykorzystują ogromne bazy danych DNA i sprytne testy laboratoryjne, aby jednocześnie wykrywać wszystkie trzy zagrożenia szybko i dokładnie, zanim skażona żywność trafi na twój stół.
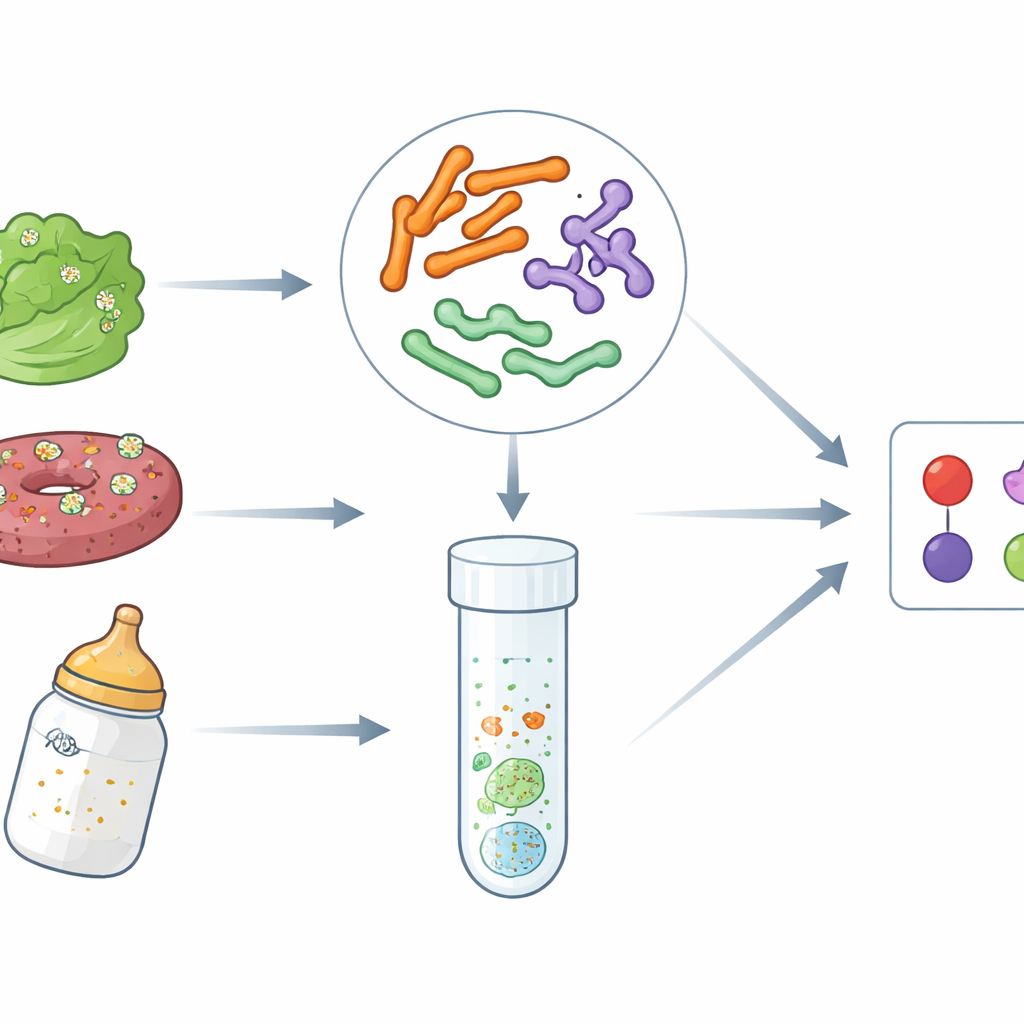
Ukryte zagrożenia w powszechnych produktach
Choroby przenoszone przez żywność wzrosły w ciągu ostatniej dekady, częściowo z powodu globalnych łańcuchów dostaw i ogromnej liczby produktów przetworzonych i gotowych do spożycia. EHEC O157:H7, wysoce toksyczna forma E. coli, może wywoływać krwotoczną biegunkę i niewydolność nerek. Salmonella powoduje miliony zatruć pokarmowych rocznie, a Cronobacter, choć mniej znany, może być śmiertelny dla noworodków, zwłaszcza w związku z proszkiem do przygotowywania mleka modyfikowanego. Tradycyjne metody laboratoryjne często koncentrują się na jednym patogenie naraz i wymagają dni hodowli, co spowalnia dochodzenia epidemiologiczne i rutynowe badania przesiewowe. Autorzy postawili sobie za cel opracowanie szybszych testów opartych na DNA, które mogą wykrywać te trzy patogeny razem w jednej, uproszczonej procedurze.
Znajdowanie „kodów kreskowych” w morzu DNA
Aby to osiągnąć, zespół najpierw potrzebował wiarygodnych genetycznych „kodów kreskowych” — krótkich fragmentów DNA obecnych w niemal wszystkich szczepach danego patogenu, ale nieobecnych u innych. Zamiast przeszukiwać kilka genomów, sięgnęli do ogromnej publicznej kolekcji 1,46 miliona genomów bakteryjnych z 50 różnych rodzajów. W przypadku EHEC O157:H7 porównali tysiące genomów E. coli i przeanalizowali ponad 100 000 rodzin genów dodatkowych, by znaleźć sekwencje DNA unikalne dla tego niebezpiecznego podtypu. Po kilku rundach filtrowania i weryfikacji wobec ponad miliona nie-E. coli genomów wytypowali gen nazwany z0340 jako wysoce swoisty marker dla EHEC O157:H7. Stosując podobną strategię na ponad pół milionie genomów Salmonella i niemal milionie innych genomów bakteryjnych, zidentyfikowali inny gen, sbcC, jako wiarygodny marker dla grupy Salmonella jako całości.
Przekształcenie markerów w testy praktyczne
Z tymi dwoma nowymi kodami kreskowymi — oraz specyficznym dla Cronobacter genu ygcB, który grupa wcześniej odkryła — badacze zaprojektowali testy laboratoryjne zdolne wykrywać wszystkie trzy patogeny jednocześnie. Zbudowali assay PCR multipleksowy, który działa jak molekularna kserokopiarka celująca w określone fragmenty DNA, oraz bardziej czułą wersję TaqMan qPCR, mierzącą w czasie rzeczywistym ilość docelowego DNA. Gdy testy poddano próbie z 23 szczepami tych trzech patogenów i 100 szczepami innych powszechnych bakterii, poprawnie rozpoznawały tylko zamierzone cele za każdym razem, wykazując 100% swoistości. Podstawowy PCR multipleksowy wykrywał nawet 1 pikogram DNA na mikrolitr, podczas gdy wersja TaqMan sięgała 0,5 pikograma, co wskazuje na wysoką czułość.
Próba metod na żywności
Dokładność w laboratorium ma sens tylko wtedy, gdy testy działają w złożonych, rzeczywistych próbkach. Aby to sprawdzić, naukowcy celowo skażali sałatę, wołowinę mieloną i proszek do przygotowywania mleka modyfikowanego znanymi ilościami EHEC O157:H7, Salmonella lub Cronobacter. Po standardowych etapach namnażania, pozwalających bakteriom wzrosnąć, zastosowali swoje assay PCR multipleksowy i TaqMan qPCR. We wszystkich przypadkach metody prawidłowo wykryły wprowadzony patogen i nie dały fałszywych alarmów w próbach negatywnych. Wyniki były spójne we wszystkich trzech typach żywności, co sugeruje, że tłuszcze, składniki roślinne czy złożone dodatki nie miały zauważalnego wpływu na wykrywanie.
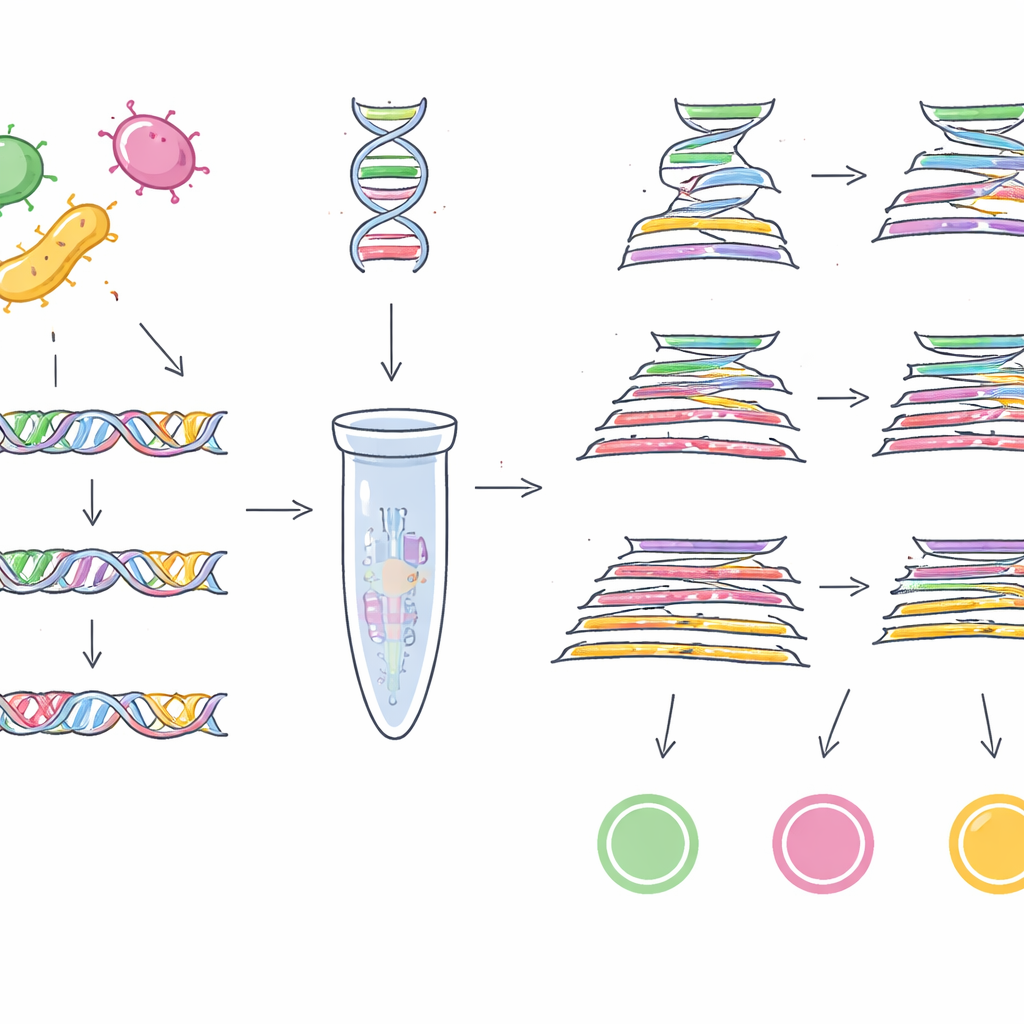
Ograniczenia i przyszłe usprawnienia
Mimo mocnych rezultatów autorzy zaznaczają, że ich panel walidacyjny nadal reprezentuje jedynie ułamek różnorodności mikrobów występującej w przyrodzie. Na przykład w laboratorium przetestowali tylko jeden szczep EHEC O157:H7, choć ich przegląd genomowy obejmował dziesiątki tysięcy takich szczepów. Pracowali też z relatywnie wysokimi poziomami zanieczyszczeń w porównaniu z niezwykle niskimi liczbami bakterii, które wciąż mogą powodować choroby. Przyszłe prace będą musiały przebadać znacznie więcej izolowanych szczepów z rzeczywistych przypadków, przeanalizować naturalnie skażone produkty oraz dodać wewnętrzne kontrole, które ochronią przed substancjami w żywności hamującymi amplifikację DNA.
Co to oznacza dla konsumentów
Mówiąc prosto, badanie to pokazuje, że starannie dobrane genetyczne kody kreskowe mogą pozwolić laboratoriom zajmującym się bezpieczeństwem żywności przesiewać wiele wysokiego ryzyka drobnoustrojów jednocześnie, z dużą dokładnością i w krótszym czasie niż tradycyjne metody oparte na hodowli. Poprzez przeszukanie milionów genomów, badacze zidentyfikowali trzy sygnatury genetyczne — jedną dla EHEC O157:H7, jedną dla Salmonella i jedną dla Cronobacter — które wydają się być zarówno wysoce swoiste, jak i stabilne. Opracowane testy mogłyby wzmocnić rutynowy nadzór nad żywnością, taką jak sałaty, mięsa czy mleko modyfikowane, wykrywając skażenia wcześniej i bardziej niezawodnie. Poza tymi trzema patogenami ta sama podejście oparte na genomach może posłużyć do zaprojektowania szybkich testów dla wielu innych groźnych mikroorganizmów, oferując potężne narzędzie do zwiększenia bezpieczeństwa globalnych łańcuchów żywnościowych.
Cytowanie: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Słowa kluczowe: patogeny przenoszone przez żywność, PCR multipleksowy, markery genomowe, Salmonella i EHEC, wykrywanie Cronobacter