Clear Sky Science · pl
Badawcze badanie pilotażowe nad spójnością protokołów i powtarzalnością miar grafowych w konektomach ważonych mikrostrukturą
Dlaczego mapie okablowania mózgu potrzebny jest test wiarygodności
Lekarze i naukowcy coraz częściej patrzą na mózg jak na ogromną mapę okablowania, gdzie obszary komunikują się ze sobą za pośrednictwem pęczków włókien nerwowych. Nowe metody oparte na MRI potrafią przekształcić to okablowanie w matematyczne sieci, które mogą ujawniać wczesne oznaki chorób, takich jak stwardnienie rozsiane czy choroba Alzheimera. Zanim jednak takie pomiary zaczną kierować rozpoznaniem lub leczeniem, musimy poznać coś podstawowego: czy zeskanowanie tego samego zdrowego mózgu wielokrotnie, albo na różnych skanerach z nieco odmiennymi ustawieniami, da w zasadzie tę samą sieć?
Od ruchu wody do map mózgowych autostrad
Aby zbudować te mapy okablowania, autorzy wykorzystują formę MRI, która śledzi, jak poruszają się cząsteczki wody w tkance mózgowej. W istocie białej, gdzie biegną długie, izolowane włókna nerwowe, woda ma tendencję do poruszania się wzdłuż włókien, a nie przez nie. Pomiar tego ruchu w wielu orientacjach pozwala algorytmom komputerowym wnioskować o pęczkach włókien i składać „konektom” – macierz, która rejestruje, które obszary istoty szarej są połączone przez jakie drogi białej istoty. Zamiast jedynie liczyć, ile wirtualnych włókien odtworzono między regionami, to badanie koncentruje się na konektomach „ważonych mikrostrukturą”, gdzie każde połączenie jest opisane właściwościami tkanki, takimi jak uporządkowanie włókien czy ich pozorna gęstość.
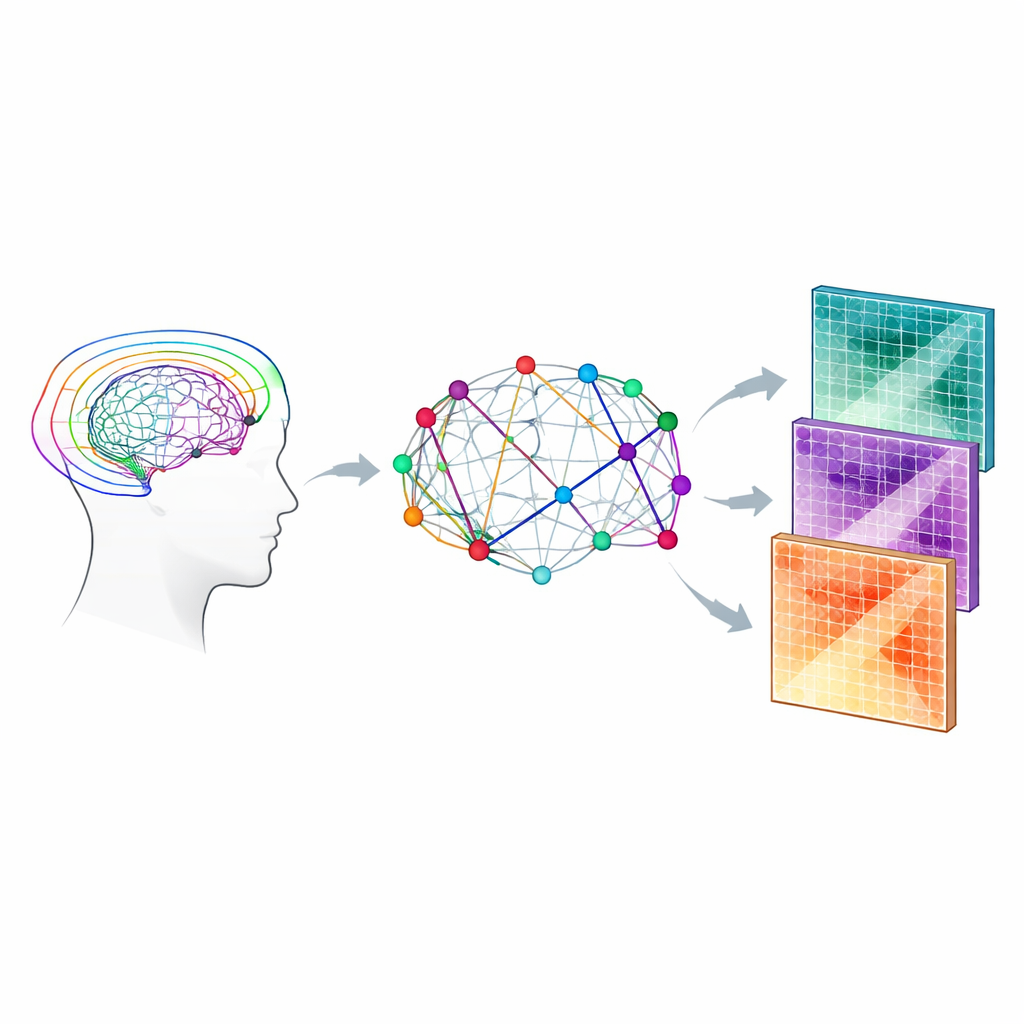
Dodawanie biologicznych szczegółów do sieci
Zespół połączył dwie rodziny modeli interpretujących sygnał dyfuzji MRI. Pierwszy, obrazowanie tensora dyfuzji, podsumowuje, jak kierunkowy jest ruch wody i jak szybko dyfunduje średnio. Drugi, zwany Bingham-NODDI, idzie o krok dalej, szacując, ile w każdej małej objętości tkanki stanowi woda wewnątrz włókien nerwowych, poza nimi lub w przestrzeniach wypełnionych płynem. Używając stosunkowo bogatego protokołu skanowania „cztero-skalowego” zaprojektowanego tak, by lepiej uchwycić złożoną geometrię włókien, obliczono kilka parametrów mikrostrukturalnych, w tym frakcję anizotropii i średnią dyfuzywność (z modelu tensora) oraz frakcje objętości wewnątrz-neuronalnej i zewnątrzkomórkowej (z Bingham-NODDI). Parametry te zostały następnie przeniesione wzdłuż każdego odtworzonego pęczka włókien i połączone, aby nadać biologicznie uzasadnioną wagę każdemu połączeniu w sieci.
Wystawienie potoku na próbę
Powtarzalność oceniano na trzy komplementarne sposoby. Po pierwsze, badacze wielokrotnie skanowali starannie zaprojektowany fizyczny fantom – plątaninę syntetycznych włókien w słonej wodzie, która naśladuje kluczowe cechy tkanki mózgowej – aby przetestować, jak stabilne są parametry w krótkich odstępach czasu. Następnie zeskanowali czterech zdrowych ochotników w dwóch szpitalach, używając tego samego modelu i marki skanera MRI oraz tych samych ustawień, by zbadać różnice między lokalizacjami. Wreszcie porównali protokół czteroskalowy z krótszym, bardziej konwencjonalnym protokołem dwuskalowym, pytając, czy oba dają podobne wartości parametrów. Dla danych mózgowych odtworzono wiele wersji konektomu ważonego różnymi parametrami i wyodrębniono miary grafowe, takie jak ogólna efektywność sieci, stopień grupowania połączeń oraz jak silnie każdy region łączy się z resztą mózgu. Następnie sprawdzono, jak bardzo te miary zmieniają się między miejscami oraz jak duża część zmienności odzwierciedla rzeczywiste różnice między osobami, a nie szum pomiarowy.
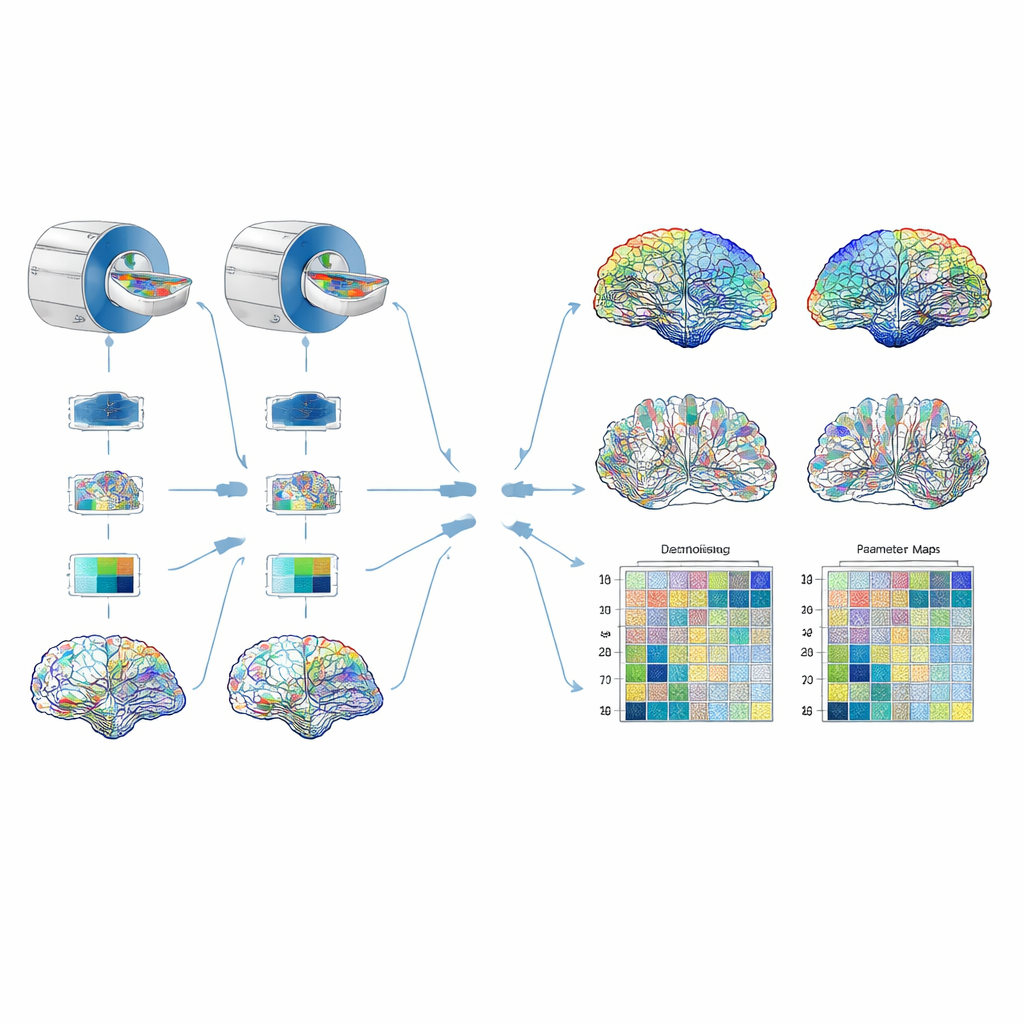
Co okazało się godne zaufania
Kilka kluczowych miar tkankowych okazało się niezwykle spójnych. Frakcja anizotropii, średnia dyfuzywność oraz frakcje objętości wewnątrz-neuronalnej i wewnątrzkomórkowej różniły się o mniej niż pięć procent w powtarzanych skanach, między różnymi lokalizacjami i (w większości regionów) między protokołami dwuskalowym a czteroskalowym. Natomiast wielkości opisujące rozproszenie orientacji włókien – oraz związany z nimi parametr „koncentracji” – były bardziej niestabilne i w związku z tym wyłączono je z konstrukcji sieci. Gdy badacze zbudowali konektomy ważone najbardziej stabilnymi miarami, wiele właściwości sieci, w tym gęstość, efektywność globalna, średnie grupowanie i średnia siła połączeń, było powtarzalnych między miejscami. Wyjątkiem była modularność, miara tego, jak wyraźnie sieć dzieli się na odrębne społeczności; okazała się ona szczególnie wrażliwa na niewielkie zmiany w wagach. Konektomy ważone frakcją objętości zewnątrzkomórkowej wypadły najsłabiej, z kilkoma miarami grafowymi wykazującymi słabą zgodność między miejscami.
Dlaczego to ma znaczenie dla zdrowia mózgu
Badanie pokazuje, że samo liczenie odtworzonych włókien nie wystarcza przy poszukiwaniu markerów chorób w okablowaniu mózgu. Poprzez staranny dobór stabilnych parametrów mikrostrukturalnych do ważenia każdego połączenia, badacze mogą budować bogatsze, biologicznie ugruntowane sieci, których kluczowe właściwości są powtarzalne między skanerami i protokołami. W testowanych warunkach konektomy ważone frakcją anizotropii, średnią dyfuzywnością i frakcją objętości wewnątrz-neuronalnej wydawały się na tyle odporne, że ich podstawowe statystyki sieciowe mogłyby pełnić rolę kandydatów na markery w zaburzeniach naruszających łączność mózgu. Jednocześnie praca wskazuje na bardziej kruche miary, takie jak modularność i niektóre zaawansowane wskaźniki mikrostrukturalne, które należy traktować ostrożnie, dopóki większe, wieloośrodkowe badania nie potwierdzą ich wiarygodności.
Cytowanie: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Słowa kluczowe: łączność mózgu, dyfuzyjne MRI, konektom, powtarzalność sieci, obrazowanie mikrostruktury