Clear Sky Science · pl
Nowa splotowa sieć neuronowa do identyfikacji bakterii w danych konfokalnej mikroskopii
Dlaczego szybkie wykrywanie zarazków ma znaczenie
Gdy lekarze próbują ustalić, które bakterie wywołują infekcję, czas jest kluczowy. Tradycyjne testy laboratoryjne mogą trwać wiele godzin, a nawet dni, i wymagają wysoko wykwalifikowanych ekspertów do oceny obrazów mikroskopowych wzrokiem. W tym badaniu przedstawiono nowy system widzenia komputerowego, nazwany CM-Net, który potrafi automatycznie odczytywać specjalistyczne obrazy mikroskopowe i szybko rozróżniać dwa powszechne, istotne medycznie gatunki bakterii, jednocześnie rozpoznając, które komórki są żywe, a które martwe. Praca sugeruje drogę do szybszej, bardziej niezawodnej diagnostyki, która pewnego dnia mogłaby być stosowana w szpitalach i laboratoriach badawczych na całym świecie.
Przekształcanie świecących zarazków w użyteczne obrazy
Naukowcy zaczęli od potężnego narzędzia obrazowania, znanego jako konfokalna mikroskopia skaningowa laserowa. Mówiąc prosto, mikroskop ten używa skupionego lasera i barwników fluorescencyjnych, aby sprawić, że bakterie świecą na różne kolory w zależności od tego, czy są żywe, czy martwe. Żywe komórki widoczne są na zielono, natomiast martwe na czerwono. Poprzez skanowanie próbki w bardzo cienkich warstwach mikroskop buduje ostre, szczegółowe obrazy bakterii na szkiełkach. Zespół pracował z dwoma dobrze znanymi gatunkami często wywołującymi infekcje szpitalne: pałeczkowatym Escherichia coli oraz kulistym Staphylococcus aureus. Te wysokiej jakości obrazy stanowią surowy materiał, który CM-Net musi się nauczyć rozumieć.
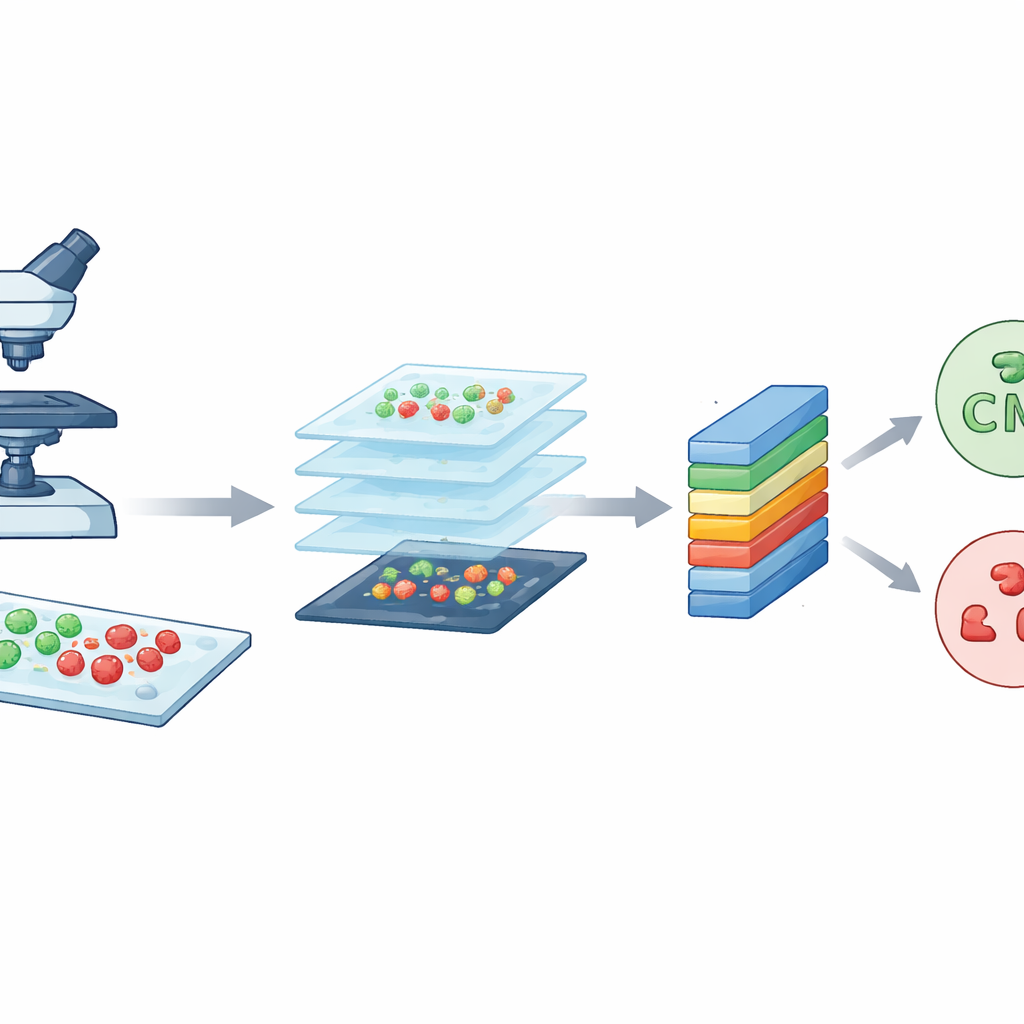
Tworzenie wielu małych płytek z dużych obrazów
Chociaż każdy obraz konfokalny jest bogaty w detale, jest też bardzo duży — około 3000 na 3000 pikseli. Trenowanie modelu komputerowego bezpośrednio na tak ogromnych obrazach byłoby wolne i wymagałoby nadmiernej mocy obliczeniowej. Aby to rozwiązać, zespół pociął każdy duży obraz na wiele mniejszych kwadratowych płytek, każda o rozmiarze 224 na 224 piksele, co jest standardową wielkością w analizie obrazów. Ten proces, zwany augmentacją danych, zarówno zmniejsza obciążenie techniczne, jak i mnoży liczbę przykładów treningowych. Z pierwotnego zestawu 300 obrazów na typ bakterii wygenerowano łącznie 7066 płytek. Płytki te przechwytują lokalne wzory kształtów, kolorów i tekstur z różnych obszarów preparatów, dając modelowi zróżnicowany i zbilansowany zestaw przykładów do nauki.
Jak cyfrowy obserwator uczy się widzieć
CM-Net to starannie zaprojektowany model uczenia głębokiego stworzony specjalnie dla mikroskopii bakterii, a nie zaadaptowany z ogólnych zbiorów zdjęć. Jest to rodzaj splotowej sieci neuronowej, klasy programów doskonale odnajdujących wzorce na obrazach. CM-Net przetwarza każdą płytkę przez serię etapów. Wczesne warstwy wyszukują proste cechy wizualne, takie jak krawędzie i plamki; głębsze łączą je w bardziej złożone wzory, które rozróżniają pałeczki od kulek oraz żywe od martwych komórek. Sieć wykorzystuje techniki takie jak normalizacja wsadowa (batch normalization), która utrzymuje stabilność jej sygnałów wewnętrznych, oraz przyciętą formę funkcji aktywacji, co zapobiega ekstremalnym odpowiedziom mogącym destabilizować naukę. Późniejsze warstwy kondensują wydobyte informacje i podejmują ostateczną decyzję o typie bakterii i stanie komórki.
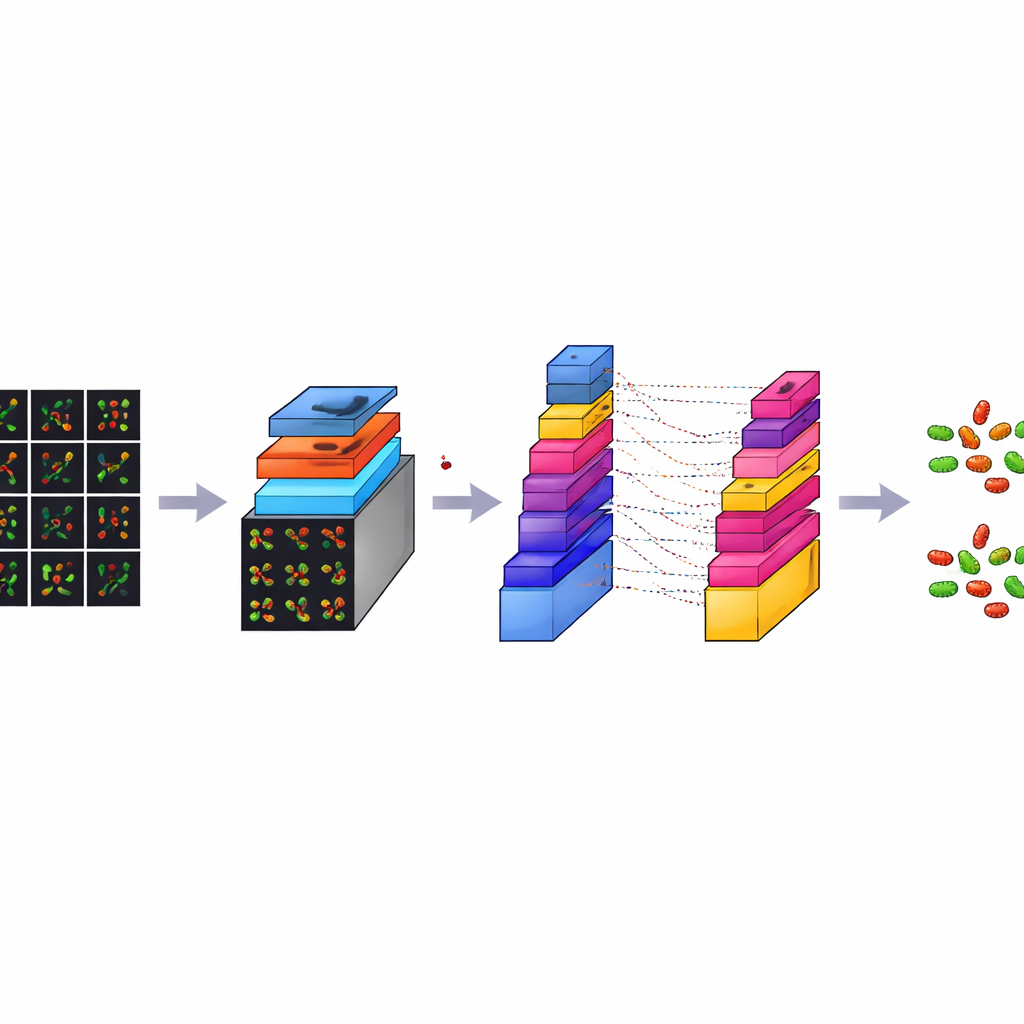
Przewyższając popularne modele „z półki”
Aby sprawdzić, jak dobrze działa CM-Net, autorzy trenowali i testowali go 30 razy, za każdym razem używając nowego podziału danych na grupy treningowe i testowe. Mierzyli dokładność (accuracy), czyli jak często model ma rację ogólnie; czułość (sensitivity), czyli jak dobrze wykrywa każdy cel; specyficzność (specificity), czyli jak dobrze unika fałszywych alarmów; oraz kilka innych standardowych wskaźników. CM-Net osiągnął średnio około 96% dokładności, przy czułości i specyficzności również na poziomie około 96%, wykazując silną równowagę między obiema klasami. Potrzebował też mniej parametrów wewnętrznych i mniej pamięci niż kilka szeroko stosowanych modeli wstępnie wytrenowanych, w tym GoogLeNet, MobileNetV2, ResNet18 i ShuffleNet, a przy tym działał szybciej. Narzędzia wizualizacyjne pokazały, że CM-Net skupia swoją uwagę na rzeczywistych ciałach bakteryjnych na obrazach, a nie na przypadkowych elementach tła, co wspiera tezę, że uczy się biologicznie sensownych cech.
Co to oznacza dla przyszłej pracy w laboratorium
Mówiąc potocznie, badanie pokazuje, że system uczenia głębokiego zaprojektowany do konkretnego zadania potrafi „czytać” złożone obrazy mikroskopowe bakterii dokładnie, efektywnie i w sposób zgodny z oczekiwaniami ekspertów. Na razie CM-Net został wytrenowany tylko na dwóch gatunkach bakterii i na danych z jednego typu mikroskopu, więc przed jego zastosowaniem jako ogólnego narzędzia diagnostycznego potrzeba więcej pracy. Autorzy planują rozszerzyć go o kolejne gatunki, różne stany komórek oraz większe, bardziej zróżnicowane zbiory danych. Mimo to wyniki sugerują, że systemy takie jak CM-Net w przyszłości mogą pomóc laboratoriom szybciej identyfikować infekcje, wspierać decyzje terapeutyczne oraz udostępnić zautomatyzowaną analizę eksperymentów mikrobiologicznych użytkownikom bez specjalistycznej wiedzy obrazowej.
Cytowanie: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Słowa kluczowe: klasyfikacja obrazów bakterii, mikroskopia konfokalna, uczenie głębokie, splotowe sieci neuronowe, diagnostyka medyczna