Clear Sky Science · pl
ConvAHKG: Hybrydowy graf wiedzy oparty na działaniach z dwu‑kanałowym podejściem konwolucyjnym do repozycjonowania leków
Znajdowanie nowych zastosowań dla starych leków
Wprowadzenie całkowicie nowego leku na rynek może zająć ponad dekadę i kosztować miliardy dolarów, a wiele kandydatów kończy się porażką po drodze. W tym badaniu autorzy badają sprytnsze skróty: wykorzystanie danych i sztucznej inteligencji do odkrywania nowych chorób, które istniejące, już zatwierdzone leki mogłyby bezpiecznie leczyć. Przedstawiają ramy nazwane ConvAHKG, które splatają różne rodzaje informacji biomedycznych w jedną spójną mapę, a następnie używają nowoczesnej sieci neuronowej do wykrywania obiecujących par lek–choroba — oferując szybszą, tańszą drogę do nowych terapii.
Bogata mapa interakcji między lekami a chorobami
Rdzeniem tej pracy jest „hybrydowy graf wiedzy”, olbrzymia mapa łącząca leki, choroby, białka, skutki uboczne, struktury chemiczne i szlaki biologiczne. Zamiast zapisywać jedynie proste powiązania tak/nie (na przykład „lek A leczy chorobę B”), mapa rejestruje, jak lek działa na białko — czy je aktywuje, hamuje czy wiąże — oraz w jaki sposób białka uczestniczą w chorobach, na przykład jako biomarkery lub poprzez zmianę aktywności. Graf zawiera ponad 11 000 jednostek i 59 typów relacji, w tym szczegółowe informacje o klasyfikacjach leków, skutkach ubocznych, interakcjach białko–białko i podstrukturach chemicznych. Dzięki uchwyceniu tych wielu warstw kontekstu graf może odzwierciedlać większą część rzeczywistej biologicznej złożoności stojącej za efektami terapeutycznymi i reakcjami niepożądanymi. 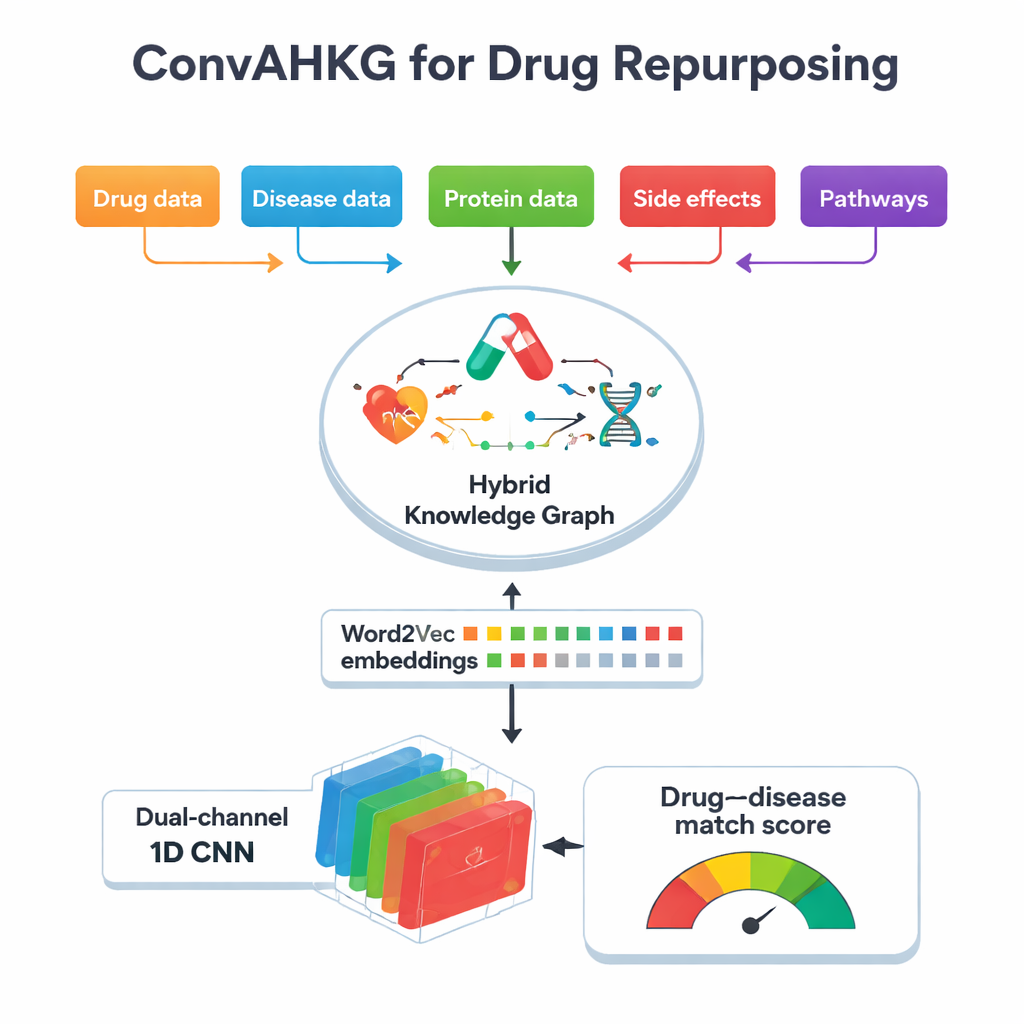
Nauczanie komputera języka biologii
Aby uczynić tę złożoną mapę użyteczną dla uczenia maszynowego, zespół konwertuje każde połączenie w grafie na prostą trzyczęściową „zdanie”: głowa (na przykład choroba), relacja (na przykład biomarker) i ogon (na przykład białko). Następnie stosują Word2Vec, metodę pierwotnie opracowaną do przetwarzania języka naturalnego, aby wyuczyć numeryczne „wektory osadzenia” dla każdego leku, choroby i białka. Elementy, które często pojawiają się razem w tych zdaniach, kończą blisko siebie w tej przestrzeni matematycznej, podobnie jak słowa o podobnym znaczeniu w tekście. To podejście jest znacznie prostsze i szybsze niż wiele technik osadzania specyficznych dla grafów, a mimo to wychwytuje subtelne wzorce. W testach w porównaniu z kilkoma popularnymi metodami osadzania grafów, Word2Vec dorównywał lub przewyższał ich zdolność predykcyjną przy znacznie mniejszym koszcie obliczeniowym.
Podwójna ścieżka neuronowa dla decyzji tak/nie o leczeniu
Gdy każdy lek i każda choroba zostaną przetłumaczone na wektor liczbowy, ConvAHKG podaje je do dwu‑kanałowej jednowymiarowej konwolucyjnej sieci neuronowej. Jeden kanał przetwarza wektor leku, a drugi wektor choroby, wykorzystując sekwencję filtrów konwolucyjnych, które wykrywają wzorce lokalne i szersze motywy, inspirowane konstrukcjami z rozpoznawania obrazów takimi jak InceptionNet i AlexNet. Po tym osobnym przetworzeniu dwa strumienie są łączone i przekazywane przez kilka w pełni połączonych warstw, które zwracają pojedyncze prawdopodobieństwo: czy ta para lek–choroba reprezentuje prawdopodobne skuteczne leczenie, czy raczej szkodliwy skutek uboczny? Aby poradzić sobie z faktem, że znane pary pozytywne są znacznie rzadsze niż negatywne, autorzy wprowadzają ważoną funkcję straty, która surowiej karze pominięcie prawdziwych terapii, poprawiając wydajność w tych trudnych do znalezienia przypadkach. 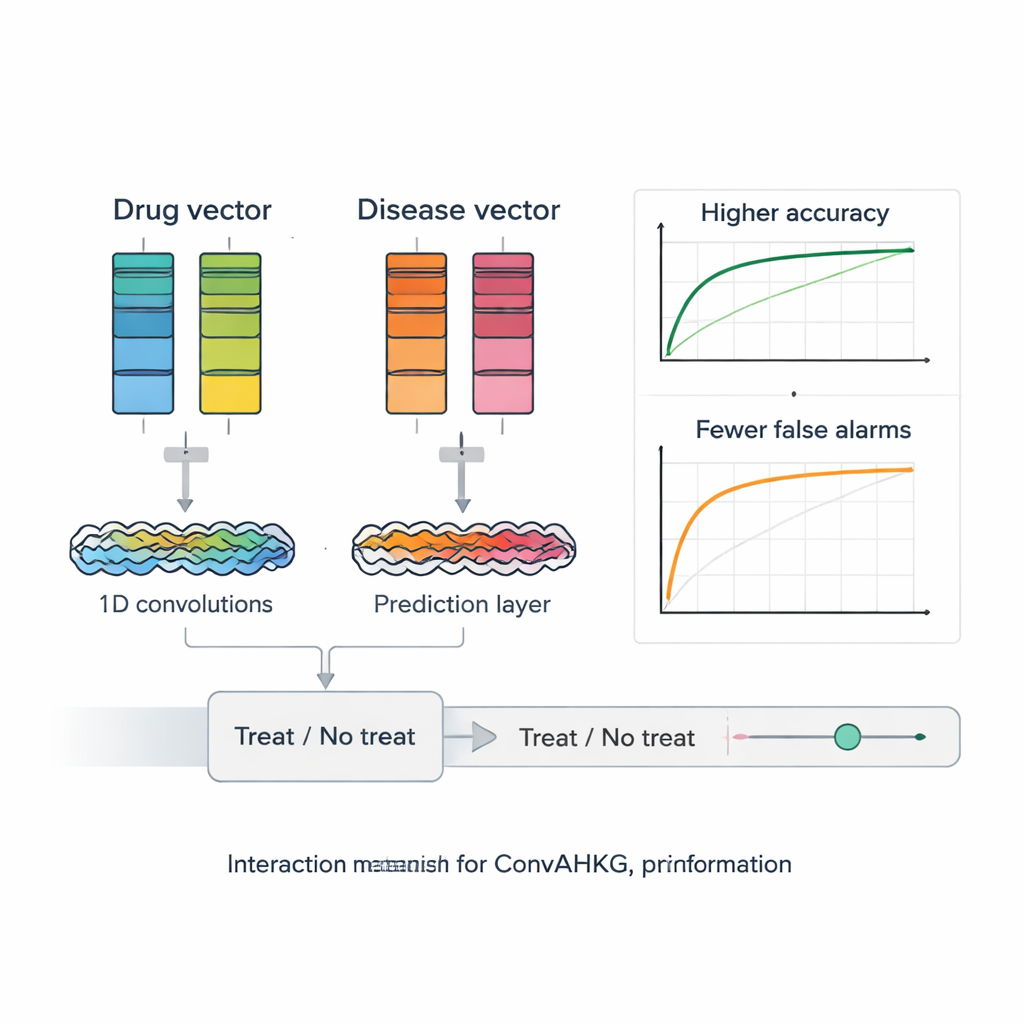
Pokonanie istniejących metod i wykrywanie kandydatów na raka
Badacze rygorystycznie testują swoje ramy przeciwko kilku najnowocześniejszym narzędziom do repozycjonowania leków, które używają faktoryzacji macierzy, grafowych sieci neuronowych i głębokich autoenkoderów. ConvAHKG osiąga pole pod krzywą ROC równe 0,9836 oraz pole pod krzywą precyzja–czułość równe 0,9686, przewyższając wszystkie konkurencyjne podejścia na tym samym zbiorze testowym. Następnie stosują model do niedrobnokomórkowego raka płuca, najczęstszej i najgroźniejszej postaci raka płuca na świecie. ConvAHKG wyróżnia kilka leków wcześniej nieoznaczonych jako terapie dla tej choroby, w tym przeciwciało trastuzumab, które celuje w białko HER2 i już ma wspierające dowody kliniczne w raku płuca, a także inne leki biologiczne, a nawet klasyczny antybiotyk benzylopenicylinę. Symulacje dokowania sugerują, że benzylopenicylina może silnie wiązać się z DNA i z topoizomerazą II alfa, enzymem często podwyższonym w tych guzach, co sugeruje możliwy mechanizm przeciwnowotworowy, który teraz wymaga testów laboratoryjnych.
Dlaczego to ma znaczenie dla pacjentów
Mówiąc prosto, ConvAHKG działa jak wysoko poinformowana firma łącząca istniejące leki z chorobami, używając szczegółowej mapy działań biologicznych i potężnego silnika rozpoznawania wzorców do przewidywania, które stare leki mogą zadziałać w nowych zastosowaniach. Traktując leki sprawdzone pod względem bezpieczeństwa jako wielokrotnego użytku moduły zamiast narzędzi jednorazowego zastosowania, te ramy mogą przyspieszyć odkrywanie terapii dla schorzeń takich jak rak płuca, szczególnie tam, gdzie konwencjonalny rozwój leków jest zbyt powolny lub kosztowny. Chociaż przewidywania wciąż wymagają starannej walidacji eksperymentalnej i klinicznej, badanie pokazuje, że łączenie bogatej wiedzy biologicznej z nowoczesną sztuczną inteligencją może znacznie zawęzić przestrzeń poszukiwań, przybliżając potencjalnie ratujące życie terapie w krótszym czasie.
Cytowanie: Khodadadi AghGhaleh, M., Abedian, R., Zarghami, R. et al. ConvAHKG: Action-based hybrid knowledge graph with a dual-channel convolutional approach for drug repurposing. Sci Rep 16, 7592 (2026). https://doi.org/10.1038/s41598-026-38656-8
Słowa kluczowe: repozycjonowanie leków, graf wiedzy, uczenie głębokie, rak płuca, odkrywanie leków