Clear Sky Science · pl
Sekwencjonowanie genomu Bacillus daqingensis i Alkalicoccus luteus ujawnia wnioski taksonomiczne i mechanizmy adaptacyjne
Życie w słonych miejscach
Od jezior solnych po gleby zasadowe — niektóre mikroby rozwijają się w warunkach, które wysuszyłyby i zabiły większość innych form życia. W tym badaniu przyjrzano się DNA dwóch takich organizmów sprzyjających soli, aby zrozumieć, jak przetrwają w ekstremalnych środowiskach i ustalić, gdzie naprawdę należą na drzewie życia. Poprzez szczegółowe porównanie ich genomów badacze pokazują, że to, co wcześniej uważano za odrębne gatunki bakterii, w rzeczywistości reprezentuje ten sam rodzaj organizmu, a także ujawniają molekularne sztuczki, których te mikroby używają do radzenia sobie z intensywnym stresem solnym.
Dlaczego ci miłośnicy soli są istotni
Bakterie będące osią tej pracy pierwotnie nazwano Bacillus daqingensis i Alkalicoccus luteus. Obie wyizolowano z zasolonych, zasadowych środowisk, takich jak jeziora sodowe i gleby solne, gdzie większość życia ma trudności. Naukowcy podejrzewali, że Bacillus daqingensis może faktycznie należeć do rodzaju Alkalicoccus, lecz brak pełnej sekwencji genomu pozostawiał jego status formalnie niepewnym. Sequencjonując i analizując kompletne genomy tych mikroorganizmów oraz porównując je z pokrewnymi gatunkami, autorzy dążyli do rozwiązania tej zagadki taksonomicznej i jednocześnie do poznania, jak przedstawiciele rodzaju Alkalicoccus radzą sobie w tak surowych warunkach.
Czytanie i porównywanie genomów mikroorganizmów
Zespół hodował bakterie w laboratorium, wyizolował ich DNA i sekwencjonował je metodami wysokoprzepustowymi. Następnie poskładali miliony małych fragmentów DNA w niemal kompletne mapy genomowe i sprawdzili ich jakość. Zarówno Bacillus daqingensis, jak i Alkalicoccus luteus okazały się mieć podobnej wielkości genomy — około 3,4–3,5 miliona par zasad — z niemal identyczną zawartością genetyczną i bardzo wysoką kompletnością. Kluczowy marker genetyczny znany jako gen 16S rRNA był w obu organizmach zasadniczo taki sam: jedno porównanie wykazało 99,8 procent zgodności z wcześniejszymi pomiarami laboratoryjnymi, a co istotne, sekwencje 16S obu szczepów były względem siebie idealnie zgodne w 100 procentach.
Odkodowywanie przetrwania w soli i stresie
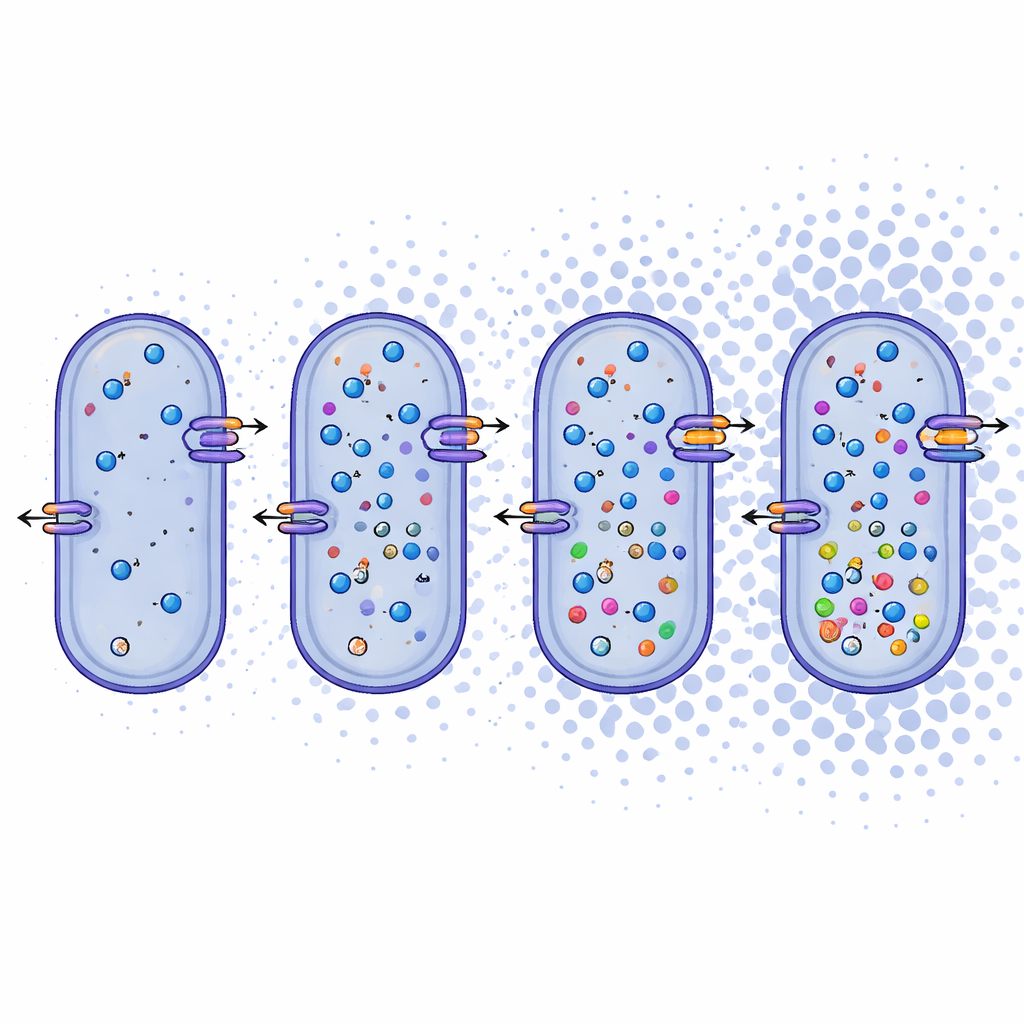
Idąc dalej niż nazwy, badacze zbadali, co genom ujawnia o sposobach życia tych mikroorganizmów. Stwierdzili, że Bacillus daqingensis i wszystkie przebadane gatunki Alkalicoccus dzielą podstawowe szlaki metaboliczne, w tym standardowe drogi rozkładu cukrów oraz zmodyfikowany cykl zwany szlakiem gloksylowym, który pomaga oszczędzać węgiel w warunkach stresu. Najbardziej uderzające było to, że genomy zawierały rozbudowany zestaw narzędzi do radzenia sobie z wysokim stężeniem soli. Bakterie wydają się stosować dwie komplementarne taktyki: systemy „salt-in”, które przemieszczają nieorganiczne jony, takie jak sód i potas, przez błonę komórkową, oraz systemy „salt-out”, które syntetyzują lub importują małe organiczne cząsteczki, takie jak betaina, ectoina i niektóre aminokwasy, działające jak wewnętrzne poduszki chroniące przed odwodnieniem. Geny kodujące transportery jonów, antyportery i biosyntezę tych zgodnych substancji występują w całym rodzaju, co wskazuje na solidną, elastyczną odpowiedź na stres osmotyczny.
Udowadnianie, kto jest kim
Aby rozstrzygnąć kwestię taksonomiczną, autorzy porównali całe genomy przy użyciu kilku liczbowych miar, które są obecnie standardem w systematyce drobnoustrojów. Średnia tożsamość nukleotydowa (ANI) mierzy, jak podobne są sekwencje DNA w całym genomie, podczas gdy średnia tożsamość aminokwasowa (AAI) robi to samo na poziomie białkowym. Pomiędzy Bacillus daqingensis a Alkalicoccus luteus ANI osiągnęło 98,2 procent, a AAI 98,5 procent — znacznie powyżej zwyczajowo stosowanych progów definiujących ten sam gatunek, a nawet ten sam rodzaj. Drzewa filogenetyczne zbudowane na podstawie wielu genów, wraz z porównaniami wspólnych klastrów białkowych, wykazały, że oba szczepy grupują się ściśle razem i dzielą więcej klastrów genów między sobą niż z jakimkolwiek innym gatunkiem Alkalicoccus. Tradycyjne cechy, takie jak kształt komórek, profil kwasów tłuszczowych i kluczowe reakcje biochemiczne, również były w zasadzie identyczne między nimi.
Co to oznacza dla nazw mikroorganizmów
Składając wszystkie linie dowodowe, badanie konkluduje, że Bacillus daqingensis nie reprezentuje odrębnego rodzaju bakterii. Należy on do rodzaju Alkalicoccus i jest tym samym gatunkiem co Alkalicoccus luteus, wcześniej znany jako Bacillus luteus. Autorzy formalnie proponują nowe połączenie nazwowe Alkalicoccus daqingensis i traktują je, wraz z wcześniejszą nazwą Bacillus, jako późniejsze synonimy Bacillus luteus/Alkalicoccus luteus. Dla osób spoza specjalizacji wniosek jest taki, że staranne sekwencjonowanie genomów może ujawnić, kiedy różne etykiety dotyczą w gruncie rzeczy tego samego mikroba, co pomaga uporządkować system nazewnictwa. Równocześnie praca podkreśla, jak te bakterie lubiące sól polegają na kombinacji pomp jonowych i ochronnych cząsteczek, by przetrwać w środowiskach, które w przeciwnym razie byłyby zbyt zasolone dla życia.
Cytowanie: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Słowa kluczowe: bakterie halofilne, sekwencjonowanie genomu, taksonomia drobnoustrojów, adaptacja do stresu solnego, Alkalicoccus luteus