Clear Sky Science · pl
Zautomatyzowana i odporna nieniejowa rejestracja szeregowych obrazów mikroskopowych z użyciem PiCNoR
Widzenie tkanek w 3D bez utraty detali
Nowoczesna biologia często polega na przekształcaniu cienkich skrawków tkanki w pełne obrazy 3D narządów i mózgów. Jednak gdy każdy mikroskopowy plaster jest cięty, barwiony i obrazowany, może się rozciągać, drzeć lub przesuwać. Jeśli te skrawki nie zostaną prawidłowo wyrównane, otrzymany obraz 3D może wprowadzać w błąd. W artykule wprowadzono nową metodę komputerową o nazwie PiCNoR, która pomaga naukowcom dokładniej i automatycznie wyrównywać takie obrazy, tak aby drobne struktury w embrionach i mózgach zostały zachowane w rekonstrukcjach 3D.
Dlaczego wyrównywanie skrawków jest takie trudne
Aby zbudować widok 3D, badacze obrazują długie serie ultracienkich sekcji pobranych z tego samego fragmentu tkanki. W teorii każdy skrawek powinien pasować idealnie nad poprzednim, jak karty w starannie ułożonym stosie. W rzeczywistości każdy plaster może podczas cięcia i barwienia zdeformować się w nieco inny sposób. Kolory mogą się różnić, elementy mogą się rozciągać, a cechy przesuwać. Tradycyjne metody „sztywnego” wyrównania zakładają, że cały skrawek jedynie przesuwa się lub obraca, co często bywa niewystarczające. Istnieją bardziej elastyczne, „sprężyste” metody, ale bywają wolne, wymagają starannego strojenia przez ekspertów lub silnie zależą od jasności obrazu, która może się różnić między skrawkami.
Nowe podejście: lokalne fragmenty współpracujące ze sobą
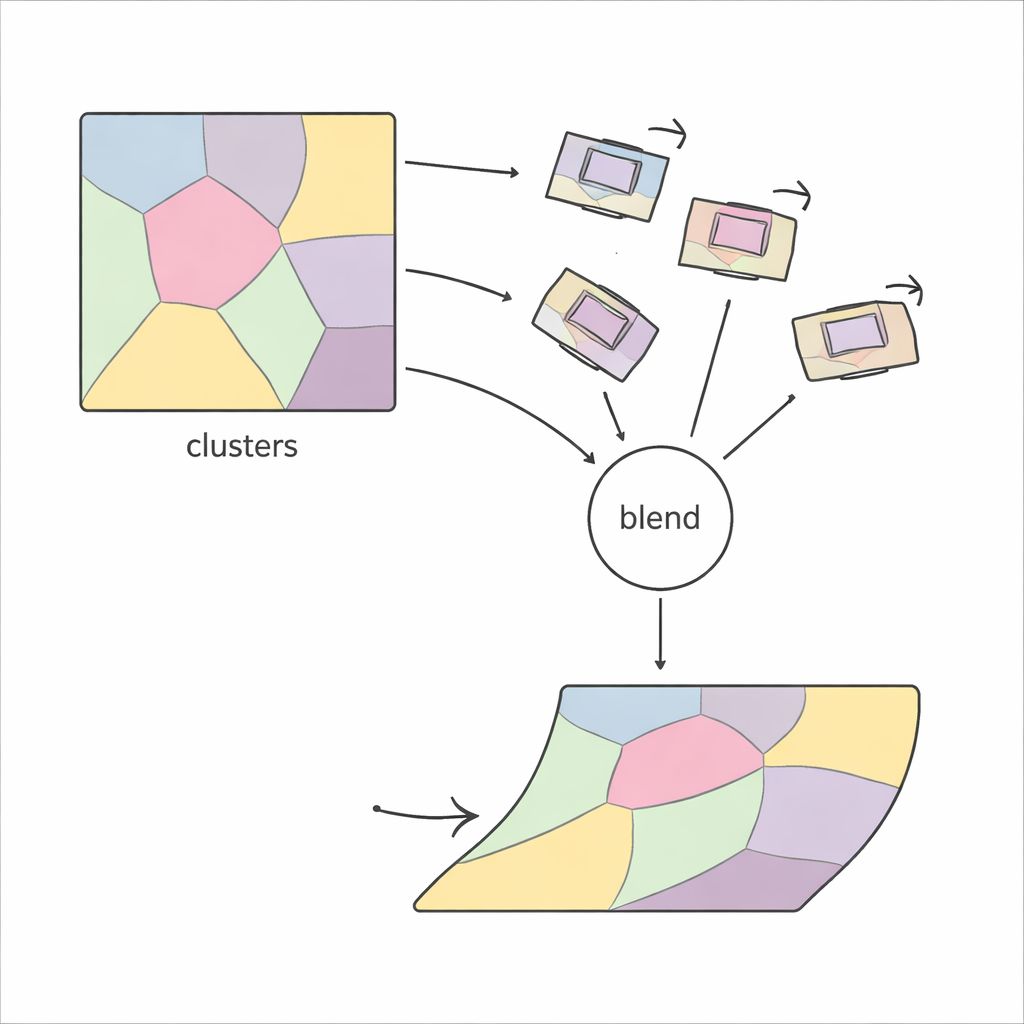
PiCNoR przyjmuje inne, bardziej lokalne spojrzenie na problem. Zamiast próbować wyginać cały obraz naraz, najpierw dzieli każdy skrawek na wiele regionów w oparciu o wzorzec cech na obrazie. W każdym regionie metoda odnajduje punkty dopasowania między dwoma sąsiednimi skrawkami, używając odpornych detektorów cech, i szacuje, jak dany region musi się obrócić i przesunąć, aby się wyrównać. Te lokalne ruchy są następnie sprawdzane pod kątem wiarygodności i delikatnie łączone, tak aby każdy piksel w skrawku otrzymał przesunięcie płynnie mieszające informacje z okolicznych regionów. Efektem jest elastyczne, „nieniejowe” wyrównanie, które zachowuje kontrolowane i realistyczne zachowanie.
Pozwolenie danym wybrać odpowiednią złożoność
Kluczowym wyzwaniem w każdej metodzie opartej na regionach jest decyzja, ile regionów wykorzystać: za mało — metoda nie skoryguje drobnych odkształceń; za dużo — staje się niestabilna i wolna. Poprzednie podejścia często opierały się na metodzie prób i błędów, wielokrotnie sprawdzając wizualną jakość wyniku. PiCNoR unika ręcznego strojenia, stosując narzędzie statystyczne zwane kryterium informacyjnym Bayesa (BIC), które automatycznie równoważy stopień szczegółowości z ryzykiem przeuczenia. W praktyce oznacza to, że algorytm sam decyduje, ile regionów jest potrzebnych dla konkretnego zestawu danych, bez nadzoru człowieka, co oszczędza czas i zmniejsza uprzedzenia.
Zachowanie niezawodności i wydajności wyników
Nie każde oszacowane lokalne przesunięcie jest godne zaufania — niektóre mogą być zniekształcone przez szum lub błędne dopasowania. PiCNoR rozwiązuje to, reprezentując każdy region jako węzeł w grafie, w którym sąsiednie regiony wzajemnie się wpływają. Ruchy, które wyglądają nierealistycznie pod względem rotacji lub przesunięcia, są zastępowane ważoną średnią bardziej wiarygodnych ruchów z okolicy. Zwięzła reprezentacja matematyczna pomaga efektywnie łączyć te ruchy. Wreszcie ruch każdego piksela jest obliczany jako mieszanka regionalnych przesunięć ważona prawdopodobieństwem, co zapewnia, że przejścia między regionami pozostają płynne, bez nagłych załamań czy zagięć tkanki.
Dowód skuteczności na rzeczywistych danych biologicznych
Naukowcy przetestowali PiCNoR na trzech bardzo różnych zestawach danych: przekrojach ludzkiego embrionu z kolekcji w Kioto, serii mikroskopii elektronowej rdzenia nerwowego muszki owocowej oraz nowym stosem obrazów z mikroskopu świetlnego z hipokampa szczura. W tych przykładach PiCNoR konsekwentnie dawał lepsze pokrycie między skrawkami niż standardowe metody sztywne i powszechnie stosowane metody nieniejowe. Zachowywał ciągłość delikatnych struktur w widokach 3D i unikał przesadnych zniekształceń obserwowanych czasem przy innych narzędziach. Co istotne, osiągał to przy użyciu mniejszej liczby regionów lokalnych niż niektórzy konkurenci i przy kosztach obliczeniowych pozostających praktycznymi dla dużych stosów.
Co to oznacza dla przyszłej mikroskopii 3D
Dla osób spoza specjalności wniosek jest taki, że PiCNoR oferuje bardziej niezawodny sposób przekształcania stosów dwuwymiarowych obrazów mikroskopowych w wierne rekonstrukcje 3D. Dzięki automatycznemu doborowi stopnia szczegółowości wyrównania i zabezpieczeniom przed błędnymi lokalnymi korektami zachowuje rzeczywiste kształty tkanek przy jednoczesnym zachowaniu rozsądnego czasu przetwarzania. Ułatwia to biologom i patologom zaufanie do tego, co widzą w 3D — czy to analizując rozwój embrionu, czy rozmieszczenie komórek mózgowych — i toruje drogę do dokładniejszej, zautomatyzowanej analizy złożonych zestawów mikroskopowych danych.
Cytowanie: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Słowa kluczowe: mikroskopia 3D, rejestracja obrazów, obrazowanie mózgu, histologia, nieniejowe dopasowanie