Clear Sky Science · pl
Mikrobiota jelitowa i profile rezystomu u szwajcarskich emigrantów w Afryce ujawnione przez metagenomikę Nanopore
Dlaczego twoje mikroby jelitowe zmieniają się, gdy mieszkasz za granicą
Wielu ludzi spędza miesiące lub lata za granicą, często w miejscach, gdzie bakterie oporne na antybiotyki są powszechne. W tym badaniu postawiono proste, lecz ważne pytanie: czy gdy szwajcarscy emigranci mieszkają w krajach afrykańskich o wysokim obciążeniu zakażeń lekoopornych, społeczność drobnoustrojów i genów oporności w ich jelitach zmienia się w sposób, który może wpływać na ich zdrowie oraz na szersze rozprzestrzenianie się oporności na środki przeciwdrobnoustrojowe?
Niewidoczna społeczność wewnątrz nas
Nasze jelita są siedliskiem bilionów mikrobów, głównie bakterii, które pomagają trawić pokarm, kształtować układ odpornościowy i powstrzymywać szkodliwe patogeny. Obok tych pożytecznych drobnoustrojów znajduje się „rezystom” – zbiór genów nadających bakteriom oporność na antybiotyki. Nawet zdrowi ludzie noszą wiele takich genów. Gdy osoby przeprowadzają się do lub podróżują przez regiony, gdzie bakterie wielolekooporne są powszechne, mogą po cichu nabywać nowe geny oporności oraz ruchome elementy DNA, zwane plazmidami, które je rozprzestrzeniają. Zrozumienie, jak to się dzieje, jest kluczowe dla kontroli globalnej oporności na antybiotyki.
Porównanie emigrantów w Europie i w Afryce
Naukowcy przeanalizowali próbki kału od 72 zdrowych szwajcarskich emigrantów powracających do Szwajcarii: 39 mieszkało w krajach afrykańskich, a 33 w innych krajach europejskich. Zamiast hodować bakterie w laboratorium, zastosowali technologię sekwencjonowania długich odczytów DNA zwaną Nanopore shotgun metagenomics, która odczytuje cały materiał genetyczny w próbce naraz. Pozwoliło to zmapować, które bakterie występują (mikrobiota) oraz jakie geny oporności i plazmidy niosą (rezystom i plazmidom). Każdą próbkę sekwencjonowano dwukrotnie dla wiarygodności, a zaawansowane oprogramowanie wykorzystano do identyfikacji grup bakteryjnych, genów oporności oraz do składania dłuższych fragmentów genomu z mieszanego DNA.
Zaskakująca stabilność mikrobioty jelitowej
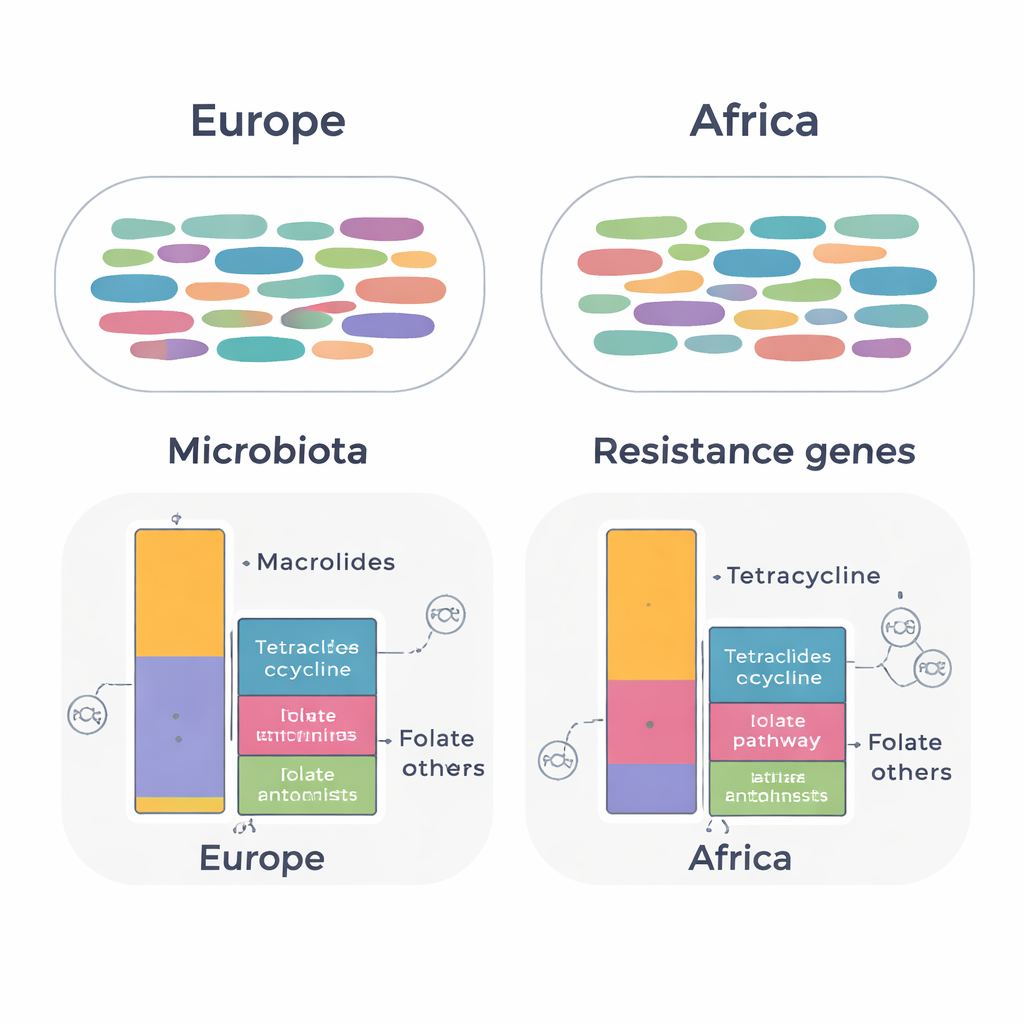
Mimo że w grupie afrykańskiej więcej osób było skolonizowanych bakteriami wielolekoopornymi w wcześniejszych testach hodowlanych, ogólny skład ich mikrobioty jelitowej wyglądał zaskakująco podobnie do tej u emigrantów, którzy mieszkali w Europie. Miary różnorodności – ile różnych rodzajów bakterii było obecnych i jak równomiernie były reprezentowane – nie różniły się w zależności od kontynentu, a analizy statystyczne nie wykazały wyraźnego grupowania próbek z Afryki kontra Europy. W obu grupach dominowały dobrze znane mieszkańcy jelita, takie jak Blautia, Faecalibacterium i Bacteroides, co sugeruje, że długotrwały pobyt za granicą nie musi koniecznie rewolucjonizować podstawowej społeczności bakteryjnej u zdrowych dorosłych.
Geny oporności i ruchome DNA opowiadają inną historię
Gdy zespół skupił się na genach oporności, ujawniły się subtelniejsze, ale istotne różnice. W całym zbiorze próbek wykryto 134 różne geny oporności należące do 14 klas antybiotyków. Łączny wzorzec genów był ogólnie podobny między kontynentami, ale emigranci, którzy mieszkali w Afryce, nosili wyższe poziomy genów chroniących bakterie przed tetracyklinami oraz lekami celującymi w szlak folianowy (takimi jak trimetoprim‑sulfametoksazol). Dla kontrastu, emigranci z krajów europejskich wykazywali wyższe poziomy genów nadających oporność na makrolidy. Wiele z tych genów powiązano z powszechnymi bakteriami jelitowymi, w tym Ruminococcoides, Bifidobacterium i Bacteroides. Klinicznie istotne geny, takie jak blaCTX‑M‑15, które mogą inaktywować zaawansowane cefalosporyny, wykryto w Escherichia coli w obu grupach.
Plazmidy jako globalne nośniki oporności
Badanie śledziło także plazmidy – małe, często przenośne koliste cząsteczki DNA, które transportują geny oporności między bakteriami i środowiskami. Dzięki długim odczytom DNA badacze mogli czasem zobaczyć geny oporności i markery „replicon” plazmidów na tym samym złożonym fragmencie DNA, potwierdzając, że podróżują razem. Zidentyfikowali 46 różnych typów plazmidów, niektóre unikatowe dla poszczególnych kontynentów, inne wspólne. Co istotne, niektóre plazmidy niosły wiele genów oporności i przypominały plazmidy znane z ludzi, zwierząt, żywności i ścieków w różnych częściach świata. Jeden typ plazmidu, często powiązany z Enterococcus i znajdowany w kurczakach oraz ściekach, był częstszy w próbkach kału emigrantów z Afryki, co podkreśla, jak żywność, zwierzęta i środowisko mogą przyczyniać się do tego, co trafia do naszego jelita.
Co to oznacza dla życia codziennego i zdrowia publicznego
Dla czytelnika niebędącego specjalistą główny wniosek jest taki, że samo zamieszkanie w regionie o wysokim ryzyku nie wydaje się radykalnie zmieniać, jakie bakterie jelitowe posiadasz, ale może zmieniać skład genów oporności na antybiotyki i ruchomych elementów DNA, które je rozprzestrzeniają. Te ukryte zmiany, częściowo kształtowane przez lokalne wzorce stosowania antybiotyków, mogą mieć znaczenie dla przyszłych infekcji oraz dla tego, jak cechy oporności przemieszczają się między ludźmi, zwierzętami i środowiskiem. Praca ta pokazuje również, że przenośne sekwencjonowanie długich odczytów może działać jako narzędzie wczesnego ostrzegania, ujawniając, jak geny oporności i plazmidy krążą wśród zdrowych podróżnych i emigrantów, zanim wywołają choroby.
Cytowanie: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Słowa kluczowe: mikrobiom jelitowy, oporność na antybiotyki, emigranci, plazmidy, metagenomika