Clear Sky Science · pl
Pierwsze mitochondrialne genom dla Sterictiphorinae (Hymenoptera: Argidae) i wnioski dotyczące filogenezy Argidae
Dlaczego mali liściorobowcy mają znaczenie
Pilarki z rodziny Argidae mogą wyglądać niepozornie, ale ich gąsienico‑podobne młode potrafią obgryzać liście w uprawach i lasach, co czyni je ważnymi szkodnikami rolniczymi. Tymczasem na poziomie ich DNA, zwłaszcza w mitochondriach — „elektrowniach” komórek — te owady były słabo poznane. W artykule opisano pierwszy kompletny genom mitochondrialny koreańskiej pilarki, Sterictiphora koreana, i użyto go do zbadania, jak ta pełna szkodników rodzina ewoluowała przez ponad 160 milionów lat.
Zajrzeć do elektrowni pilarki
Autorzy rozszyfrowali całe mitochondrialne DNA pojedynczej samicy S. koreana. Jak u większości zwierząt, ten mikroskopijny „genom elektrowni” ma postać pętli DNA zawierającej 37 genów pomagających komórce pozyskiwać energię. U S. koreana pętla jest nietypowo długa — około 17 900 par zasad wobec około 15 600 u trzech spokrewnionych gatunków Argidae — głównie dlatego, że jeden niekodujący odcinek bogaty w A i T uległ wydłużeniu. Pomimo różnicy rozmiaru, ogólny układ genów jest zgodny z typowym wzorcem obserwowanym u innych pilarek: większość genów znajduje się na jednym włóknie DNA, a mniejszy zestaw na przeciwnej nici, a geny tRNA składają się w klasyczne struktury koniczyny z kilkoma odstępstwami.

Wzory liter sugerujące więzy rodzinne
DNA mitochondrialne u wielu owadów jest silnie zdominowane przez zasady A i T, i te pilarki nie są wyjątkiem. Wszystkie cztery badane gatunki Argidae mają genomy składające się w przybliżeniu w 80 procentach z A lub T, lecz ich proporcje nie są identyczne. Trzy wcześniej poznane gatunki, wszystkie z podrodziny Arginae, mają jeszcze większy udział A+T niż S. koreana, przedstawicielka podrodziny Sterictiphorinae. Subtelne nierównowagi w częstości występowania A względem T oraz G względem C różnią się między gatunkami i między częściami genomu. Jeden gatunek, Arge aurora, nawet odwraca niektóre z tych odchyłów, wyróżniając się spośród krewnych. Badacze pokazują także, że niektóre aminokwasy — jak leucyna, izoleucyna, metionina i fenyloalanina — są kodowane częściej niż inne, co odzwierciedla, jak ta zniekształcona „alfabetyczna” baza kształtuje genetyczne „słowa” używane przez pilarki.
Przemieszczone geny i powoli zmieniający się kod
Chociaż ogólny plan mitochondrialny jest zachowawczy, małe geny tRNA są podatne na przemieszczanie się, a ich nowe pozycje mogą wyznaczać duże gałęzie drzewa rodowego pilarek. U gatunków Arginae jeden gen tRNA (trnW) przeskoczył na nowe miejsce w pobliżu regionu bogatego w A+T. U S. koreana inny zestaw tRNA (trnK, trnD, trnI i trnM) został przearanżowany w spójny wzorzec. Te różne przestawienia prawdopodobnie oznaczają, że dwie podrodziny są odrębnymi liniami ewolucyjnymi. Kiedy zespół zbadał tempo akumulacji zmian w genach kodujących białka, stwierdził, że większość mutacji jest eliminowana przez dobór naturalny, wzorzec zwany selekcją oczyszczającą. Szczególnie jeden gen, cox1, zmienia się wyjątkowo powoli, co potwierdza jego przydatność jako DNA „paska kodowego” do rozróżniania gatunków.
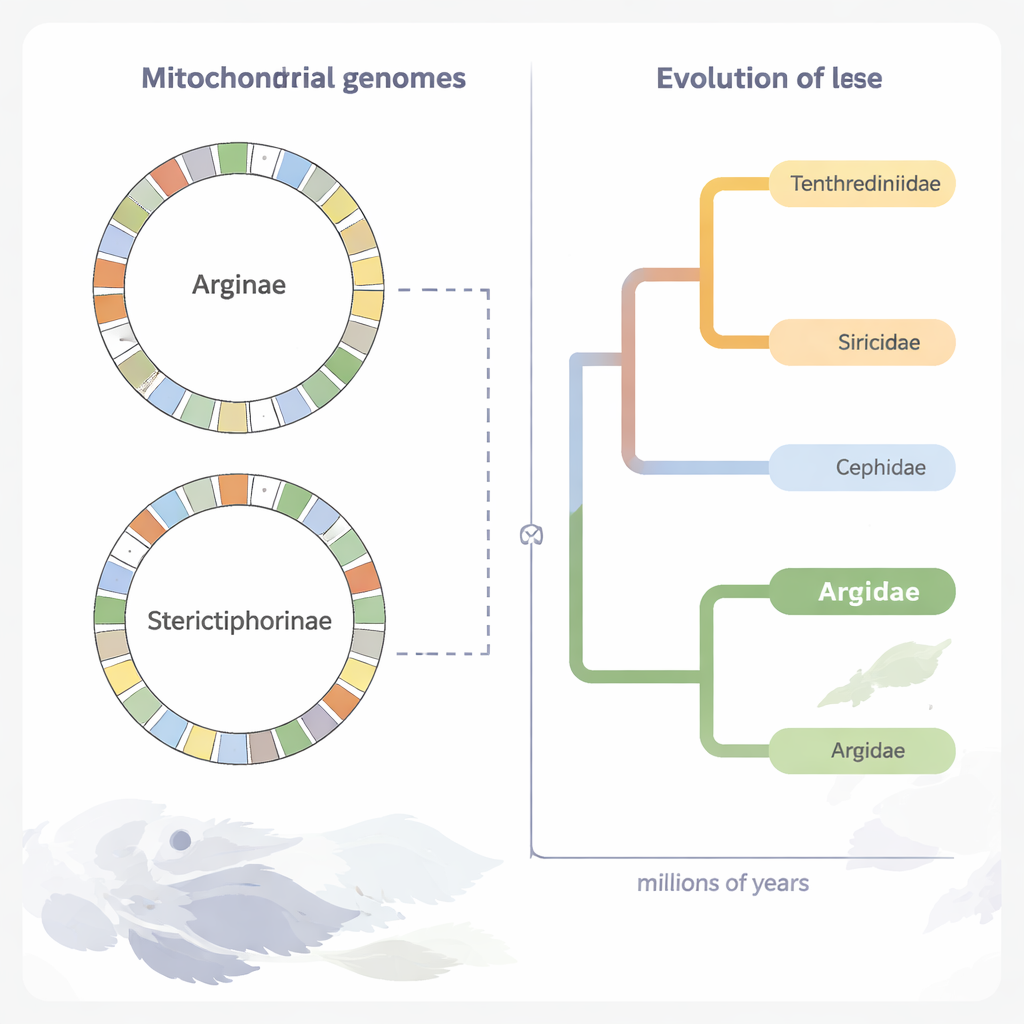
Odtwarzanie odległego drzewa rodowego pilarek
Wykorzystując części kodujące białka mitochondrialnego DNA z 70 gatunków pilarek, badacze zrekonstruowali szczegółowe drzewo ewolucyjne. Ich analizy potwierdzają, że Argidae tworzą naturalną grupę i są blisko spokrewnione z inną rodziną, Pergidae, w ramach większego nadrodziny pilarek Tenthredinoidea. Zanurzając się w dowodach kopalnych, oszacowali, że rozdział linii Argidae–Pergidae od innych rodzin pilarek nastąpił około 206 milionów lat temu, a sama rodzina Argidae powstała mniej więcej 166 milionów lat temu, w środkowym jury. Dwie główne podrodziny Argidae, Arginae i Sterictiphorinae, wydają się rozdzielić wczesnej kredy, około 126 milionów lat temu, w czasie, gdy rośliny kwiatowe także się różnicowały.
Co to znaczy dla nauki i kontroli szkodników
Ten pierwszy genom mitochondrialny ze Sterictiphorinae wypełnia istotną lukę w naszym genetycznym obrazie Argidae. Pokazuje, że cechy drobnego kalibru — takie jak długość genomu, kolejność genów i uprzedzenia literowe — mogą wiarygodnie rozdzielać główne grupy w tej rodzinie szkodników i pomagać w ich umiejscowieniu w szerszym drzewie pilarek. Dla osób niezajmujących się specjalistycznie tematem, główny wniosek jest taki, że czytając i porównując te maleńkie pętle DNA w „elektrowniach” komórek owadów, naukowcy mogą odtwarzać, jak spokrewnione są destrukcyjne liściożerne pilarki, szacować, kiedy ich linie się pojawiły, i w efekcie budować solidniejsze ramy do identyfikacji gatunków oraz rozumienia ich rozprzestrzeniania się w uprawach i lasach.
Cytowanie: Park, B., Hwang, U.W. The first mitochondrial genome for Sterictiphorinae (Hymenoptera: Argidae) and insights into argid phylogeny. Sci Rep 16, 7154 (2026). https://doi.org/10.1038/s41598-026-38021-9
Słowa kluczowe: ewolucja pszczołowatych, genom mitochondrialny, filogeneza owadów, szkodniki leśne i upraw, DNA barcoding