Clear Sky Science · pl
Identyfikacja szkodliwych wariantów w całym transkryptomie w genach kandydujących związanych z paratuberkulozą bydła
Ukryte geny stojące za kosztowną chorobą bydła
Paratuberkuloza bydła, znana również jako choroba Johne’a, po cichu osłabia zdrowie i wydajność stad mlecznych na całym świecie, przynosząc rolnikom straty sięgające setek milionów dolarów rocznie i budząc obawy o związki z ludzkimi zaburzeniami jelitowymi. W tym badaniu zajrzano „pod maskę” genetyczną krów rasy Holsztyn, aby postawić proste, lecz istotne pytanie: jakie różnice w ich genach mogą pomagać niektórym zwierzętom opierać się zakażeniu, podczas gdy inne ulegają? Czytając RNA — robocze kopie genów — we krwi i tkance jelit, badacze śledzili, jak subtelne zmiany w DNA w kluczowych genach odpornościowych mogą kierować przebiegiem choroby.
Dlaczego ta choroba krów ma znaczenie
Paratuberkulozę wywołuje bakteria Mycobacterium avium podgatunek paratuberculosis (MAP). Krowy zwykle zakażają się we wczesnym okresie życia, ale objawy często pojawiają się dopiero po wielu latach. W fazach bezobjawowych i podklinicznych zwierzęta wyglądają na zdrowe, lecz mogą wydalać niewielkie ilości bakterii i produkować mniej mleka. W fazie klinicznej rozwija się przewlekła biegunka, silne chudnięcie i znaczący spadek wydajności mlecznej. Wskaźniki zakażeń na poziomie stada mogą przekraczać 50% w wielu regionach, w tym w częściach Europy i Ameryki Północnej, co tworzy wyzwanie ekonomiczne i dobrostanu zwierząt. Ponieważ bakterie mogą również działać jako środowiskowy czynnik wywoławczy ludzkich chorób zapalnych, takich jak choroba Crohna, rośnie presja na poprawę strategii kontroli u bydła.
Odczytywanie pracującego genomu
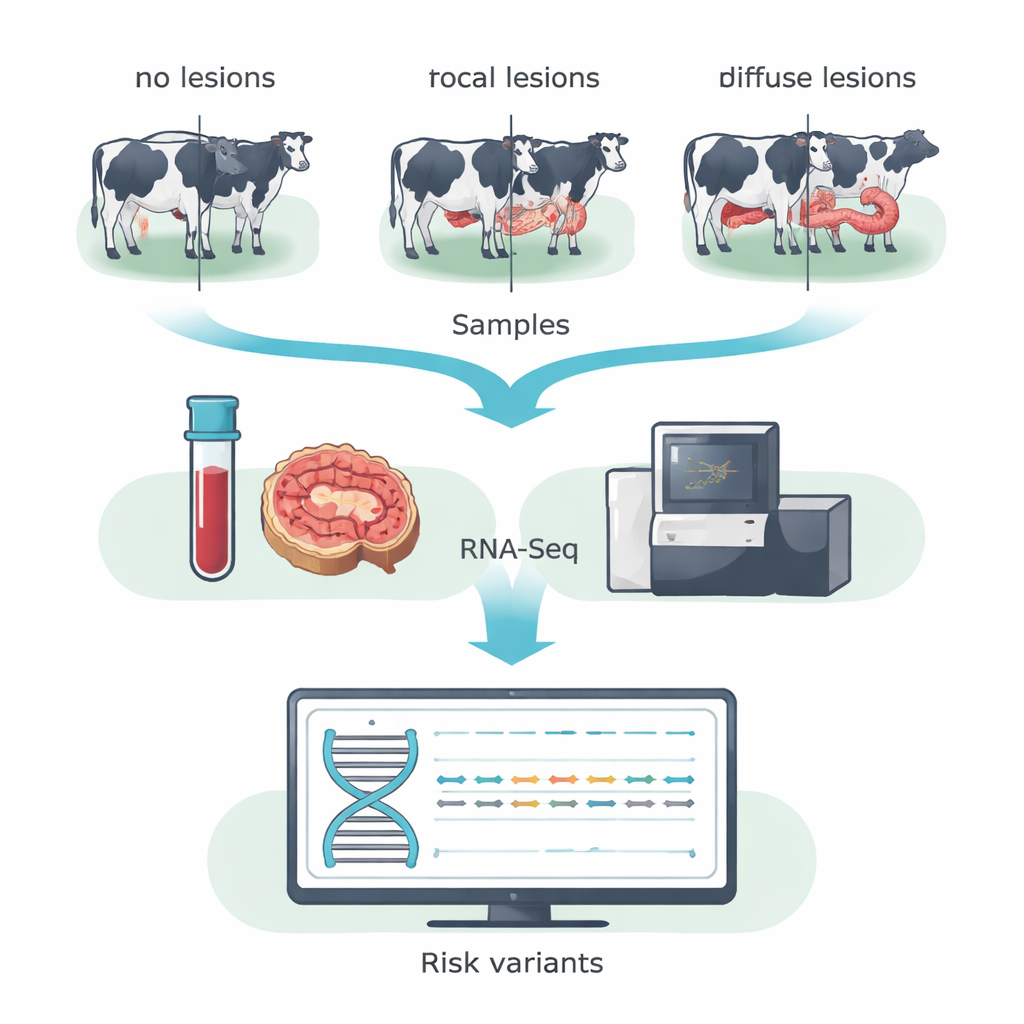
Zamiast skanować całe sekwencje DNA, zespół zastosował sekwencjonowanie RNA (RNA-Seq), aby skupić się na genach faktycznie aktywnych u zwierzęcia. Pobierali krew oraz próbki z zastawki krętniczo-kątniczej — odcinka jelita silnie dotkniętego przez MAP — od 14 krów rasy Holsztyn z hiszpańskiego gospodarstwa mlecznego. Na podstawie badania mikroskopowego tkanek jelitowych krowy podzielono na trzy kategorie: zwierzęta bez wykrywalnych zmian, zwierzęta z niewielkimi, zlokalizowanymi (ogniskowymi) zmianami typowymi dla długotrwałego stanu podklinicznego oraz zwierzęta z ciężkimi, rozległymi (rozlanymi) zmianami związanymi z chorobą kliniczną. Łącząc dane z krwi i jelita w każdej grupie, badacze zwiększyli swoją zdolność wykrywania jedno-literowych zmian w DNA w ekspresowanych genach, znanych jako kodujące SNP.
Wyszukiwanie szkodliwych zmian w kluczowych genach odpornościowych
Z setek tysięcy wariantów zespół skupił się na tych, które zmieniają sekwencję białka i są przewidywane jako uszkadzające funkcję białka — tzw. warianty deleterious. Zastosowano rygorystyczne filtry, aby zapewnić wysokie zaufanie, a następnie użyto uznanych narzędzi predykcyjnych do oznaczania ryzykownych zmian. Ten proces odsiewu ujawnił 31 takich wariantów unikatowych dla krów bez zmian, 15 unikatowych dla krów z ogniskowymi zmianami oraz 31 unikatowych dla krów z rozlanymi zmianami. Wiele z nich występowało w genach kierujących tym, jak komórki odpornościowe rozpoznają i usuwają zakażenia, regulują śmierć komórkową oraz zarządzają metabolizmem. Na wyróżnienie zasługuje rodzina genów BOLA, bydlęca wersja kompleksu zgodności tkankowej klasy II, która pomaga komórkom odpornościowym prezentować fragmenty bakterii limfocytom T. Różne potencjalnie szkodliwe warianty w BOLA znaleziono we wszystkich trzech grupach krów, co sugeruje, że konkretne wersje BOLA mogą przechylać zwierzęta w stronę oporności, kontrolowanego zakażenia lub szkodliwego zapalenia.
Od wariantów DNA do szlaków chorobowych
Aby zrozumieć, co te zmiany genów mogą oznaczać w praktyce, badacze przeanalizowali, które szlaki biologiczne były wzbogacone w każdej grupie. Krowy bez zmian wykazywały zmienione warianty w genach związanych z przetwarzaniem antygenu, transportem pęcherzykowym i równowagą odporności jelitowej, w tym BOLA, AP3B1 i CHGA. Te zmiany mogą sprzyjać efektywnemu trawieniu bakterii w komórkach odpornościowych oraz stabilnemu środowisku jelitowemu, które ogranicza uszkodzenia. U krów z ogniskowymi zmianami szkodliwe warianty skupiały się w genach (ORMDL3 i KANK2) tłumiących zaprogramowaną śmierć komórkową i modulujących metabolizm komórkowy, co potencjalnie pomaga gospodarzowi utrzymać niską liczbę bakterii podczas długiej, podklinicznej fazy. U krów z rozlanymi zmianami dotknięte geny wskazywały na nadaktywne szlaki odpornościowe, takie jak różnicowanie komórek Th1/Th2 i prezentacja antygenu, wraz z transportem żółci i szlakami odpowiedzi na leki. W tym przypadku zmienione geny rodziny BOLA mogą napędzać silną, niekiedy samouszkadzającą reakcję zapalną, przypominającą wzorce obserwowane w wielu ludzkich chorobach autoimmunologicznych i zapalnych.
Wskazówki dla hodowli bardziej odpornych stad
Poza wyjaśnieniem, jak różne warianty genetyczne kształtują odpowiedź immunologiczną na MAP, badanie powiązało te ryzykowne zmiany ze znanymi regionami genomu bydła związanymi z cechami zdrowotnymi, w tym podatnością na paratuberkulozę i inne infekcje. Chociaż wyniki te wymagają jeszcze walidacji w większych stadach i nie mogą być obecnie używane jako samodzielne markery diagnostyczne, oferują obiecujący katalog kandydackich wariantów i genów. Mówiąc prosto, praca sugeruje, że niektóre krowy noszą wersje genów pozwalające im cicho kontrolować zakażenie, podczas gdy inne mają wersje sprzyjające wymykającemu się zapaleniu i ciężkiej chorobie. W przyszłości takie informacje mogą wspierać selektywną hodowlę i testy genetyczne, które przesuną stada w stronę większej naturalnej odporności, zmniejszając zarówno straty ekonomiczne, jak i potrzebę intensywnych działań kontrolnych.
Cytowanie: Badia-Bringué, G., Lam, S., Cánovas, Á. et al. Whole-transcriptome identification of deleterious variants in candidate genes linked to bovine paratuberculosis. Sci Rep 16, 6243 (2026). https://doi.org/10.1038/s41598-026-37675-9
Słowa kluczowe: paratuberkuloza bydła, genetyka choroby Johne’a, odporność krów mlecznych, sekwencjonowanie RNA, selekcja na odporność na choroby