Clear Sky Science · pl
Konjugacja DNA na funkcjonalizowanych powierzchniach plastikowych do sekwencjonowania pojedynczych cząsteczek sekwencyjnie i iteracyjnie
Przechowywanie jutrzejszych danych w malutkich nici
Wyobraź sobie tworzenie kopii zapasowej zdjęć, książek czy zapisów naukowych w formie, która może przetrwać wieki i zmieścić się w kropce mniejszej niż ziarnko piasku. DNA — ta sama cząsteczka, która przenosi nasze geny — wyrasta na obiecującego kandydata do bardzo gęstego, trwałego magazynowania danych. W artykule opisano nowy sposób „parkowania” danych w DNA wewnątrz zwykłych plastikowych probówek laboratoryjnych, a następnie wielokrotnego odczytywania ich bez niszczenia oryginalnych cząsteczek.
Nowy rodzaj „pamięci przenośnej”
Obecne dyski twarde i pamięci flash z czasem się zużywają i mieszczą znacznie mniej informacji na gram niż potencjalnie DNA. Naukowcy już pokazali, jak przekształcać pliki cyfrowe w sekwencje „liter” DNA. Jednak za każdym razem, gdy te nici są kopiowane lub sekwencjonowane, część materiału oryginalnego jest zużywana — jak atrament blaknący przy nadmiernym kserowaniu strony. W tym badaniu autorzy przekształcili prostą plastikową probówkę PCR — powszechny element w laboratoriach biologicznych — w wielokrotnego użytku nośnik fizyczny. Chemicznie przyłączyli nici DNA zawierające zakodowane dane do wewnętrznej powierzchni probówki, dzięki czemu DNA pozostaje unieruchomione, a kopie mogą być wielokrotnie tworzone i odczytywane. 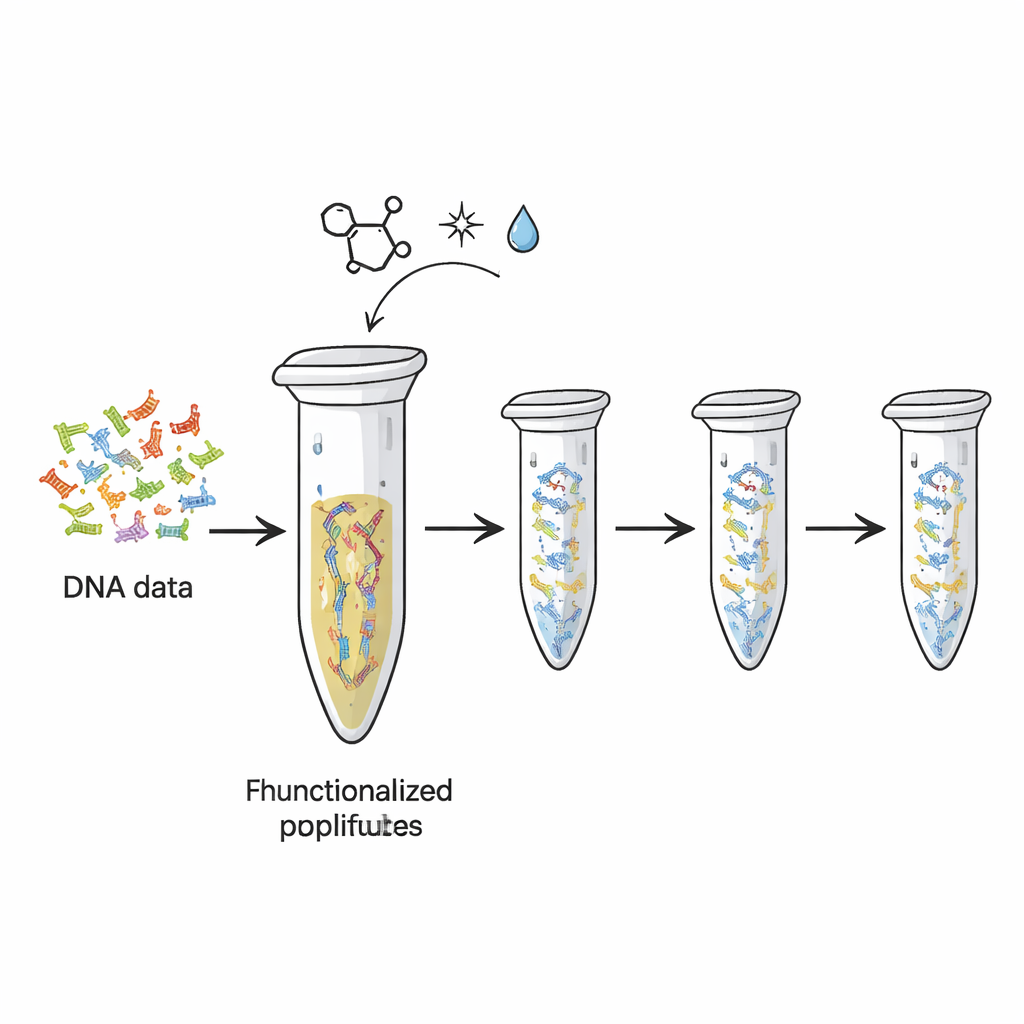
Przyklejanie DNA do plastiku metodą „klik”
Zespół wykorzystał specyficzny rodzaj „chemii kliknięć” — reakcje cenione za szybkość, niezawodność i łagodność działania. Najpierw dodano specjalne chemiczne ogony do końców nici DNA reprezentujących różne „pliki” danych. Te ogony, oparte na cząsteczce zwanej TCO, są zaprojektowane tak, by zablokować się z dopasowanymi grupami (MTz) zaimplantowanymi na powierzchni plastiku probówki. Gdy te dwa elementy się zetkną, tworzą stabilne wiązanie kowalencyjne, skutecznie „przyklejając” DNA do plastiku. Testy z fragmentem kontrolnym pokazały, że po inkubacji niemal całe DNA zniknęło z roztworu, co wskazuje, że zostało unieruchomione na ściance probówki. Platforma mogła pomieścić rzędy setek femtomoli DNA, co sugeruje praktyczną pojemność dla zestawów danych.
Odtwarzanie cyfrowych „plików” na żądanie
Aby sprawdzić, czy to DNA związane z powierzchnią nadal zachowuje się jak użyteczne archiwum, badacze zakodowali tekst i inne dane w puli około 15 000 krótkich nici DNA, pogrupowanych w 18 „grup plików”. Każda grupa mogła być selektywnie kopiowana przy użyciu własnej pary starterów — krótkich sekwencji inicjujących kopiowanie maszynerii molekularnej na odpowiednie cele. Zespół wielokrotnie wykonywał standardowe reakcje PCR w tej samej probówce, za każdym razem wybierając inną grupę plików do amplifikacji. Po każdym cyklu usuwali skopiowane DNA, oczyszczali probówkę enzymami trawiącymi pozostałe produkty w roztworze i przechodzili do następnego pliku. Sekwencjonowanie nanoporowe skopiowanego materiału wykazało, że większość grup plików została odzyskana z wysoką dokładnością, a zanieczyszczenia krzyżowe z wcześniejszych cykli były bardzo niskie — zwykle około 1 procenta lub mniej.
Poszukiwanie łagodniejszego sposobu odczytu
Był jednak pewien problem: przy powtarzaniu PCR w tej samej probówce do 18 razy ilość odzyskiwanego DNA stopniowo malała. PCR opiera się na szybkim podgrzewaniu i schładzaniu, i autorzy wnioskowali, że powtarzane wysokie temperatury uszkadzają unieruchomione DNA lub jego połączenie z plastikiem, mimo że testy kontrolne sugerowały, iż DNA nie jest po prostu zmywane do roztworu. Aby to rozwiązać, sięgnęli po wzmacnianie przez replikazę z rekombinazą (RPA), nowszą metodę pracującą w stałej, stosunkowo niskiej temperaturze zbliżonej do temperatury ciała. Stosując RPA na świeżo pokrytych DNA probówkach, ponownie zapytali wszystkie 18 grup plików kolejno. Tym razem wydajności były wysokie — około 60 ng/µL — i nie wykazywały tej samej tendencji spadkowej. Wzorzec, które nici były faworyzowane lub pomijane podczas kopiowania, również bardzo dobrze odpowiadał temu, co obserwowano, gdy DNA było wolne w roztworze. 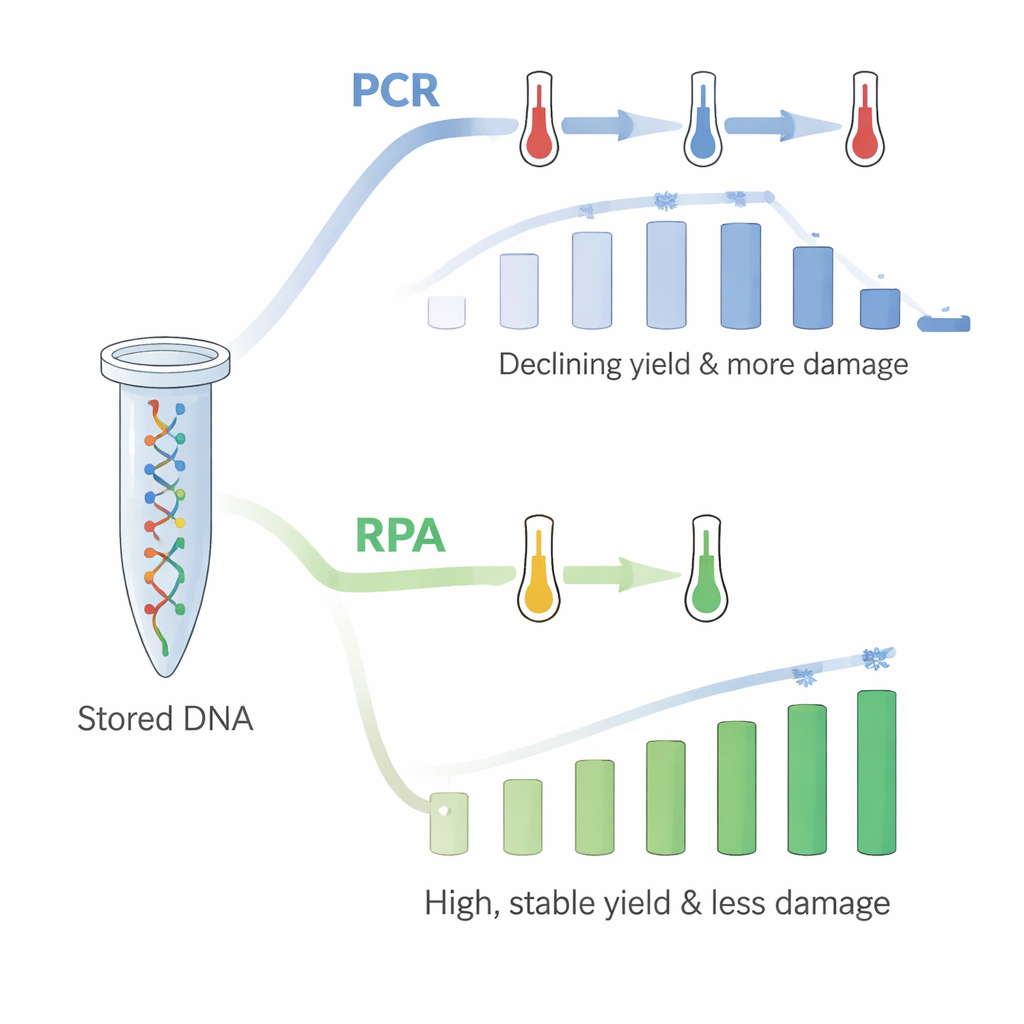
W kierunku przenośnej, długowiecznej pamięci DNA
Łącząc odporną chemię kliknięć z kopiowaniem DNA w niskiej temperaturze, praca ta wskazuje praktyczną drogę do przekształcenia prostych plastikowych probówek w wielokrotnego użytku kartridże pamięci DNA. DNA pozostaje fizycznie zablokowane na probówce, gdzie można wielokrotnie odpytywać konkretne „pliki” bez zużywania oryginalnych cząsteczek, szczególnie przy użyciu łagodniejszej metody RPA. Dla osób niebędących specjalistami kluczowy wniosek jest taki, że DNA to nie tylko kod życia — może też służyć jako kompaktowy, trwały nośnik informacji cyfrowej. Metody takie jak ta zbliżają nas do przyszłości, w której kopie zapasowe długoterminowe mogą nie spoczywać na wirujących dyskach, lecz w starannie zaprojektowanych cząsteczkach leżących spokojnie na półce w laboratorium.
Cytowanie: Roy, S., Ji, H.P. & Lau, B.T. DNA conjugation on functionalized plastic surfaces for sequential, iterative single molecule sequencing. Sci Rep 16, 6467 (2026). https://doi.org/10.1038/s41598-026-37575-y
Słowa kluczowe: przechowywanie danych w DNA, chemia kliknięć, konjugacja na powierzchni plastiku, wzmacnianie przez replikazę z rekombinazą (RPA), sekwencjonowanie nanoporowe