Clear Sky Science · pl
Szybka, niewymagająca uczenia kwantyfikacja i śledzenie organoidów z OrganoSeg2
Dlaczego małe, hodowane w laboratorium tkanki mają znaczenie
W laboratoriach na całym świecie naukowcy hodują teraz miniaturowe wersje tkanek ludzkich zwane organoidami. Te niewielkie, trójwymiarowe skupiska komórek potrafią naśladować zachowanie prawdziwych narządów lub nowotworów, dzięki czemu są potężnym narzędziem do badania chorób i testowania terapii. Istnieje jednak wąskie gardło: badacze mogą zebrać tysiące obrazów mikroskopowych o niskim powiększeniu organoidów, a mimo to mieć trudności z mierzeniem, jak każdy z nich rośnie, zmienia kształt lub obumiera w czasie. W artykule przedstawiono OrganoSeg2, przebudowane oprogramowanie, które zamienia te zwykłe, szare obrazy w bogate, wiarygodne pomiary dotyczące każdego pojedynczego organoidu — bez konieczności trenowania sztucznej inteligencji czy używania drogich układów obrazowania.
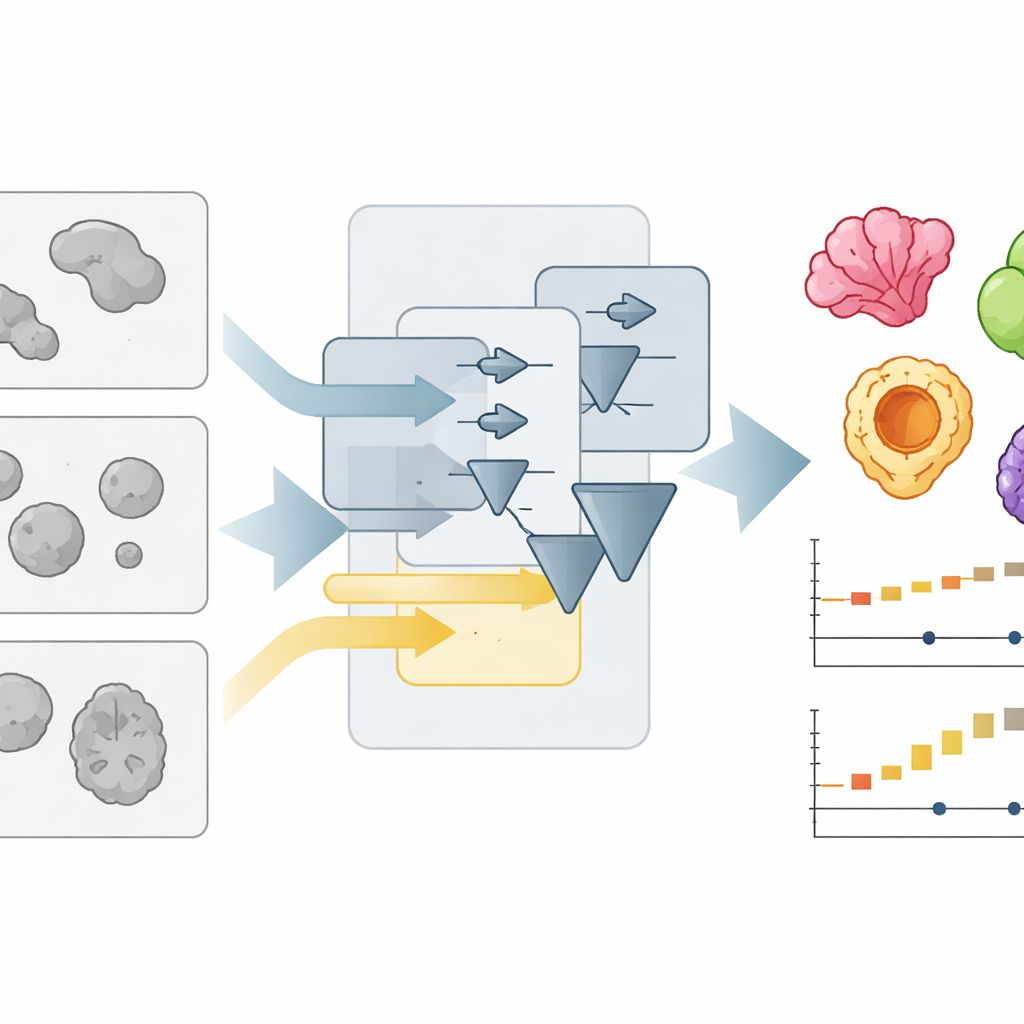
Nowy sposób czytania zatłoczonych zdjęć mikroskopowych
Organoidy są zazwyczaj obrazowane za pomocą prostych mikroskopów jasnego pola, które przedstawiają je jako słabe, nachodzące na siebie plamy. Automatyczne wyodrębnienie konturu każdej plamy — „segmentacja” obrazu — jest znacznie trudniejsze, niż się wydaje, szczególnie gdy laboratoria stosują różne formaty hodowli, oświetlenie lub obiektywy. Autorzy wcześniej stworzyli OrganoSeg, program radzący sobie z podstawową segmentacją, ale spowalniający i stający się niewygodnym przy kolekcjach obrazów sięgających setek. W OrganoSeg2 przebudowano oprogramowanie od podstaw, wdrożono nowocześniejszy interfejs, uproszczono wewnętrzny kod i udostępniono kilka dotąd ukrytych ustawień, aby użytkownicy mogli precyzyjnie dostroić, jak program oddziela organoidy od tła, rozdziela stykające się sąsiadujące obiekty oraz ignoruje artefakty przy krawędziach obrazu. Aplikacja teraz zapisuje te decyzje jako metadane, dzięki czemu analizy są odtwarzalne i łatwe do udostępnienia.
Przyspieszenie pracy bez utraty szczegółów
Poza elastycznością, zespół skupił się silnie na szybkości i wygodzie użytkowania. W wcześniejszych wersjach oprogramowanie automatycznie obliczało wszystkie możliwe pomiary dla każdego organoidu, nawet gdy potrzebnych było tylko kilka. OrganoSeg2 zamiast tego dokonuje jedynie wybranych przez użytkownika obliczeń i reorganizuje powiązane kalkulacje tak, aby kosztowne czasowo kroki były wykorzystywane ponownie. Ogranicza też ilość informacji rysowanych na ekranie, pokazuje etykiety tylko wtedy, gdy są potrzebne, oraz dodaje skróty klawiszowe i narzędzia interaktywne do szybkiego usuwania odpadków lub obiektów niebędących organoidami. Te rozwiązania projektowe skracają typowe operacje — takie jak segmentacja obrazów, wyświetlanie obrysów i eksport danych — około dziesięciokrotnie, co sprawia, że obsługa dużych, kafelkowanych obrazów i długich eksperymentów w czasie rzeczywistym jest praktyczna na zwykłym komputerze.
Przewyższając zaawansowane technologicznie konkurenty na rzeczywistych danych
Aby sprawdzić działanie OrganoSeg2, autorzy porównali go z kilkoma innymi narzędziami do segmentacji, w tym z systemami uczenia głębokiego, które wymagają trenowania na ręcznie oznaczonych przykładach. Zebrali zestawy obrazów z sześciu różnych źródeł — takich jak organoidy jelita grubego, płuc, trzustki, mózgu i piersi, a także ciała embrioidalne — gdzie eksperci ludzie już wyrysowali granice organoidów. Używając standardowego wskaźnika dokładności mierzącego nakładanie się zautomatyzowanych obrysów z ręcznymi, OrganoSeg2 dorównywał lub przewyższał wyspecjalizowane narzędzia w większości zestawów danych i wyraźnie prowadził na trudnych obrazach raka piersi pełnych luźnych materiałów i o nietypowych kształtach organoidów. Co istotne, OrganoSeg2 osiągnął te wyniki bez konieczności użycia dziesiątek tysięcy przykładów treningowych i działał przynajmniej tak szybko jak konkurencja, w tym systemy oparte na sztucznej inteligencji.
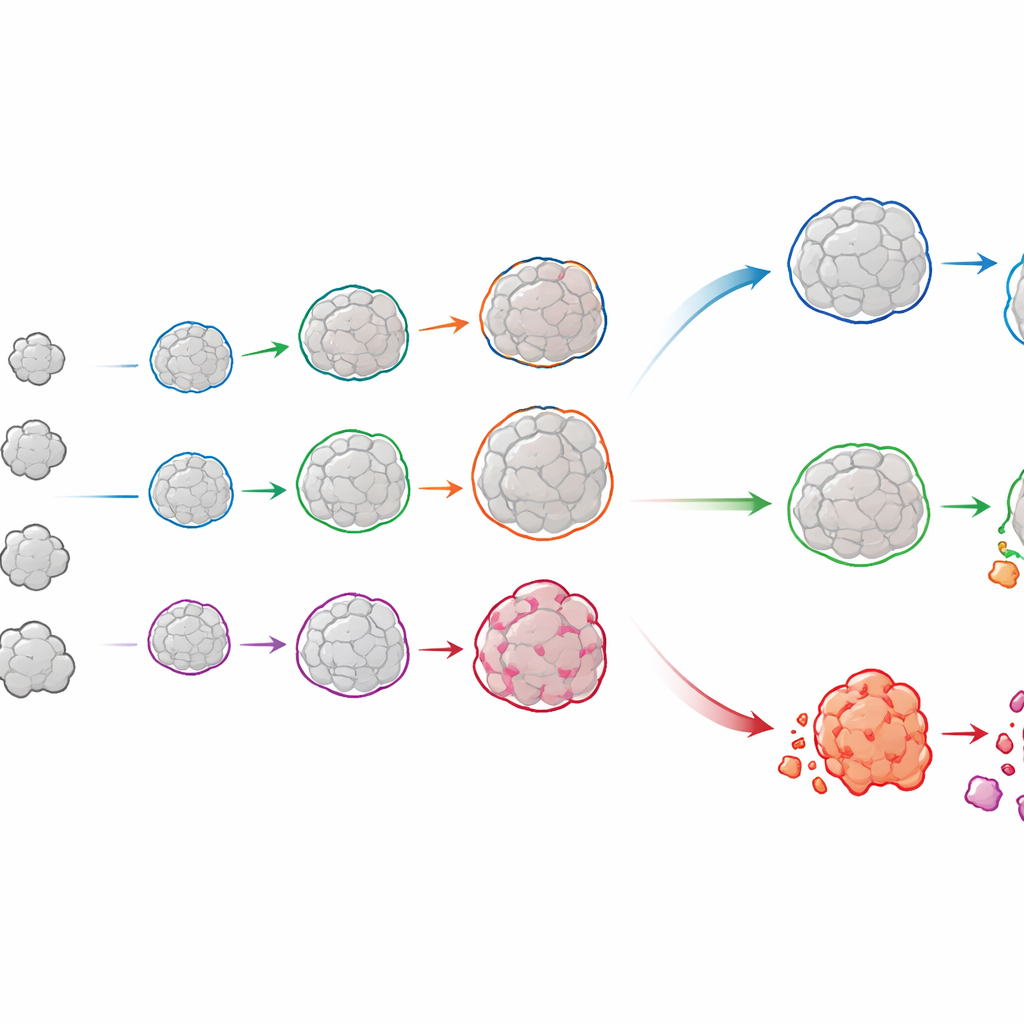
Śledzenie historii życia każdego organoidu
OrganoSeg2 robi więcej niż wyznaczanie konturów organoidów na pojedynczych klatkach. Potrafi wyrównać obrazy wykonane w różnych dniach i powiązać ten sam organoid w czasie, budując historię wzrostu dla każdego z nich. Gdy autorzy zastosowali to do organoidów hodowanych bezpośrednio z luminalnych guzów piersi pacjentów, zaobserwowali, że poszczególne organoidy rzadko rosły równomiernie; wiele z nich spowalniało lub plateauało, odzwierciedlając fakt, że prawdziwe guzy zawierają mieszankę regionów szybko i wolniej rosnących. Dopasowując te trajektorie do prostego modelu wzrostu, zespół mógł zmierzyć zarówno tempo rozrostu każdego organoidu, jak i prawdopodobny rozmiar końcowy. Porównanie tych wzorców między pacjentami ujawniło, że guzy o podobnym ogólnym tempie wzrostu mogą kryć bardzo różne proporcje zachowań wewnętrznych — różnice, które mogą mieć znaczenie przy przewidywaniu reakcji na leczenie.
Obserwowanie, jak komórki nowotworowe żyją i umierają po napromienianiu
Oprogramowanie łączy także obrazy jasnego pola z barwnikami fluorescencyjnymi raportującymi stan komórek. W nowych eksperymentach autorzy wystawili organoidy raka piersi na dawki promieniowania zbliżone do tych stosowanych w klinice i zabarwili je markerem żywych komórek, który świeci podczas programowanej śmierci komórkowej, oraz drugim barwnikiem ujawniającym martwe komórki na końcowym punkcie czasowym. OrganoSeg2 wykorzystał obraz jasnego pola do zdefiniowania kształtu organoidu, a następnie mierzył sygnały fluorescencyjne w każdym z nich przez wiele dni. Pozwoliło to zespołowi śledzić, organoid po organoidzie, kiedy promieniowanie wywołuje śmierć i jak silna jest ta odpowiedź. Niektóre organoidy pacjentów reagowały słabo, podczas gdy inne wykazywały wysoką wrażliwość nawet przy niższych dawkach, podkreślając, jak zróżnicowane mogą być odpowiedzi guzów.
Co to znaczy dla przyszłych badań i opieki
Podsumowując, praca pokazuje, że staranna, konfigurowalna obróbka obrazów może rywalizować lub przewyższać złożone metody głębokiego uczenia dla szerokiego zakresu obrazów organoidów, pozostając jednocześnie przejrzysta i łatwa do dostrojenia. OrganoSeg2 zamienia proste, niskopowiększeniowe filmy organoidów w szczegółowe zapisy tego, jak każde małe tkanki rosną i przetrwają w różnych warunkach. Dla badaczy podstawowych oferuje solidny sposób na rozłożenie ukrytej różnorodności kultur organoidów. W badaniach nad rakiem w szczególności otwiera drzwi do wykorzystania organoidów pochodzących od pacjentów nie tylko do prostych testów „tak‑lub‑nie” na leki, lecz także do bogatych, czasowo rozdzielonych pomiarów wzrostu i śmierci komórek, które być może pewnego dnia pomogą precyzyjniej dobierać terapie.
Cytowanie: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Słowa kluczowe: organoidy, analiza obrazów, badania nad rakiem, mikroskopia, reakcja na promieniowanie