Clear Sky Science · pl
Odkrywanie potencjalnych MTA, genów kandydackich i sieci regulacyjnych microRNA zaangażowanych w tolerancję na zasolenie wywołaną w irańskim Aegilops tauschii
Dlaczego zasolone gleby zagrażają naszemu codziennemu chlebowi
W miarę jak zmiany klimatu powodują susze, a woda do nawadniania staje się coraz bardziej zasolona, ogromne obszary gruntów rolnych stają się zbyt słone dla zwykłej pszenicy. To ma znaczenie dla każdego, kto polega na chlebie jako podstawowym pokarmie. Streszczenie przedstawionego badania zwraca uwagę na dziką trawę, Aegilops tauschii, bezpośredniego przodka współczesnej pszenicy chlebowej, aby odkryć ukryte narzędzia genetyczne — i maleńkie cząsteczki regulatorowe — które pomagają roślinom radzić sobie z zasolonymi warunkami. Mapując te naturalne mechanizmy obronne, badacze mają nadzieję dostarczyć hodowcom nowe sposoby opracowywania odmian pszenicy, które pozostaną produktywne nawet wtedy, gdy gleba stanie się zasolona.
Dzikie kuzynostwo pszenicy jako ukryte źródło
Aegilops tauschii występuje naturalnie na obszarze Żyznego Półksiężyca, w tym w Iranie, gdzie przez tysiące lat adaptowała się do surowych, suchych i często zasolonych środowisk. Gatunek ten dostarczył składową „D” genomu, którą nosi dzisiejsza pszenica chlebowa. Ponieważ współczesne, wysoko plenne odmiany pszenicy wywodzą się z relatywnie wąskiej puli genetycznej, często brakuje im pełnego spektrum cech tolerancji na stres, które wciąż występują u ich dzikich krewniaków. Autorzy zgromadzili 77 ekotypów (lokalnych form) irańskiego Aegilops tauschii i uprawiali je na etapie siewek zarówno w warunkach normalnych, jak i zasolonych, mierząc cechy takie jak długość korzenia i pędu, masę świeżą i suchą oraz powierzchnię liści i korzeni. Zasolenie wyraźnie zmniejszyło wszystkie te cechy, potwierdzając, że wysoki poziom soli rzeczywiście szkodzi młodym roślinom.
Czytanie odcisków DNA tolerancji na sól
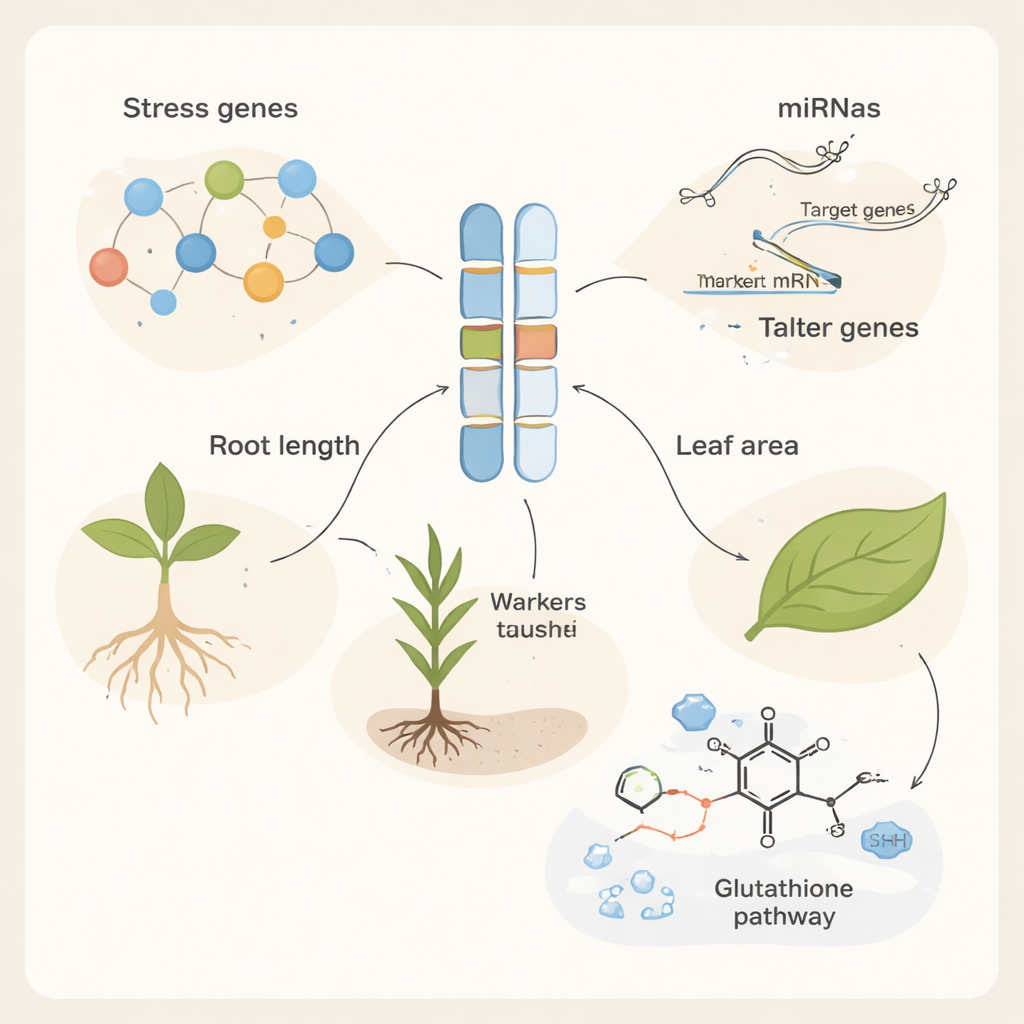
Aby zrozumieć, dlaczego niektóre dzikie rośliny lepiej radziły sobie z solą niż inne, zespół sięgnął po markery DNA — krótkie, łatwe do zmierzenia sekwencje rozmieszczone w całym genomie, które działają jak kody kreskowe dla pobliskich genów. Przy użyciu kombinacji markerów „losowych” i półlosowych markerów RAMP oceniono setki prążków DNA i sprawdzono rzeczywiste zróżnicowanie kolekcji. Stwierdzono wysoki poziom zmienności genetycznej, przy czym niektóre systemy markerów, takie jak ISJ9 i OPE03-Xgwm44-7DF, wykazały szczególnie dużą zdolność do rozróżniania poszczególnych ekotypów. To bogactwo różnorodności oznacza, że irańskie Aegilops tauschii wciąż zawiera wiele unikalnych wariantów genetycznych, z których hodowcy mogą czerpać. Poprzez statystyczne powiązanie konkretnych prążków DNA z cechami siewek pod stresem solnym, badacze zidentyfikowali 115 asociacji marker–cecha, wskazując regiony genomu wpływające na rozwój korzeni, pędów i liści w warunkach zasolenia.
Od markerów do funkcjonalnych genów obrony przed stresem
Znalezienie użytecznego markera DNA to dopiero pierwszy krok; następnie autorzy zastanawiali się, które rzeczywiste geny leżą w pobliżu tych markerów i mogą pełnić funkcję. Korzystając z referencyjnego genomu pszenicy, przeszukali 500 000 par zasad wokół każdego z powiązanych markerów i odkryli 254 geny kandydackie. Wiele z tych genów zostało niezależnie potwierdzonych przez obszerne zbiory danych RNA-seq jako zmieniające swoją aktywność w górę lub w dół, gdy rośliny napotykały stres środowiskowy, w tym zimno, upał, niedobór składników odżywczych i choroby. Geny kandydackie były wzbogacone w role związane z reakcjami obronnymi oraz ochroną przed upałem i uszkodzeniem oksydacyjnym. Kilka z nich koduje białka takie jak receptory odpornościowe, szaperony indukowane przez ciepło oraz tzw. białka typu taumatin i osmotyna, które pomagają stabilizować komórki, gdy sól powoduje utratę wody i nagromadzenie szkodliwych reaktywnych form tlenu. Analiza ścieżek metabolicznych uwypukliła metabolizm glutationu, kluczowy system chemiczny wykorzystywany przez rośliny do odtruwania produktów ubocznych stresu.
Maleńkie wyłączniki RNA, które dopracowują reakcje na stres
Geny nie działają w izolacji; są kontrolowane przez microRNA, bardzo krótkie cząsteczki RNA, które mogą wyłączać lub tłumić aktywność genów. Badacze przewidzieli, które pszeniczne microRNA mogą celować w ich geny kandydackie i odkryli 107 odrębnych microRNA tworzących gęste sieci regulacyjne. Wiele z tych maleńkich regulatorów było już znanych z reagowania na suszę, upał, metale lub zasolenie. Na przykład specyficzne microRNA wcześniej powiązane z tolerancją na sól, tolerancją na wysoką temperaturę lub „pamięcią stresu” okazały się kontrolować kluczowe geny obronne i detoksykacyjne zidentyfikowane w tym badaniu. Niektóre geny były celem wielu microRNA, co sugeruje, że rośliny nakładają na siebie kilka przełączników regulatorowych, aby precyzyjnie dostosować odpowiedź w miarę zmiany poziomu stresu.
Wprowadzenie dzikiej odporności na pola uprawne
Razem katalog zróżnicowanych markerów DNA, 254 genów kandydackich oraz 107 regulujących microRNA tworzy mapę drogową do poprawy wydajności pszenicy na zasolonych glebach. Hodowcy mogą przekształcić najbardziej informacyjne markery w proste testy laboratoryjne, aby przesiewać duże liczby roślin pod kątem ukrytych cech tolerancji na sól — strategia znana jako selekcja wspomagana markerami. W dłuższej perspektywie najbardziej obiecujące geny i ich regulatory microRNA mogłyby zostać świadomie wprowadzone lub edytowane w wrażliwych odmianach pszenicy w celu wzmocnienia ich naturalnych mechanizmów obronnych. Chociaż autorzy podkreślają potrzebę dalszej walidacji eksperymentalnej w warunkach zasolenia na żywych roślinach, badanie wyraźnie pokazuje, że dziki krewny Aegilops tauschii posiada potężne narzędzia genetyczne, które, stosowane rozważnie, mogą pomóc zabezpieczyć plony pszenicy wobec nasilających się presji związanych z zasoleniem i zmianami klimatu.
Cytowanie: Sabouri, H., Nikkhah, N., Kazerani, B. et al. Uncovering the potential MTAs, candidate genes and microRNAs regulatory networks involved in salinity stress tolerance triggered in Iranian Aegilops tauschii. Sci Rep 16, 6877 (2026). https://doi.org/10.1038/s41598-026-37365-6
Słowa kluczowe: tolerancja na zasolenie, hodowla pszenicy, Aegilops tauschii, geny reagujące na stres, roślinne microRNA