Clear Sky Science · pl
Porównawcza analiza kariotypu jedenastu gatunków Lilium z Chin przy użyciu FISH z oligonukleotydowymi sondami rDNA
Dlaczego chromosomy lilii mają znaczenie poza laboratorium
Ogrodówki lilia to nie tylko piękne kwiaty i tradycyjne leki — są również modelami genetycznymi, które pomagają naukowcom zrozumieć, jak powstają nowe gatunki rólin i jak prawidłowo je klasyfikować. W niniejszym badaniu przyjrzano się wnętrzu komórek jedenastu chińskich gatunków lilii, z których wiele jest wykorzystywanych jako póżywienie lub surowiec leczniczy, aby zobaczyć, jak ułożone są ich chromosomy i jakie mają oznaczenia. Poprzez porównanie tych ukrytych struktur autorzy wyjaśnili, które lilie są rzeczywiście bliskimi krewnymi, dostarczając dowodów rozwiązujących wieloletnie spory o drzewa filogenetyczne lilii.
Rozplątywanie zawiłego drzewa rodowego lilii
Rodzaj Lilium obejmuje około 125 gatunków występujących na półkuli północnej, przy czym Chiny są jednym z głównych centrow różnorodności. Przez ponad stółecie botanicy starali się grupować te gatunki w naturalne sekcje głównie na podstawie cech widocznych, takich jak kształt kwiatu. Jednak podobieństwo kwiatów nie zawsze oznacza bliskie pokrewieństwo, a badania genetyczne chloroplastów i jąder komórkowych czasem dawały sprzeczne wyniki co do powiązań między liliami. W szczególności grupa zwana Leucolirion wraz z jej dwiema podsekcjami (6a i 6b) oraz kilka gatunków z południowo-zachodnich i centralnych Chin było trudnych do pewnego umiejscowienia.
Odczytywanie kodów kreskowych na chromosomach
Aby sprostać temu problemowi, autorzy sięgnęli po cytogenetykę, czyli naukę o chromosomach. Wszystkie jedenaście badanych gatunków ma taki sam podstawowy zestaw dwunastu chromosomów, zwykle występujących jako 24 u diploidów; dwie populacje Lilium lancifolium były triploidalne z 36 chromosomami. Pod mikroskopem każdy gatunek wykazuje dwa większe chromosomy i dziesięc mniejsze, ale subtelne różnice w ksztalcie i długości cząstko trudno dostrzec gołym okiem. Zespół dokonał zatem precyzyjnych pomiarów rozmiarów chromosomów i zastosował technikę fluorescencyjnej hybrydyzacji in situ (FISH), umieszczając świecące znaczniki DNA na specyficznych regionach rDNA (rybosomalnego DNA), które działają jak jasne kody kreskowe wzdłuż każdego chromosomu.
Znajdowanie wzorów w genomach lilii
Naukowcy zmapowali dwa typy rDNA — 5S i 35S — na chromosomach każdego gatunku. Większość lilii miała jedno miejsce 5S i od dwóch do sześciu miejsc 35S, często w charakterystycznych pozycjach. Na przykaład cztery gatunki tradycyjnie umieszczane w podsekcji Leucolirion 6a (L. leucanthum, L. sargentiae, L. sulphureum i L. regale) miały bardzo podobne wzory znaków rDNA na tych samych parach chromosomów, co wskazuje na bliskie pokrewieństwo, chociaż L. regale wykazywał pewne dodatkowe zmiany. W przeciwieństwie do tego gatunki siostrzanej podsekcji 6b oraz niektóre lilia Sinomartagon wykazały wyraźnie rozne układy rDNA, podkreślając realny podział między tymi dwiema grupami. Poza Leucolirion silnie wspólne wzory łączyły szeroko uprawiane L. lancifolium z L. pumilum i L. davidii, co zgadza się z wcześniejszymi badaniami sekwencji DNA, które grupowały je razem.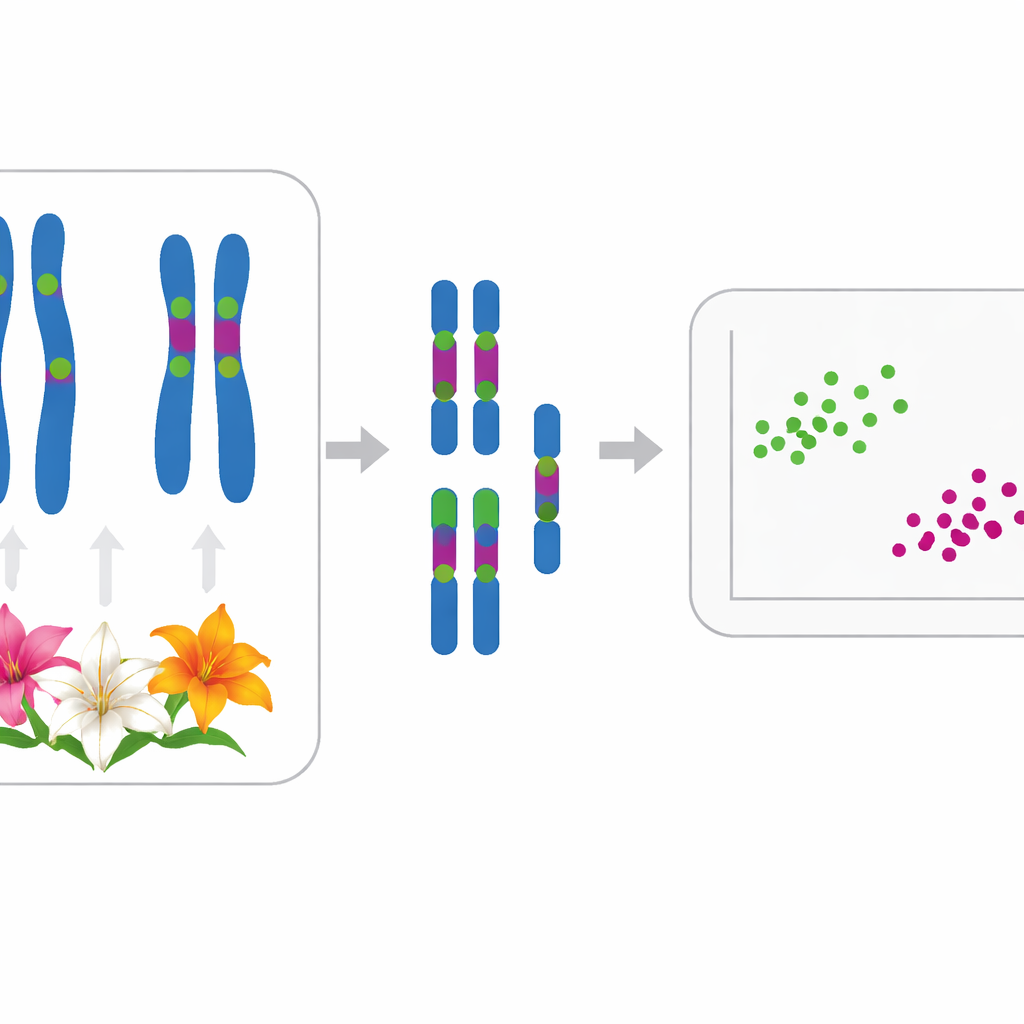
Przekształcanie pomiarów w mapę powiązań
Ponadto zespół skwantyfikował, jak niejednorodny jest każdy kariotyp — zarówno w połozeniu centromerów ("talia" chromosomu), jak i w długościach chromosomów. Użyto dwóch indeksów statystycznych, MCA i CVCL, aby uchwycić te cechy i naniesiono jedenaście gatunków na dwuwymiarowy wykres. Każdy gatunek zajmował odrebne miejsce, pokazując, że nawet pozornie podobne kariotypy można odróżnić przy dokładnych pomiarach. Szersza analiza statystyczna (analiza głównych współrzędnych) pogrupowała następnie lilie w dwa główne klastry, które dobrze pokrywają się z proponowaną historią ewolucyjną. Jeden klaster zawierał L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale oraz formy L. lancifolium i L. davidii; drugi grupował L. leucanthum, L. sargentiae, L. sulphureum, L. henryi i L. rosthornii.
Co to oznacza dla nazewnictwa i wykorzystania lilii
Łącząc szczegółowe pomiary chromosomów z mapami kodu kreskowego rDNA, badanie to wykazuje, że gatunki lilii różnią się kariotypami bardziej niż dotychczas sądzono i że te różnice niosą jasny sygnał ewolucyjny. W praktycznym wymiarze praca wspiera traktowanie podsekcji Leucolirion 6a jako naturalnej, dobrze określonej grupy w obrębie rodzaju Lilium, zgodnie z ostatnimi propozycjami klasyfikacyjnymi. Dla hodowców, praktyków ziołolecznictwa i planistów ochrony przyrody dokładniejszy obraz pokrewieństw między liliami może ukierunkować krzyżówki, chronić różnorodność genetyczną oraz zapewnić, że odmiany lecznicze i spożywcze są prawidłowo identyfikowane i wykorzystywane.
Cytowanie: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Słowa kluczowe: Lilium, chromosomy, fluorescencyjna hybrydyzacja in situ, ewolucja roślin, cytotaksonomia