Clear Sky Science · pl
Porównawcza ocena metod profilowania transkryptomu ukierunkowanego HTG i TempO‑Seq
Dlaczego to ma znaczenie dla opieki nad pacjentami z rakiem
Kiedy lekarze i naukowcy badają nowotwory, często sięgają po „cząsteczki wiadomości” komórki — RNA — aby zobaczyć, które geny są aktywne, a które wyciszone. Te wzorce mogą ujawnić, jak guz się zachowuje i które terapie mogą być najskuteczniejsze. Jednak większość szpitalnych próbek przechowywana jest w blokach parafinowych po utrwaleniu formaliną, co uszkadza wrażliwe RNA. W tym badaniu zadano praktyczne pytanie o duże konsekwencje dla badań nad rakiem: skoro powszechnie stosowany test RNA zniknął z rynku, czy nowsza metoda może go zastąpić i dostarczyć równie użyteczne wyniki z tych rutynowo utrwalonych próbek?
Dwa narzędzia do odczytu aktywności genów
Przez lata wiele laboratoriów polegało na metodzie zwanej HTG EdgeSeq Human Transcriptome Panel (HTP), pozwalającej odczytywać aktywność genów bezpośrednio z niewielkich wycinków tkanki utrwalonej w formalinie i zatopionej w parafinie (FFPE). Podejście to umożliwiało zbadanie niemal wszystkich genów ludzkich bez wcześniejszego izolowania RNA, oszczędzając czas i chroniąc ograniczony materiał. Firma stojąca za HTG EdgeSeq jednak zbankrutowała, co zmusiło badaczy do poszukiwania alternatywy. Nowa technologia, TempO‑Seq (TOS), od innego producenta obiecuje podobne możliwości: także celuje w wiele genów jednocześnie, działa na uszkodzonym RNA z próbek FFPE oraz zaprojektowana jest tak, by być czułą, powtarzalną i stosunkowo przystępną cenowo.
Próba porównawcza metod
Zespół badawczy porównał te dwie technologie w praktycznym scenariuszu. Przeanalizowali 21 przechowywanych próbek raka endometrium oraz trzy standardowe materiały referencyjne RNA — najpierw przy użyciu HTG HTP, a następnie TempO‑Seq. Obie metody korzystały z ukierunkowanych paneli obejmujących łącznie ponad 18 000 tych samych genów. Naukowcy zastosowali rygorystyczne kontrole jakości, upewniając się, że każda próbka wygenerowała wystarczającą liczbę odczytów sekwencjonowania i że pomiary były stabilne. Użyli też narzędzi statystycznych do usunięcia „efektów partii” — sztucznych różnic wynikających z faktu, że testy były wykonywane w różne dni, na różnych maszynach lub platformach.
Co się zgadza, a co nie
Analiza ekspresji pojedynczych genów wykazała, że obie metody nie zawsze się zgadzają. Różnice w projektowaniu sond, przygotowaniu próbek i zliczaniu odczytów sprawiają, że porównania pojedynczych genów mogą być obarczone szumem technicznym. Obraz ten zmienia się jednak, gdy bada się szersze wzorce łączące informacje z wielu genów jednocześnie. Sygnatury wielogenowe — takie jak te stosowane do grupowania guzów na podtypy molekularne, szacowania obecności komórek odpornościowych w próbce czy oceny czystości tkanki nowotworowej — wykazały znacznie silniejszą zgodność między TempO‑Seq a HTG. W większości przypadków wyniki lub klasyfikacje były podobne, nawet po przeprowadzeniu symulacji z mniejszą liczbą odczytów sekwencjonowania, by naśladować różne moce aparatów.
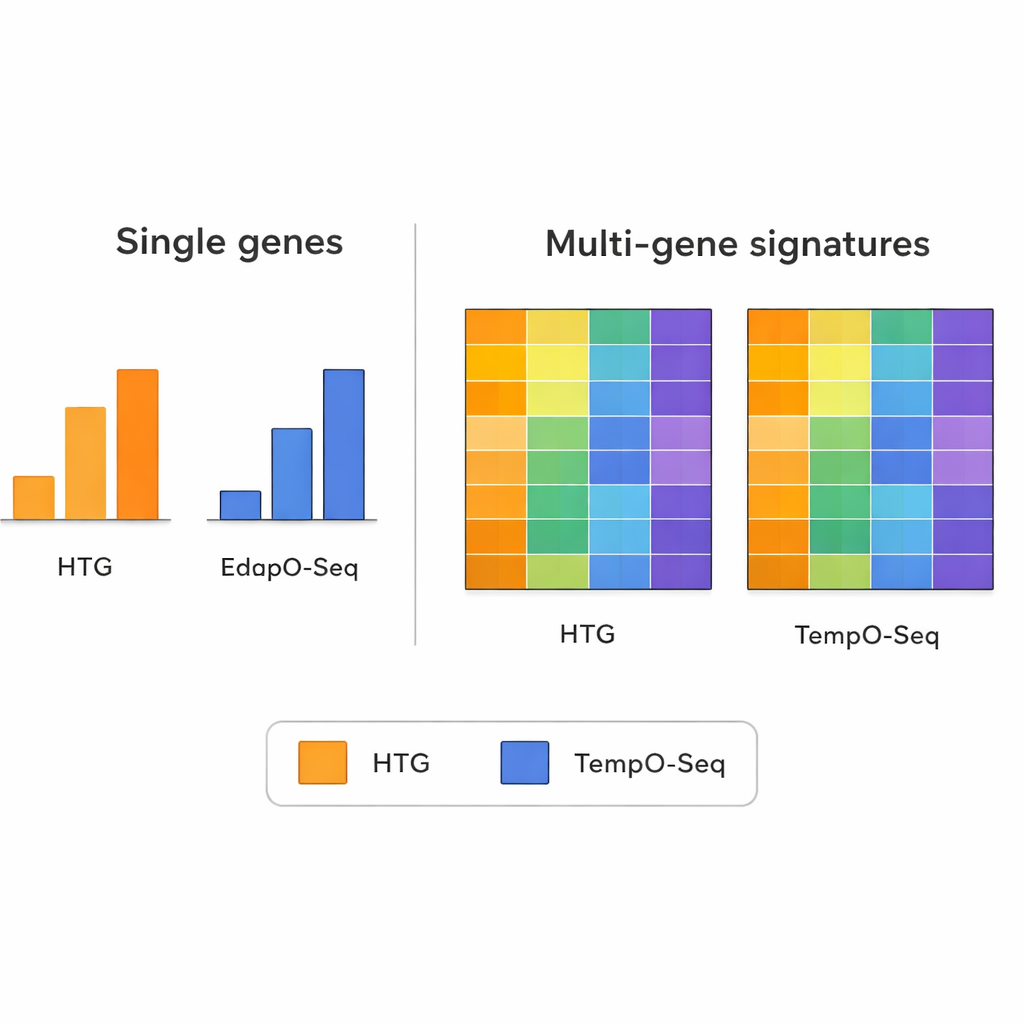
Wzorce wielogenowe jako wiarygodne sygnały
Badanie podkreśla ważną zasadę współczesnej genomiki: mierzenie pojedynczego genu może zostać zniekształcone przez usterki techniczne, podczas gdy łączenie sygnałów z kilkudziesięciu czy kilkuset genów zwykle uśrednia ten hałas. Autorzy zastosowali kilka powszechnie znanych narzędzi wielogenowych jako testów obciążających technicznie. Należały do nich panel dla raka piersi przypisujący guzy do podtypów wewnętrznych, algorytm oceniający, ile tkanki odpornościowej i łącznej jest wymieszane z próbką guza, oraz metoda estymująca udział różnych typów komórek odpornościowych. W ramach tych złożonych wyników TempO‑Seq zazwyczaj ściśle korespondował z HTG, sugerując, że rejestruje te same biologiczne sygnały, nawet jeśli niektóre drobne szczegóły różnią się.
Co to oznacza na przyszłość
Dla badaczy opierających się na archiwach FFPE do badań nad rakiem utrata zaufanej platformy mogła być poważnym problemem. To badanie porównawcze daje uspokojenie: TempO‑Seq wydaje się solidnym zamiennikiem dla HTG HTP, gdy celem są biomarkery wielogenowe i szerokie wzorce ekspresji, które stanowią podstawę wielu współczesnych narzędzi diagnostycznych i prognostycznych. Autorzy przestrzegają jednak, że bezpośrednie porównywanie wyników pojedynczych genów między platformami jest niezalecane, ponieważ każda metoda celuje w geny w nieco inny sposób. Zamiast tego zalecają skupienie się na złożonych sygnaturach wielogenowych w pracy międzyplatformowej. Mówiąc prościej, nowa metoda wydaje się zdolna kontynuować zadania swojego poprzednika dla większości praktycznych potrzeb badań onkologicznych, zwłaszcza gdy badaczy interesuje ogólny wzorzec wielu genów, a nie dokładna wartość pojedynczego genu.
Cytowanie: Fernández-Serra, A., López-Reig, R., Romero, I. et al. Comparative evaluation of HTG and TempO Seq targeted transcriptome profiling methods. Sci Rep 16, 6108 (2026). https://doi.org/10.1038/s41598-026-36810-w
Słowa kluczowe: profilowanie transkryptomiczne, rak endometrium, tkanka FFPE, ukierunkowane sekwencjonowanie RNA, biomarkery ekspresji genów