Clear Sky Science · pl
Zintegrowany identyfikator bakterii BSI na chipie wykorzystujący przybliżone dopasowanie k-merów
Dlaczego szybsze wykrywanie drobnoustrojów ma znaczenie
Dla pacjentów otrzymujących ratujące życie przeszczepy komórek macierzystych zakażenia krwi mogą przekształcić rekonwalescencję w stan nagły w ciągu kilku godzin. Lekarze wiedzą, że każda minuta się liczy, ale obecne narzędzia laboratoryjne do identyfikacji bakterii bywają powolne lub wymagają potężnych komputerów. W tym badaniu przedstawiono niewielki, energooszczędny układ scalony — nazwany PC-CAM — który może szybko skanować DNA z próbek pacjentów i w czasie rzeczywistym sygnalizować obecność groźnych bakterii, potencjalnie przy łóżku pacjenta.
Ryzyko zakażenia po leczeniu ratującym jelito
U niektórych pacjentów po przeszczepie rozwija się poważne powikłanie, w którym przeszczepione komórki odpornościowe atakują jelito biorcy. Jednym z obiecujących sposobów leczenia jest transplantacja mikrobioty kałowej, polegająca na wprowadzeniu zdrowych mikroorganizmów jelitowych od dawcy. Choć może to uratować jelito, czasem niesie ze sobą dodatkowe niebezpieczeństwo: szkodliwe bakterie z jelit mogą przedostać się do krwiobiegu i wywołać zagrażające życiu zakażenia. By leczyć takie zakażenia skutecznie, lekarze muszą jak najszybciej określić, które gatunki bakterii są obecne, lecz tradycyjne testy mogą trwać od godzin do dni i mogą przeoczyć nieznane szczepy.
Od powolnego składania genomów do szybkich fragmentów DNA
Nowoczesne sekwensery DNA potrafią odczytywać materiał genetyczny bezpośrednio z próbek krwi lub stolca niemal w czasie rzeczywistym. Wąskie gardło to już nie odczyt, lecz interpretacja. Konwencjonalne metody najpierw próbują odtworzyć całe genomy z milionów krótkich fragmentów DNA, a następnie dopasować zmontowane genomu do biblioteki referencyjnej — proces wymagający dużej mocy obliczeniowej. Autorzy zastępują to prostszą strategią: dzielą DNA na krótkie odcinki o stałej długości, zwane k-merami, i szukają tych fragmentów bezpośrednio w bazie znanych sekwencji bakteryjnych. Zamiast wymagać doskonałego dopasowania litera w literę, ich system toleruje pewną liczbę różnic, co pozwala radzić sobie z nieuniknionymi błędami sekwencjonowania i naturalnymi mutacjami. 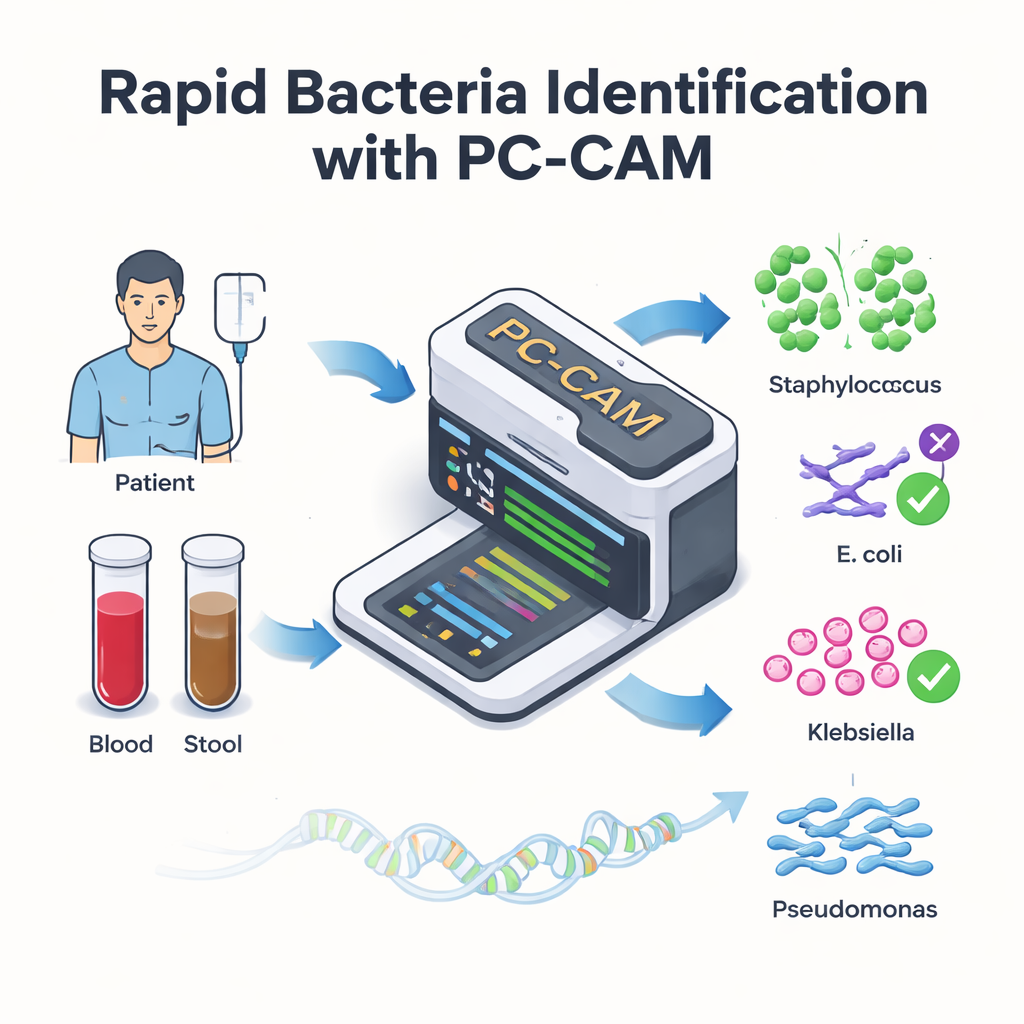
Inteligentny układ pamięci zaprojektowany do wyszukiwania DNA
W sercu PC-CAM znajduje się specjalizowany typ pamięci zwany pamięcią adresowaną treścią (content-addressable memory), która potrafi jednocześnie porównać nadchodzące dane ze wszystkim, co w niej zapisano. Badacze zaprojektowali wersję tej pamięci do „przybliżonego wyszukiwania” (ACAM), którą można wyregulować tak, by akceptowała dopasowania bliskie, a nie tylko dokładne. Każdy krótki fragment DNA jest kodowany i przechowywany jako wiersz w tej pamięci. Gdy nowy fragment z próbki pacjenta trafia na chip, układ aktywuje linię wyszukiwania przez wszystkie wiersze jednocześnie i mierzy, jak szybko maleją drobne sygnały elektryczne. Poprzez regulację dwóch napięć sterujących system ustawia próg dopuszczalnej liczby niezgodności, efektywnie określając, jak łagodne ma być dopasowanie. Porównanie na poziomie sprzętowym pozwala chipowi przesiewać wzorce znacznie szybciej i przy mniejszym zużyciu energii niż komputer ogólnego przeznaczenia.
Jak dobrze chip wykrywa prawdziwe bakterie
Zespół przetestował PC-CAM na rzeczywistych zestawach danych od pacjentów po transplantacji mikrobioty kałowej, porównując bakterie wykryte we krwi i kale z wynikami pełnej analizy genomowej opartej na oprogramowaniu. Nawet gdy chip przechowywał tylko niewielki, starannie dobrany podzbiór fragmentów DNA z każdego genomu bakteryjnego, wyniki w dużej mierze zgadzały się z droższą obliczeniowo metodą, poprawnie identyfikując kluczowe patogeny u wielu pacjentów. W rozszerzonych eksperymentach z symulowanymi odczytami DNA z różnych bakterii i przy różnych wskaźnikach błędów, czułość chipa (jego zdolność do wykrywania prawdziwych dopasowań) rosła wraz ze zwiększaniem tolerancji na różnice, podczas gdy swoistość (zdolność do unikania fałszywych alarmów) malała przy bardzo wysokich progach tolerancji. Autorzy pokazują, że proste kroki postprocessingowe — na przykład wymaganie zgody wielu fragmentów lub odrzucanie słabych dopasowań — mogą zmniejszyć liczbę tych fałszywych pozytywów. 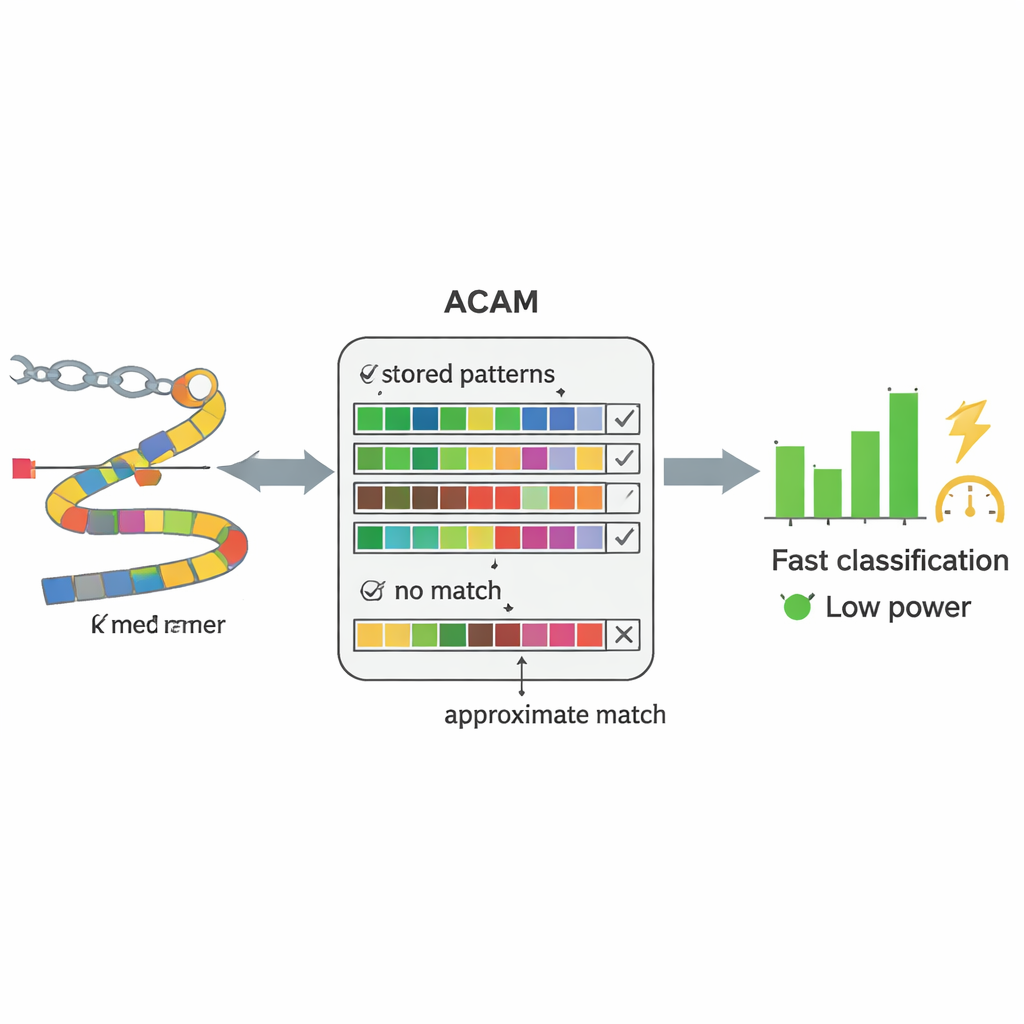
Mały sprzęt, duża prędkość i niskie zużycie energii
PC-CAM integruje pamięć ACAM z małym procesorem RISC-V na chipie o powierzchni zaledwie kilku milimetrów kwadratowych, wykonanym w standardowej technologii 65 nanometrów. Pomiary na rzeczywistym układzie pokazują, że może klasyfikować około 960 000 krótkich odczytów DNA na sekundę, zużywając około 1,27 miliwata mocy — mniej niż wiele cyfrowych zegarków naręcznych. W porównaniu z czołowym narzędziem programowym działającym na wysokiej klasy procesorze stacjonarnym, chip był mniej więcej 1900 razy szybszy w tego rodzaju zadaniu klasyfikacji. Chociaż jego dokładność jest nieco obniżona przez przechowywanie rozcieńczonej wersji każdego genomu, autorzy argumentują, że kompromis ten jest akceptowalny, gdy priorytetem są szybkość i niski pobór mocy, na przykład w opiece nagłej lub urządzeniach przenośnych.
Co to oznacza dla pacjentów i nie tylko
Mówiąc prościej, badanie pokazuje, że mały, niskomocowy chip może działać jak wyspecjalizowana wyszukiwarka DNA bakteryjnego, wykrywając groźne drobnoustroje we krwi lub kale niemal natychmiast. Nie zastępuje on pełnej analizy genetycznej wykonywanej w dużym laboratorium, ale może dostarczać szybkie wskazówki na miejscu, które bakterie są obecne, pomagając lekarzom wybrać antybiotyk szybciej i trafniej. To samo podejście można rozszerzyć na monitorowanie odporności na antybiotyki, sprawdzanie żywności i wody pod kątem skażeń lub obserwację upraw pod kątem chorób — wszystko to przy użyciu kompaktowego sprzętu, który przenosi zaawansowaną analizę DNA poza centrum danych i bliżej miejsca podejmowania decyzji.
Cytowanie: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Słowa kluczowe: zakażenie krwi, szybkie wykrywanie patogenów, sekwencjonowanie DNA, lab-on-a-chip, mikrobiom