Clear Sky Science · pl
Składanie transkryptomu pełnej długości i rozwój markerów SSR dla Spinibarbus hollandi przy użyciu sekwencjonowania PacBio SMRT
Dlaczego skromna rzeczna ryba ma znaczenie
W rzekach południowych Chin pływa Spinibarbus hollandi — ryba podobna do karpia, ceniona zarówno jako pokarm, jak i gatunek ozdobny. Hodowcy chcieliby ją hodować wydajniej, ale ryba rośnie wolno, dojrzewa późno i produkuje stosunkowo mało jaj. Opisane tu badanie wykorzystuje nowoczesne metody sekwencjonowania DNA i RNA, aby zbudować szczegółową genetyczną „listę części” dla tego gatunku. Te informacje genetyczne mogą ostatecznie pomóc hodowcom wybierać bardziej odporne i szybciej rosnące osobniki oraz wspierać ochronę dzikich populacji.
Przekształcanie wielu tkanek w mapę genetyczną
Aby uchwycić jak najwięcej informacji genetycznej, badacze pobrali sześć różnych tkanek — serce, skrzela, mózg, płetwę, wątrobę i gonady — od sześciu dorosłych samców i samic. Z tych tkanek wyizolowali RNA, cząsteczkę przenoszącą kopie aktywnych genów w komórkach. Korzystając z technologii PacBio SMRT, która odczytuje bardzo długie odcinki kopii RNA, zmontowali pierwszy transkryptom pełnej długości dla S. hollandi. Mówiąc prościej, stworzyli katalog o wysokiej rozdzielczości zawierający 15 197 odrębnych genów i 23 403 sekwencje transkryptów, z których większość jest znacznie dłuższa i pełniejsza niż to, co dawały starsze metody krótkich odczytów.
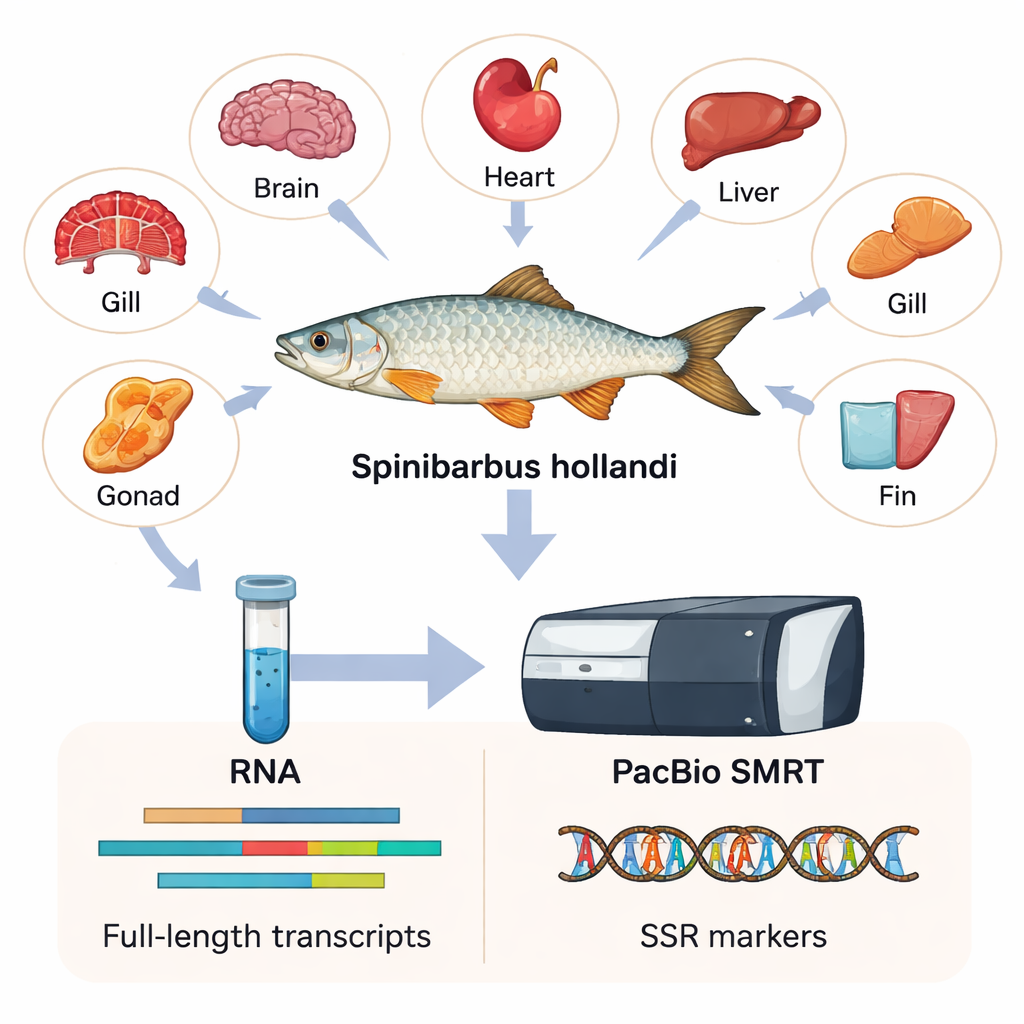
Co geny ujawniają o rybie
Następnie zespół zbadał, co te geny faktycznie robią. Porównali każdą sekwencję z dużymi publicznymi bazami danych grupującymi geny według funkcji. Ponad 95% genów dało się dopasować do znanych wpisów, co jest bardzo wysokim wskaźnikiem jakości danych. Wiele genów przyporządkowano do kategorii związanych z podstawowymi czynnościami komórkowymi, takimi jak metabolizm, przekazywanie sygnałów i rozwój, i większość była najbardziej podobna do genów innych ryb z rodziny karpiowatych. To potwierdza, że nowy transkryptom jest biologicznie poprawny i stanowi podstawę do wyszukiwania genów związanych z cechami takimi jak tempo wzrostu, tolerancja na stres i reprodukcja u S. hollandi.
Ukryte warstwy kontroli w RNA
Ponad samym identyfikowaniem genów, naukowcy przyjrzeli się także mechanizmom ich kontroli. Znaleźli 373 przypadki alternatywnego składania, gdzie ten sam gen jest przycinany i łączony na różne sposoby, tworząc odrębne komunikaty RNA. Najczęściej obserwowany wzorzec zachowywał fragmenty RNA, które u innych gatunków często są usuwane, sugerując szczególny sposób, w jaki ta ryba dopracowuje swoje białka. Odkryto też 2 397 długich niekodujących RNA — cząsteczek RNA, które nie tworzą białek, ale mogą regulować, kiedy i gdzie inne geny się włączają. Razem te odkrycia pokazują, że S. hollandi wykorzystuje bogaty zestaw mechanizmów kontroli na poziomie RNA, które mogą wpływać na wzrost, dojrzewanie płciowe i adaptację do lokalnych warunków.
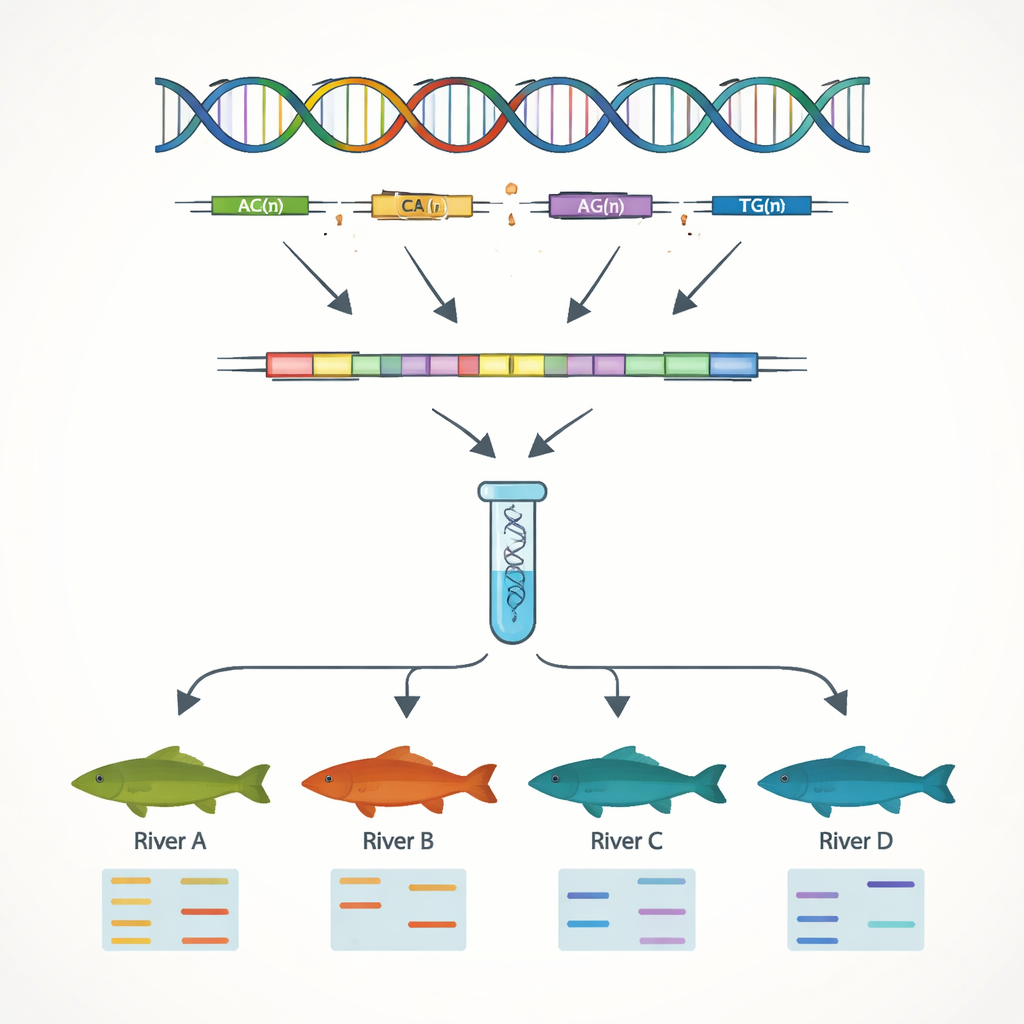
Budowanie punktów orientacyjnych DNA dla hodowli i ochrony
Głównym celem pracy było opracowanie prostych markerów DNA, które pozwolą odróżnić pojedyncze osobniki i populacje. Koncentrując się na sekwencjach genowych, autorzy wyszukali proste powtórzenia sekwencji, czyli SSR — krótkie motywy DNA, takie jak „AC” lub „AAT” powtarzane wielokrotnie. Fragmenty te zwykle różnią się między osobnikami, co czyni je użytecznymi jako genetyczne kody kreskowe. Odkryli 7 449 takich miejsc SSR i zaprojektowali dziesiątki krótkich starterów DNA do ich amplifikacji w laboratorium. Trzynaście z tych markerów okazało się silnie zmiennych i niezawodnych w testach na 51 rybach z czterech systemów rzecznych. Używając tylko tych 13 markerów, zespół mógł wyraźnie wykryć różnice genetyczne między populacjami z Jangcy a tymi z Rzeki Perłowej, co odzwierciedla łańcuchy górskie ograniczające naturalne mieszanie między dorzeczami.
Co to znaczy dla hodowców i rzek
Dla osób niezajmujących się na co dzień genetyką kluczowy wniosek jest taki, że autorzy stworzyli szczegółowy, wysokiej jakości referencyjny zasób genetyczny dla S. hollandi oraz zestaw praktycznych markerów DNA. To narzędzie pomoże badaczom wskazywać geny odpowiedzialne za wolny wzrost czy niską płodność, wesprze hodowców w doborze materiału hodowlanego o pożądanych cechach i pozwoli konserwatorom śledzić różnorodność genetyczną w systemach rzecznych. Choć potrzeba jeszcze pracy, aby powiązać konkretne geny z wydajnością w stawach czy na wolności, to badanie kładzie molekularne fundamenty pod przekształcenie tradycyjnej ryby rzecznej w nowoczesny, zarządzany zrównoważenie gatunek akwakultury.
Cytowanie: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Słowa kluczowe: Spinibarbus hollandi, transkryptom ryb, sekwencjonowanie PacBio, markery mikrosatelitarne, genetyka akwakultury