Clear Sky Science · pl
ONCOPLEX: inspirowany onkologią model hipergrafowy integrujący zróżnicowaną wiedzę biologiczną do przewidywania genów napędzających nowotwory
Dlaczego te badania są ważne
Nowotwory są napędzane przez niewielką liczbę silnych zmian genetycznych ukrytych wśród tysięcy nieszkodliwych. Znalezienie tych naprawdę groźnych genów „kierujących” jest kluczowe dla lepszej diagnostyki i terapii celowanych, ale przypomina wypatrzenie kilku przywódców w rozległym, hałaśliwym tłumie. W tym badaniu przedstawiono ONCOPLEX, nowe ramy sztucznej inteligencji, które nie rozpatrują genów pojedynczo, lecz w kontekście szlaków biologicznych, w których współdziałają, oferując ostrzejszy sposób na wskazanie genów rzeczywiście napędzających guzy.
Widzenie genów nowotworowych w ich biologicznych sąsiedztwach
Większość obecnych metod skanuje genomy nowotworów pod kątem mutacji pojawiających się nietypowo często lub wyróżniających się w prostych sieciach genowych. Te podejścia pomagają, ale biologia rzadko jest tak prosta. Geny zwykle działają w grupach w obrębie szlaków kontrolujących wzrost komórek, naprawę DNA i wiele innych procesów. ONCOPLEX akceptuje tę złożoność, reprezentując geny jako punkty, a szlaki jako większe, nakładające się grupy, które mogą jednocześnie obejmować wiele genów. Taka struktura, znana jako hipergraf, pozwala modelowi bezpośrednio uwzględniać relacje wielogenowe zamiast rozkładać je na liczne pary.
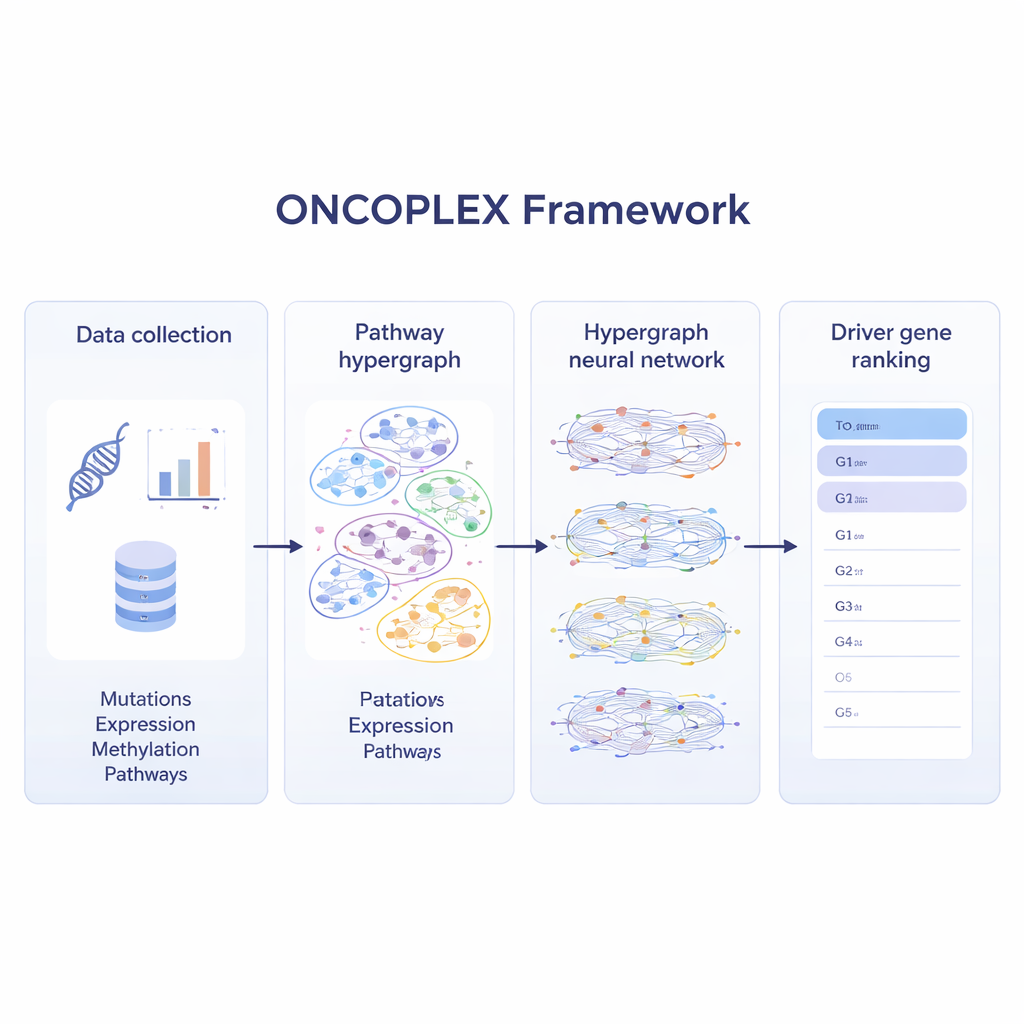
Mieszanie wielu warstw danych o raku
Aby w pełni wykorzystać współczesne zbiory danych onkologicznych, ONCOPLEX łączy kilka typów informacji o każdym genie. Wykorzystuje częstości mutacji, zmiany aktywności genów, chemiczne znaczniki na DNA (metylację) oraz bogaty zestaw cech biologicznych, takich jak zachowanie ewolucyjne i adnotacje funkcjonalne. Te cechy są przypisane do każdego genu w hipergrafie. Specjalistyczna sieć neuronowa następnie przekazuje informacje przez szlaki, pozwalając, by reprezentacja każdego genu była kształtowana zarówno przez jego własne dane, jak i przez zachowanie genów, z którymi współpracuje. Model jest trenowany przy użyciu genów już znanych jako napędzające nowotwory, przy jednoczesnym uczeniu się z wielu nieoznakowanych genów, które mogą być istotne, ale nie zostały jeszcze rozpoznane.
Przewyższanie istniejących narzędzi w wielu nowotworach
Naukowcy przetestowali ONCOPLEX na danych z The Cancer Genome Atlas, zarówno łącząc wiele typów guzów, jak i badając 11 poszczególnych nowotworów, w tym raka piersi, płuca, wątroby, pęcherza i głowy oraz szyi. Porównali go z kilkoma wiodącymi metodami opartymi na grafach i hipergrafach. We wszystkich testach ONCOPLEX lepiej rozróżniał znane geny napędzające od znacznie częstszych genów niebędących kierowcami oraz lepiej umieszczał prawdopodobne geny kierujące na szczycie list. Jego przewaga była szczególnie widoczna przy analizie genów o najwyższych rankingach, gdzie dokładne rozpoznanie ma największą wartość dla dalszych eksperymentów i translacji klinicznej.
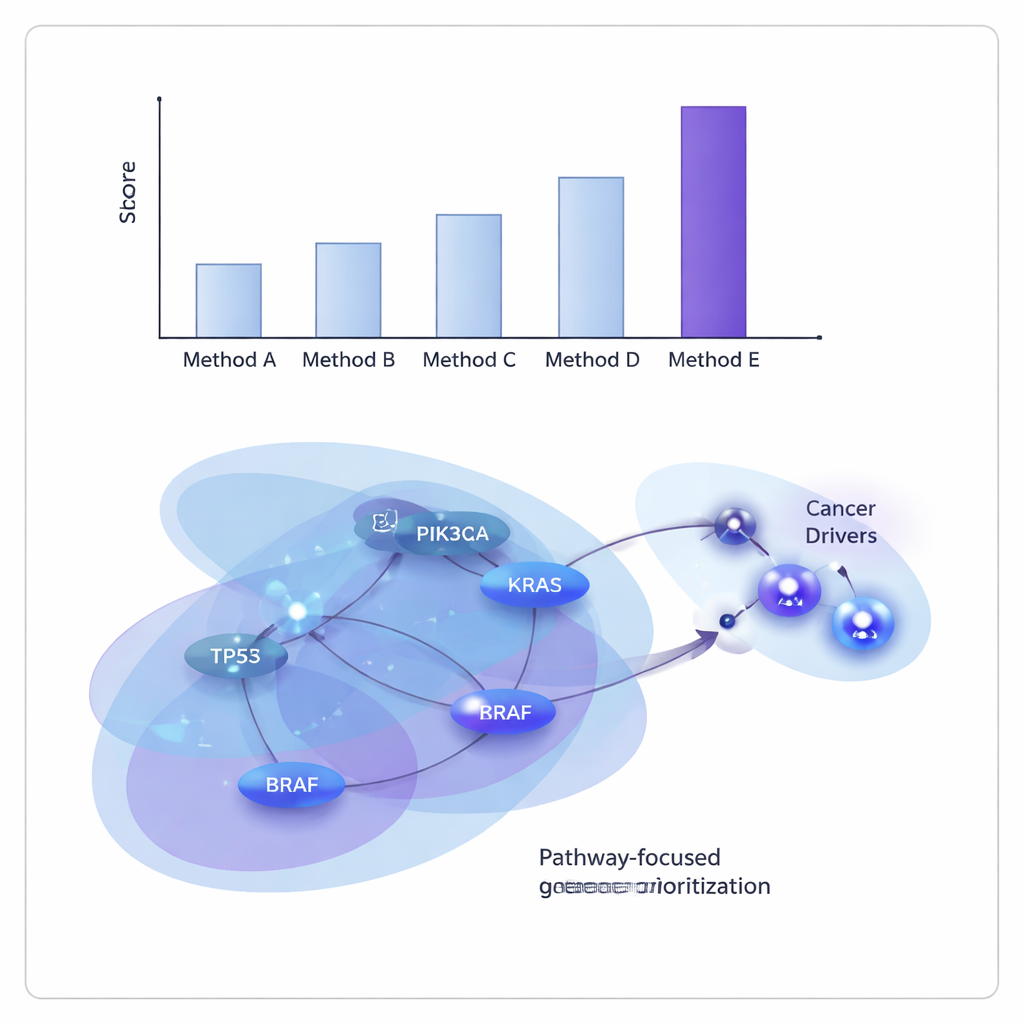
Odkrywanie wspólnych i specyficznych dla nowotworu sprawców
Ponad samymi wynikami wydajności, listy genów z ONCOPLEX odtwarzały wiele znanych genów onkologicznych, takich jak KRAS, BRAF oraz członkowie szlaku PI3K–AKT, potwierdzając, że model uchwytuje dobrze ugruntowaną biologię. Wskazał też obiecujących kandydatów, które nie są jeszcze powszechnie uznane za kierujące w niektórych typach raka, w tym geny takie jak GRB2 i MAPK3 w raku piersi oraz SHC1 w raku żołądka. Gdy zespół przeanalizował geny z najwyższych miejsc pod kątem wzbogacenia szlaków, odkrył silne sygnatury dobrze znanych ścieżek onkogennych, w tym sygnalizacji ErbB i PI3K–AKT–mTOR, a także ścieżek związanych z układem odpornościowym, co sugeruje, że ONCOPLEX koncentruje się na sieciach istotnych klinicznie.
Mocne strony, ograniczenia i co dalej
Pokazując, że bogatsze cechy biologiczne stopniowo poprawiają jego przewidywania, ONCOPLEX demonstruje wartość łączenia wielu źródeł danych w frameworku skoncentrowanym na szlakach. Jednocześnie badanie ujawnia ograniczenie: ponieważ wiele nowotworów dzieli dużą liczbę szlaków, model czasami faworyzuje szeroko działające geny „pan-cancer” kosztem tych naprawdę specyficznych dla jednego typu guza. Autorzy sugerują, by w przyszłości dopracować sposób wykorzystania informacji o szlakach, tak aby sygnały wspólne i specyficzne dla danego nowotworu można było wyraźniej rozdzielić.
Co to oznacza dla pacjentów i klinicystów
Dla osób niezaznajomionych z tematem kluczowe jest to, że ONCOPLEX oferuje bardziej biologicznie realistyczny sposób poszukiwania genów napędzających raka. Patrząc na geny w towarzystwie, w jakim występują — w obrębie szlaków, a nie w izolacji — poprawia naszą zdolność do wykrywania zarówno dobrze znanych, jak i wcześniej przeoczonych kierowców, nawet w nowotworach, o których wiadomo stosunkowo niewiele. Tego rodzaju narzędzie może pomóc badaczom priorytetyzować geny do badań laboratoryjnych, ukierunkować poszukiwania nowych celów lekowych i ostatecznie wspierać bardziej precyzyjne, świadome szlaków strategie leczenia w onkologii.
Cytowanie: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Słowa kluczowe: geny napędzające nowotwory, hipernetworki neuronowe, integracja multi-omics, analiza szlaków, precyzyjna onkologia