Clear Sky Science · pl
Analiza na poziomie haplotypów DNA środowiskowego (eDNA) ujawniła biogeografię i filogeografię ryb słodkowodnych na Półwyspie Koreańskim
Odczytywanie rzek przez niewidoczne wskazówki
Rzeki i strumienie mogą wyglądać na przejrzyste gołym okiem, ale są pełne mikroskopijnych śladów życia. Badanie pokazuje, jak naukowcy mogą odczytywać tę niewidzialną „atramentową” informację genetyczną w wodzie, by dowiedzieć się, które ryby występują gdzie, jak powiązane są ich populacje na Półwyspie Koreańskim, a nawet czy niektóre gatunki zostały przetransportowane przez ludzi między regionami. Praca ta daje wgląd w to, jak konserwatorzy przyrody wkrótce mogą monitorować bioróżnorodność i chronić rzadkie gatunki bez zarzucania sieci.
Łowienie DNA zamiast sieci
Zamiast łapać ryby, badacze pobrali proste, litrowe butelki wody z trzech małych strumieni — Seom, Gilan i Oshipcheon — zlokalizowanych w różnych regionach biogeograficznych Korei Południowej. W tych próbkach poszukiwali DNA środowiskowego (eDNA): drobnych fragmentów materiału genetycznego odrzuconego przez ryby wraz ze skórą, odchodami i śluzem. Za pomocą techniki zwanej metabarkowaniem wzmocnili i zsekwencjonowali krótki fragment DNA ryb, a następnie porównali miliony odczytów z bazami referencyjnymi, by zidentyfikować, które gatunki — a nawet które warianty genetyczne, czyli haplotypy — występowały w każdym strumieniu.
Kto mieszka gdzie w koreańskich strumieniach?
Zaledwie z 54 próbek wody pobranych na dziewięciu stanowiskach zespół wykrył 107 odrębnych wariantów DNA reprezentujących 76 gatunków ryb — około jednej trzeciej wszystkich znanych w Korei ryb słodkowodnych. Strumień Seom, nizinna rzeka powiązana z Morzem Żółtym, gościł najbogatszą społeczność rybną, z 49 gatunkami. Gilan i Oshipcheon, wyższe i bardziej strome dopływy spływające ku różnym wybrzeżom, miały po 28 gatunków. Wiele gatunków występowało wspólnie w kilku strumieniach, ale prawie 30 gatunków okazało się endemicznych dla koreańskich siedlisk słodkowodnych, a każdy strumień miał też własny, unikalny zestaw gatunków. Ogólnie wzorce te zgadzały się z długo znaną koncepcją, że życie słodkowodne Korei jest podzielone na trzy główne regiony przez pasma górskie i historię geologiczną.
Genetyczne odciski palców i ukryte transfery
Ponieważ naukowcy pracowali na poziomie haplotypów — drobnych „odmian” DNA wewnątrz gatunku — mogli zrobić więcej niż spisać listę gatunków; mogli porównywać populacje. Kilka powszechnych rodzimej fauny ryb wykazało wyraźne różnice genetyczne między regionami, co wskazuje na długotrwałe oddzielenie i ograniczone naturalne mieszanie się populacji na półwyspie. Jednocześnie dane DNA ujawniły prawdopodobne przypadki przemieszczania przez ludzi. U gatunków takich jak Pungtungia herzi, Coreoleuciscus splendidus i Nipponocypris koreanus wzorce haplotypów w wschodnim strumieniu Oshipcheon bardzo przypominały te z rzek zachodnich lub południowych, co sugeruje wcześniejsze zarybianie lub przemieszczenia. Poprzez wirtualne rekonstruowanie „drzew rodzinnych” tych wariantów DNA zespół mógł wywnioskować prawdopodobne regiony pochodzenia dla przemieszczeń — oferując rodzaj genetycznej kryminalistyki dla zarządzania rzekami.
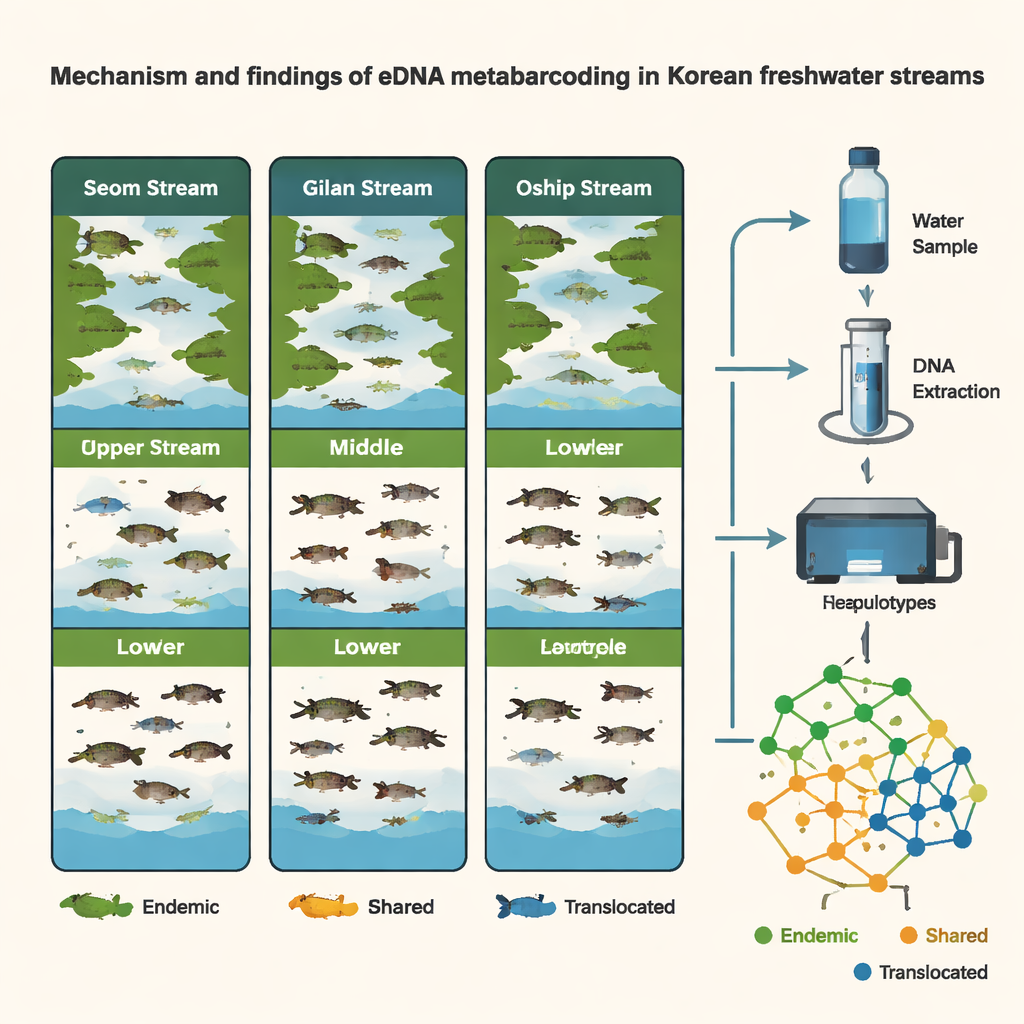
Pory roku, siedliska i zmienne cele
Badanie śledziło także, jak społeczności ryb zmieniają się w czasie i przestrzeni. Porównując próbki pobrane pod koniec zimy (marzec) i latem (sierpień), badacze stwierdzili większe bogactwo gatunkowe latem i wyraźne zmiany sezonowe, szczególnie w strumieniu Seom. W Oshipcheon eDNA gatunków wędrownych — takich jak łososie i inne ryby przemieszczające się między rzeką a morzem — pojawiało się i znikało w sposób zgodny z ich znanymi cyklami życiowymi. Co zaskakujące, w obrębie każdego stanowiska, bystrza, szybkie i stojące odcinki nie wykazywały silnych różnic w DNA ryb, prawdopodobnie dlatego, że przepływ wody bocznie miesza eDNA w tych małych kanałach. Zamiast tego główne kontrasty występowały między różnymi odcinkami strumieni (górny, środkowy, dolny) oraz między trzema samymi strumieniami, podkreślając znaczenie miejsca pobierania próbek wzdłuż rzeki.
Co to oznacza dla ochrony życia słodkowodnego
Mówiąc wprost, badanie pokazuje, że butelka wody rzeczne może ujawnić szczegółowy obraz tego, kto mieszka w strumieniu, jak lokalne populacje ryb są powiązane na dużych obszarach oraz czy ludzie zmienili te wzorce przez przemieszczanie ryb. Dla działań ochronnych oznacza to, że zarządcy mogą szybko monitorować rzadkie i endemiczne gatunki, wykrywać inwazyjne i przemieścione ryby oraz śledzić sezonowe zmiany w populacjach wędrownych bez intensywnych badań terenowych i krzywdzenia zwierząt. Choć eDNA nie może jeszcze zastąpić tradycyjnych badań genetycznych, stanowi potężne, niskoinwazyjne narzędzie do obserwacji bioróżnorodności słodkowodnej w ocieplającym się, silnie zarządzanym świecie — i do zapewnienia, że unikalne koreańskie ryby rzeczne nadal będą prosperować w swoich rodzimych siedliskach.
Cytowanie: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Słowa kluczowe: DNA środowiskowe, ryby słodkowodne, bioróżnorodność, rzeki Korei, genetyka ochrony